分子生物学工具使用指南
1. 创建、复制序列文件
1.1 手动新建序列文件
用户可在工作台通过手动输入的方式,直接创建序列文件。系统会自动过滤不可识别的字符。
1.2 上传序列文件
用户可在工作台通过上传的方式来添加序列文件。目前平台支持.dna, .fasta .gb, .ab1等格式。
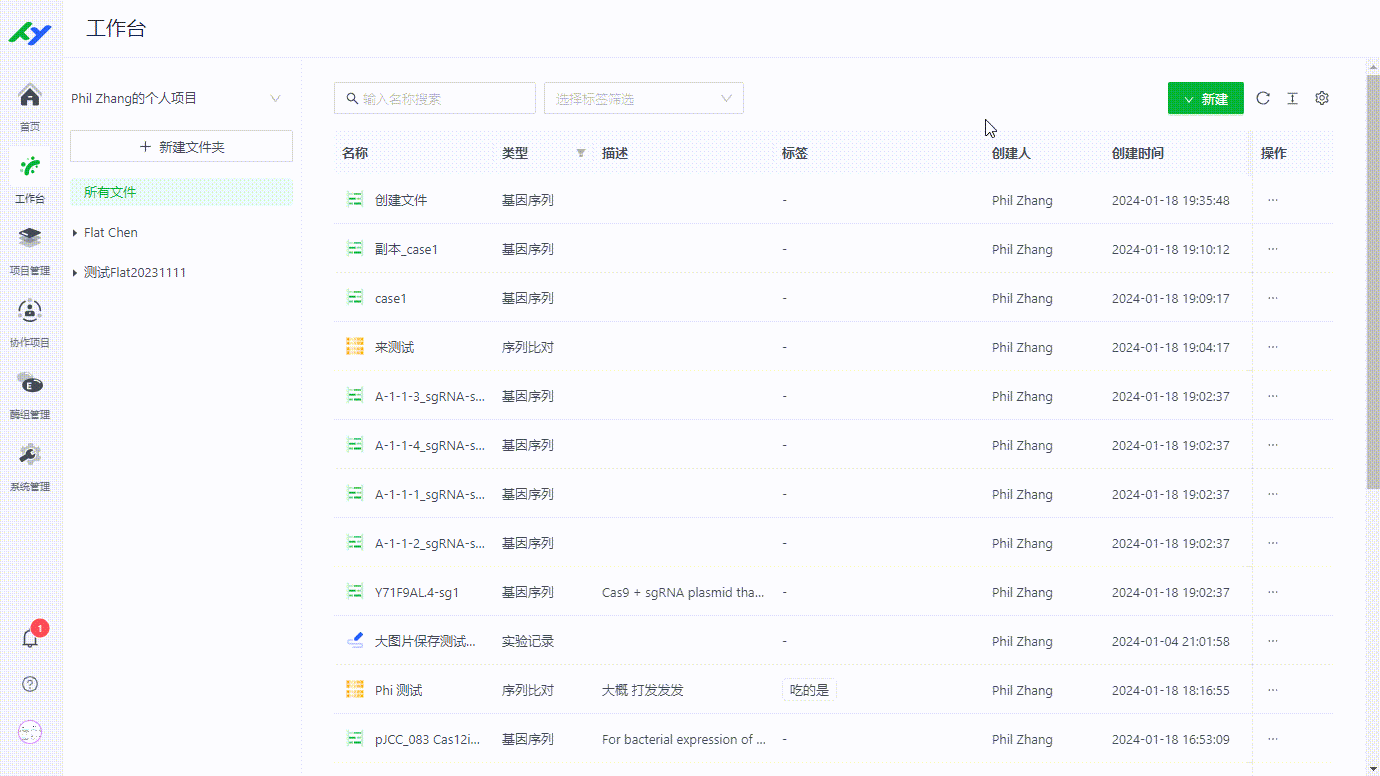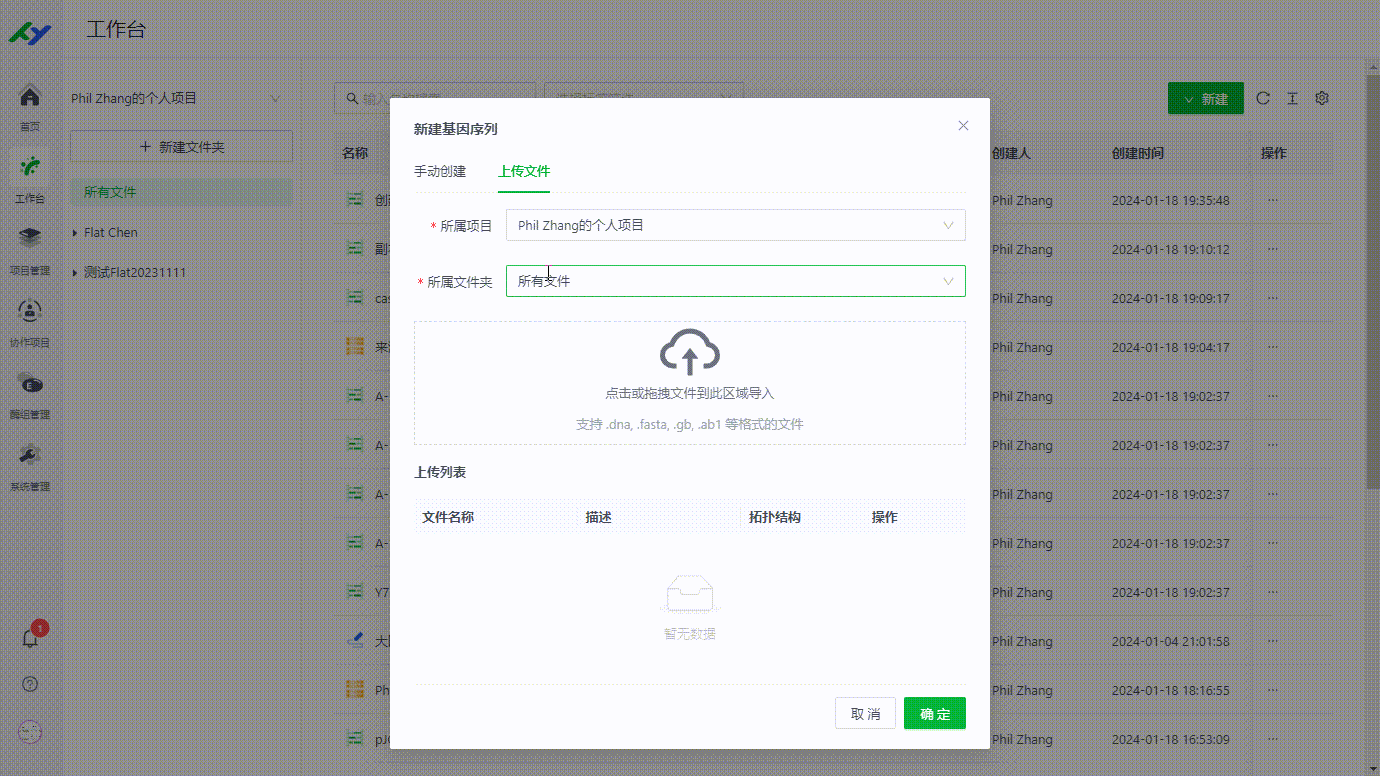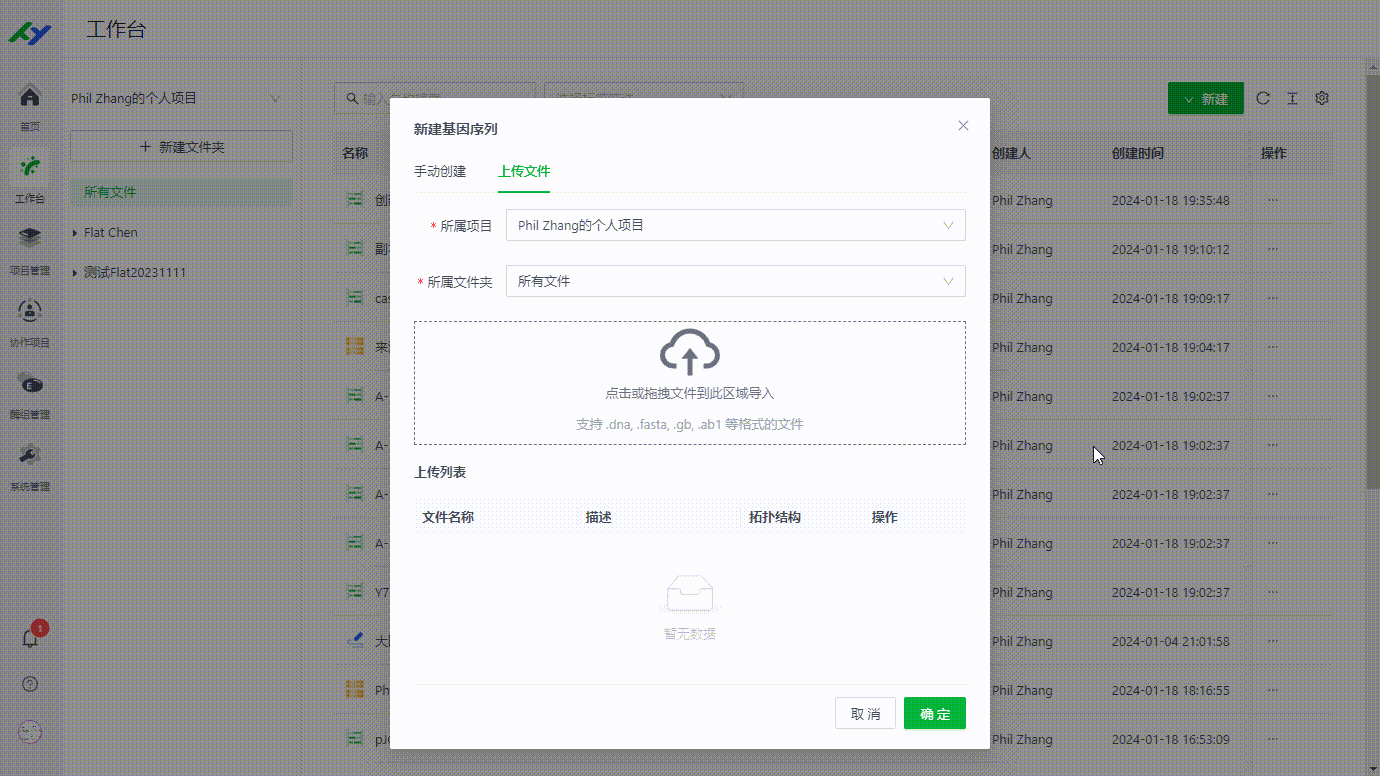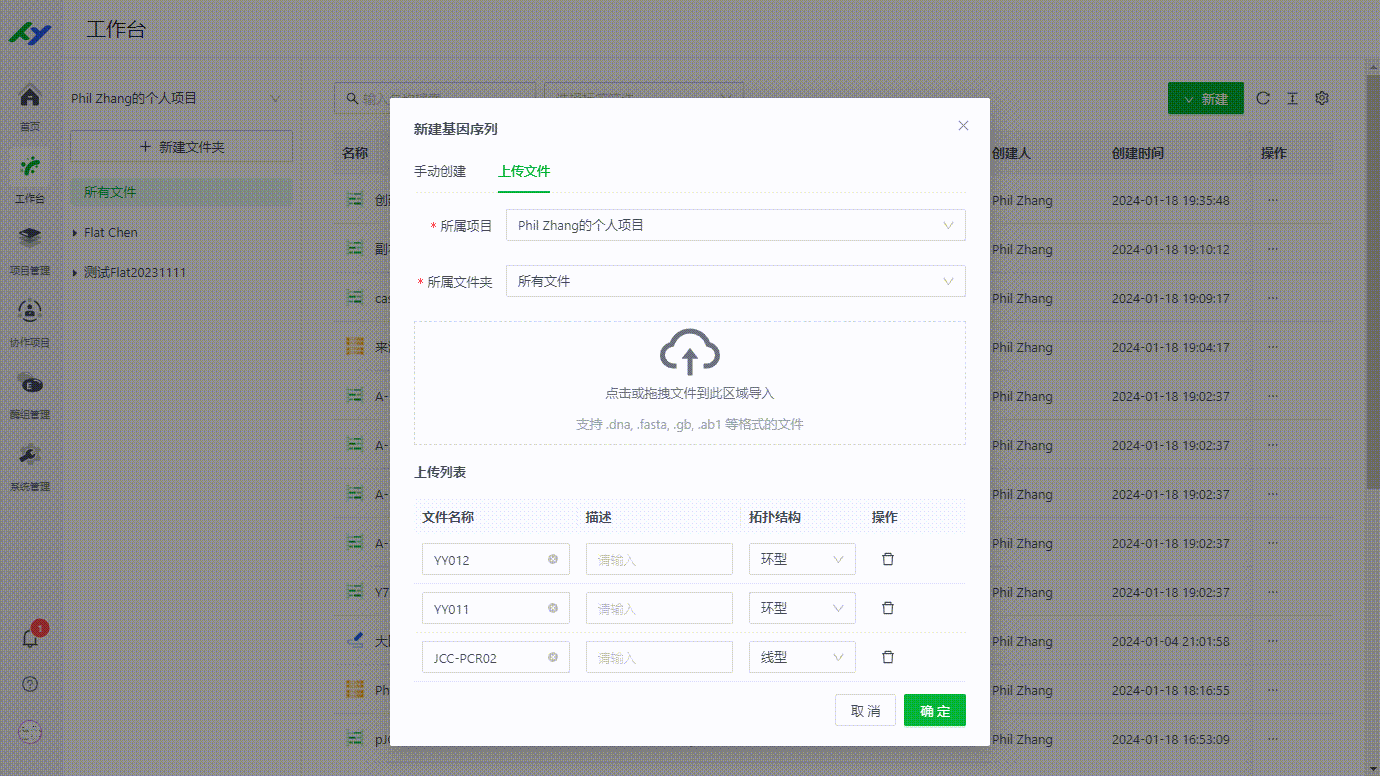
1.2.1 fasta文件导入
对.fasta文件的导入操作进行了优化,系统会自动获取全部序列及序列名称,并使用序列名称作为序列文件的名称,当无法获取时会是使用.fasta文件的名称与编号组合命名。由于.fasta文件中可以包含较多的序列信息,用户可以选择部分序列进行上传和后续操作。
1.2.2 ab1文件导入
系统支持对.ab1文件进行操作操作,导入成功后,可以在文件列表中看到该文件,打开可以查看该文件中的序列信息和峰信息。
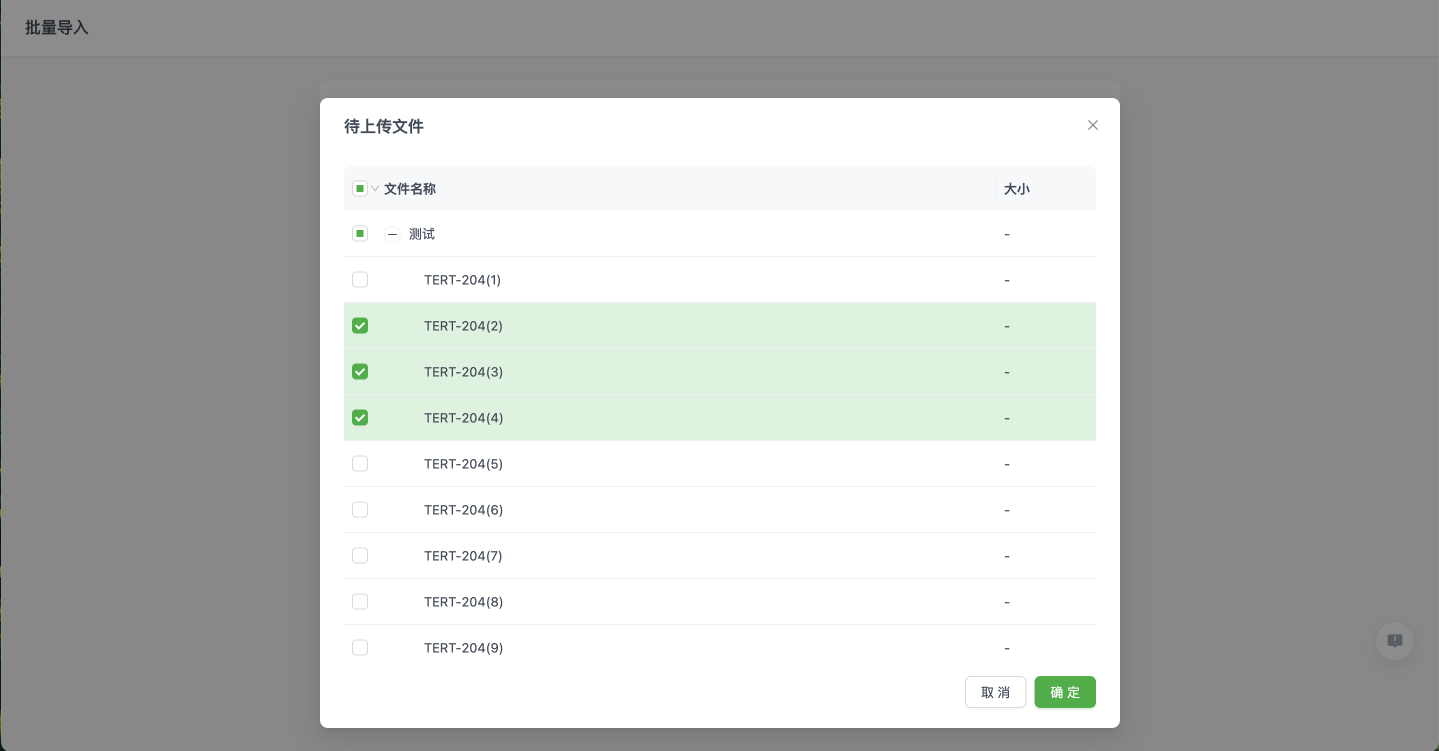
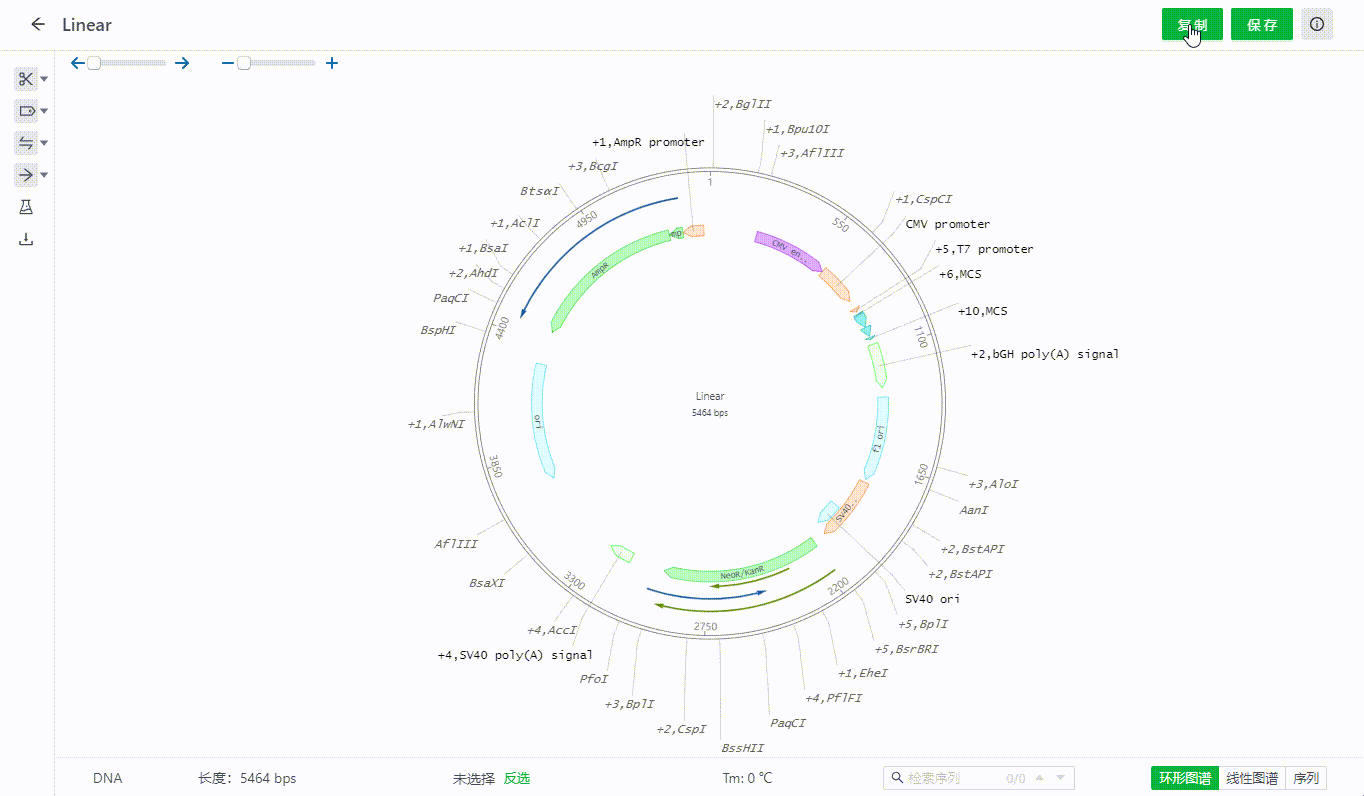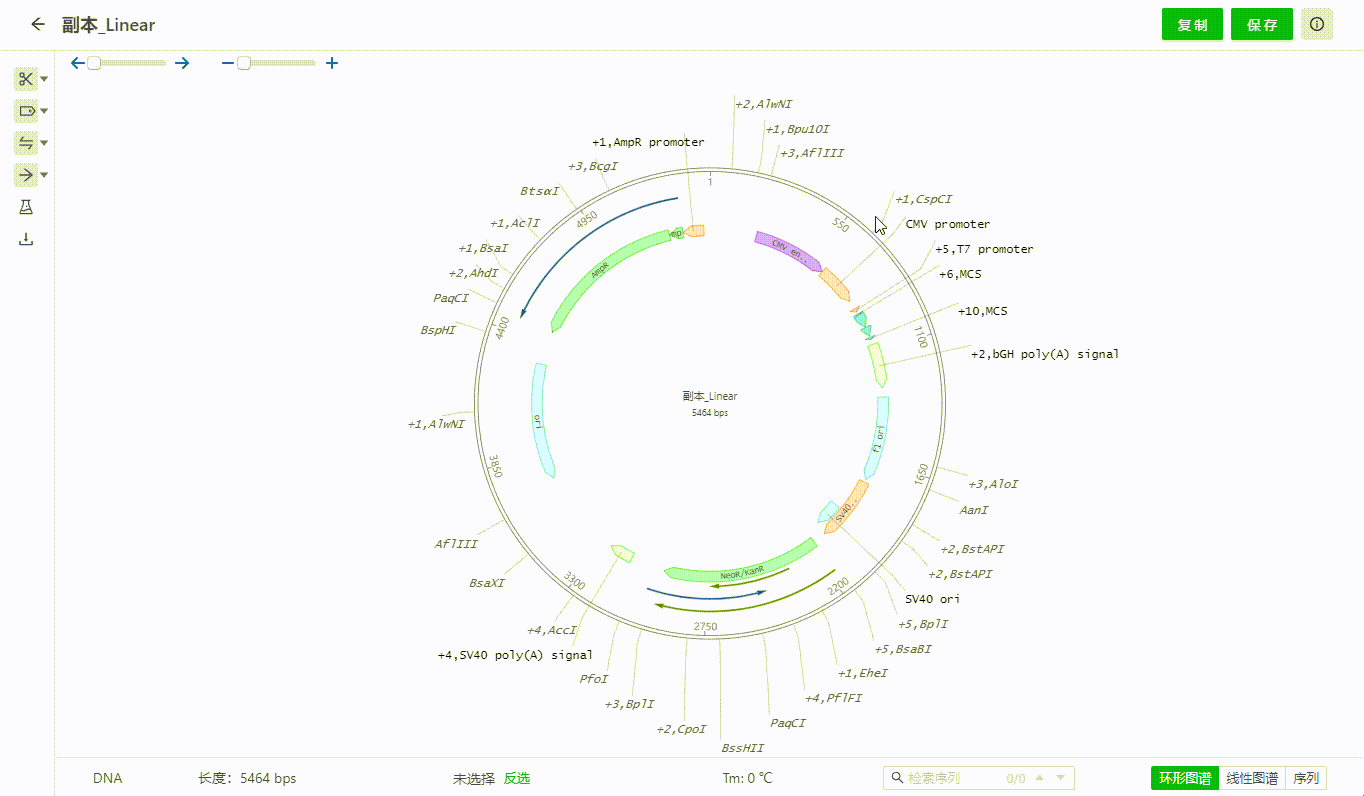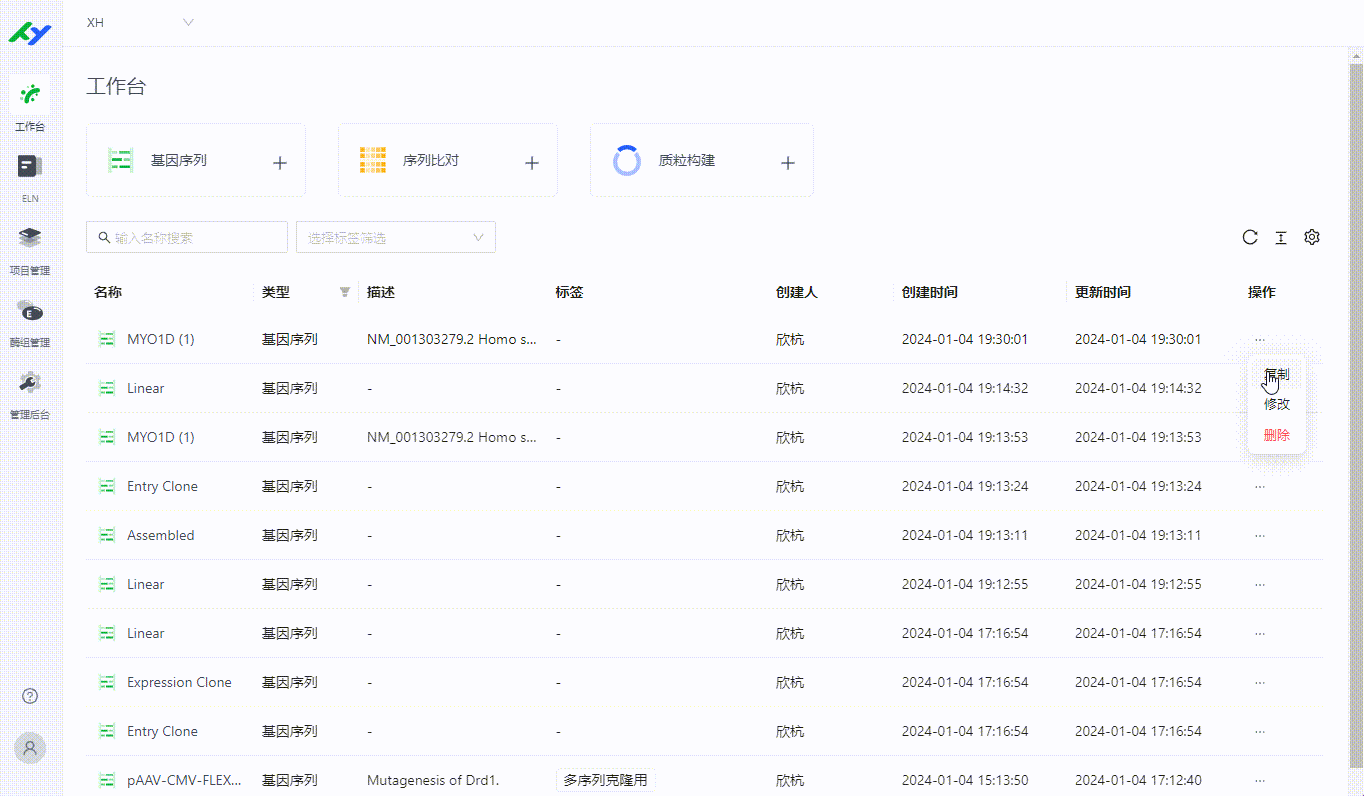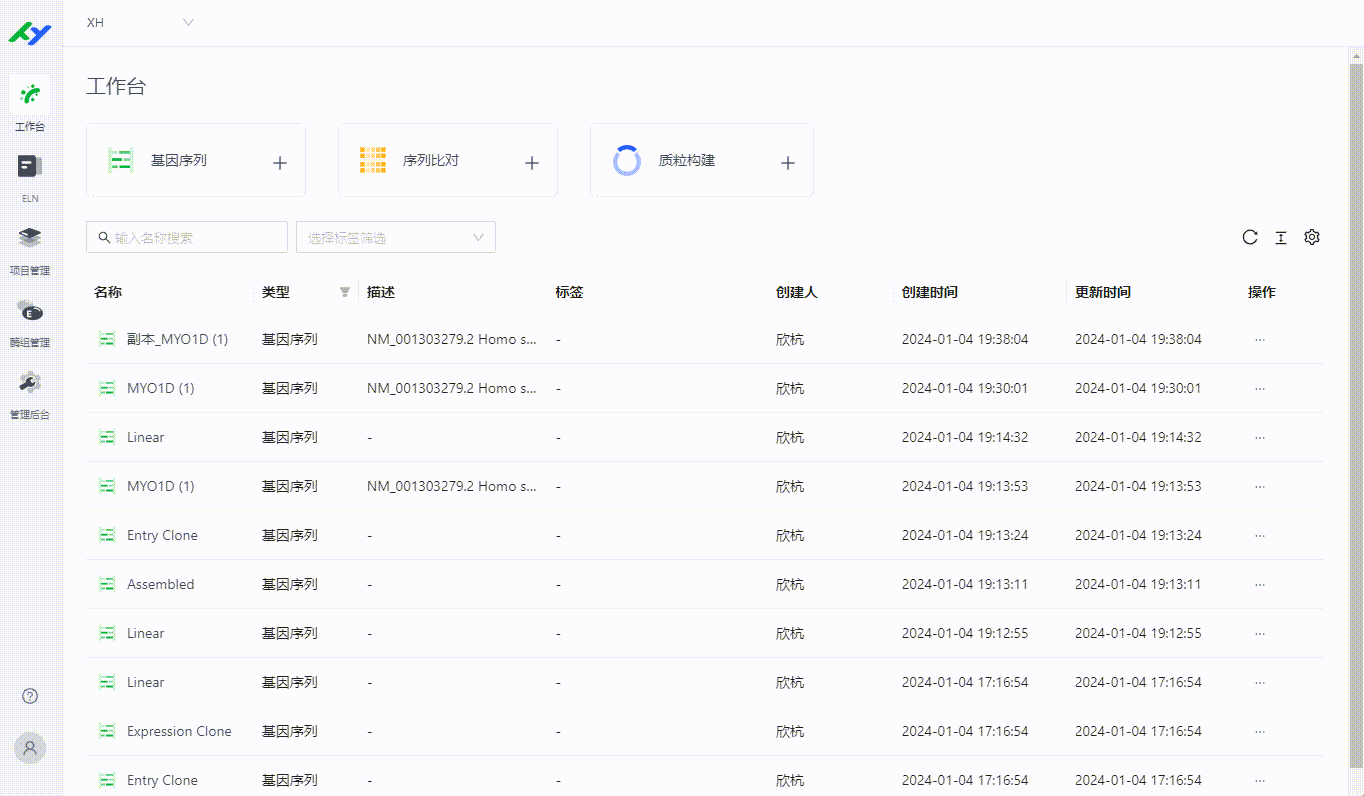
1.3 复制序列文件
用户可直接复制当前文件创建副本,也可以通过文件列表直接复制。
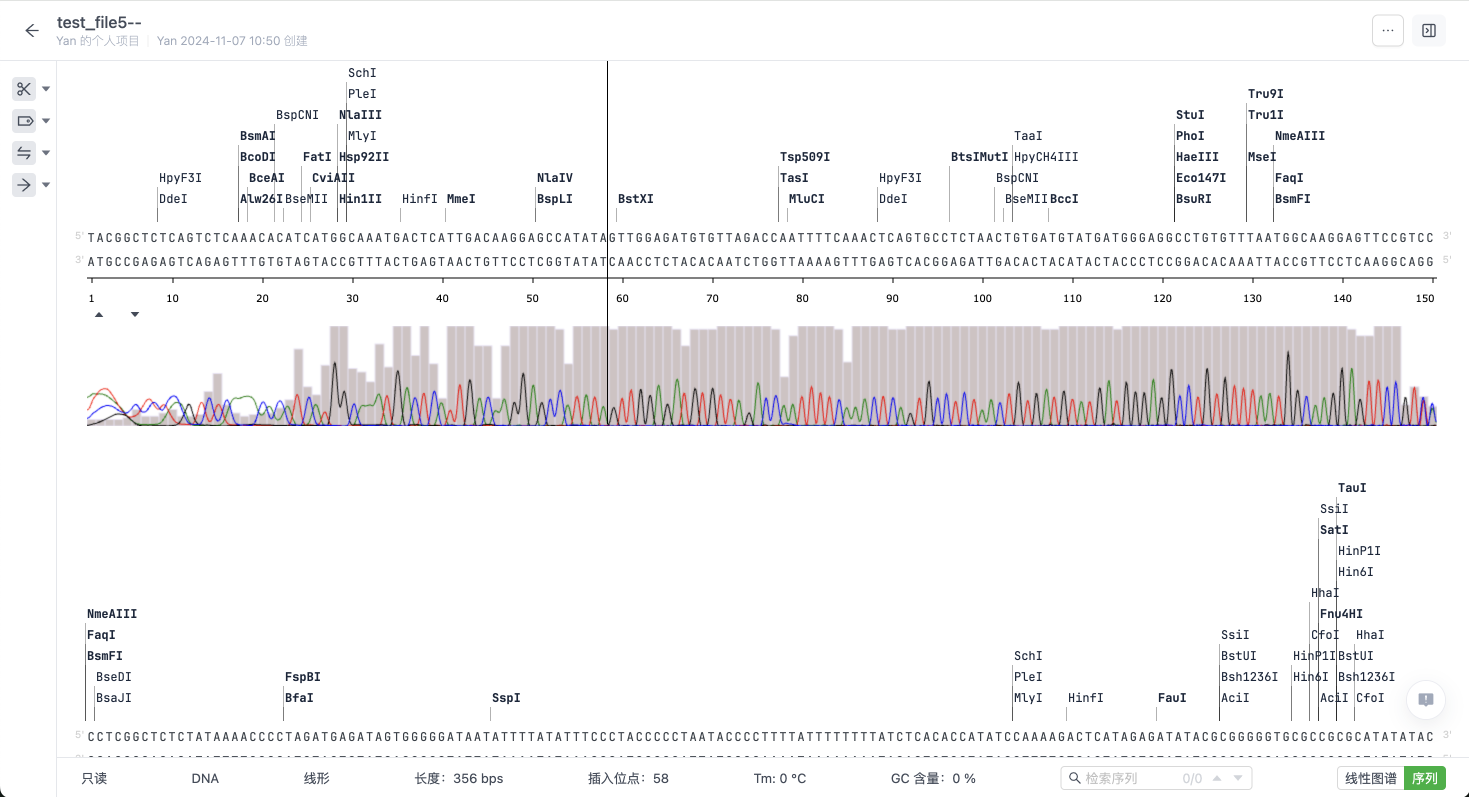
2. 编辑序列文件
2.1 修改文件名称及描述
序列文件可以�修改文件的标题及描述。

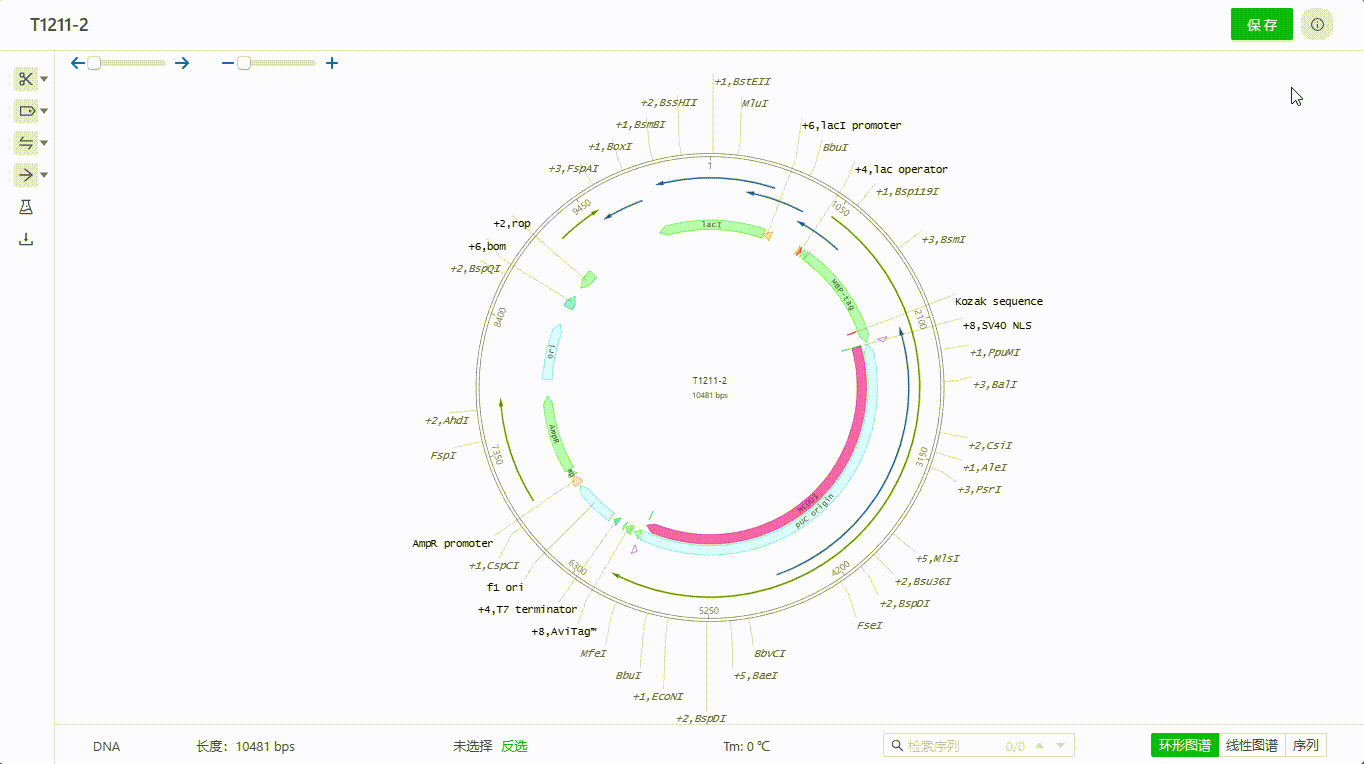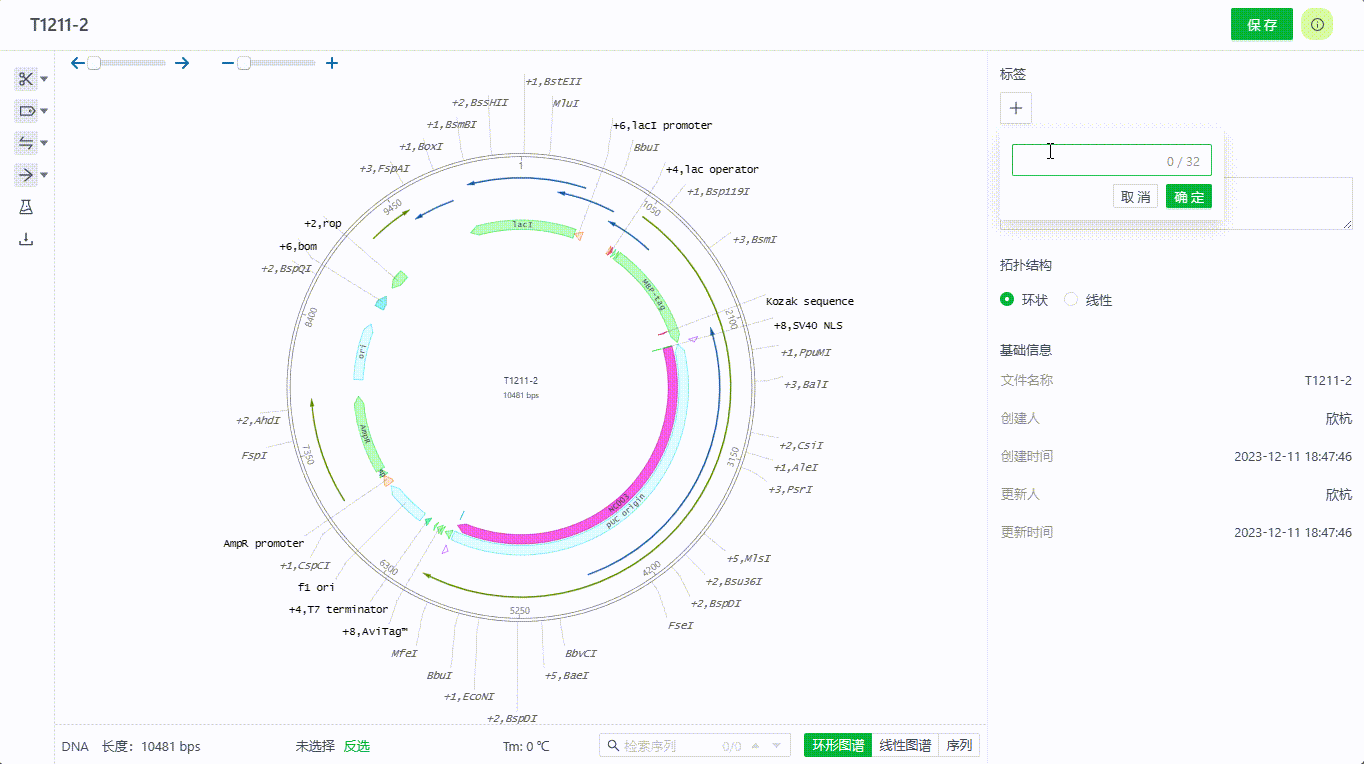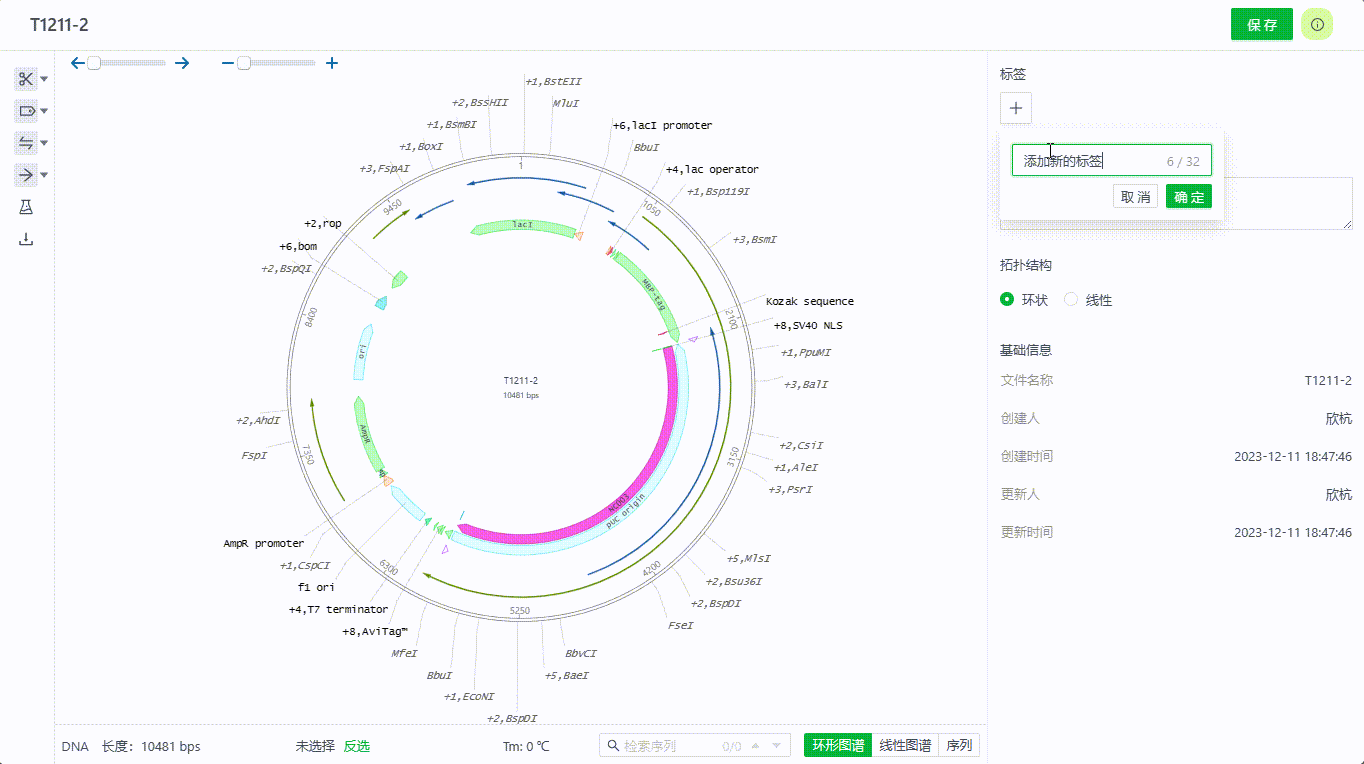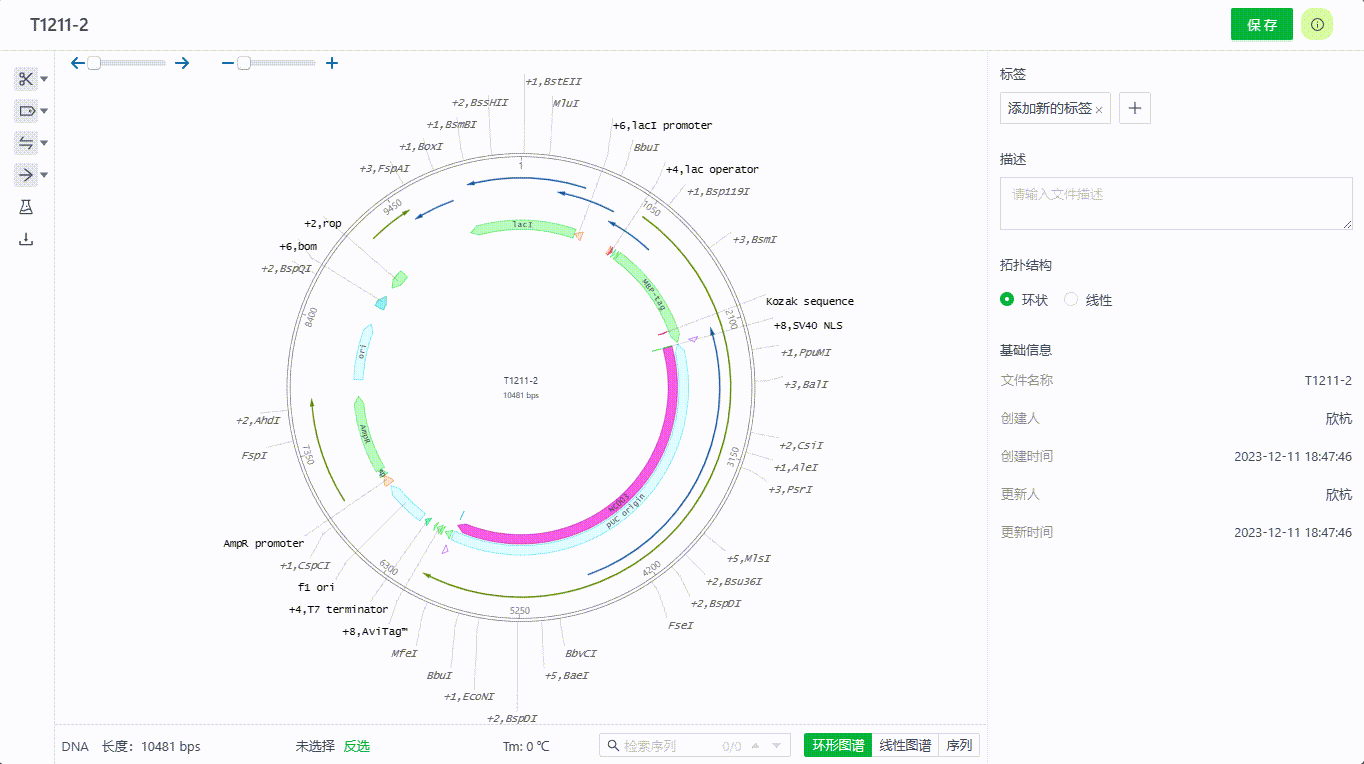
2.2 添加文件标签
进入文件后,可添加标签,便于文档归类
2.3 文件视图切换及遮盖信息展开查看
序列文件可以在页面右下角切换三种视图查看。
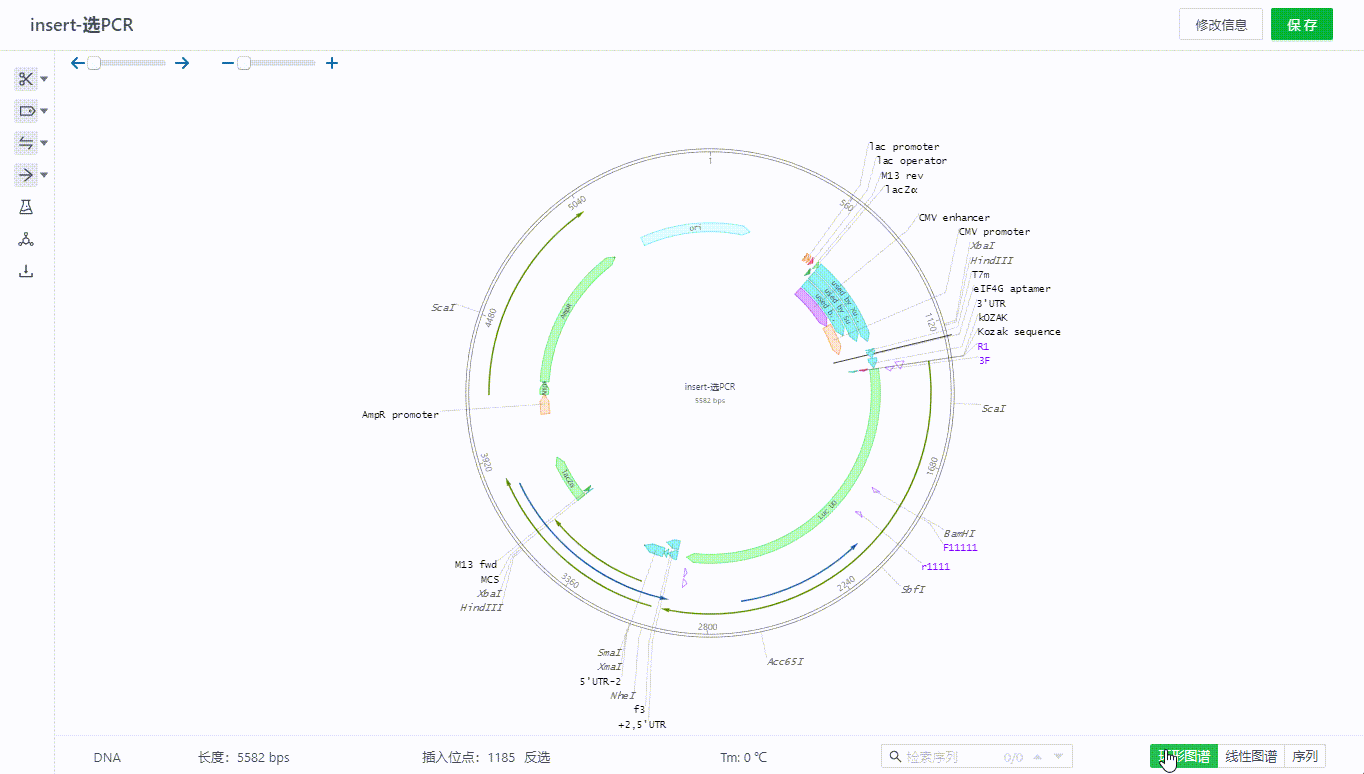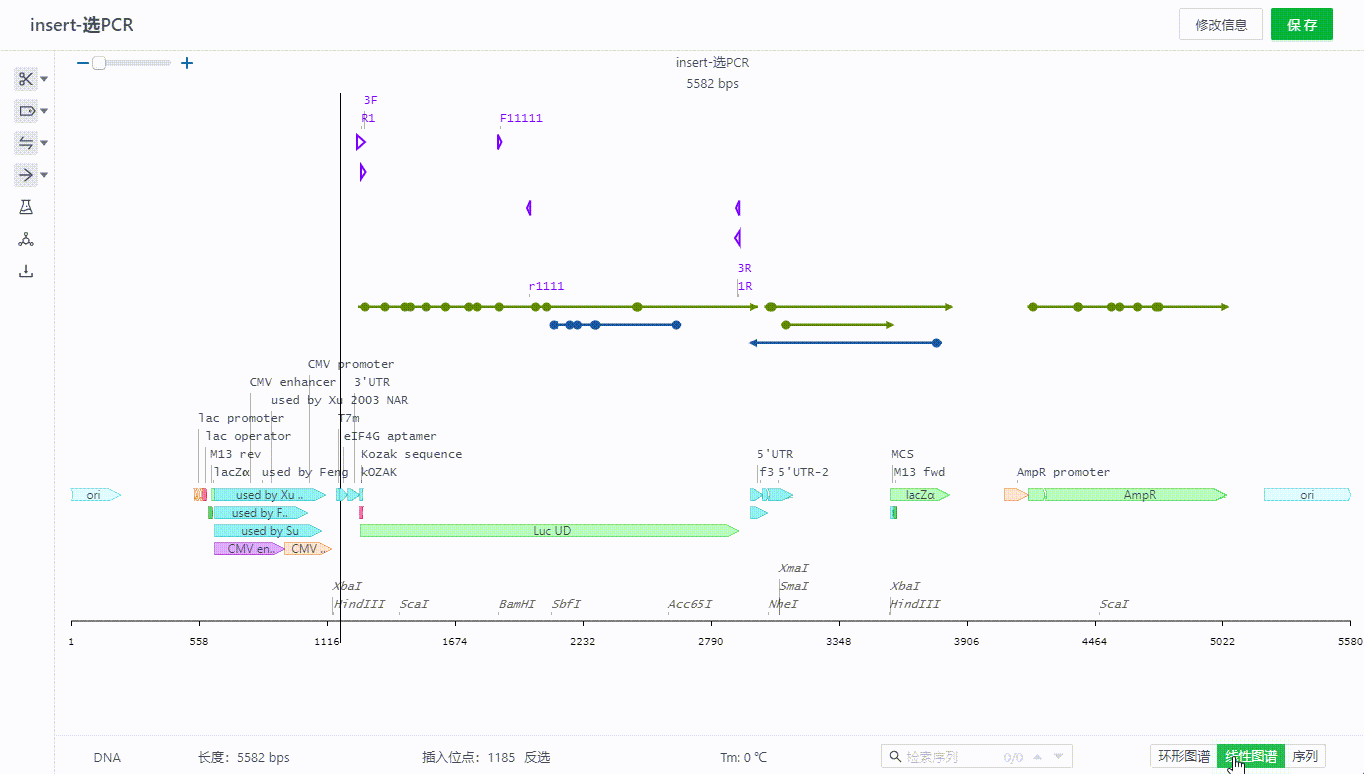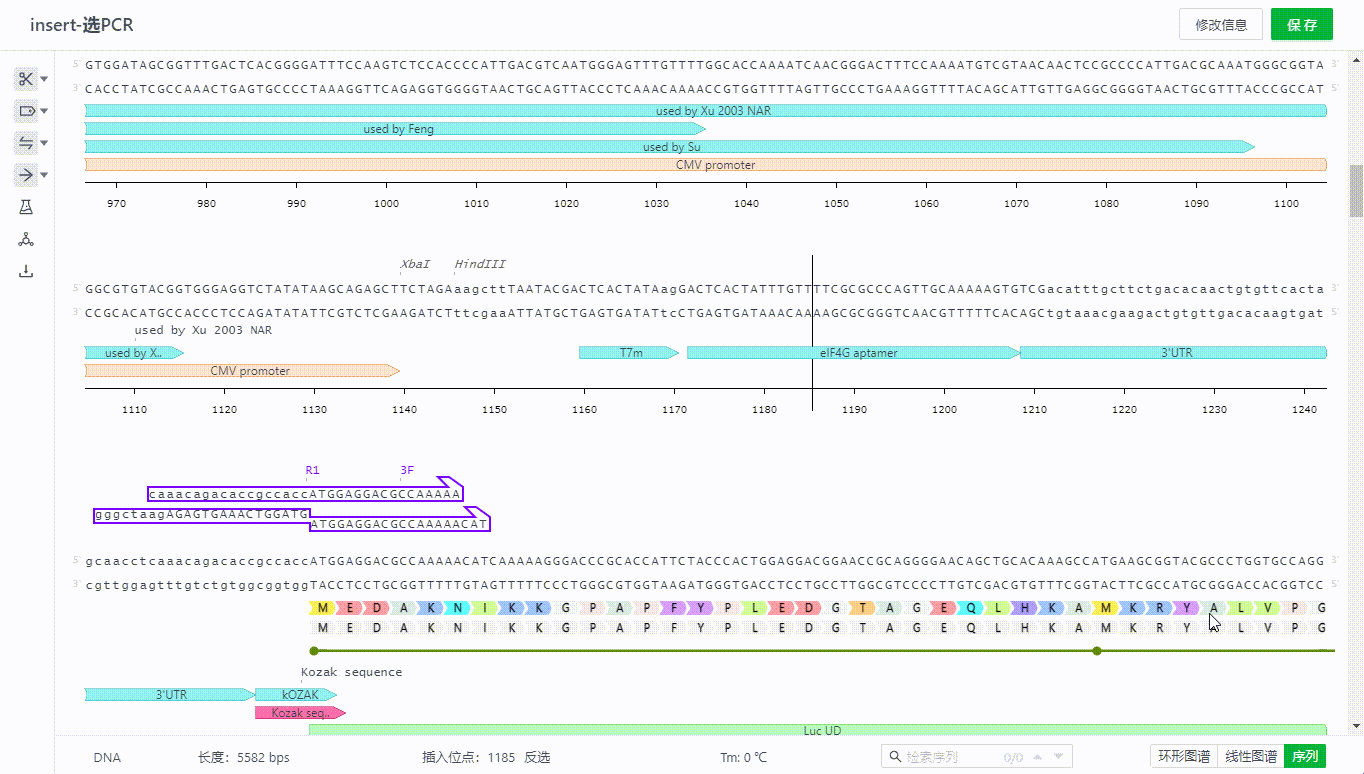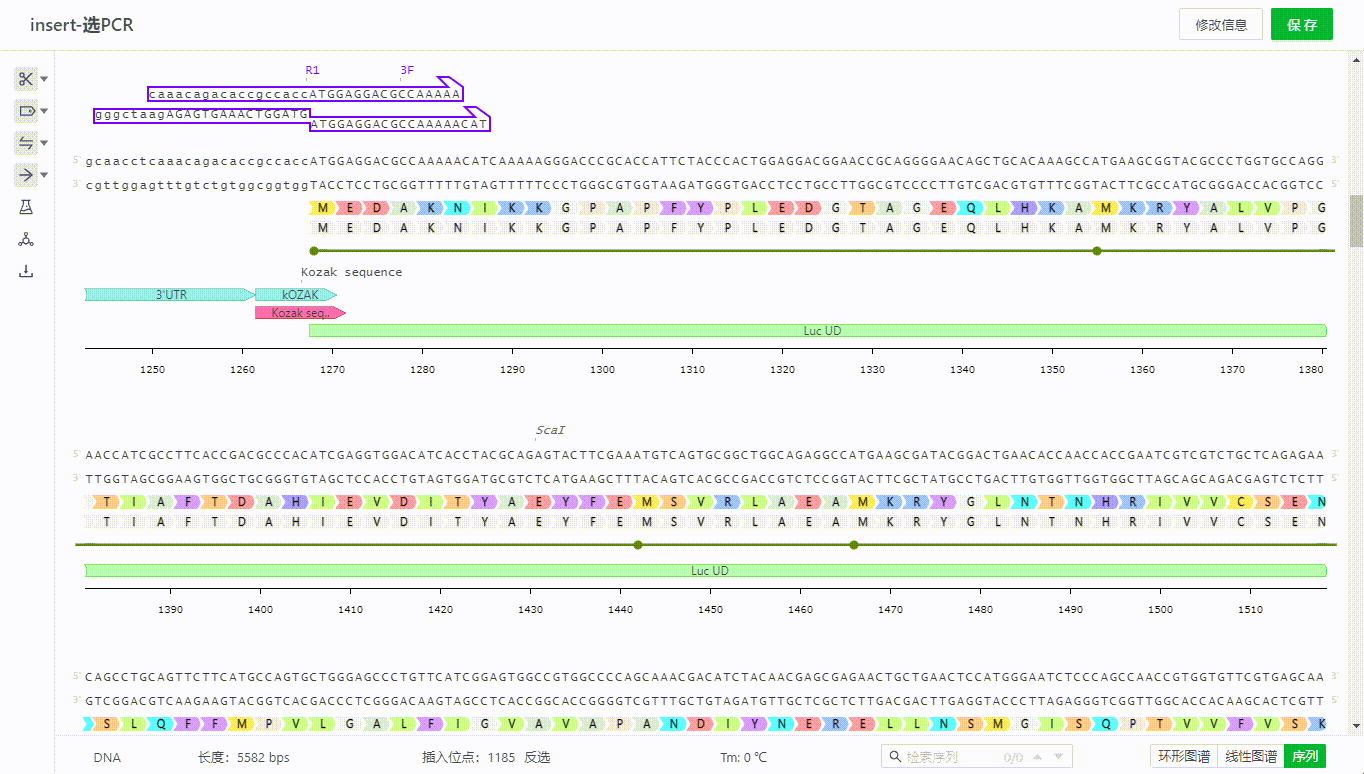
如有多个信息重叠的部分可以鼠标移动到+号旁查看明细,只要出现在该坐标范围附近的引物、特征、酶等信息都会通过+号来展开查看。
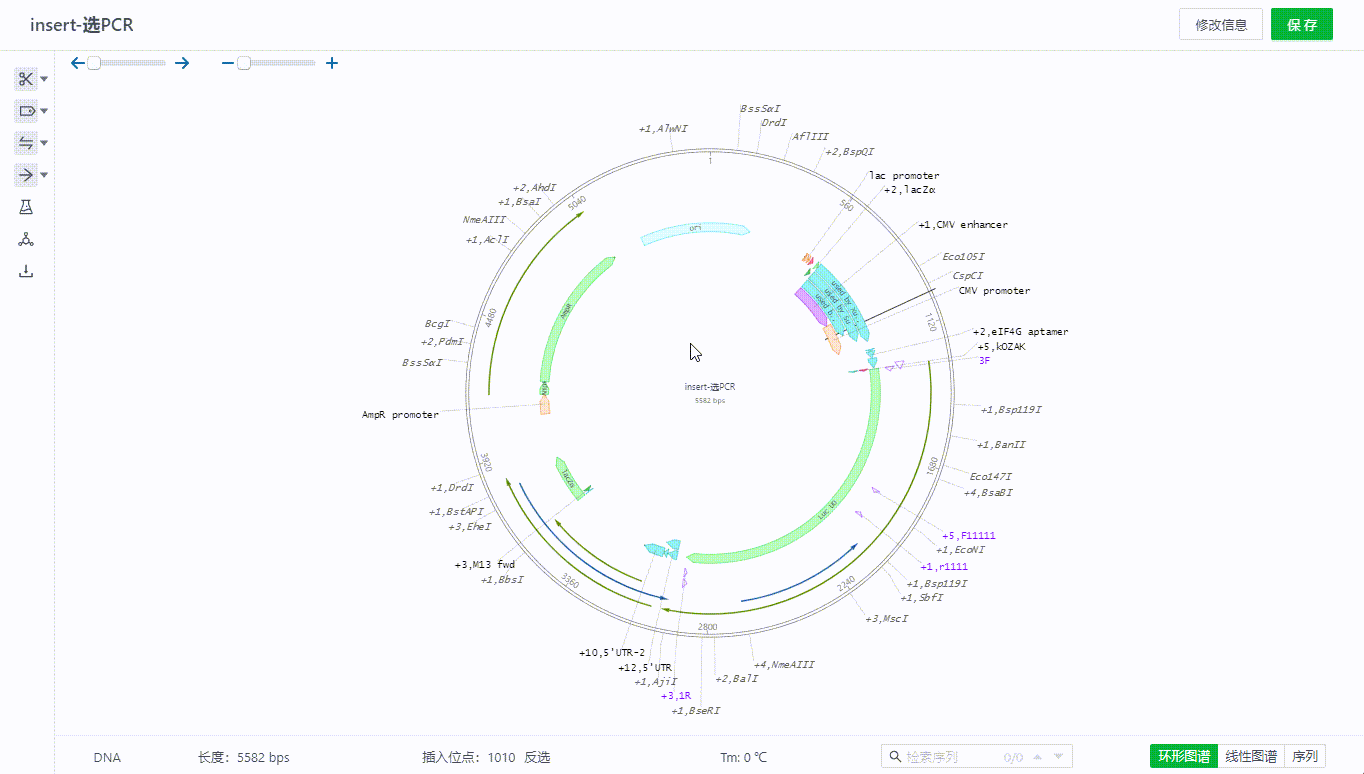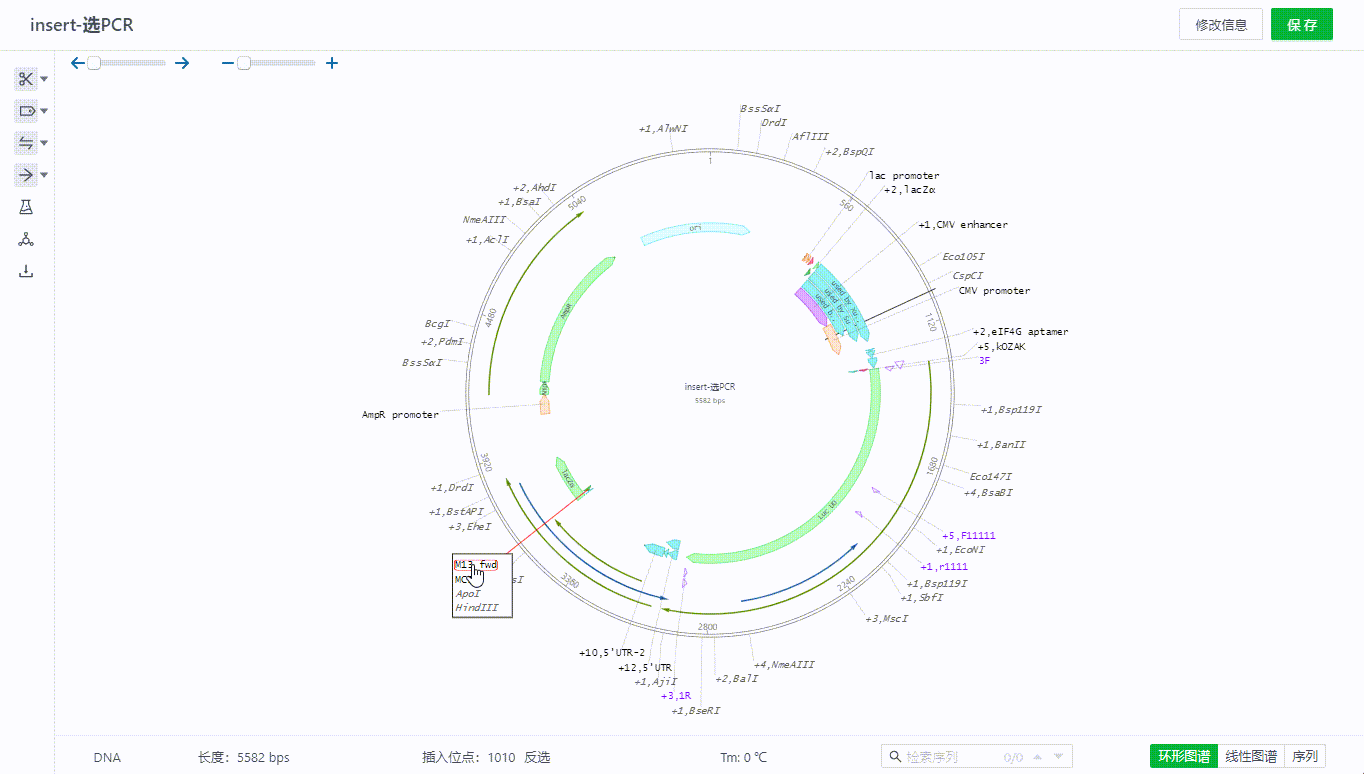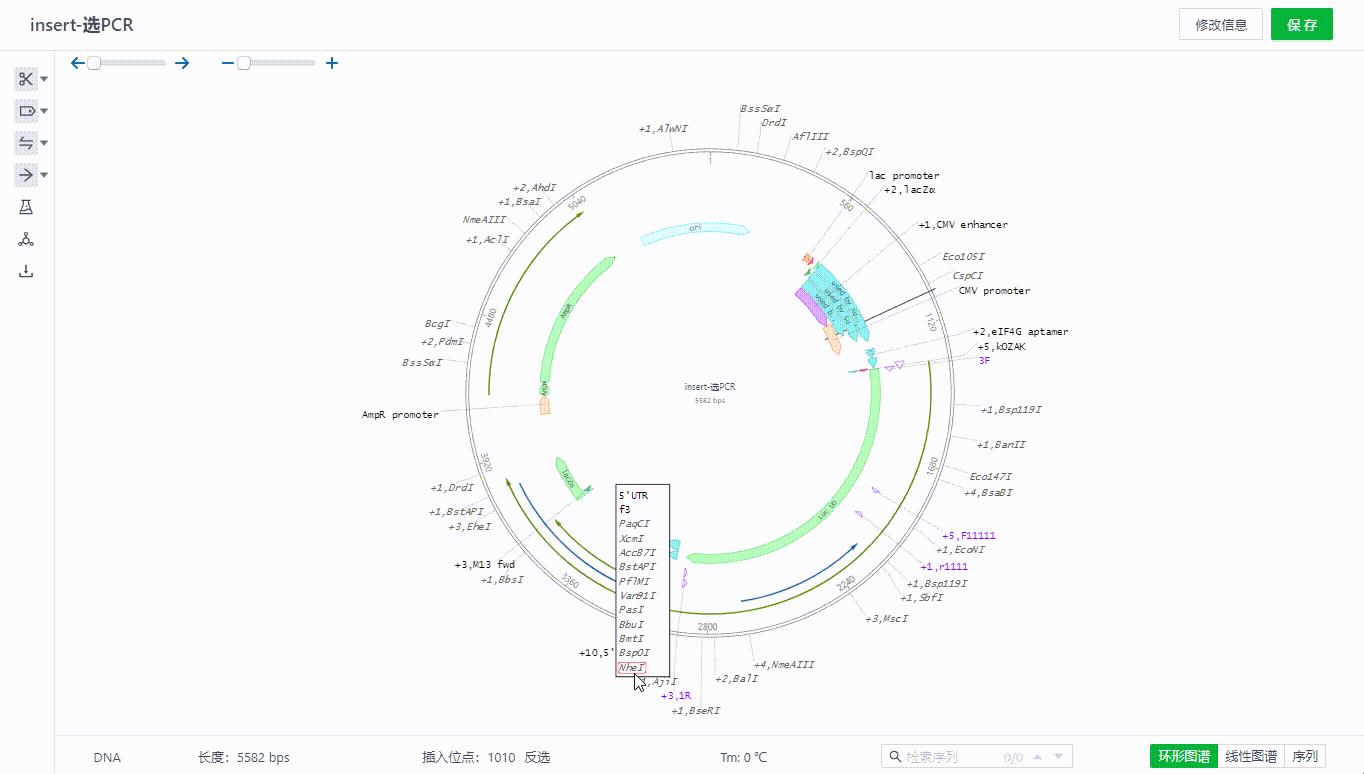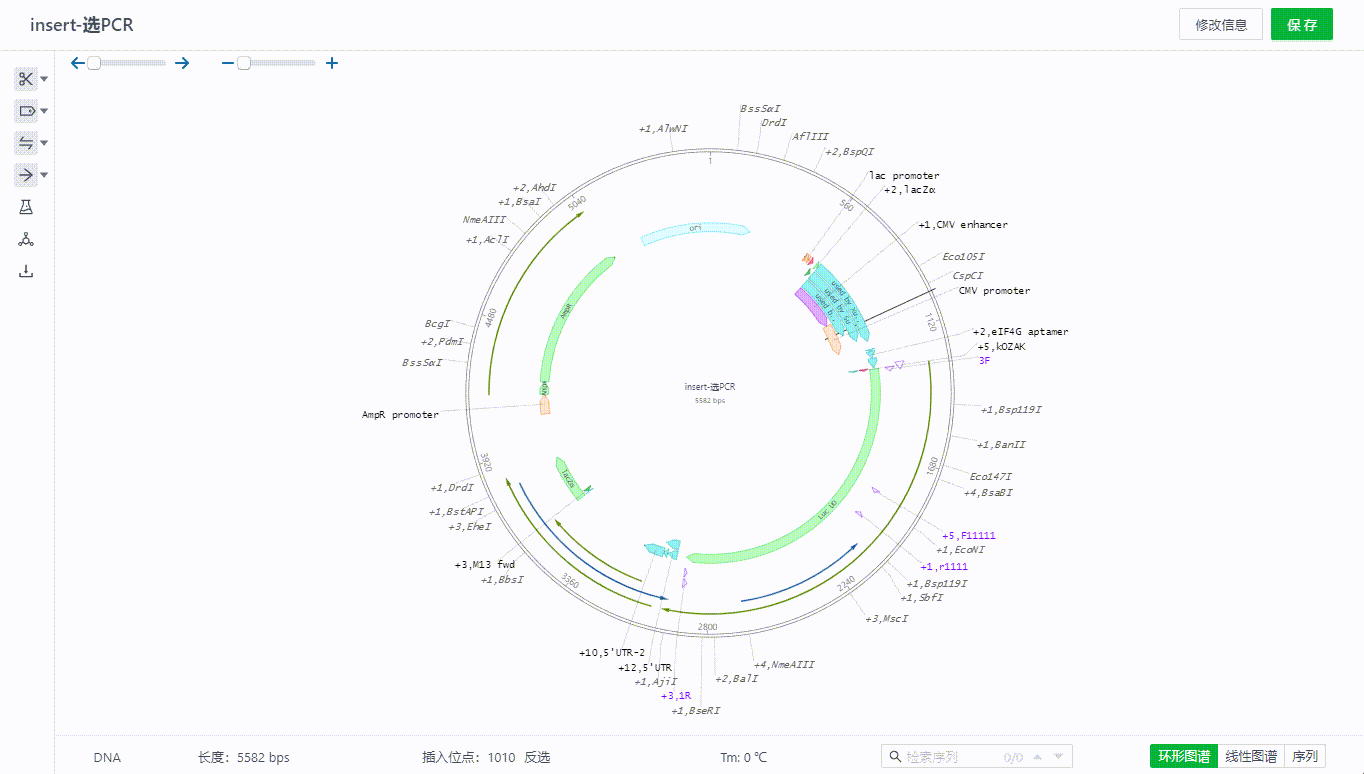
2.4 复制、剪切、插入、修改序列
用户可以直接在序列界面,通过右键的方式或者ctrl+c、ctrl+v、ctrl+x等快捷键实现序列的复制、剪切、插入、修改等操作。
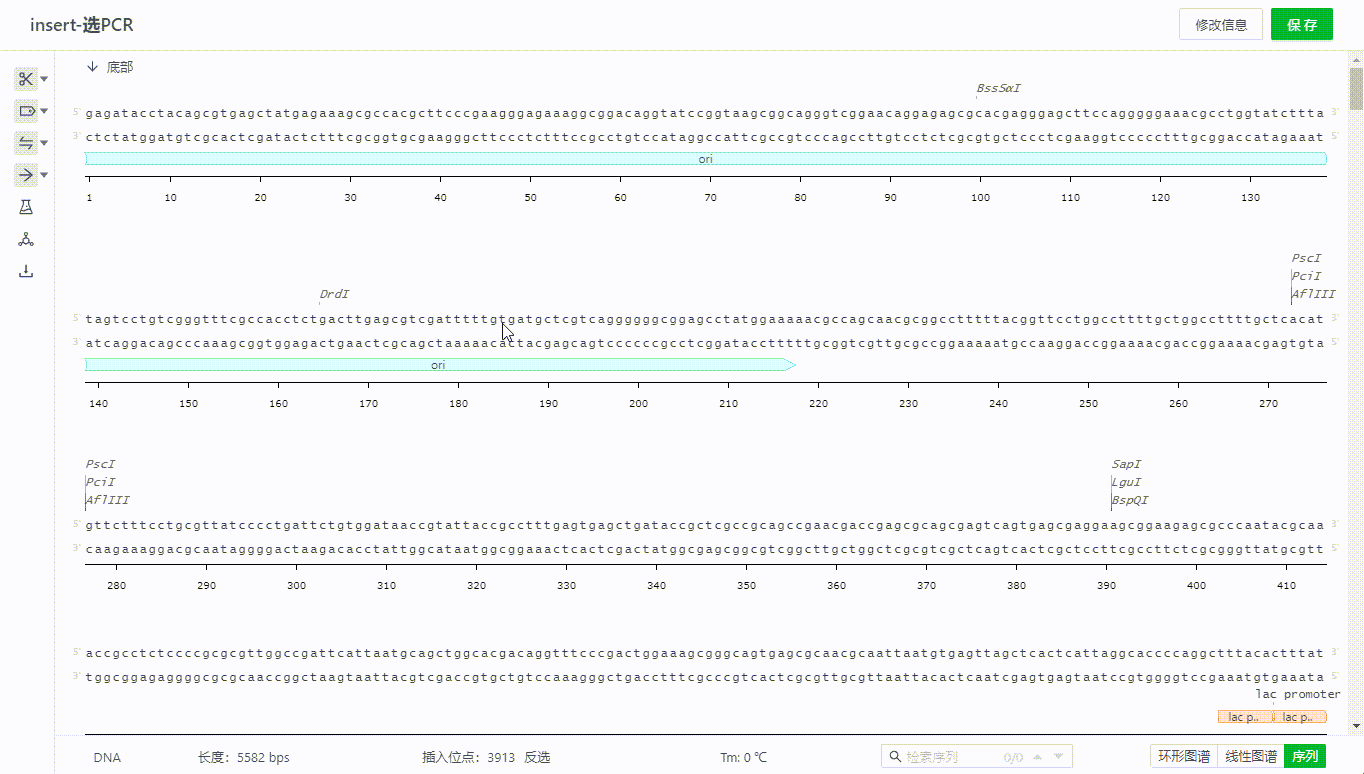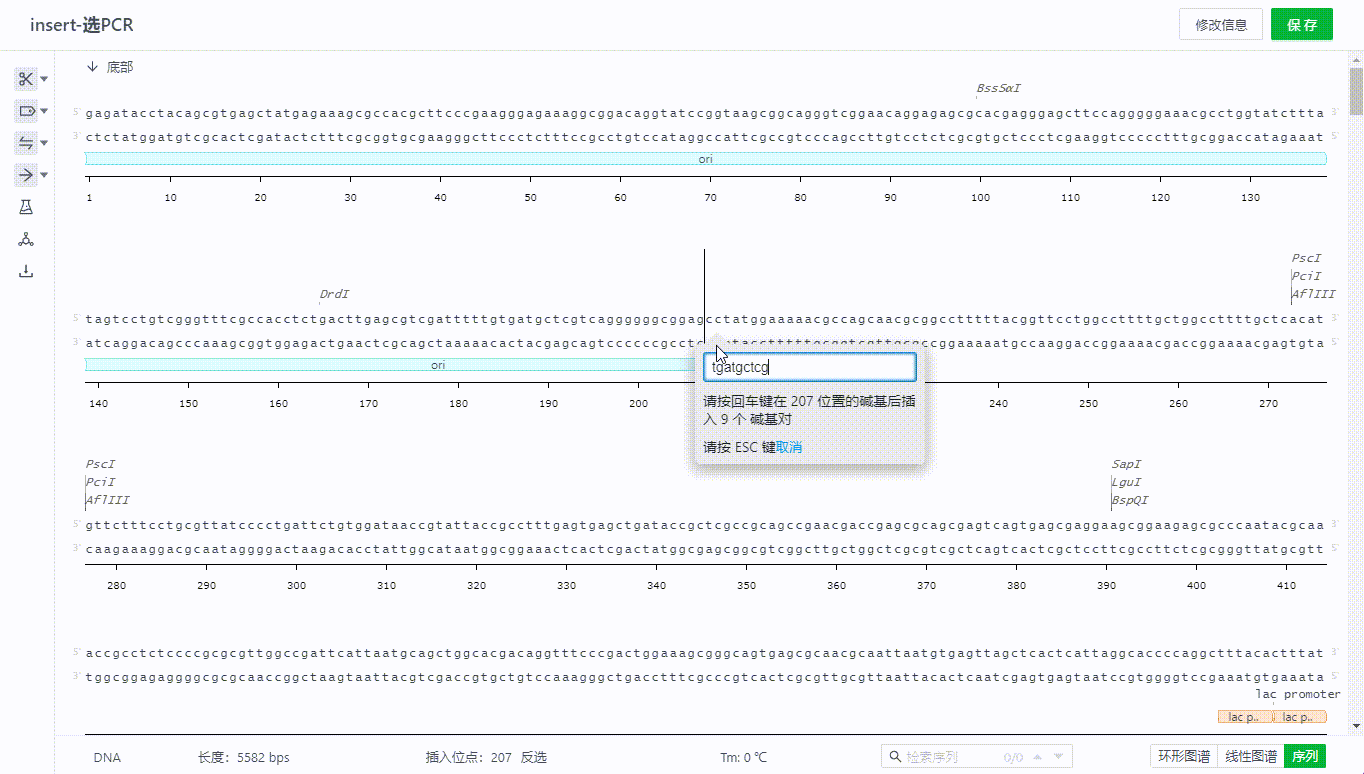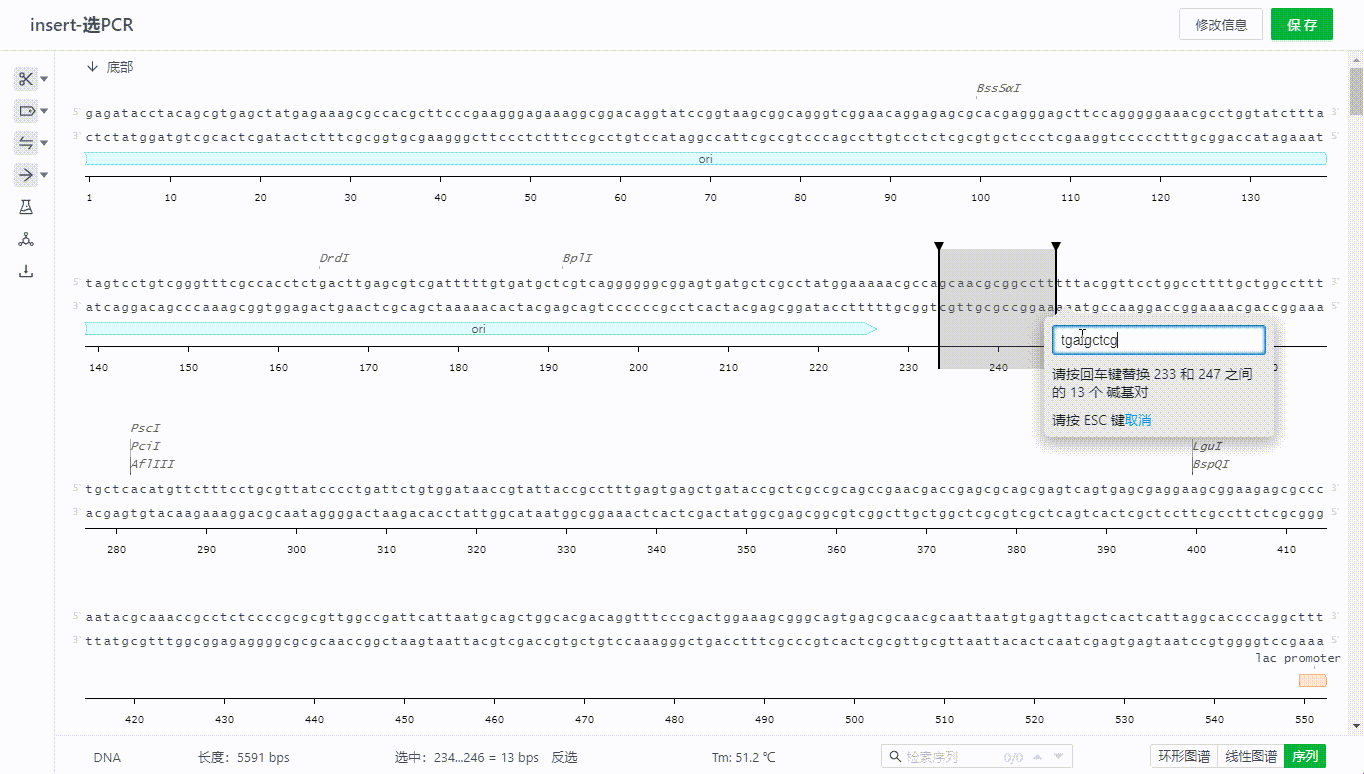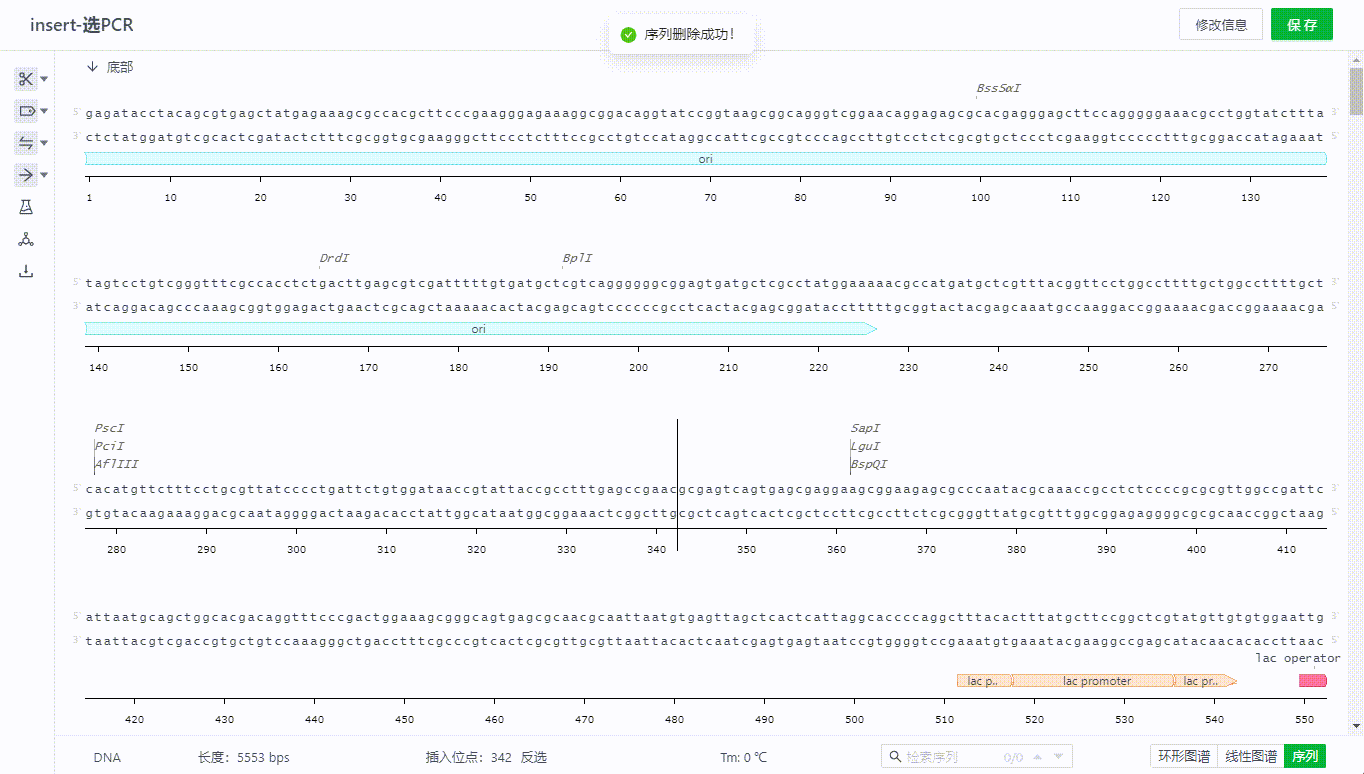
如果要复制底部序列,可以选取所需要的序列区域,然后右键选择复制——底部链(反义链)来实现。
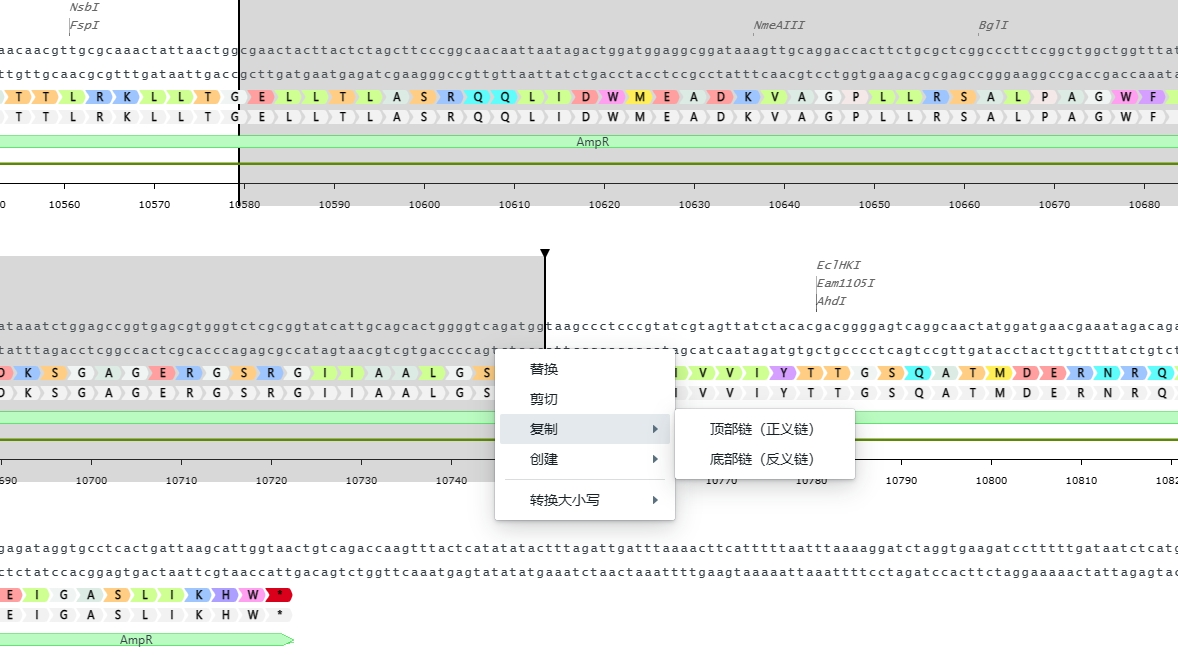
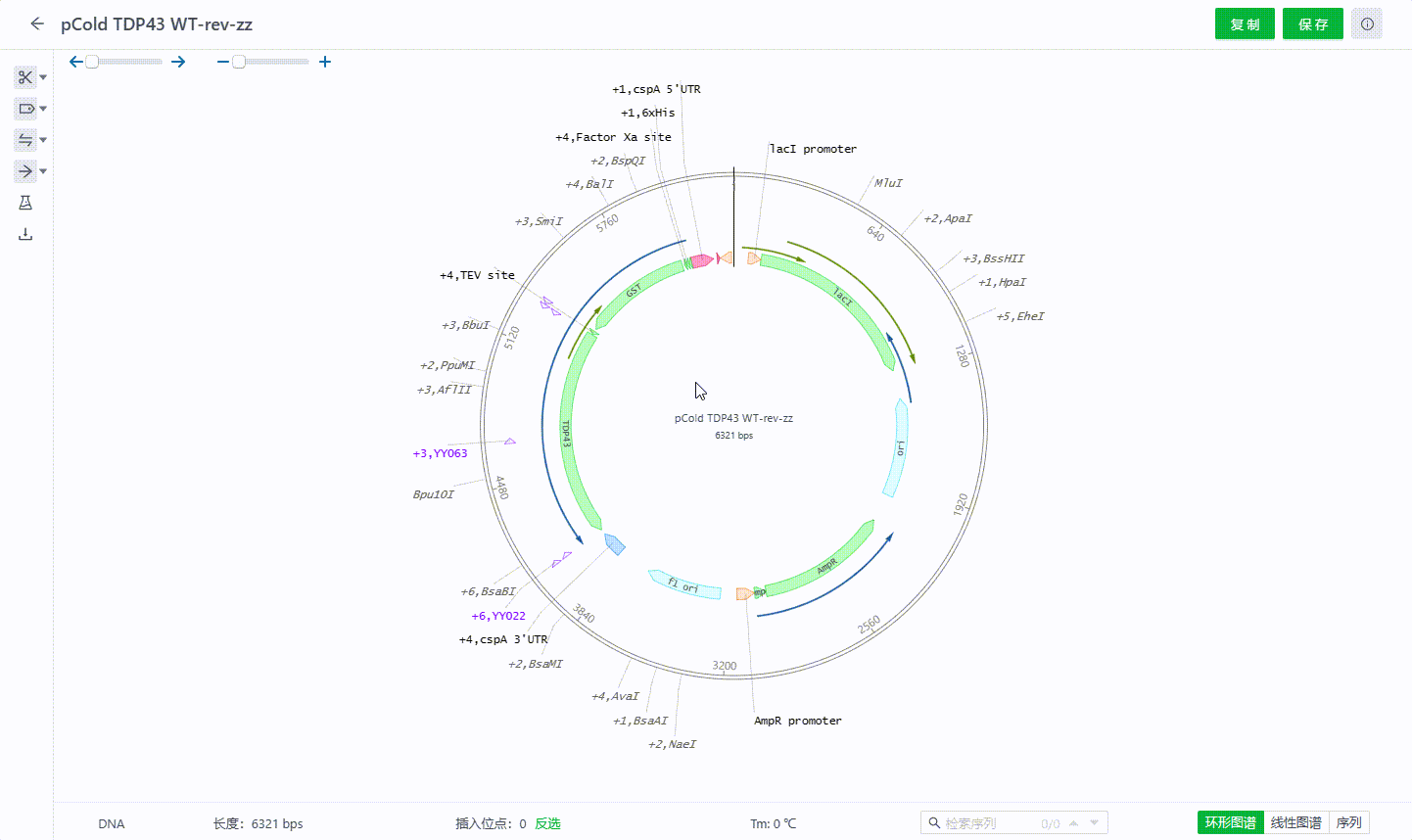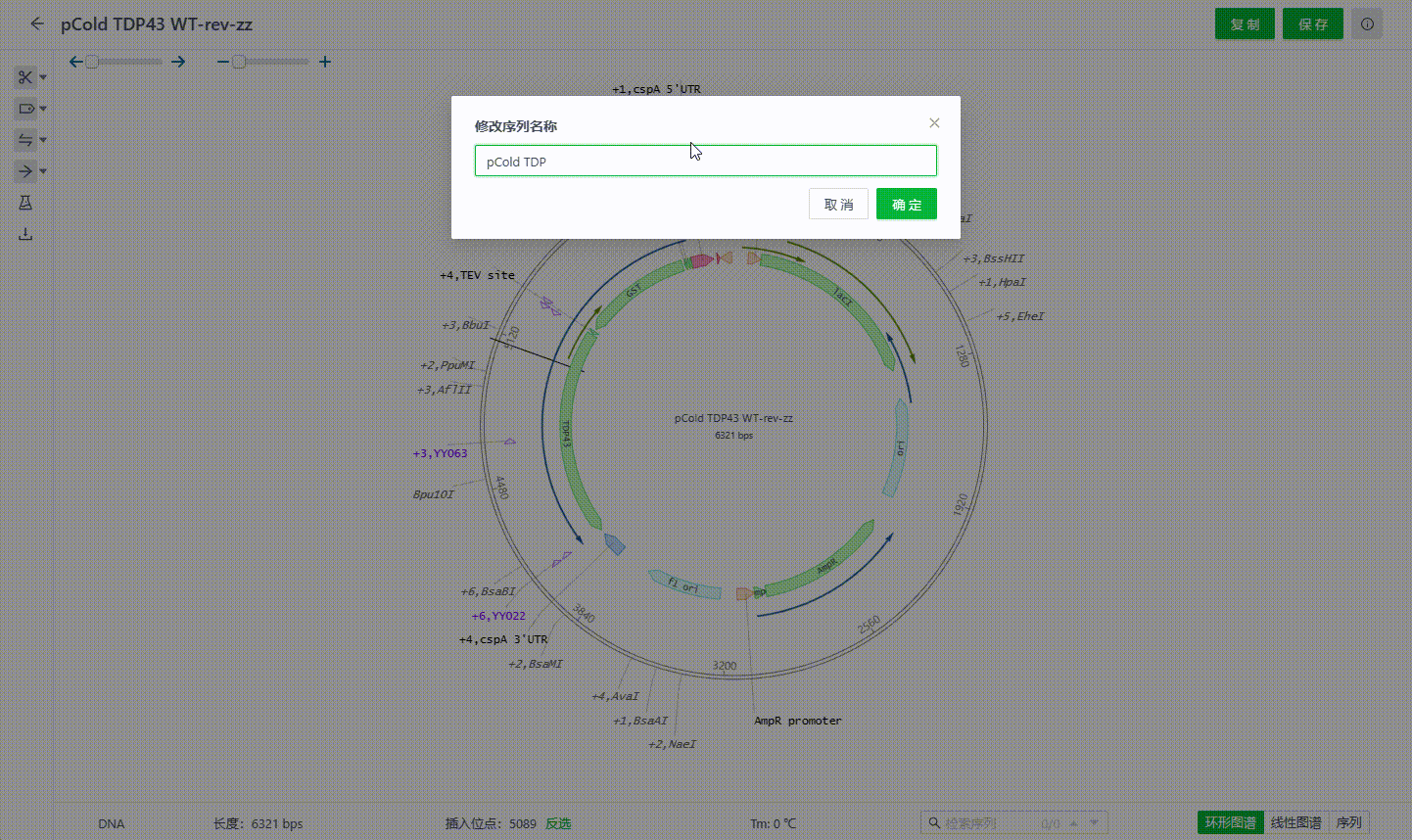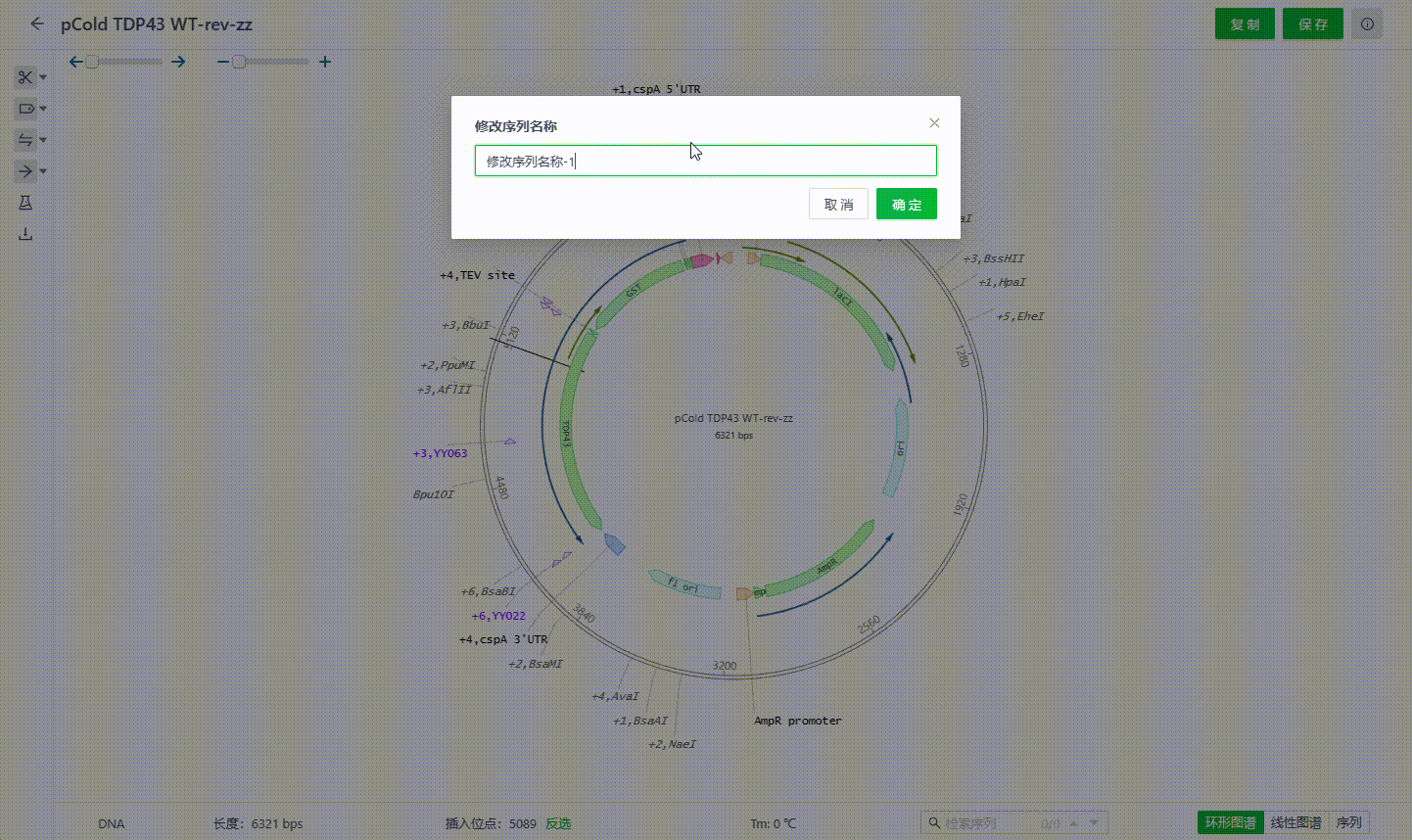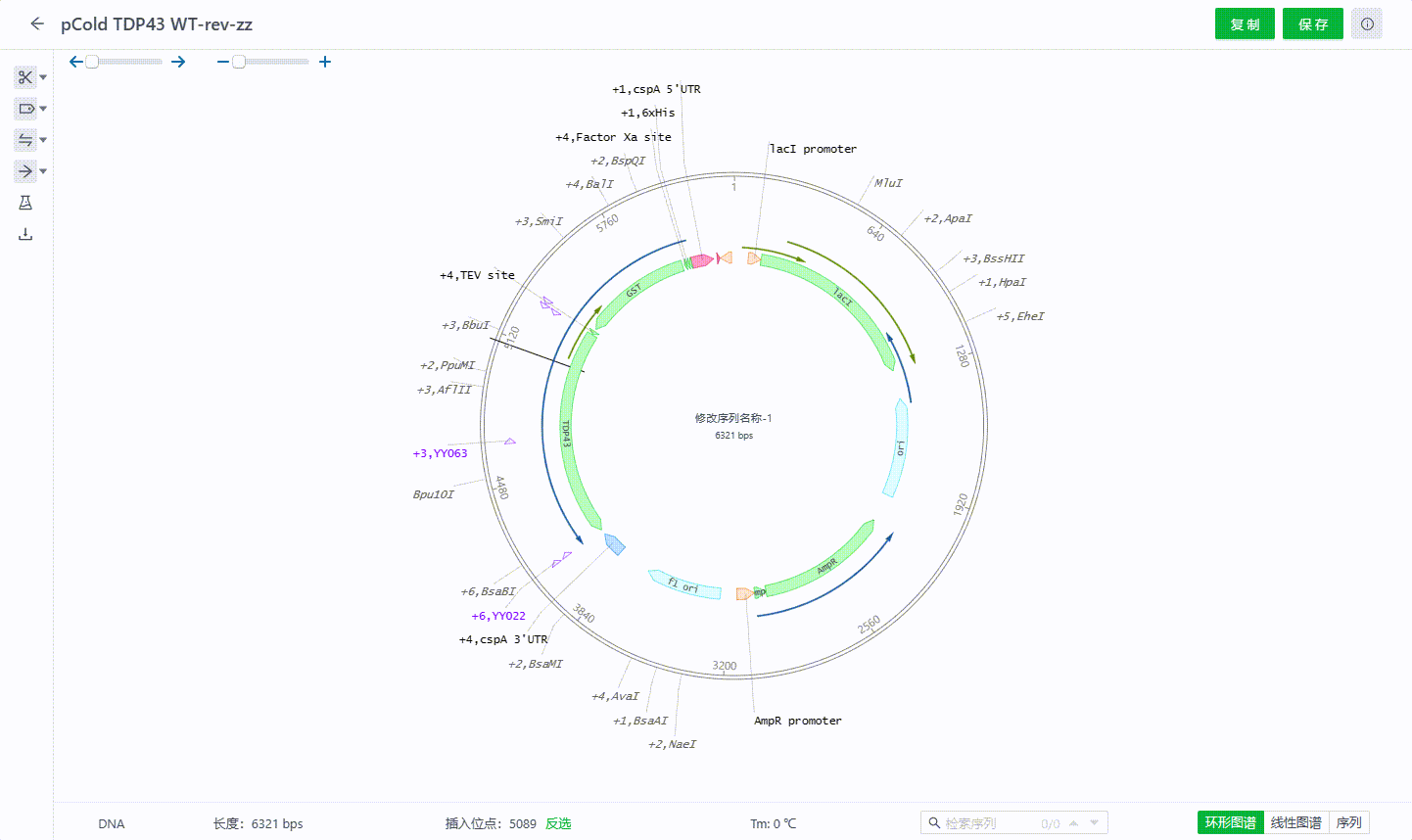
2.5 修改序列名称
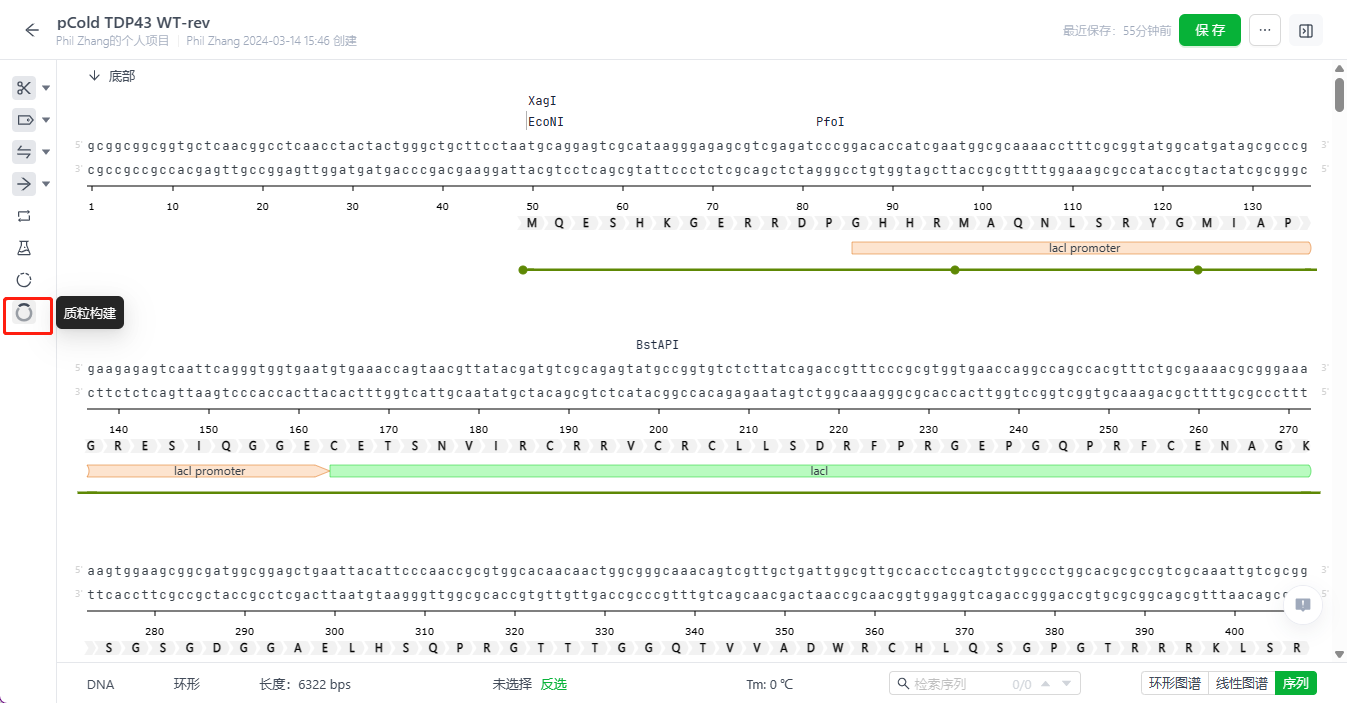
系统支持用户可以将序列名称与文件名称分开设置。点击环形图谱中间的序列名称,填写名称并保存即可完成修改,该名称与文件名称不会同步修改。
2.6 翻转序列
用户可以通过工具栏直接翻转整个序列,或者通过右键的方式快捷翻转。
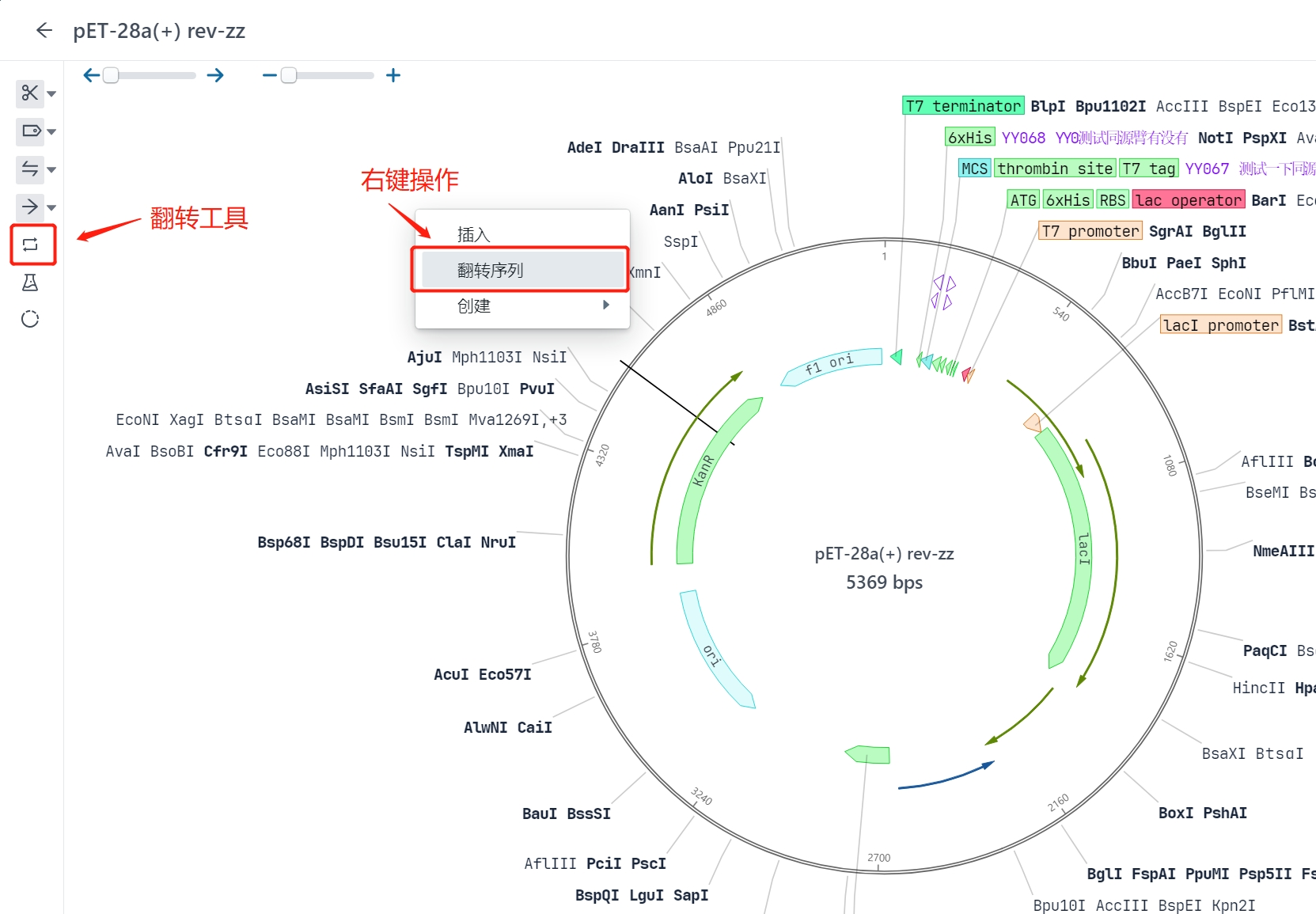
2.7 拓扑结构修改
用户可以将序列文件的拓扑结构进行调整。
- 将环状文件修改为线性文件
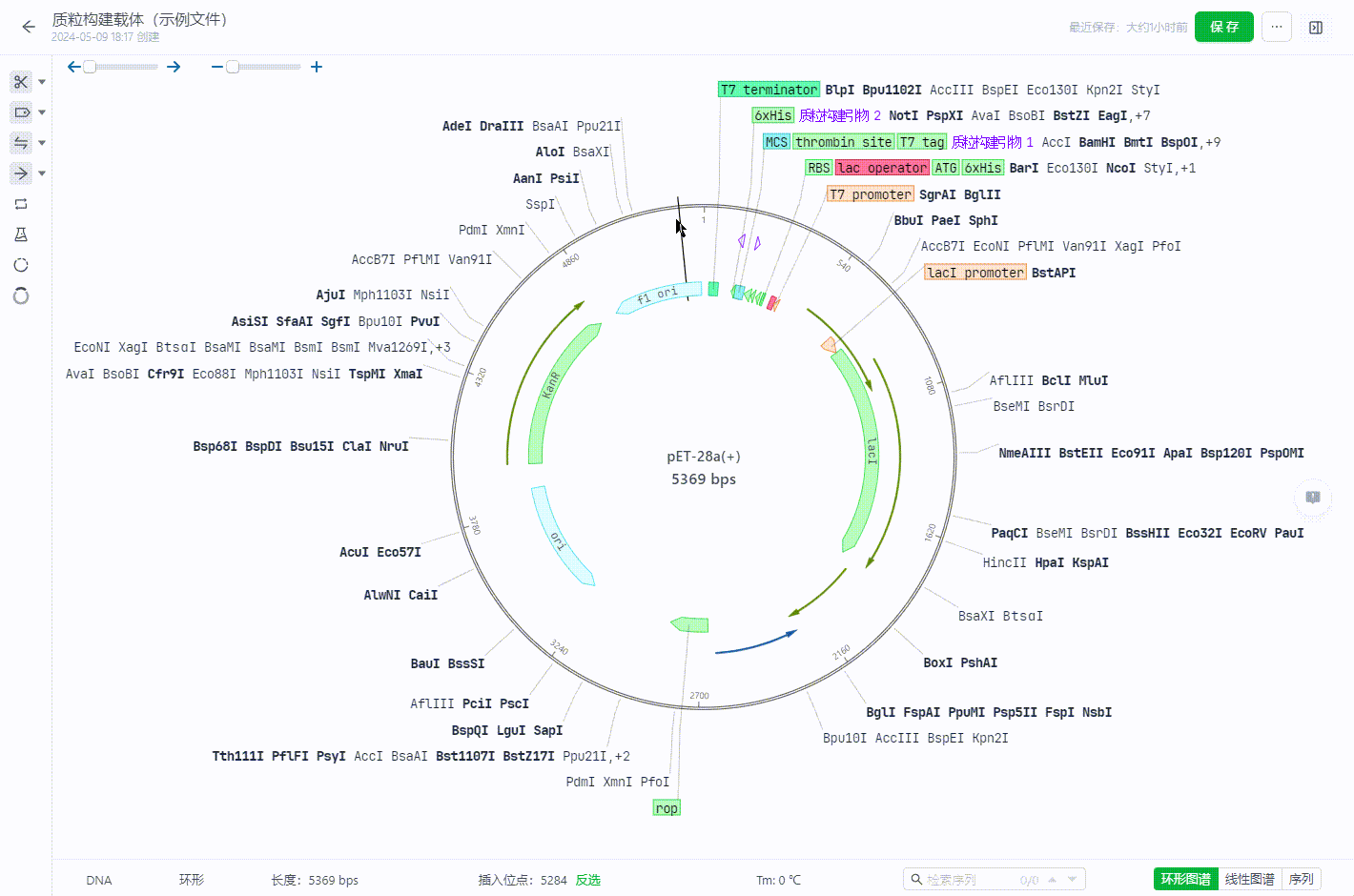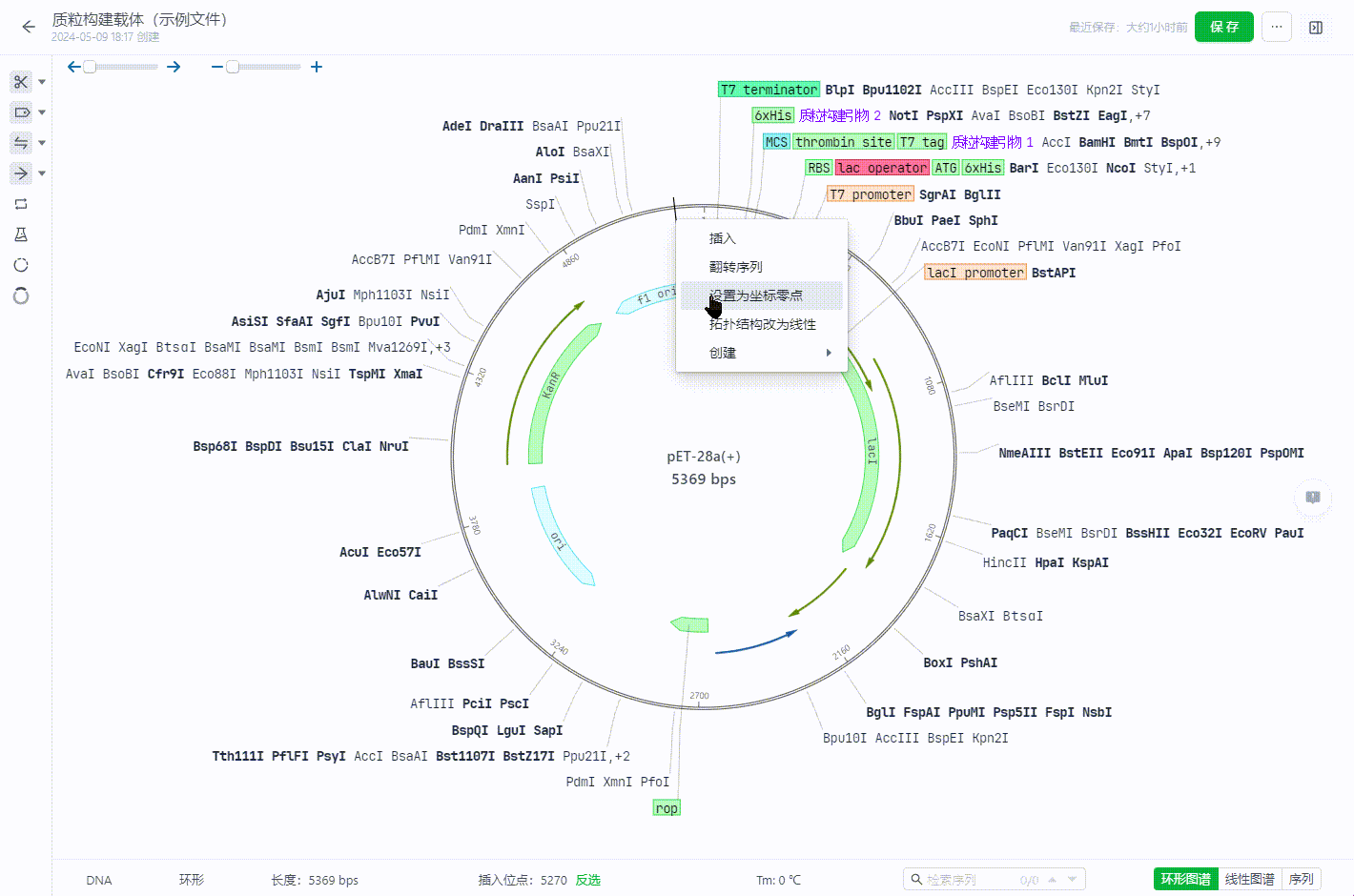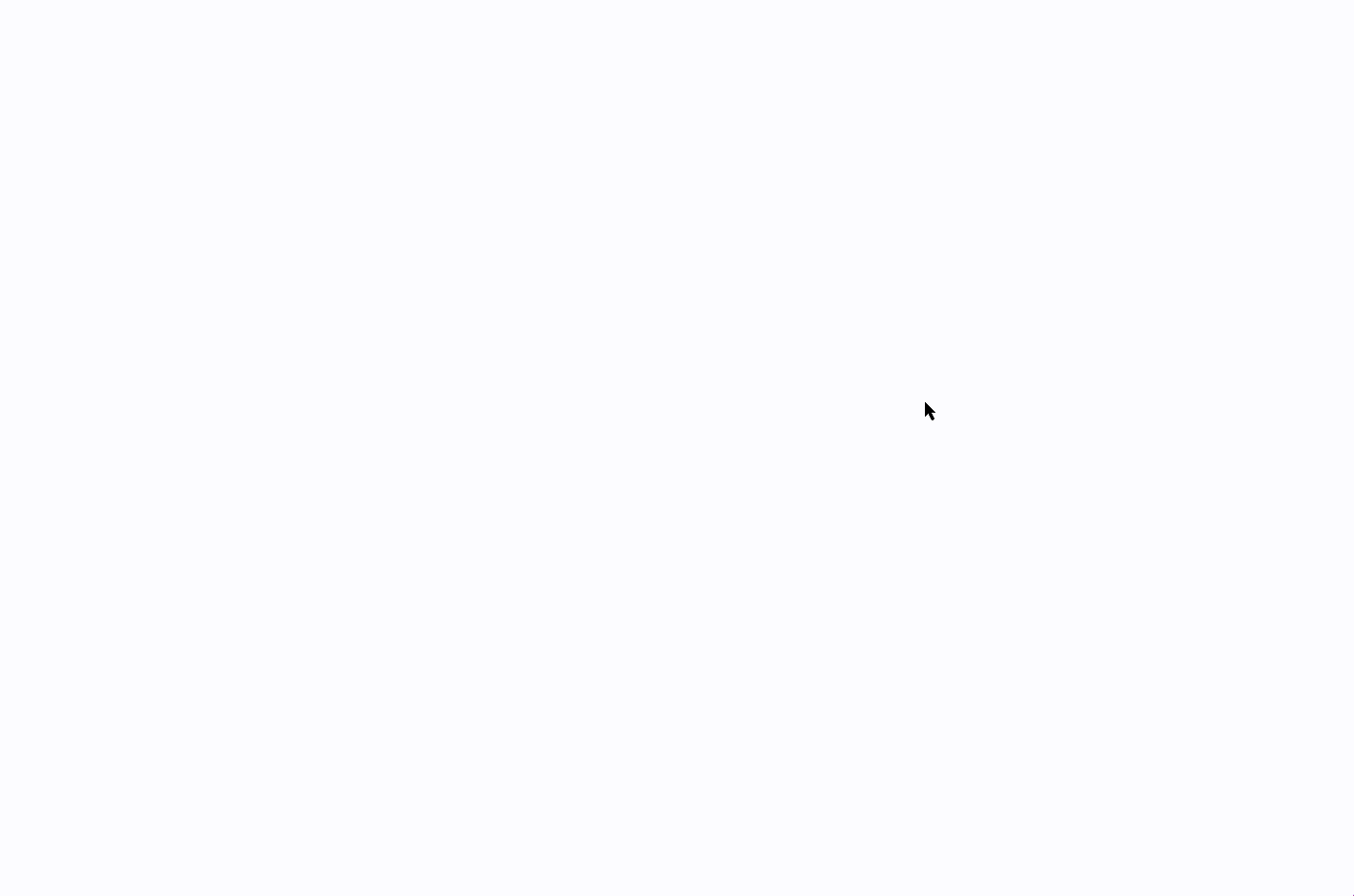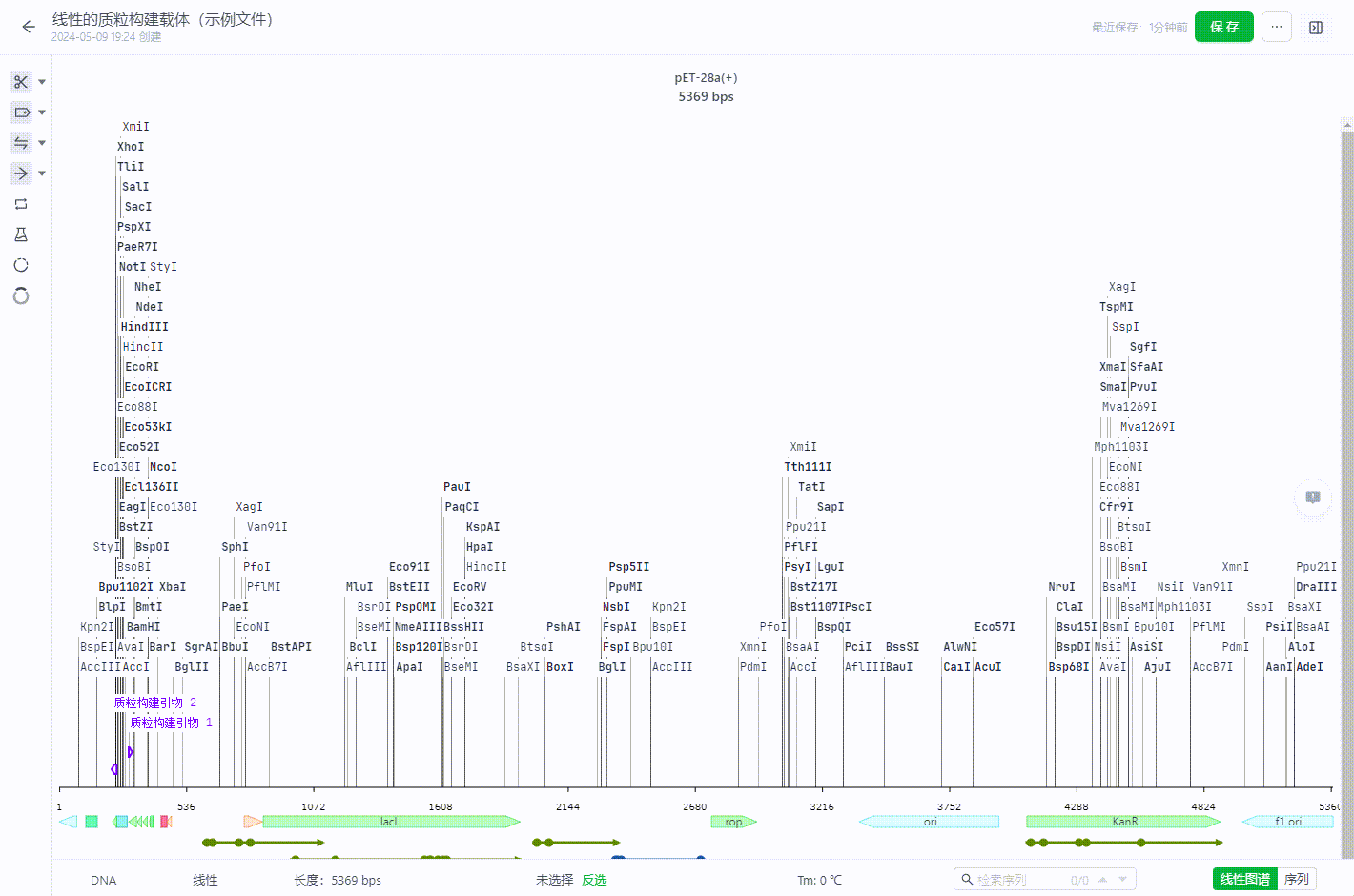
若在任一坐标处右键,则会在此坐标处打断序列,然后展平为线性序列。 若选择一个区�域右键,则会在原点处处打断序列,然后展平为线性序列。
- 将线性文件修改为环状文件
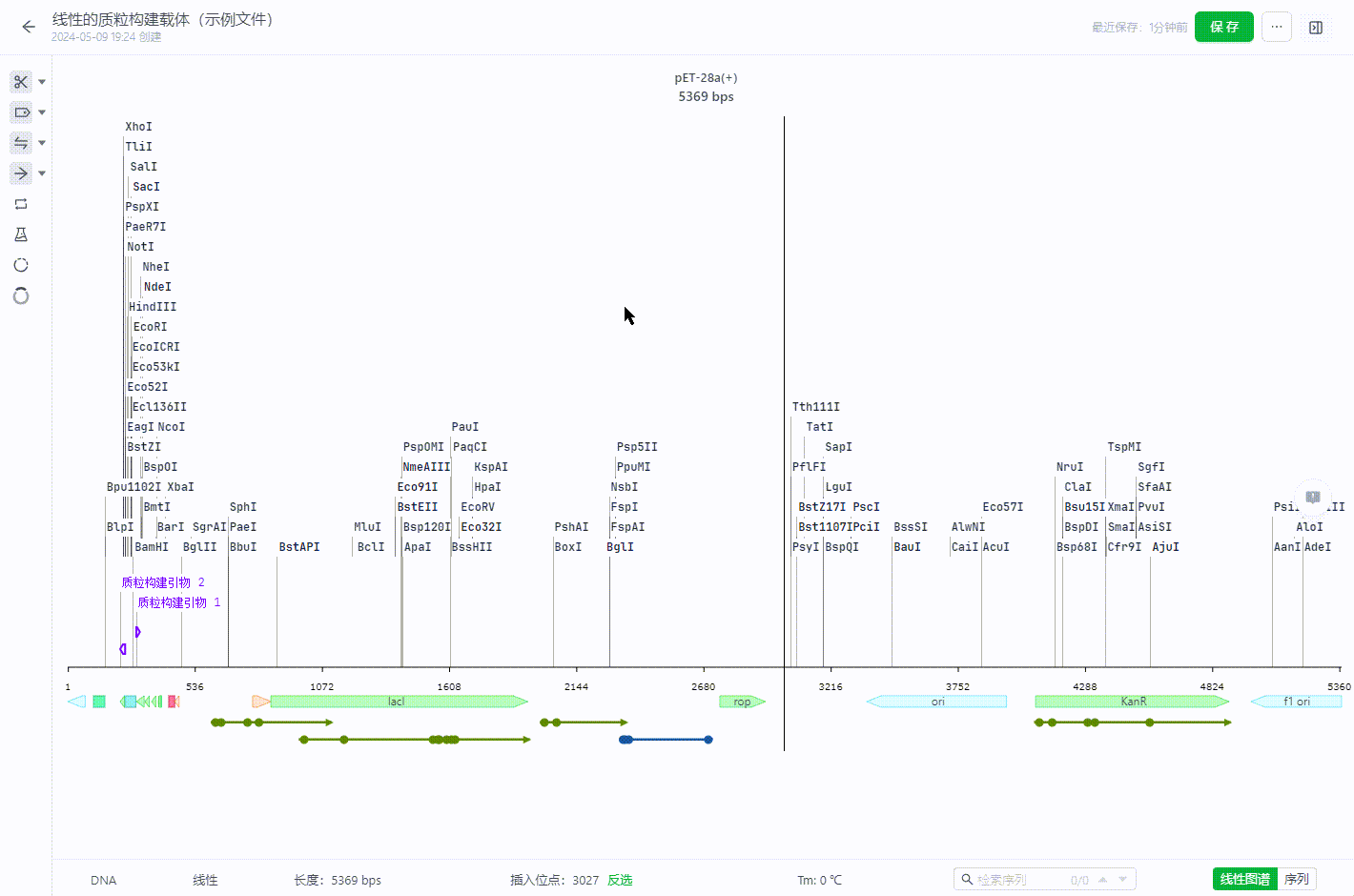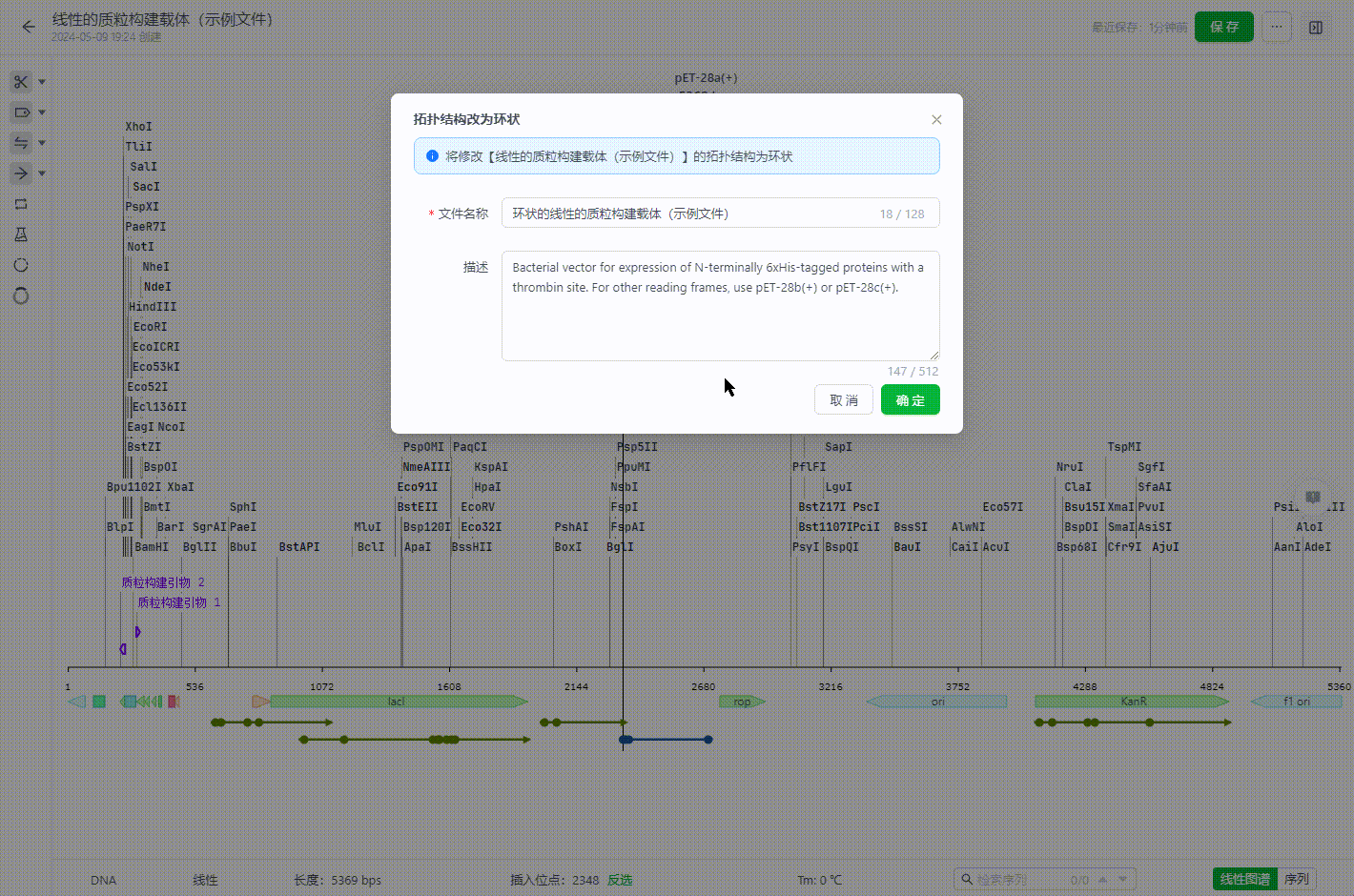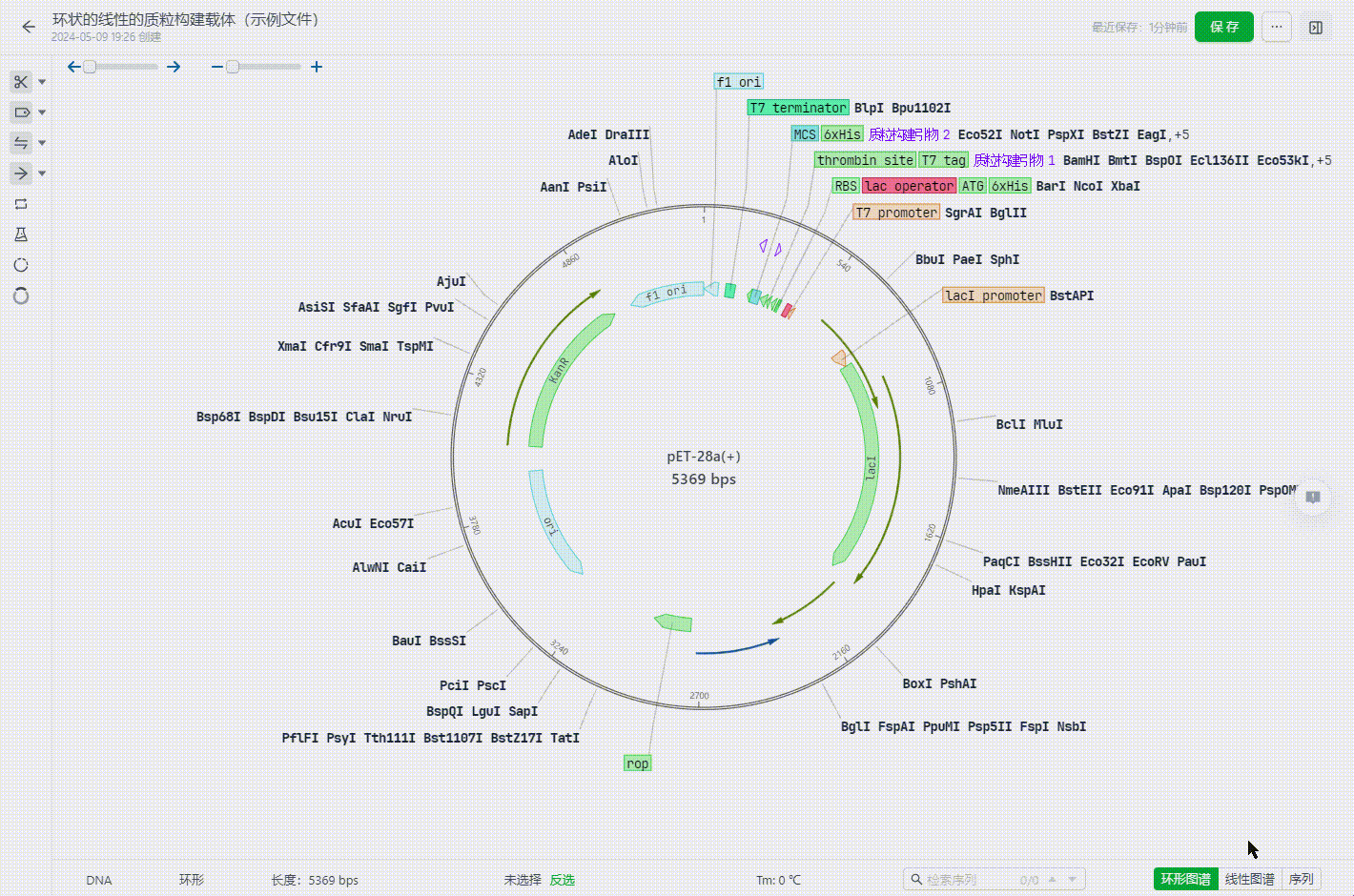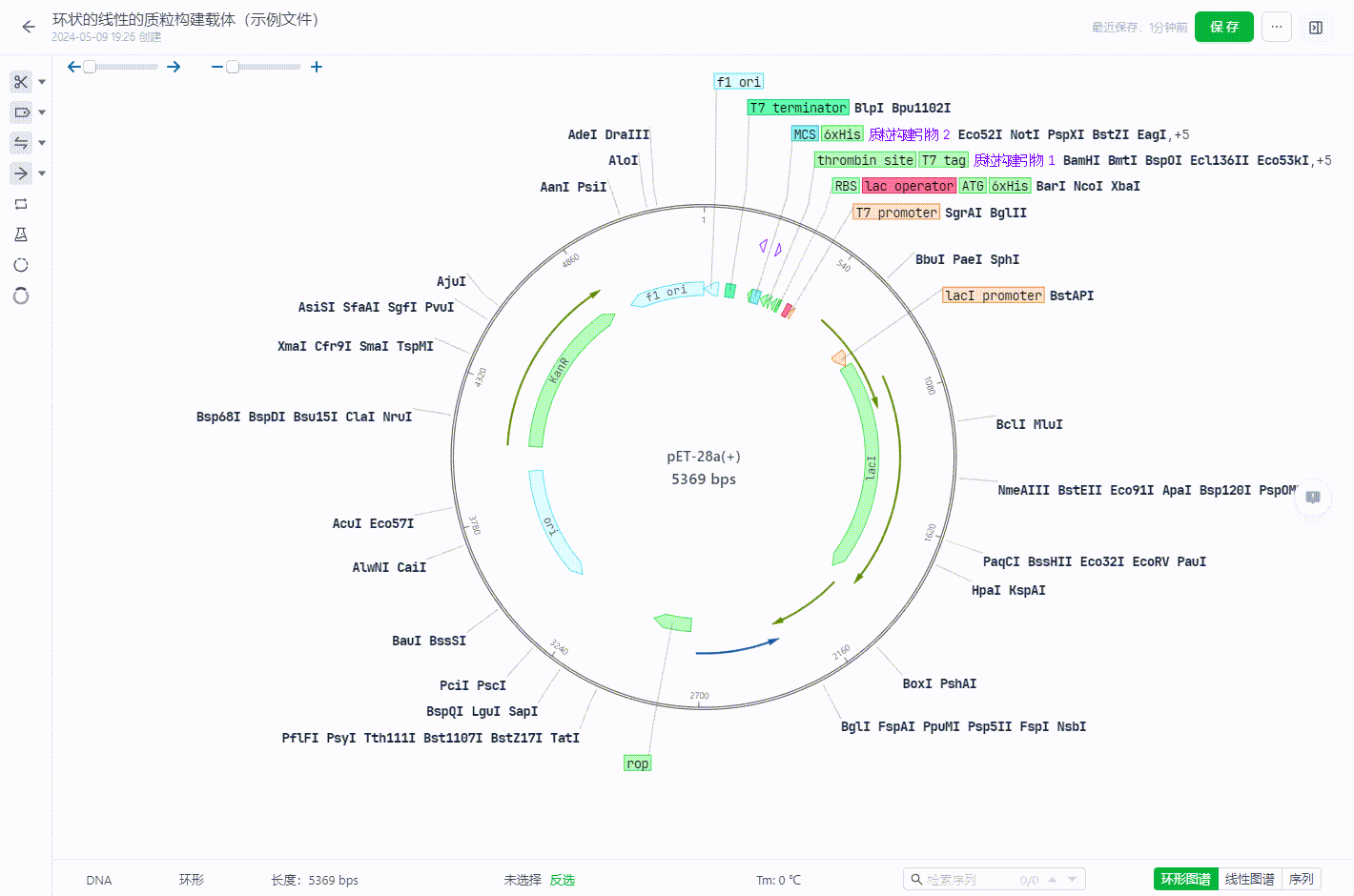
在任一位置右键即可将线性文件的头尾相连,形成环状文件。 目前头尾是粘性末端的序列不支持拓扑结构的调整。
2.8 环状文件原点修改
环状文件可以通过在某个坐标处右键直接修改文件原点。
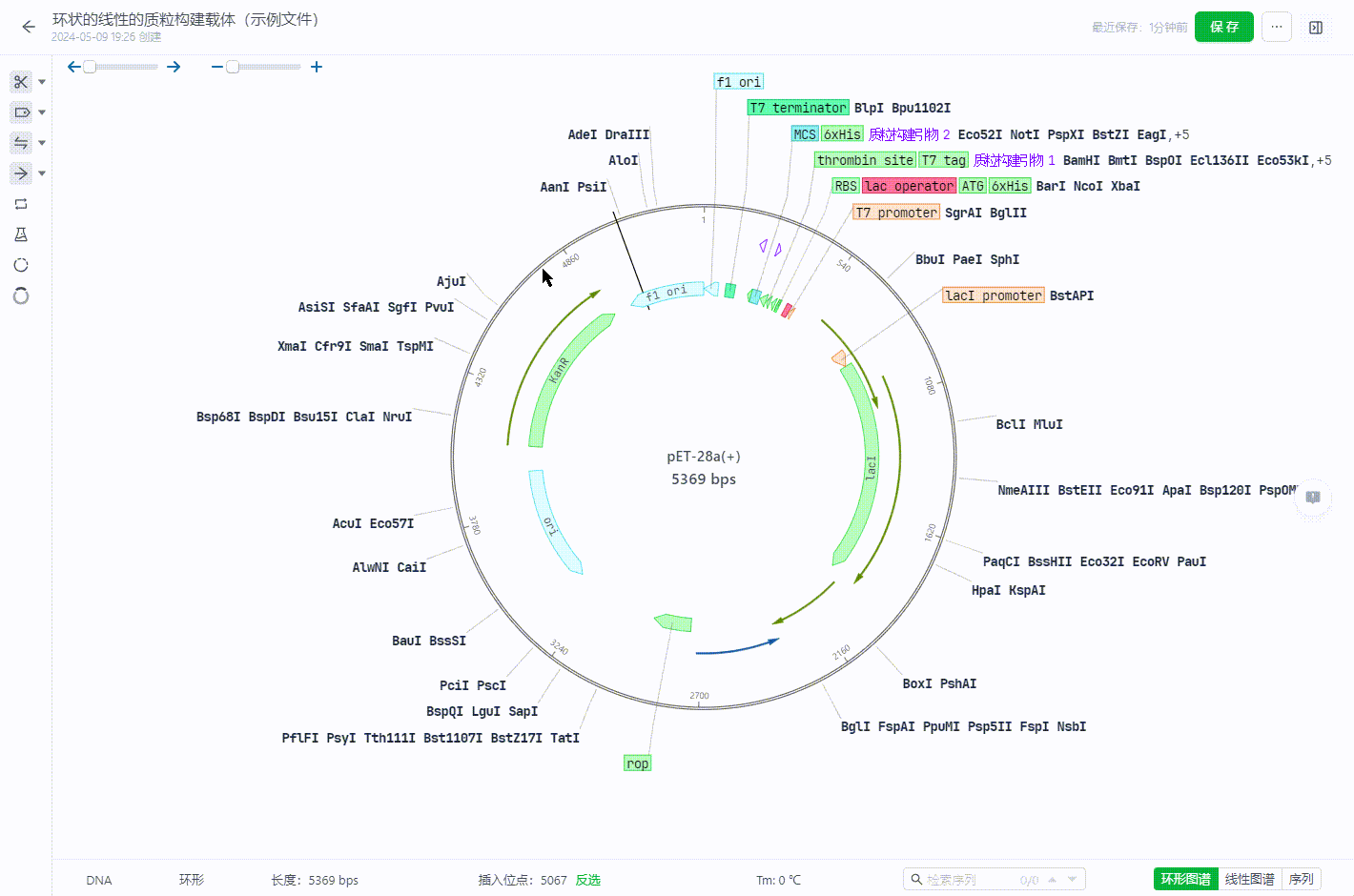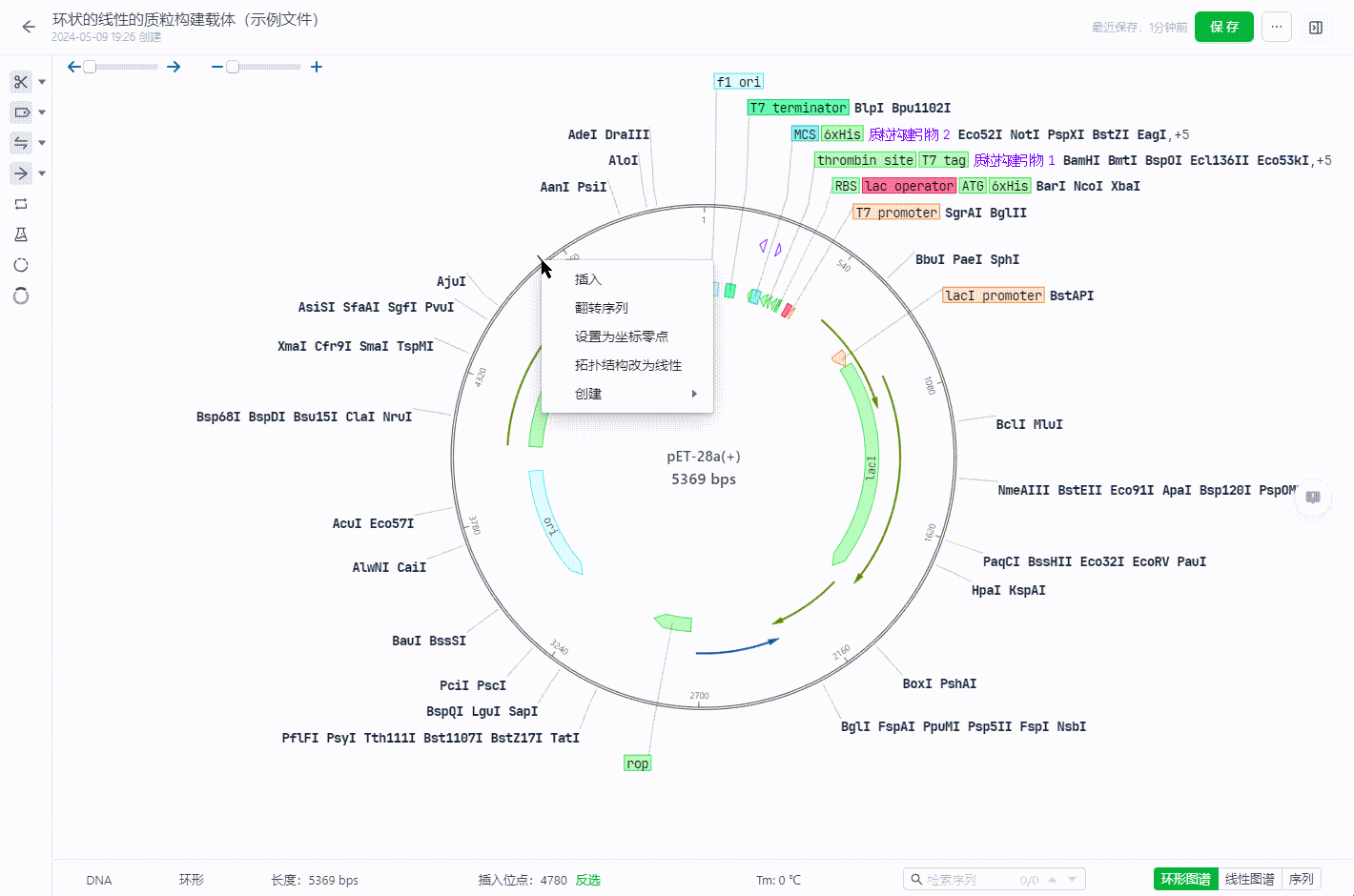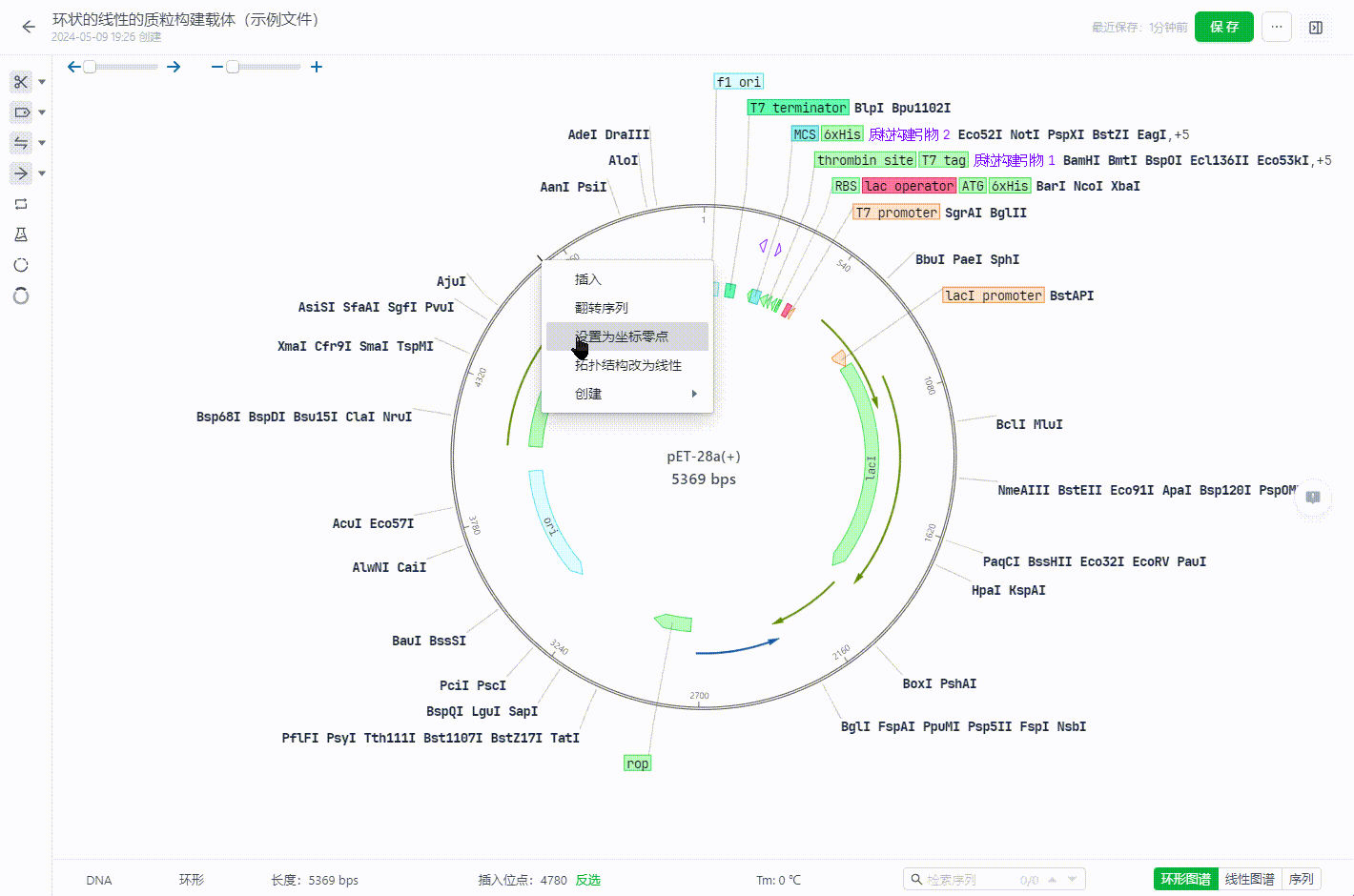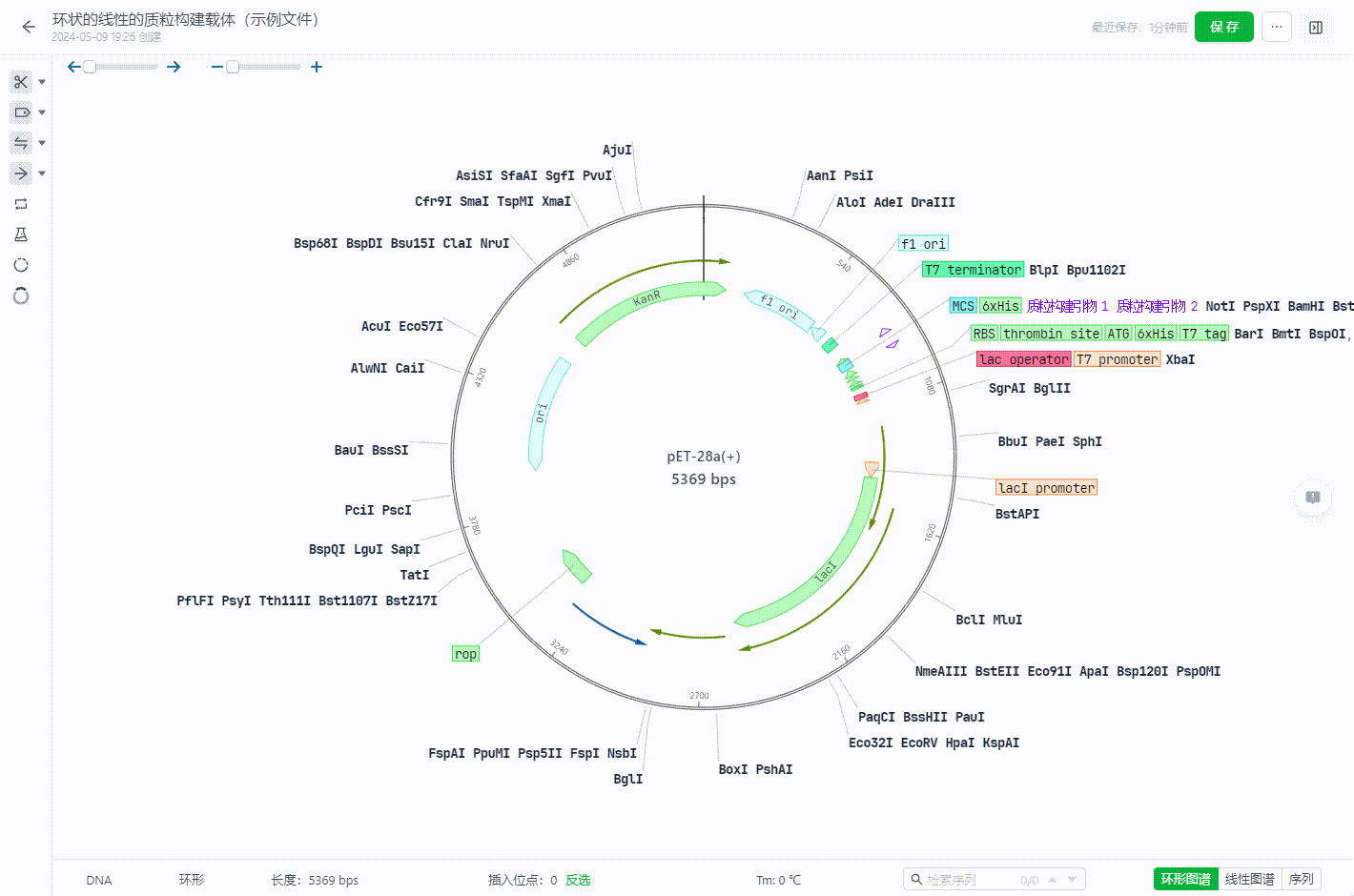
2.9 复制氨基酸序列
- 用户可以在打开的序列文件中,选择序列通过右键操作菜单中的“复制”功能复制氨基酸序列信息到剪切板。
3. 保存、导出文件
3.1 保存文件
目前系统暂不支持自动保存,需要手动点击保存。
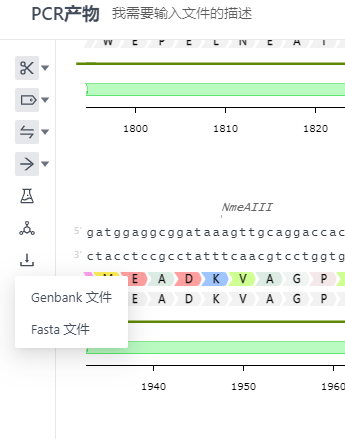
3.2 导出文件
系统目前支持导出.gb .fasta格式的文件。
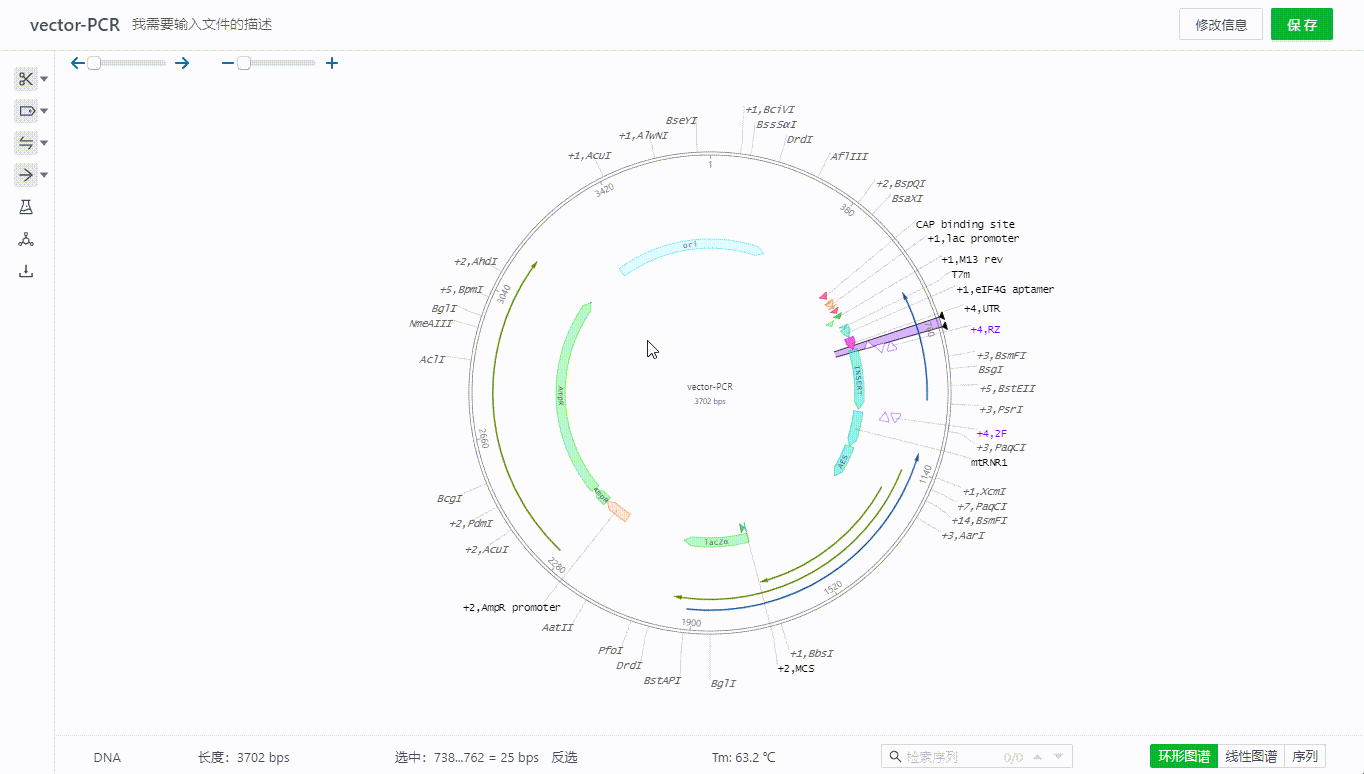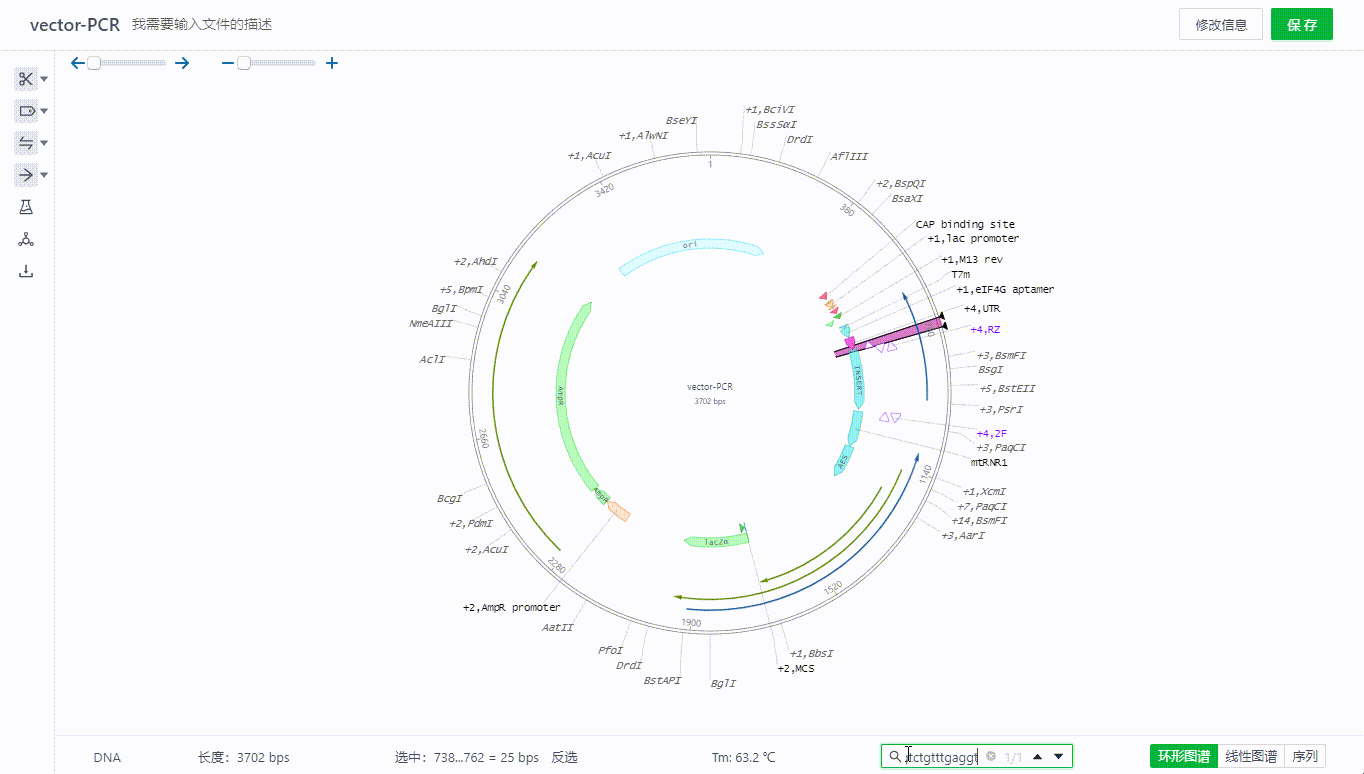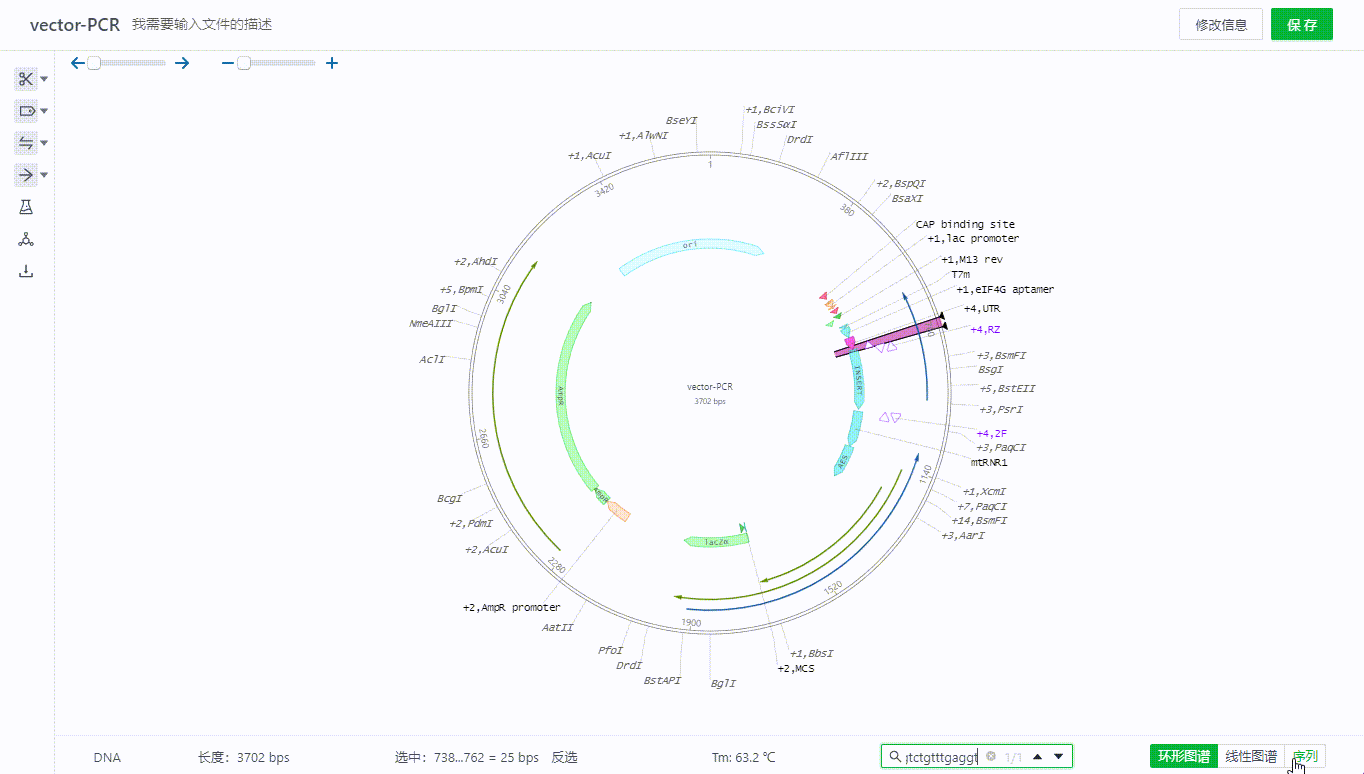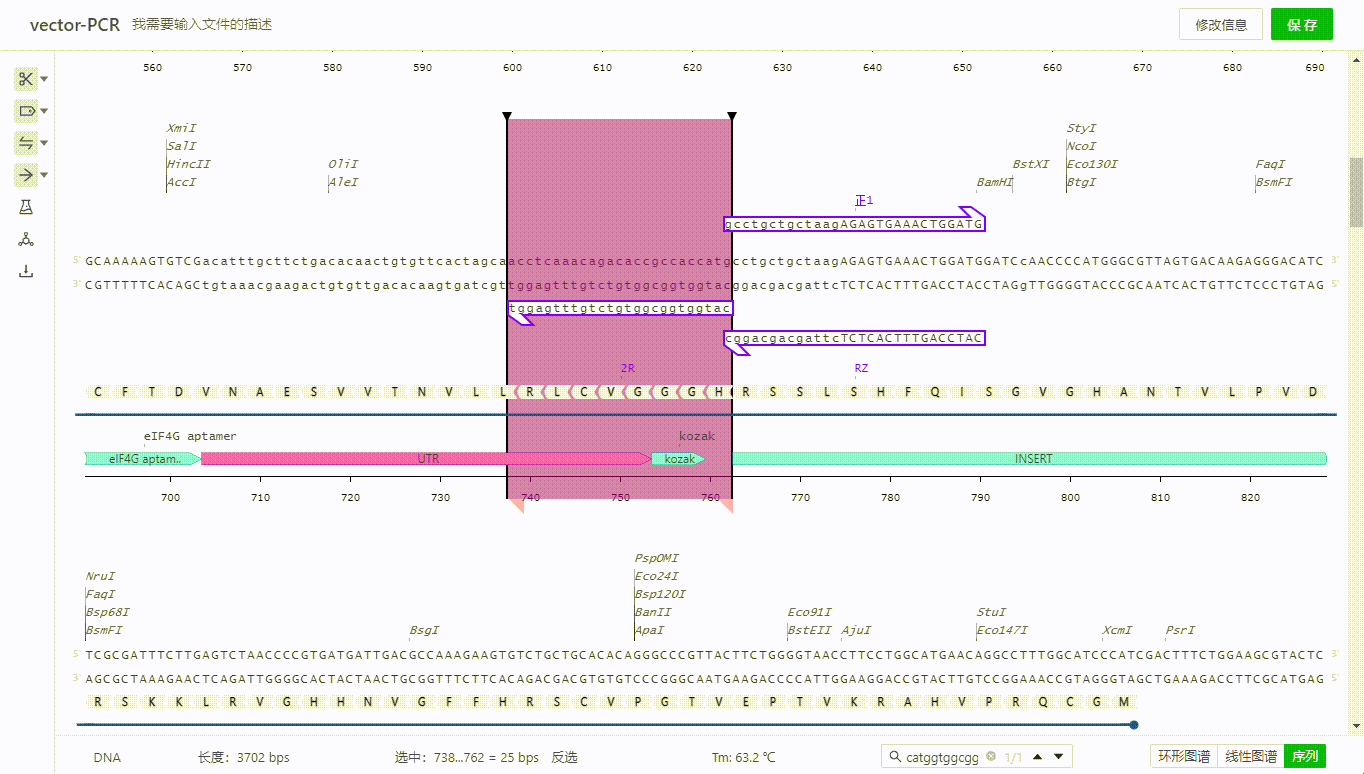
4. 检索序列
4.1 检索序列
用户可以将需要搜索的序列在右下角输入,检索序列的空格内,系统会把完整匹配的序列选取,可以点击不同视图,将会直接定位到被选取的区域。
5. 酶相关操作
5.1 酶展示开关
用户可以通过左侧的开关来展示或者隐藏不同视图下的酶。
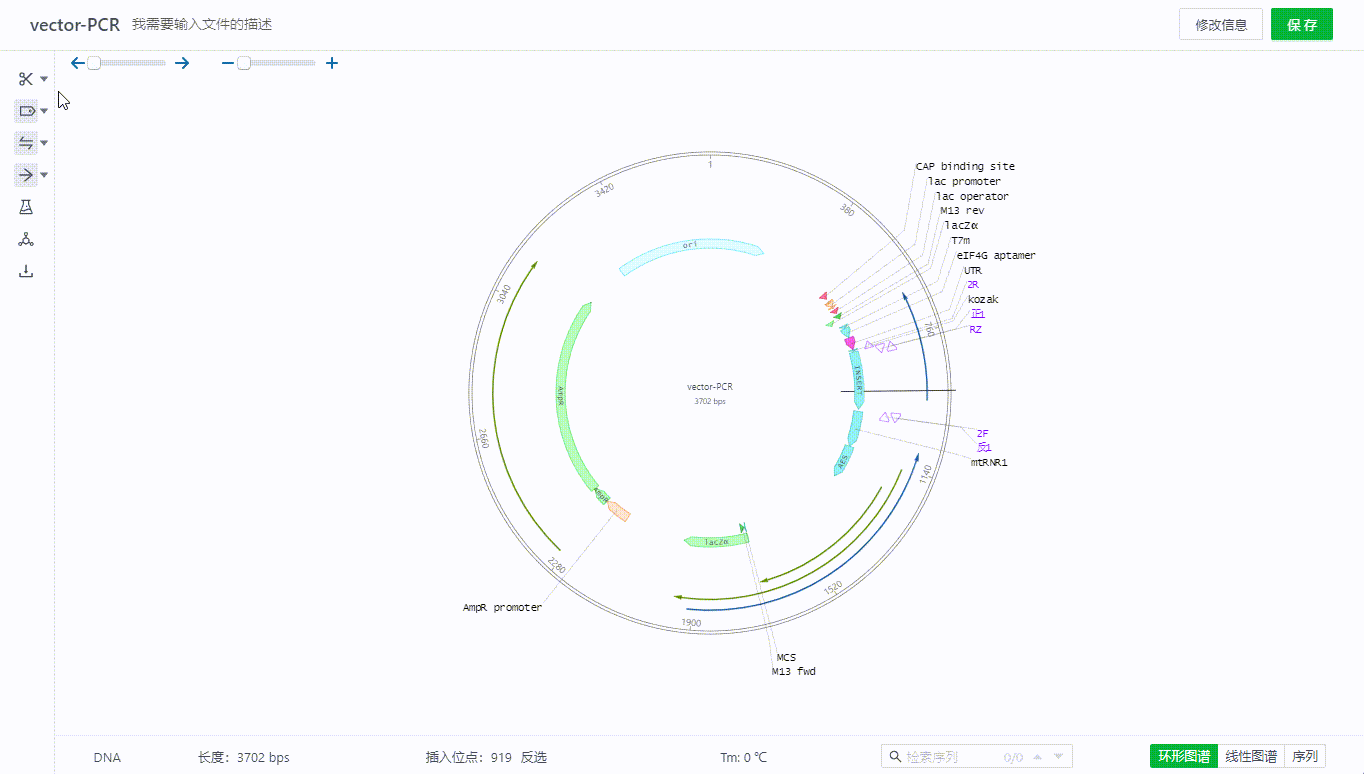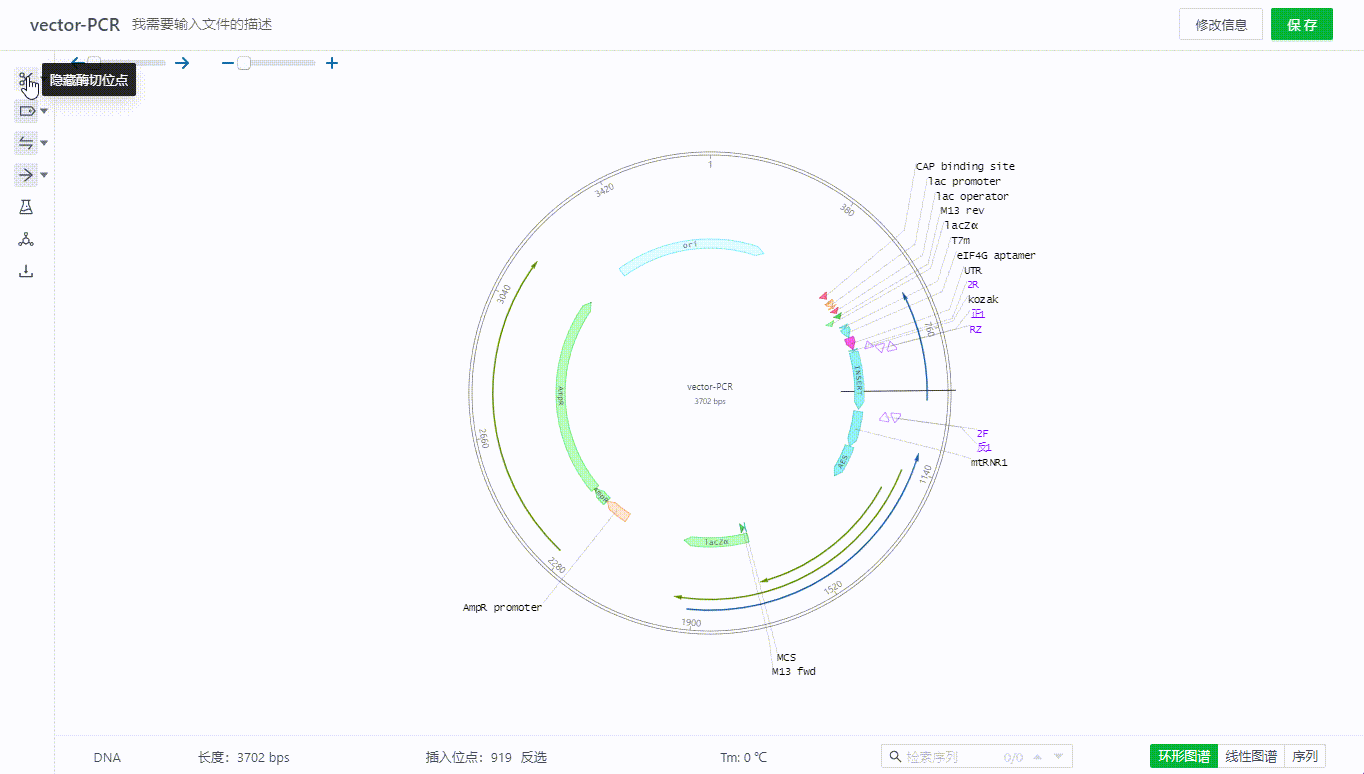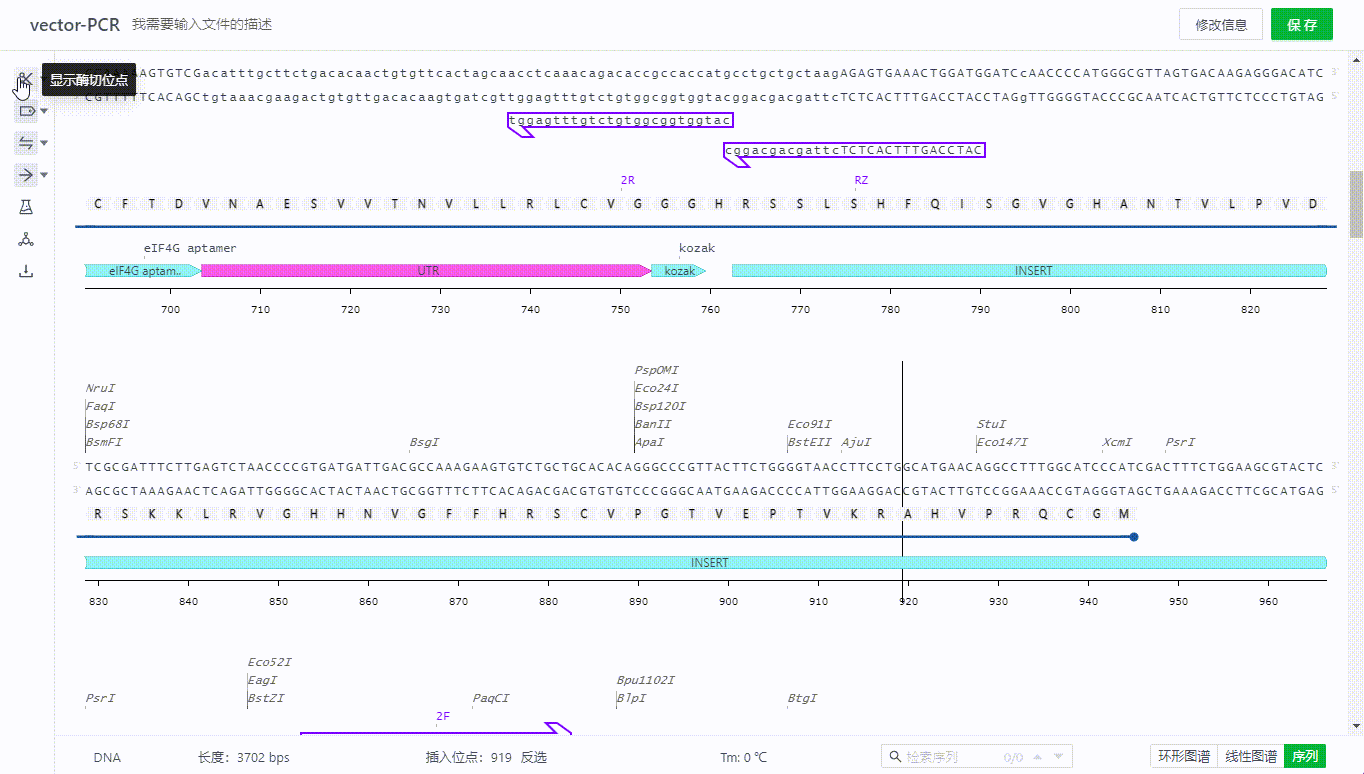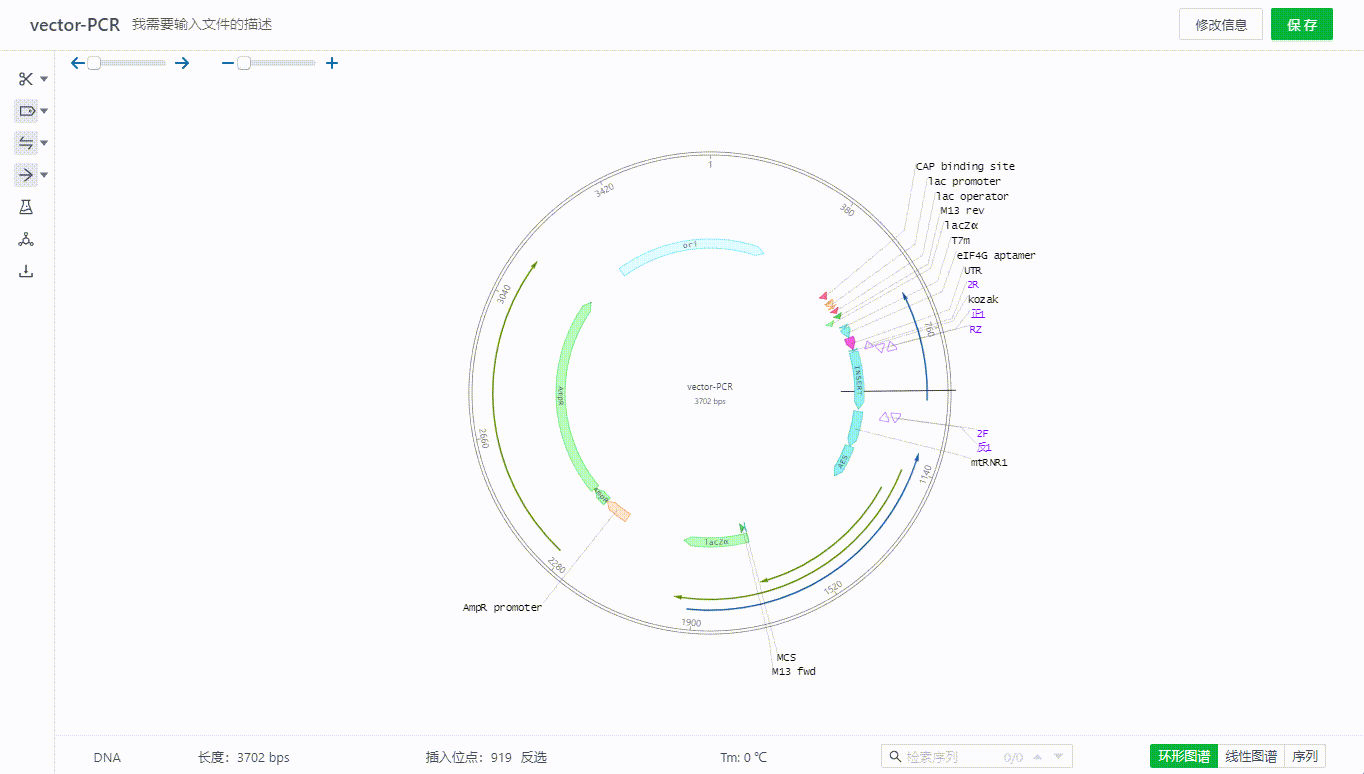
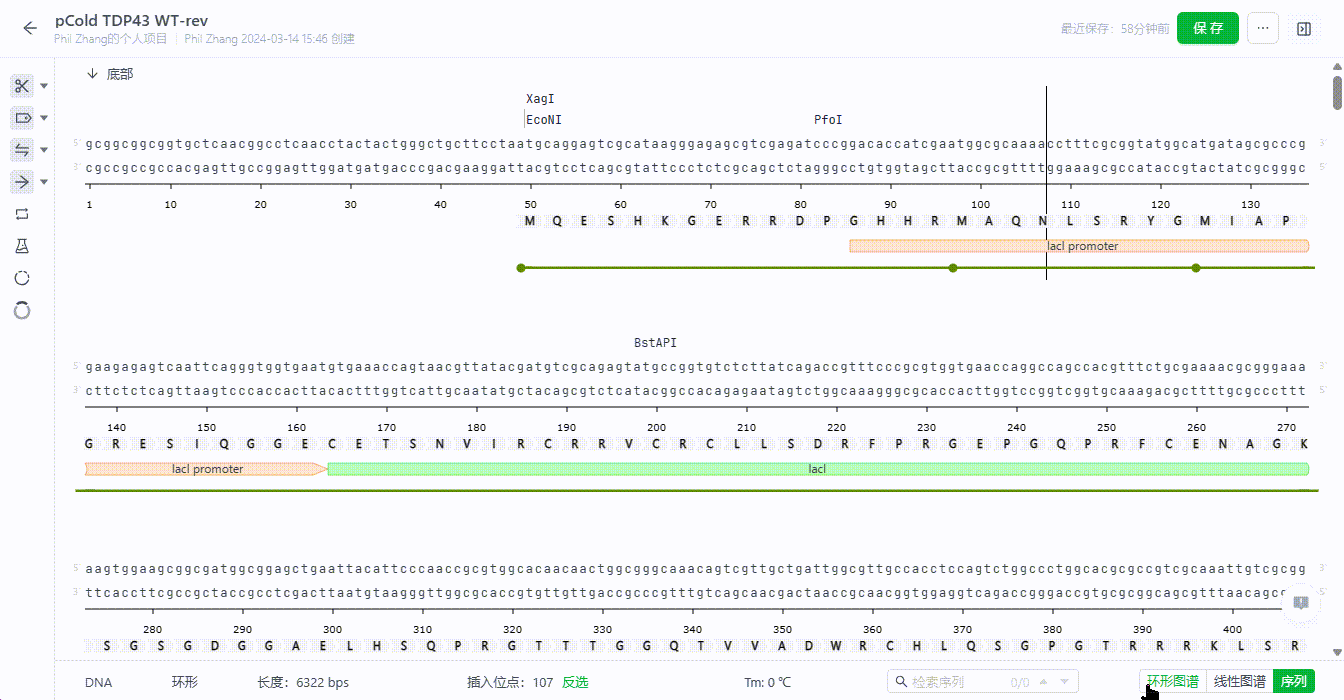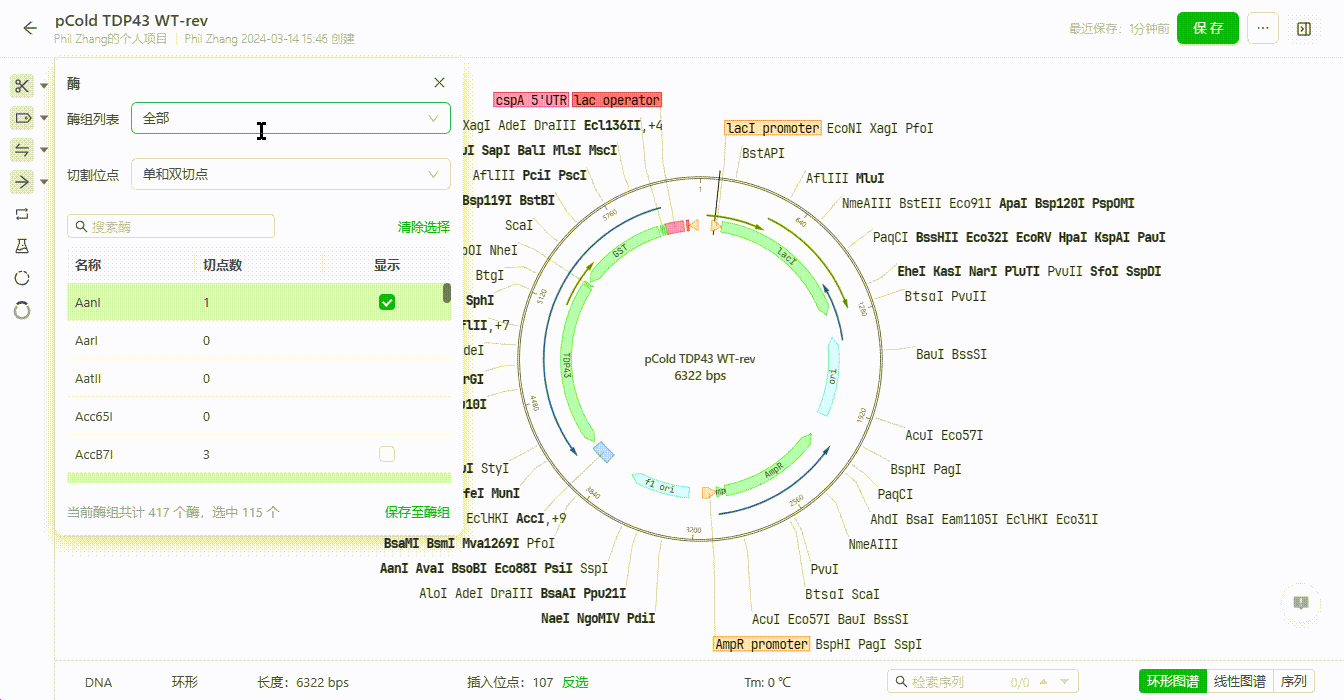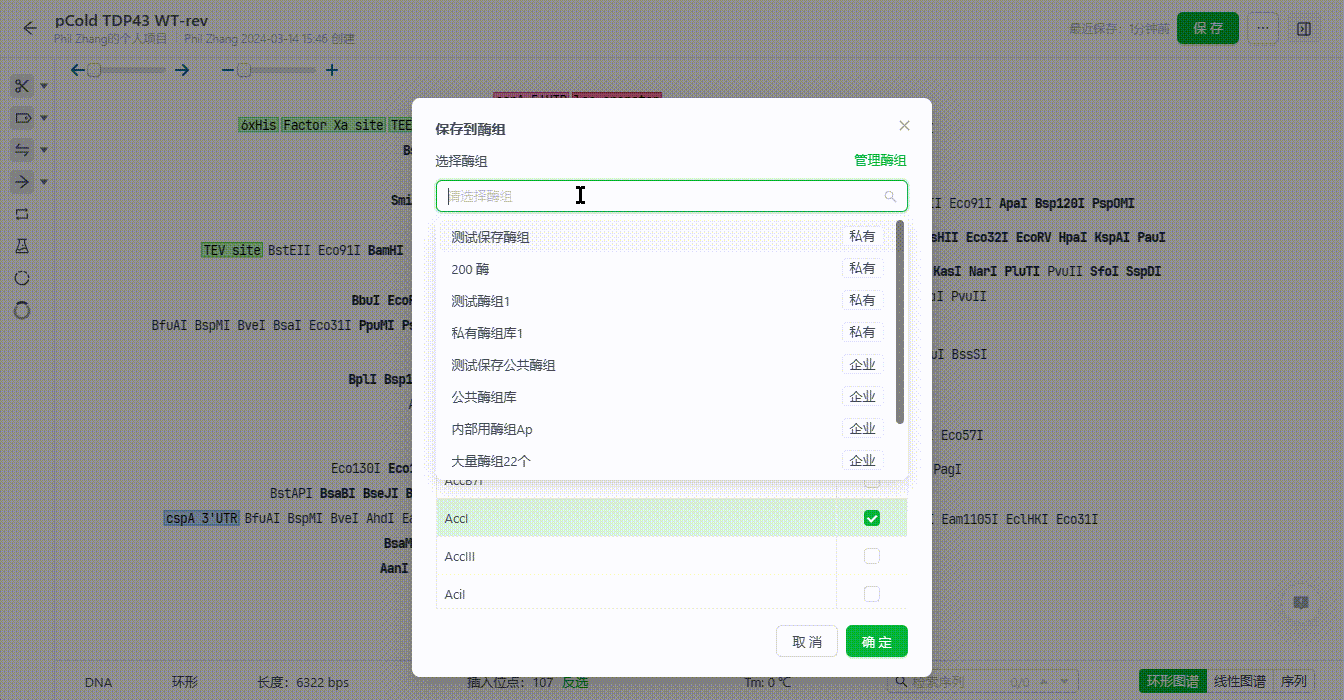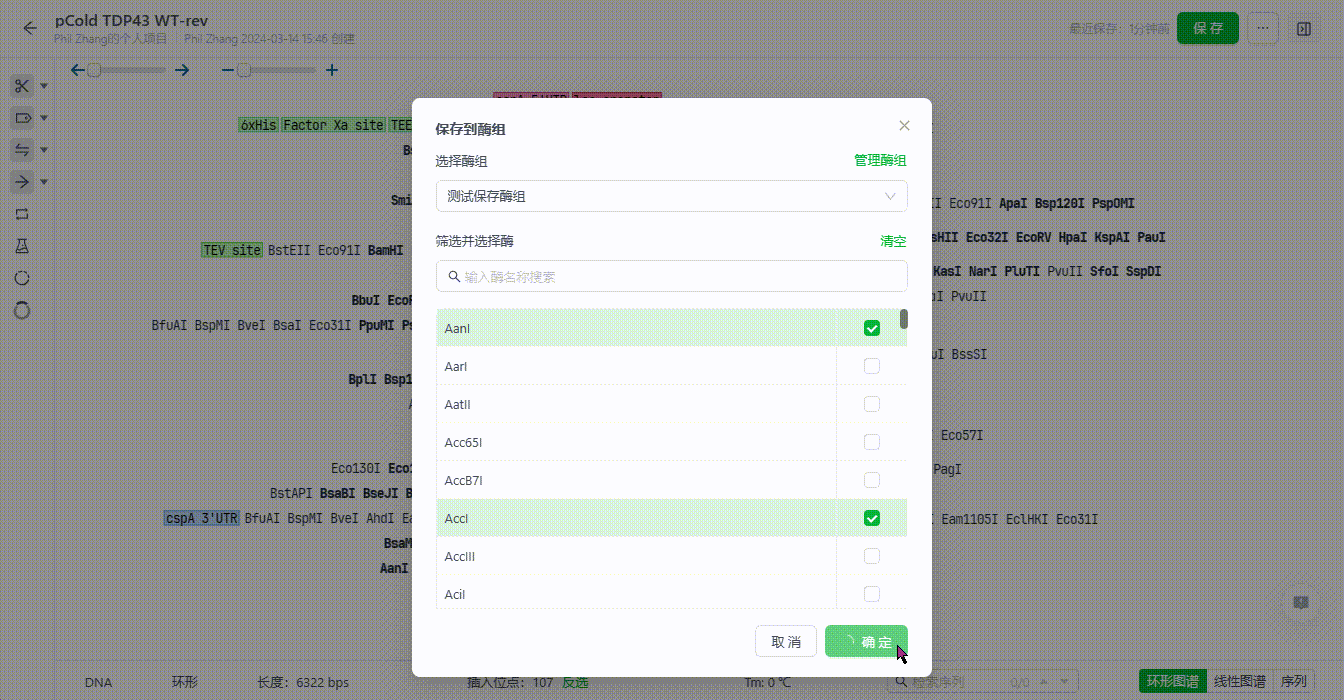
5.2 筛选视图中展示的酶
用户在这里可以通过选择不同的酶组,包括自定义的酶组(自定义酶组点此了解),用户可以进一步从中筛选当前序列中单双切位的酶,在筛选酶的列表中将展示已筛选的酶,如果有不需要单独展示的只需要去掉勾选即可。
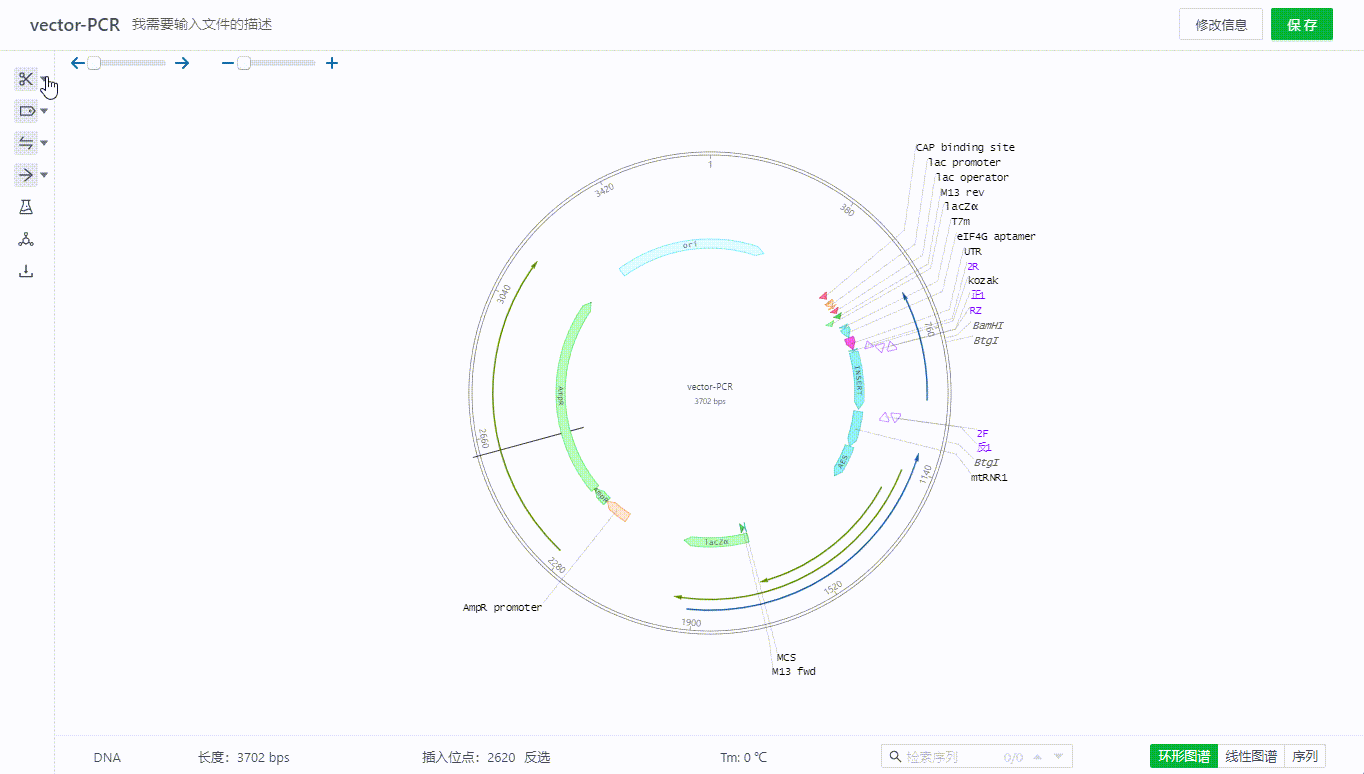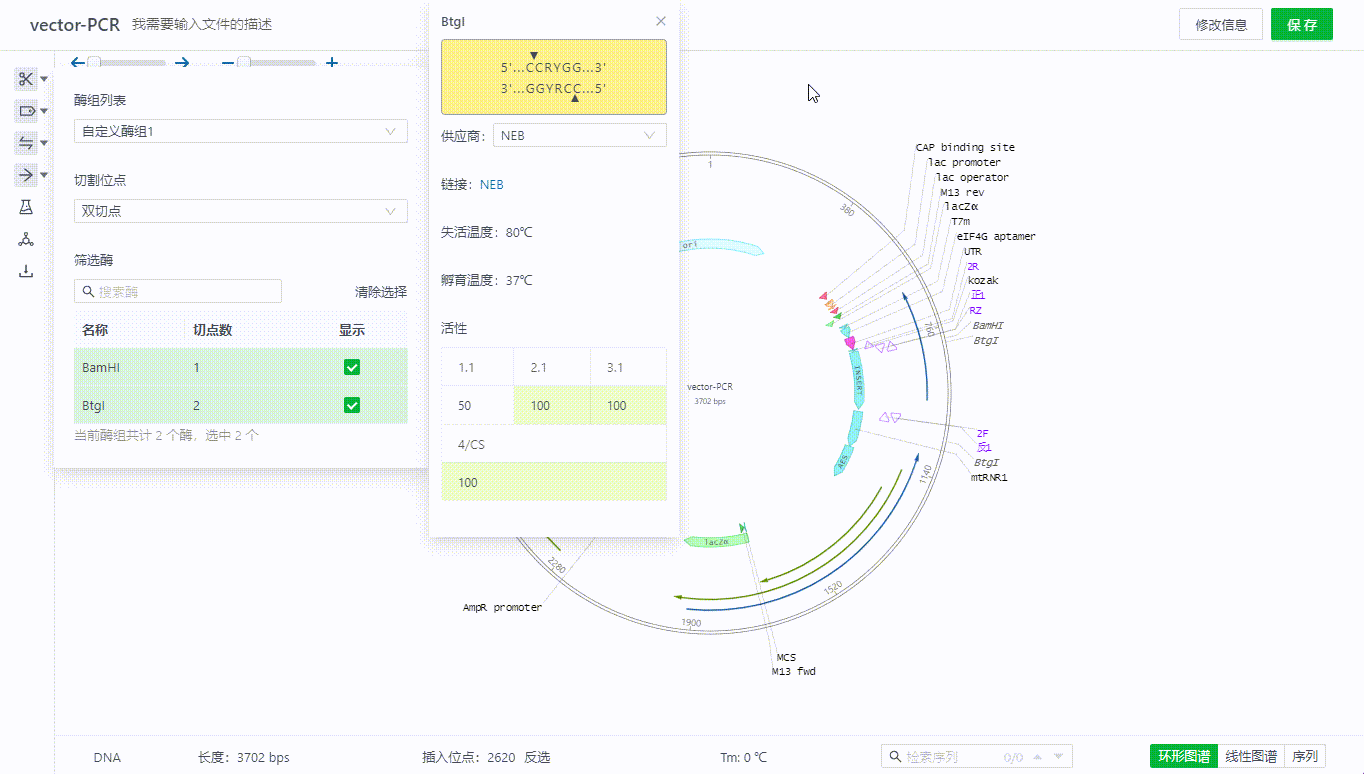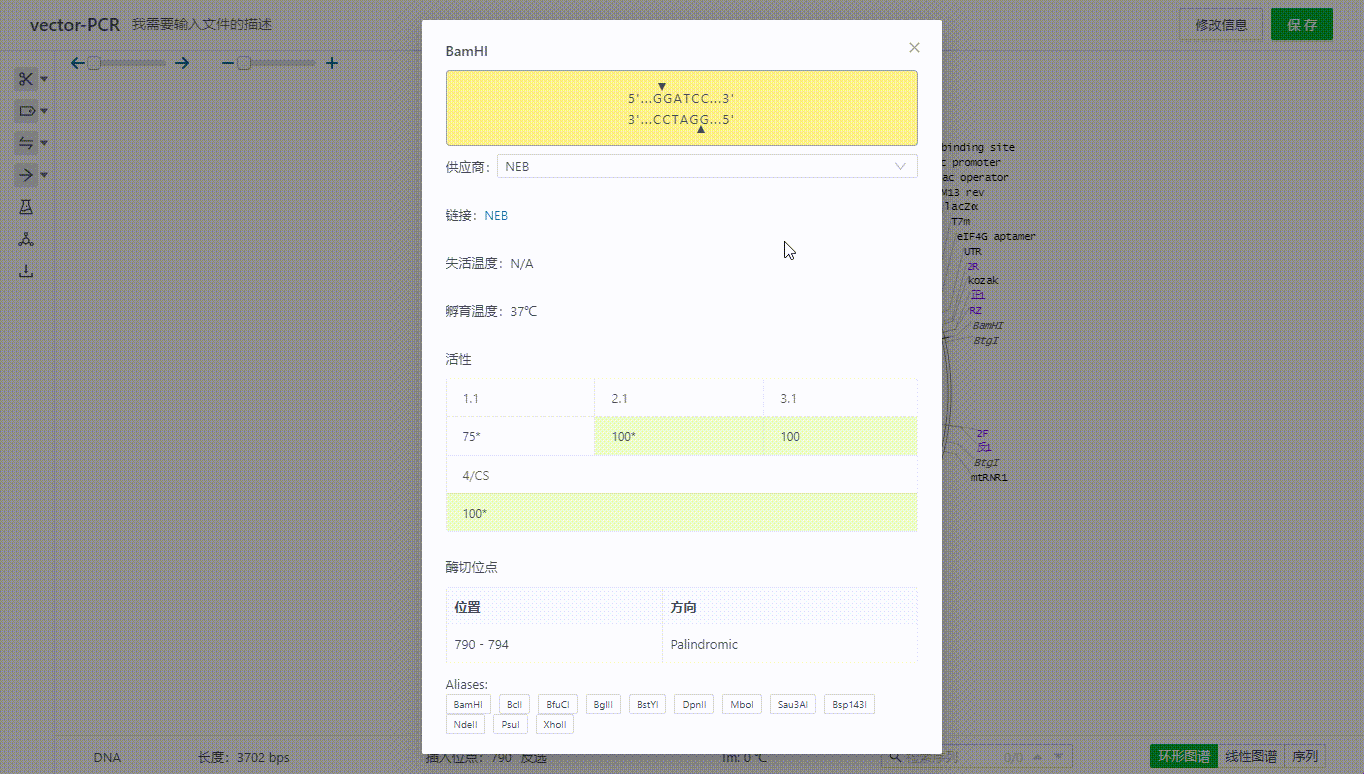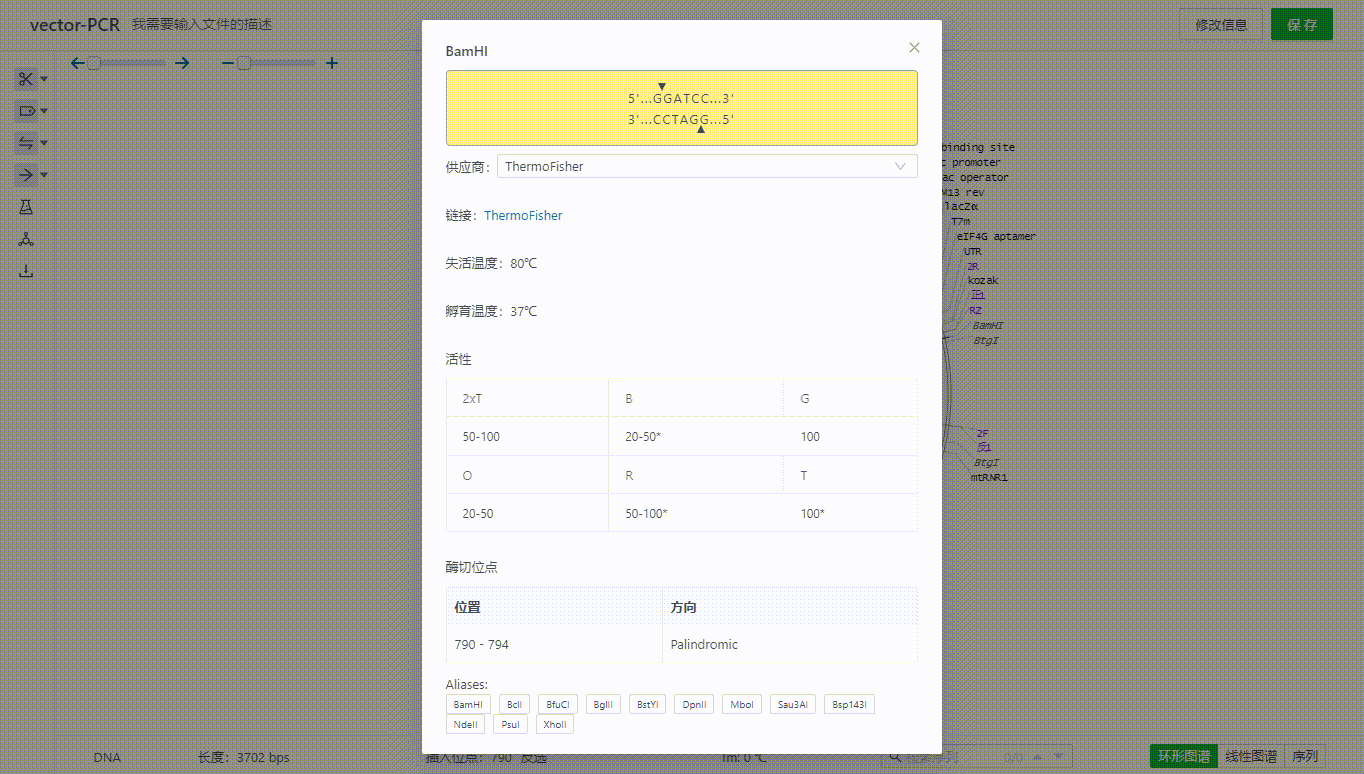
5.3 查看酶有关的信息
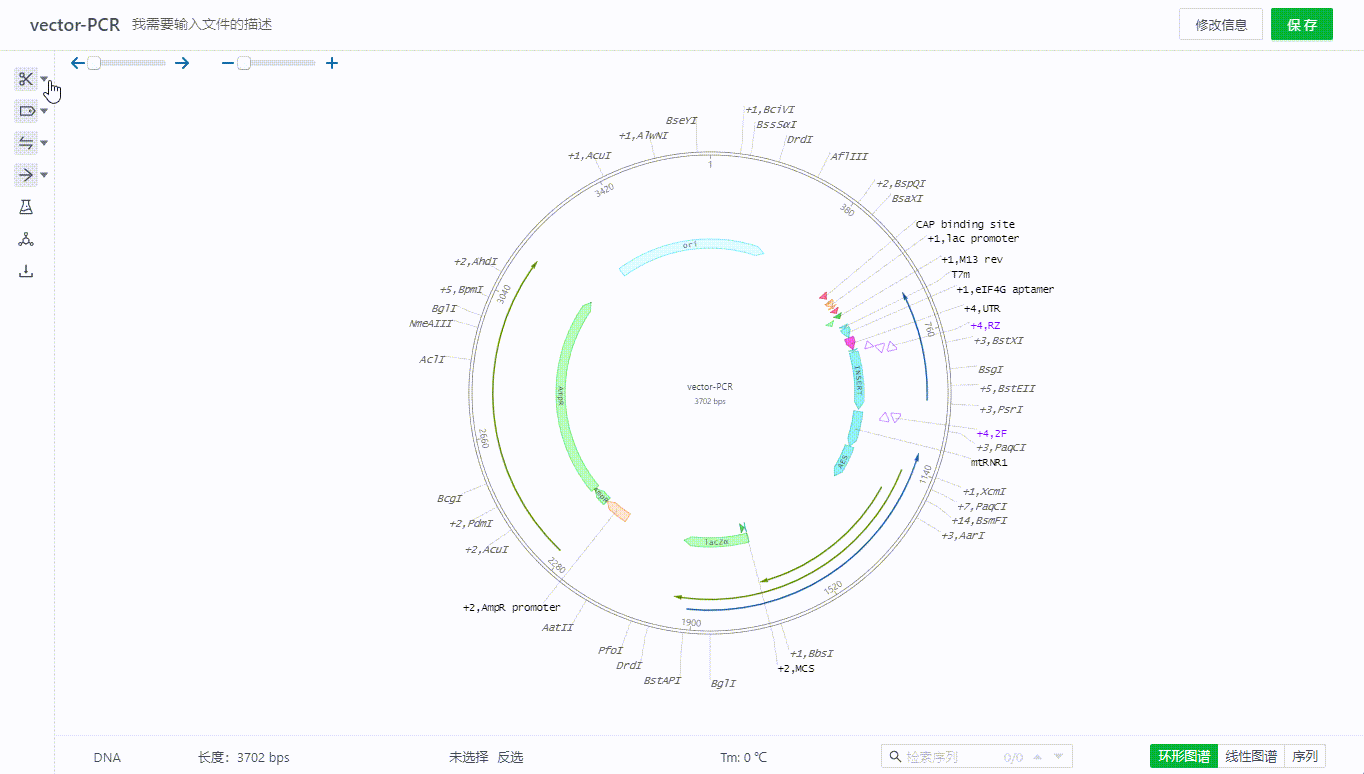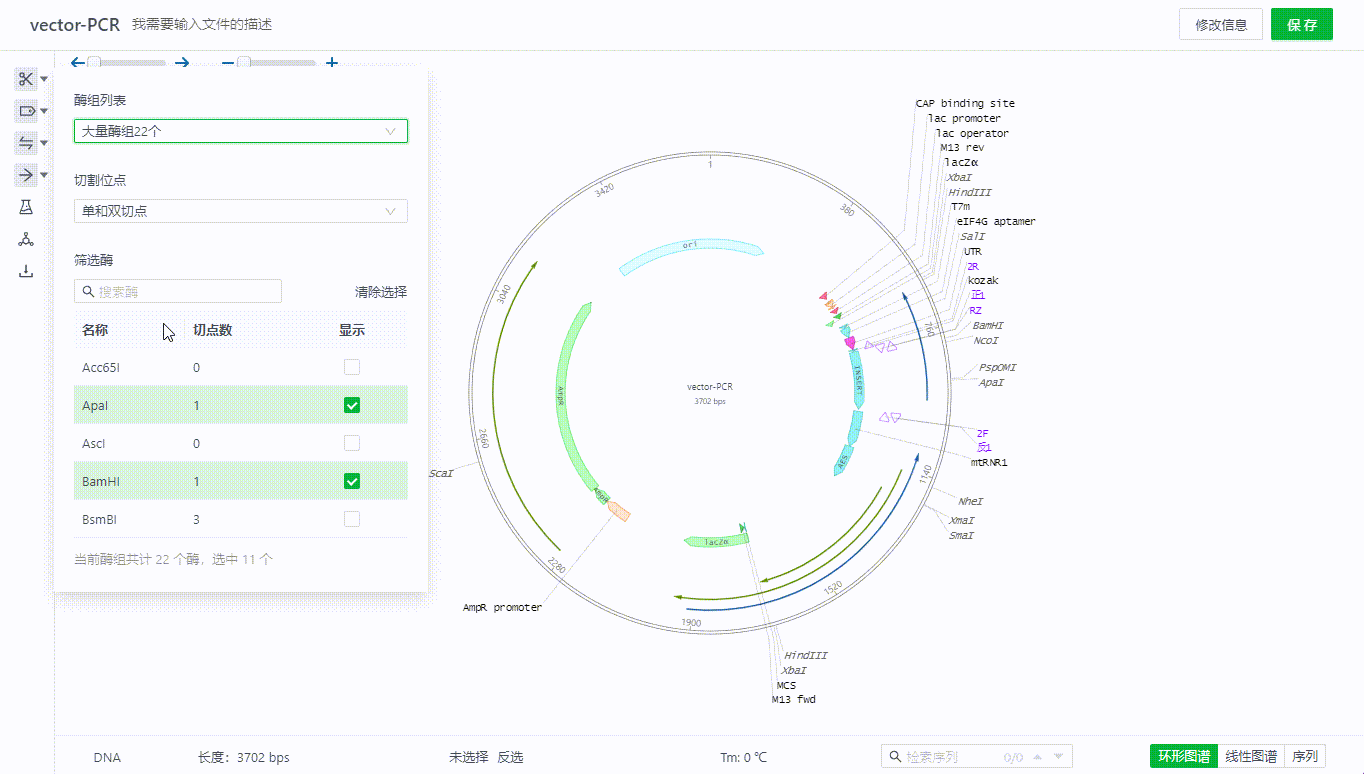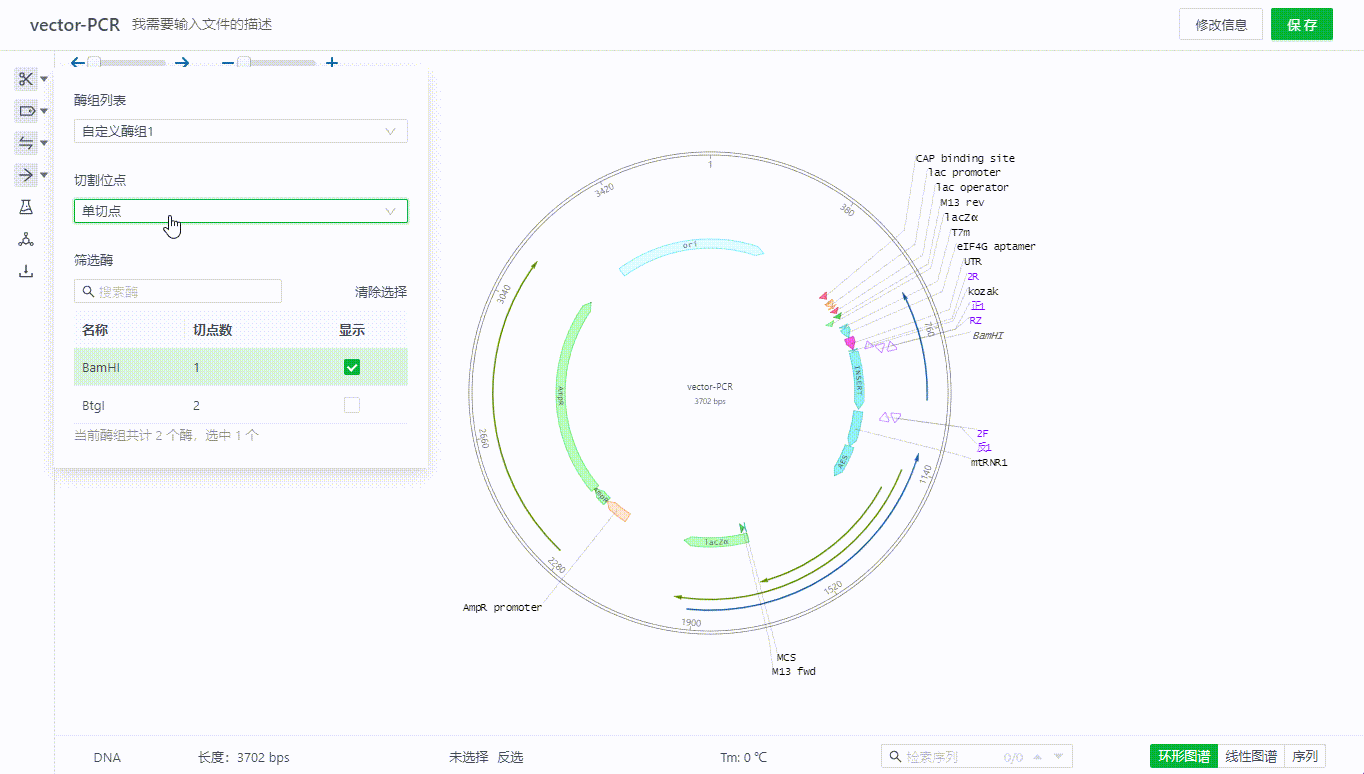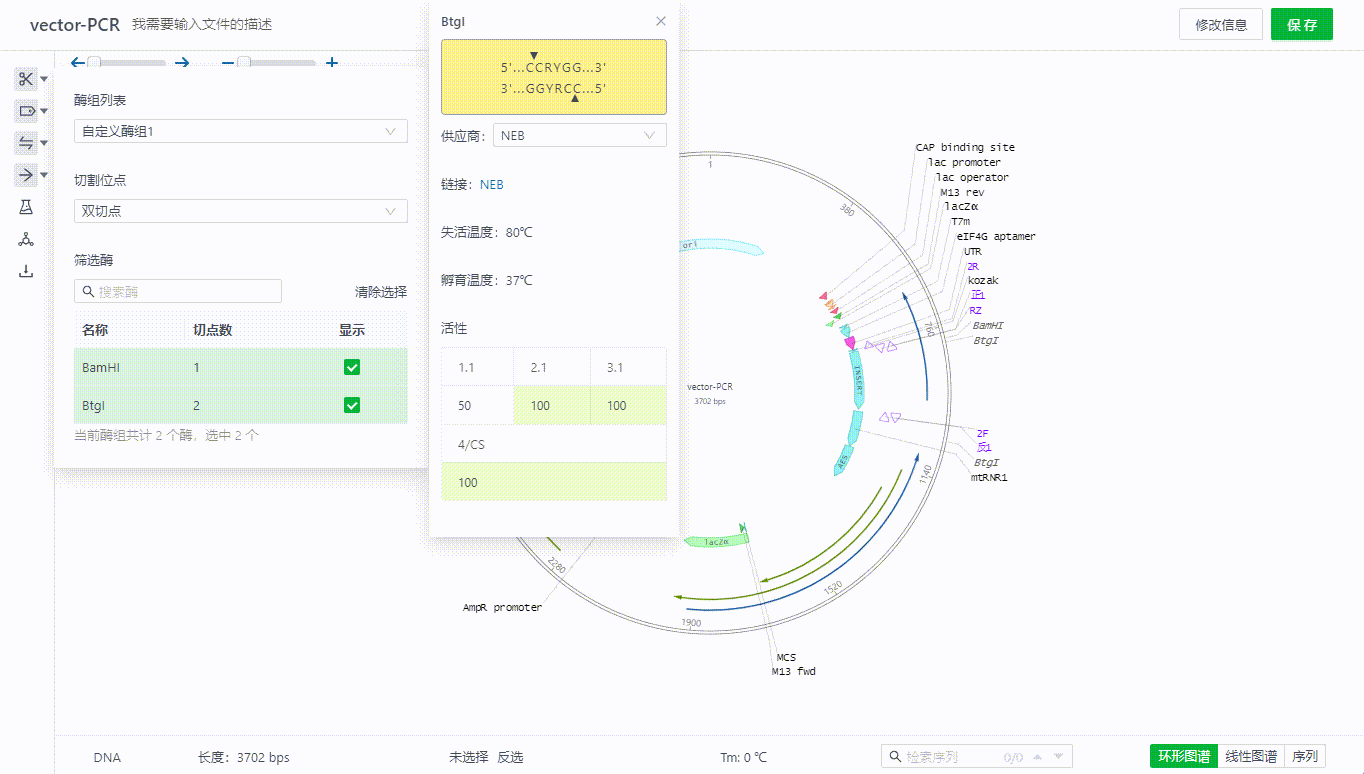
用户可以通过筛选界面查看酶的详情信息,或者直接双击视图中的酶名称查看。
5.4 保存至酶组
用户可以在编辑序列时,将筛选后常用的酶直接保存为酶组。
6. 特征相关操作
6.1 特征展示开关��、添加编辑特征
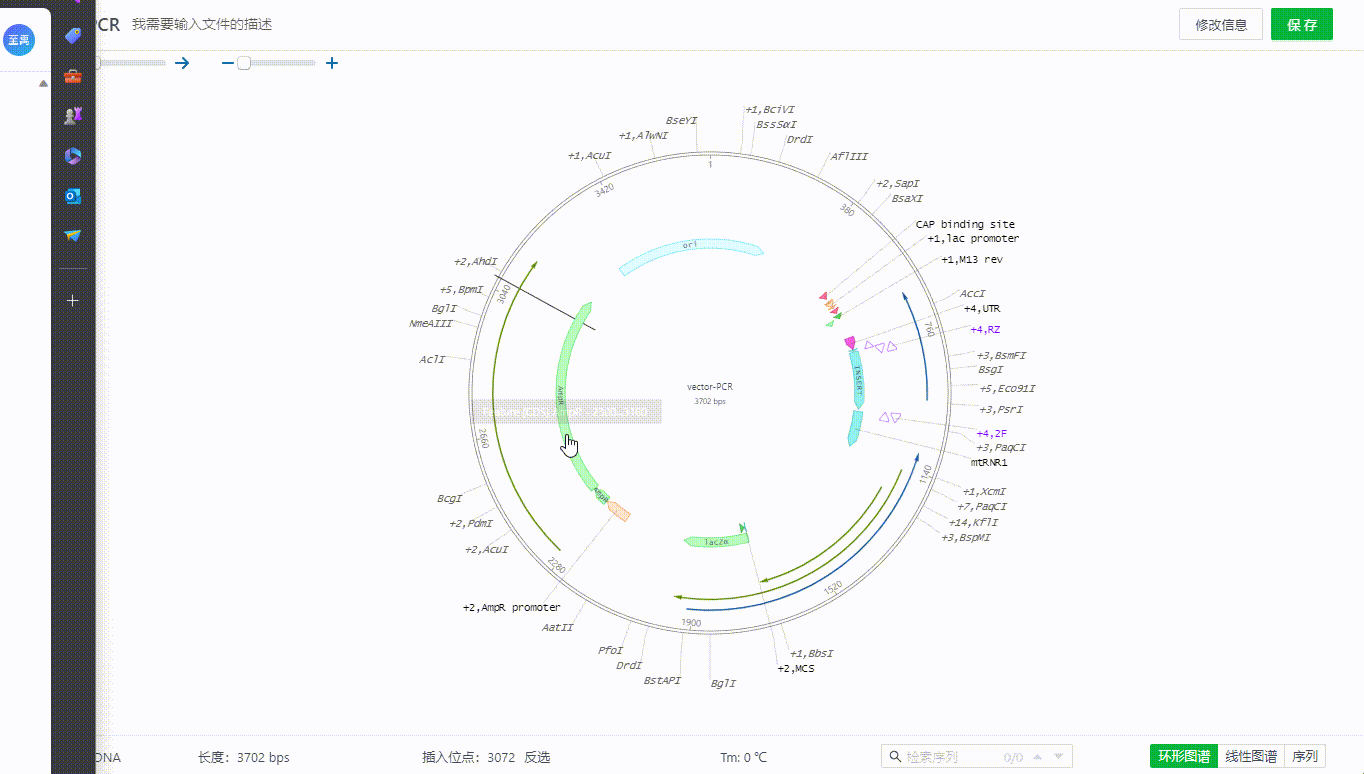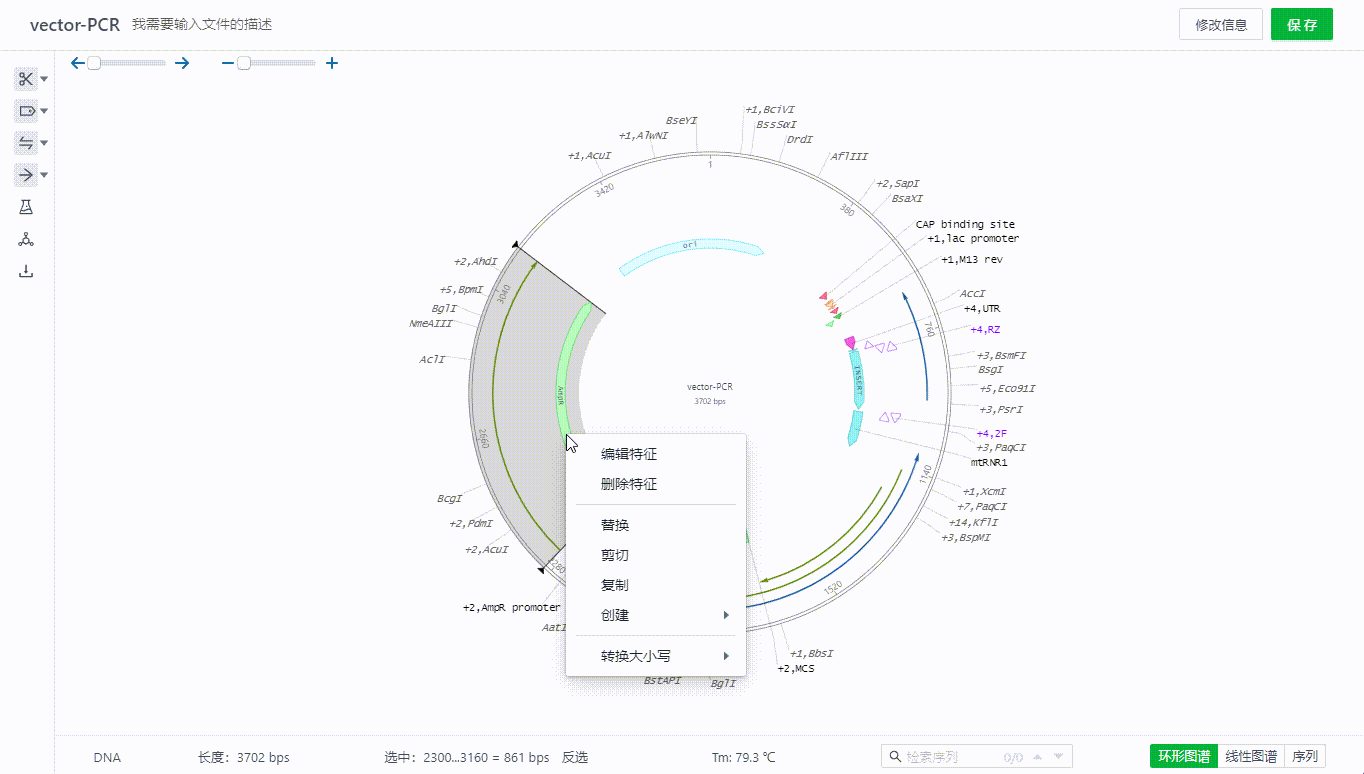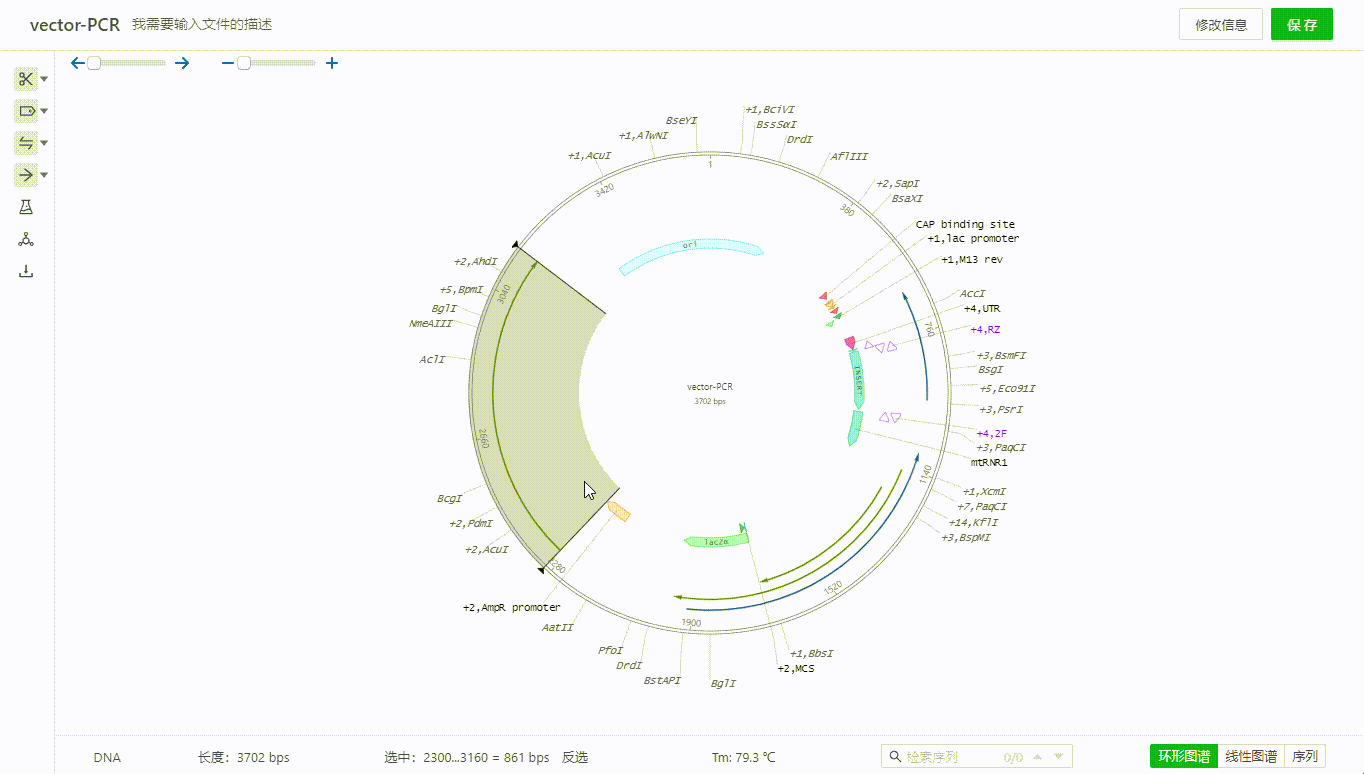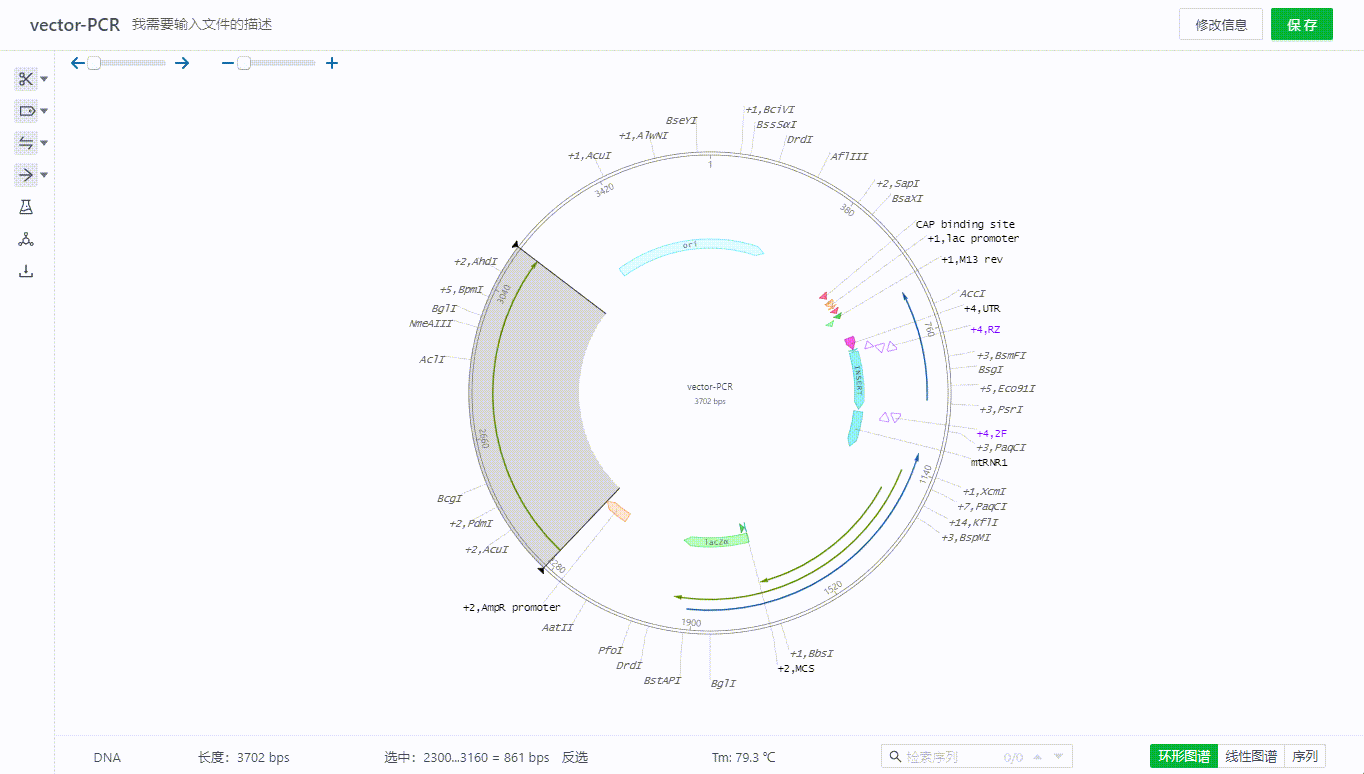
用户可以通过左侧特征按钮用户可以选取一段序列,右键添加特征。目前支持对特征赋予标注类型,颜色,并添加描述。
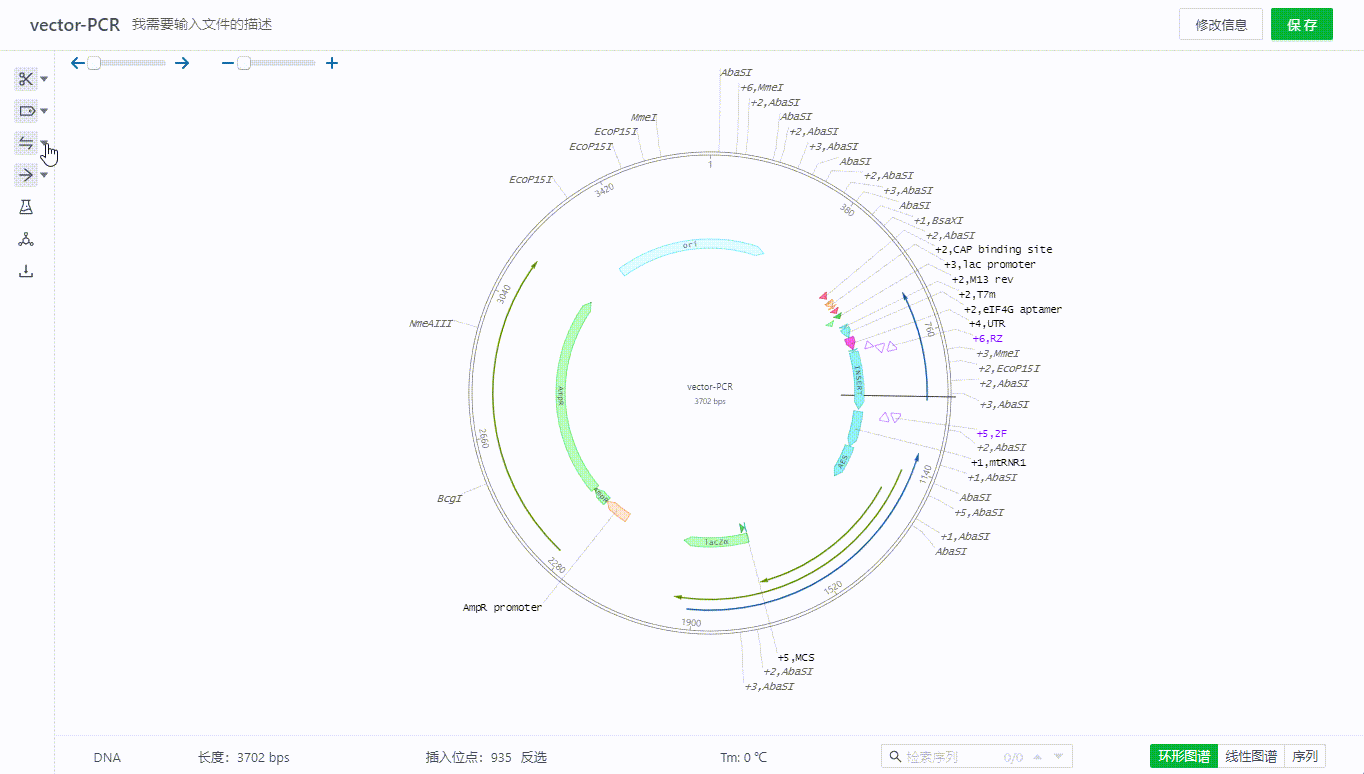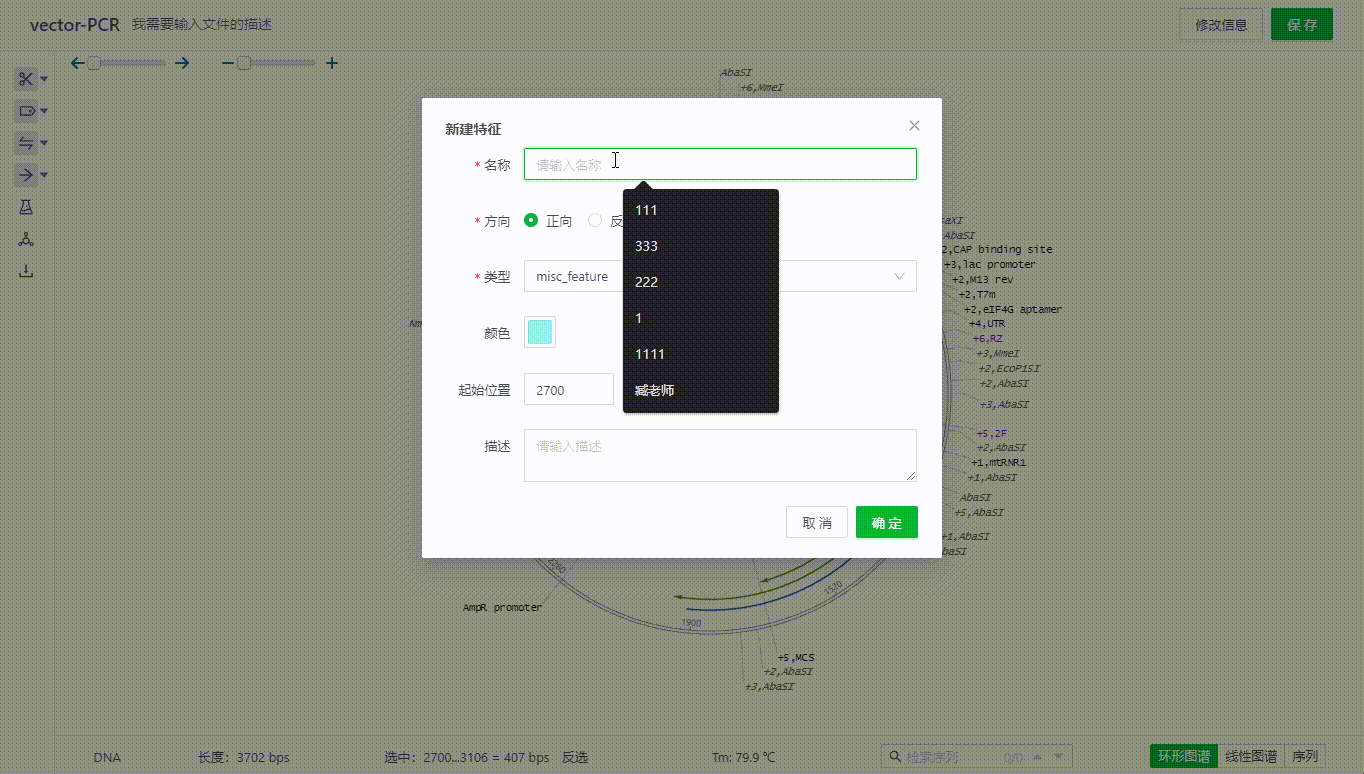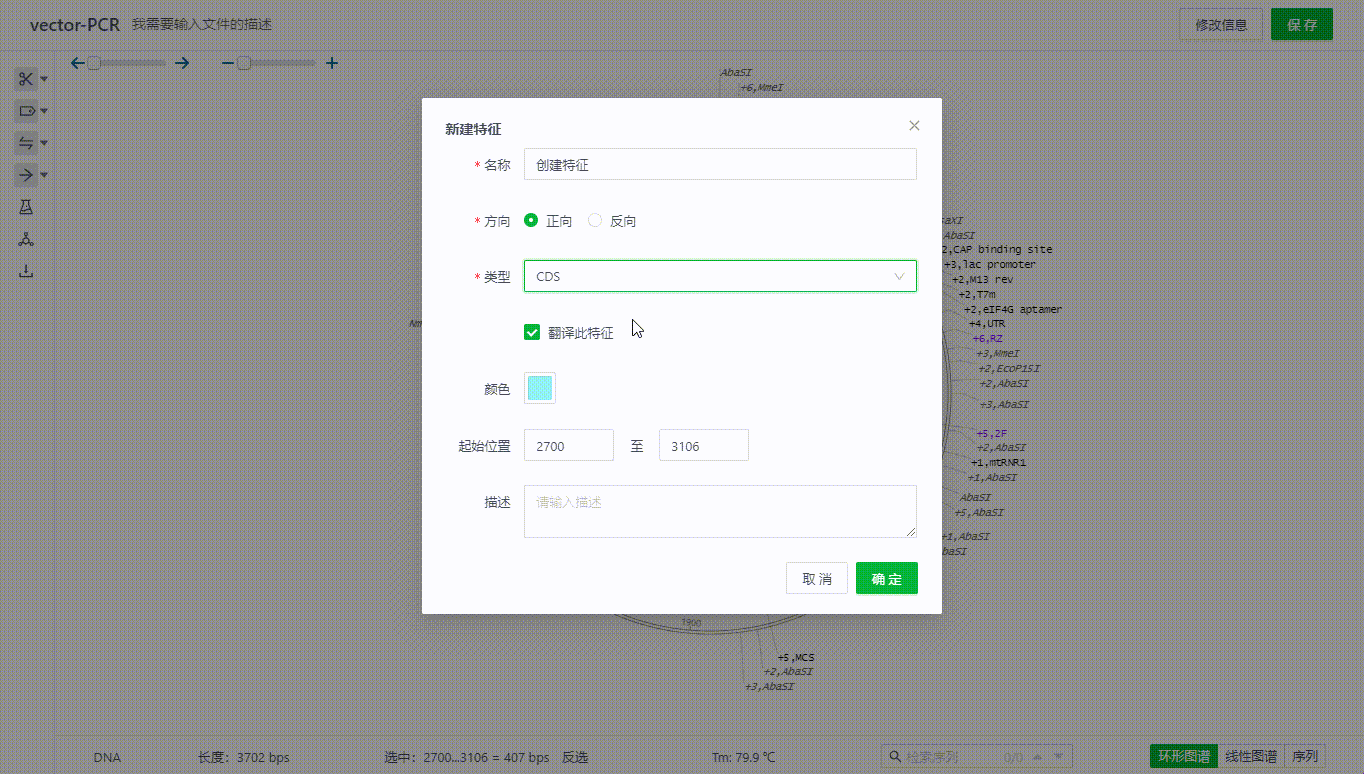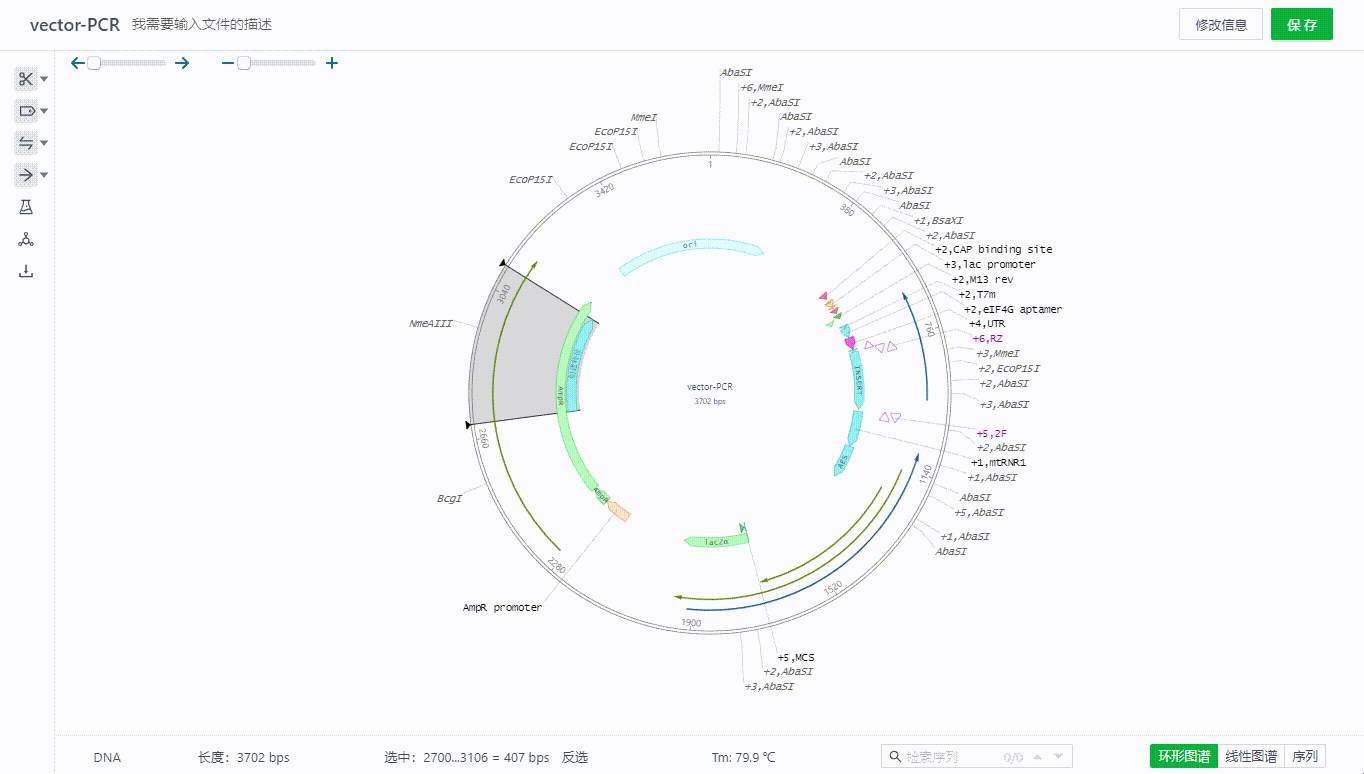
双击特征可以查看,编辑特征,也可以通过特征列表隐藏单个特征。
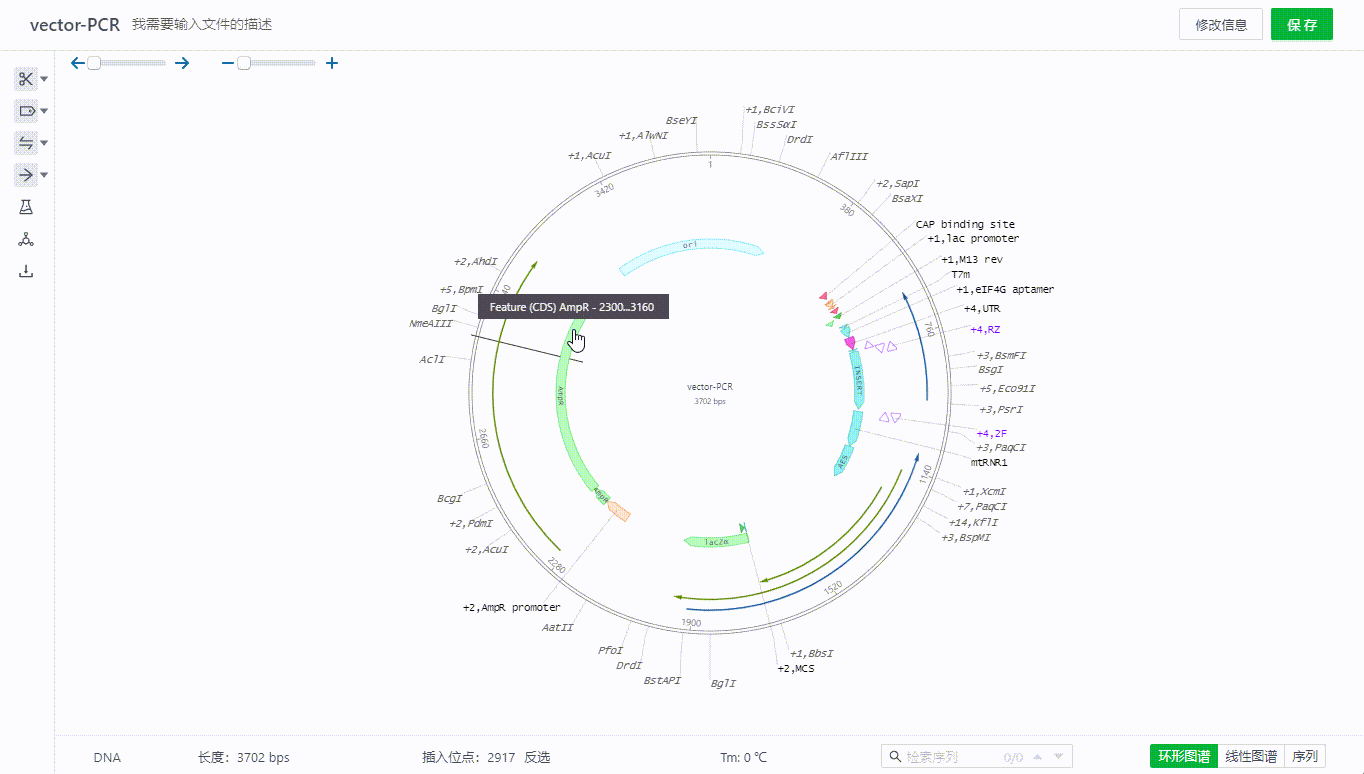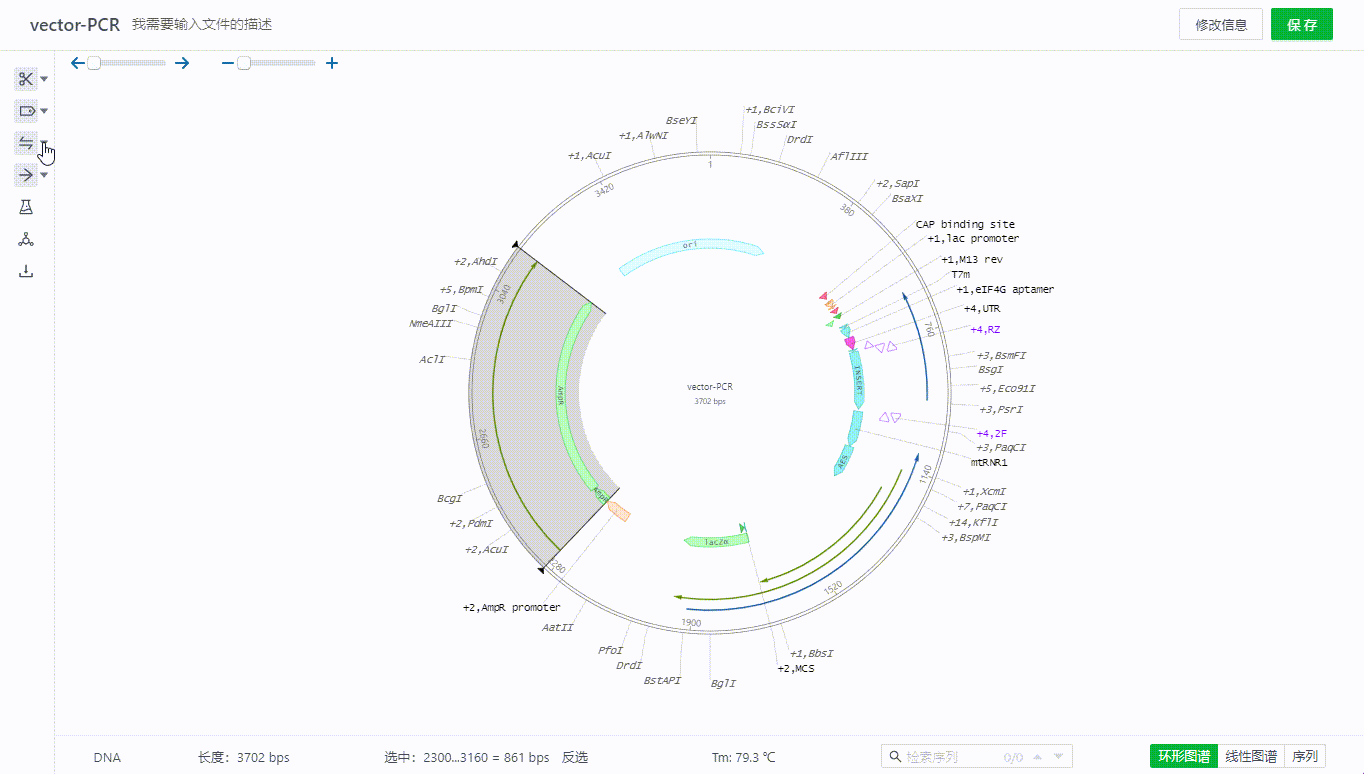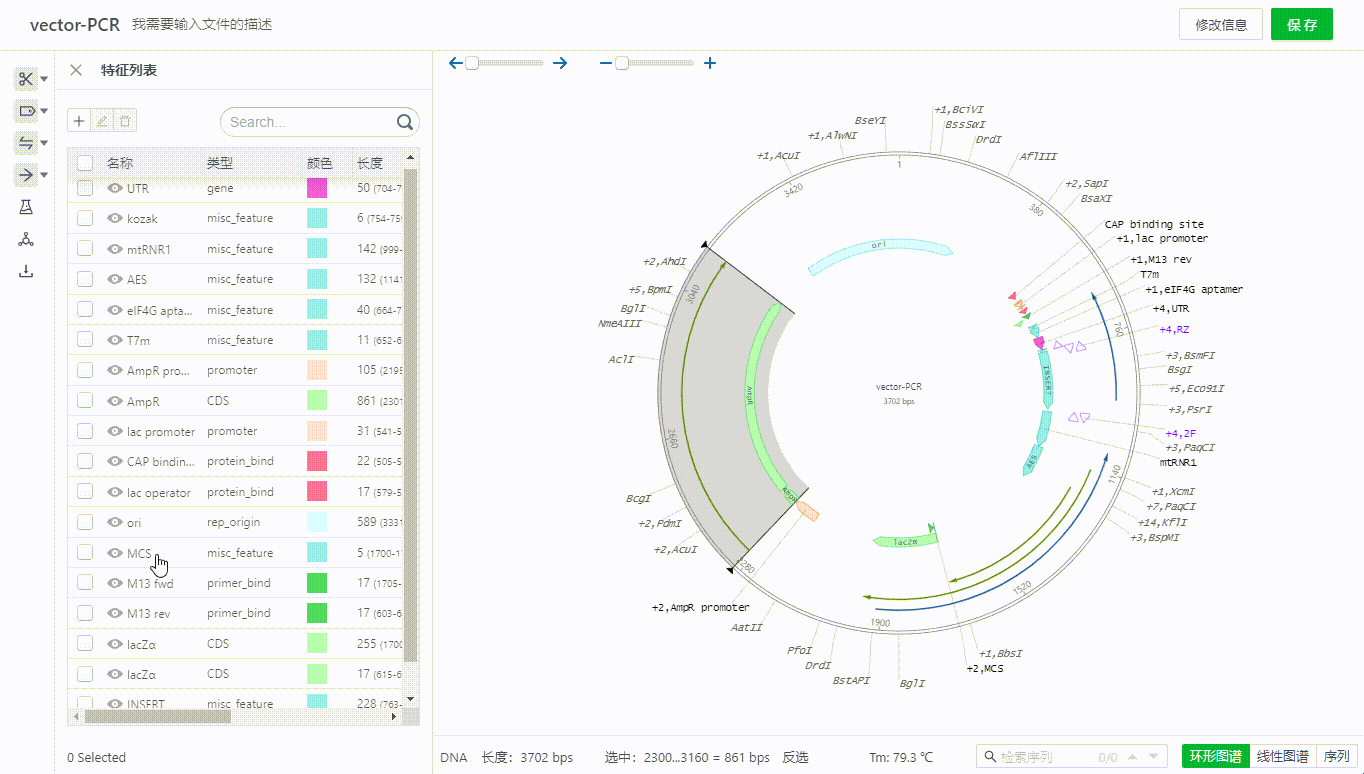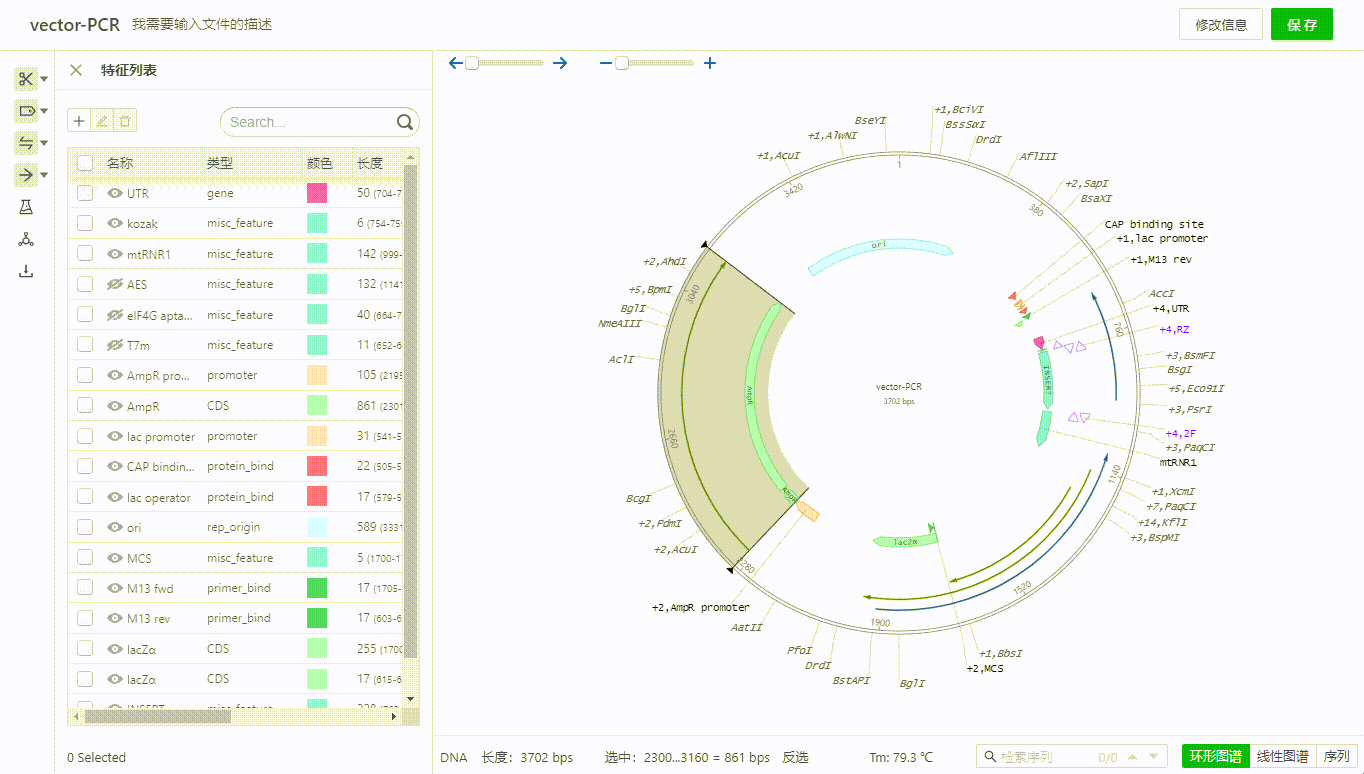
或者在图谱上右键删除特征。
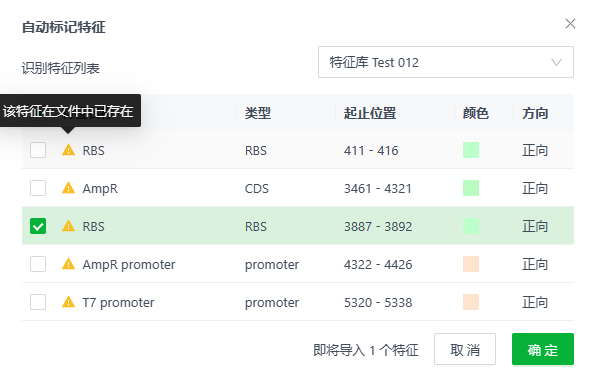
6.2 自动标记特征
用户可以通过点击工具栏中的自动标记特征来选中一个特征库,并将库中可识别的特征标记至序列文件中。
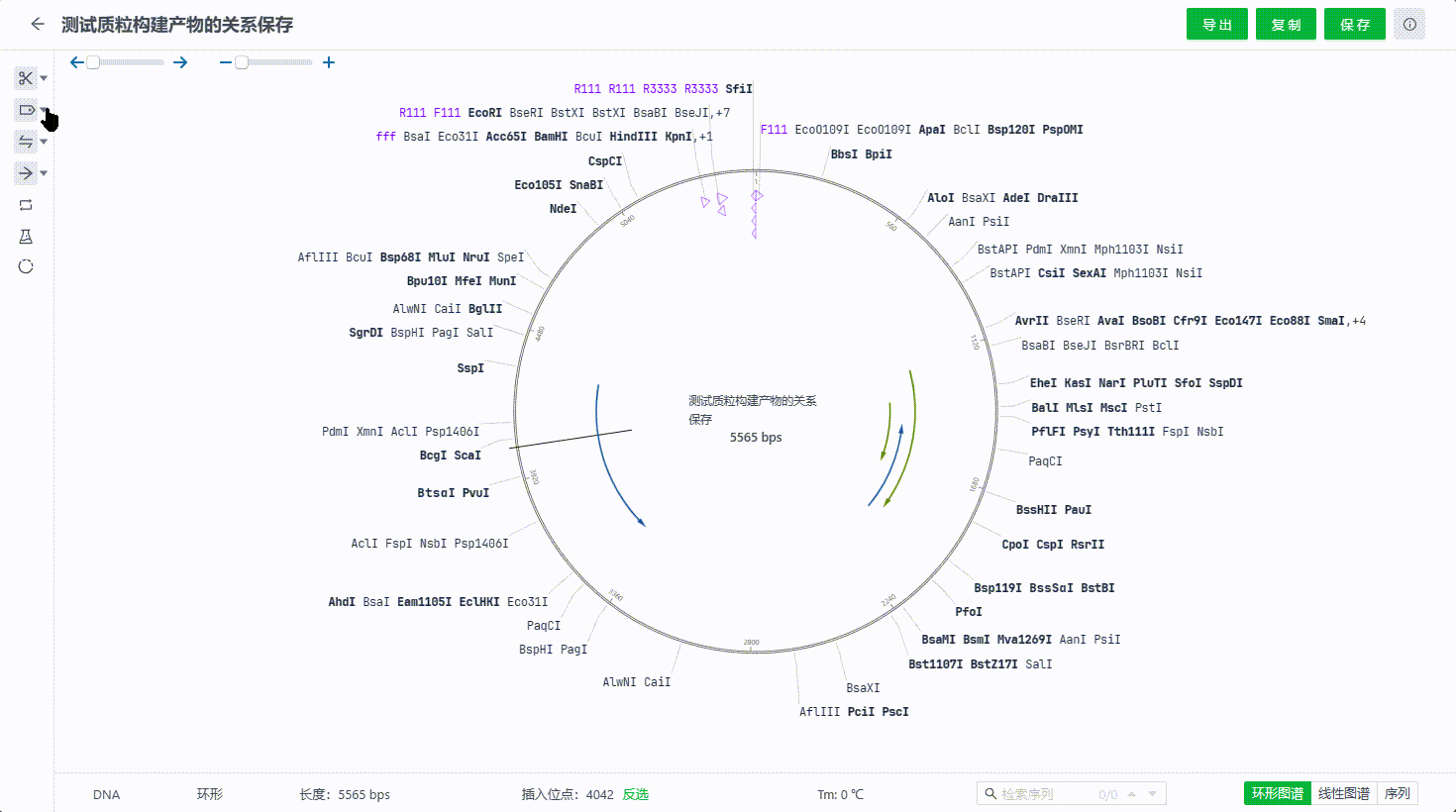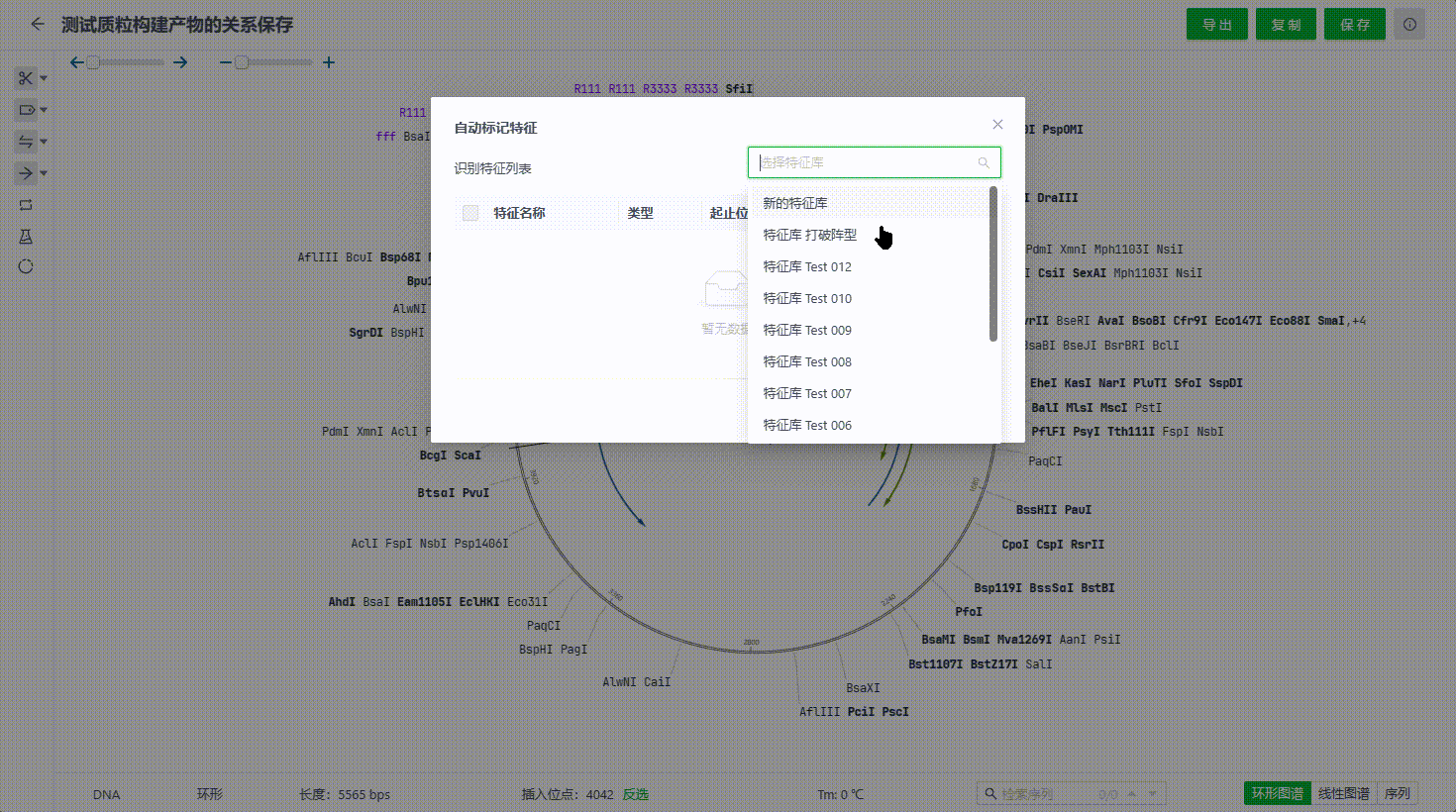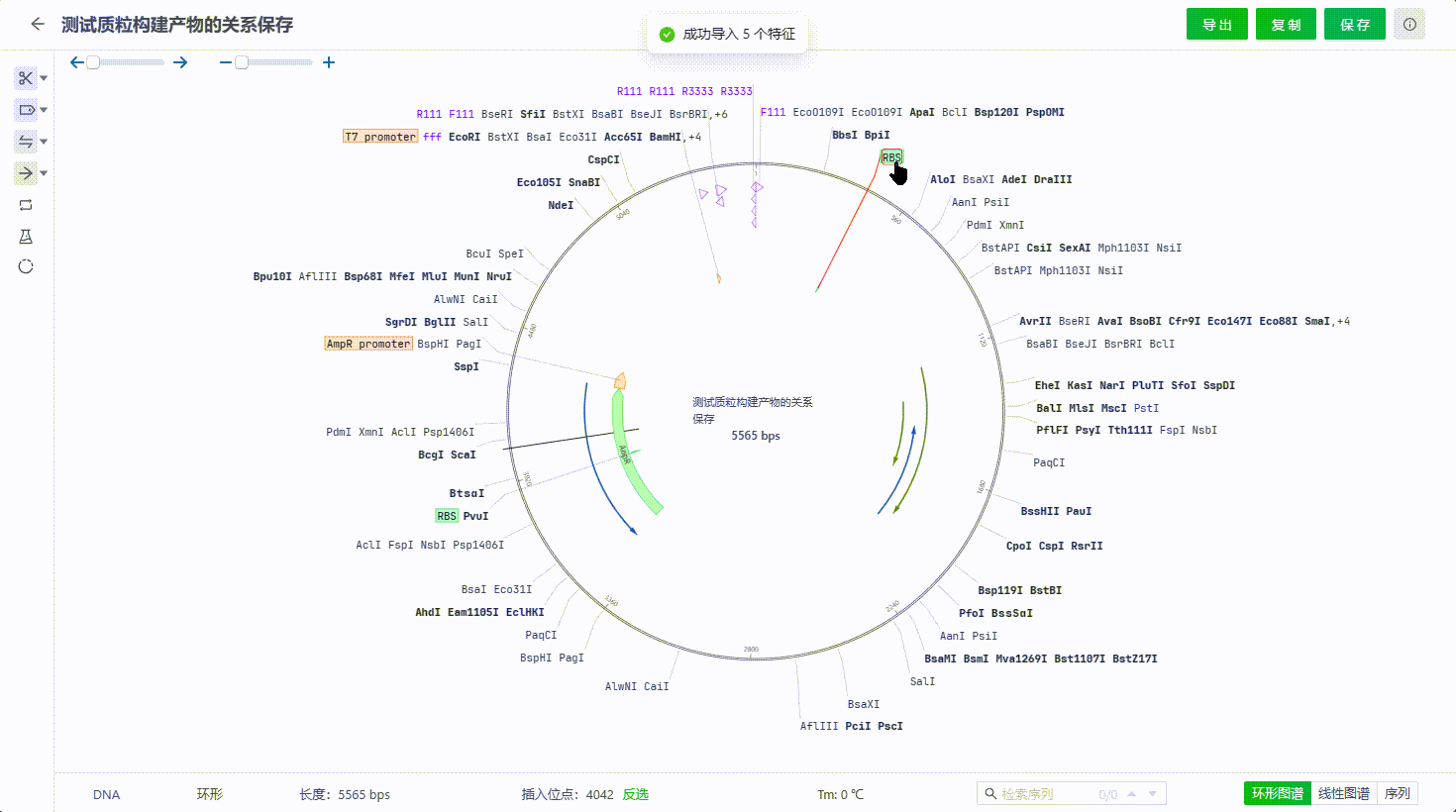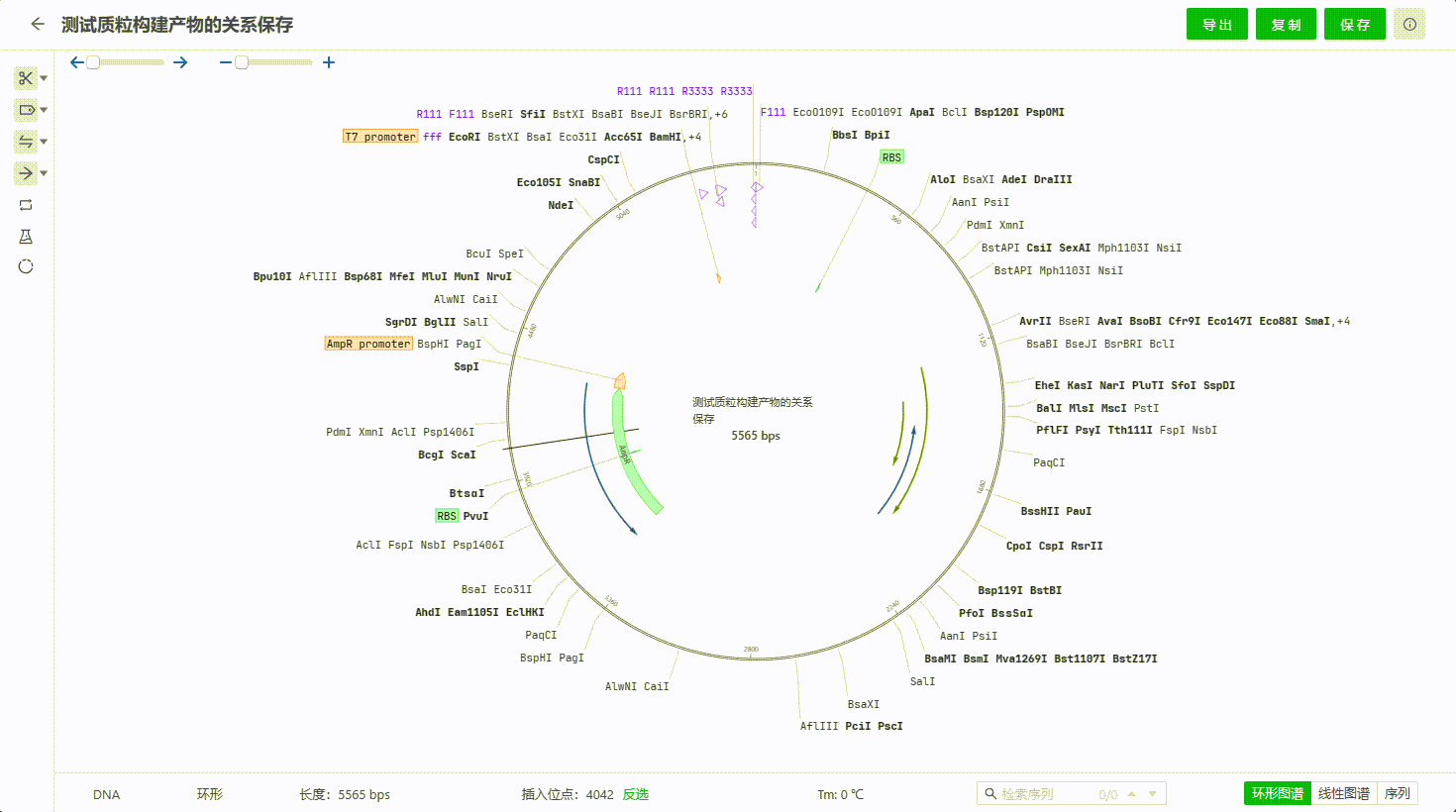
识别过程中如果有起止位置、方向等等重复的特征系统会判断为重复特征,默认不会勾选,用户如果需要还是可以标记到文件中。
6.3 保存特征至特征库�
用户可以在序列编辑的过程中将有价值的特征保存至特征库中,便于用户给类同研究的序列文件快速标记。目前支持两种方式保存。
- 右键一个特征保存
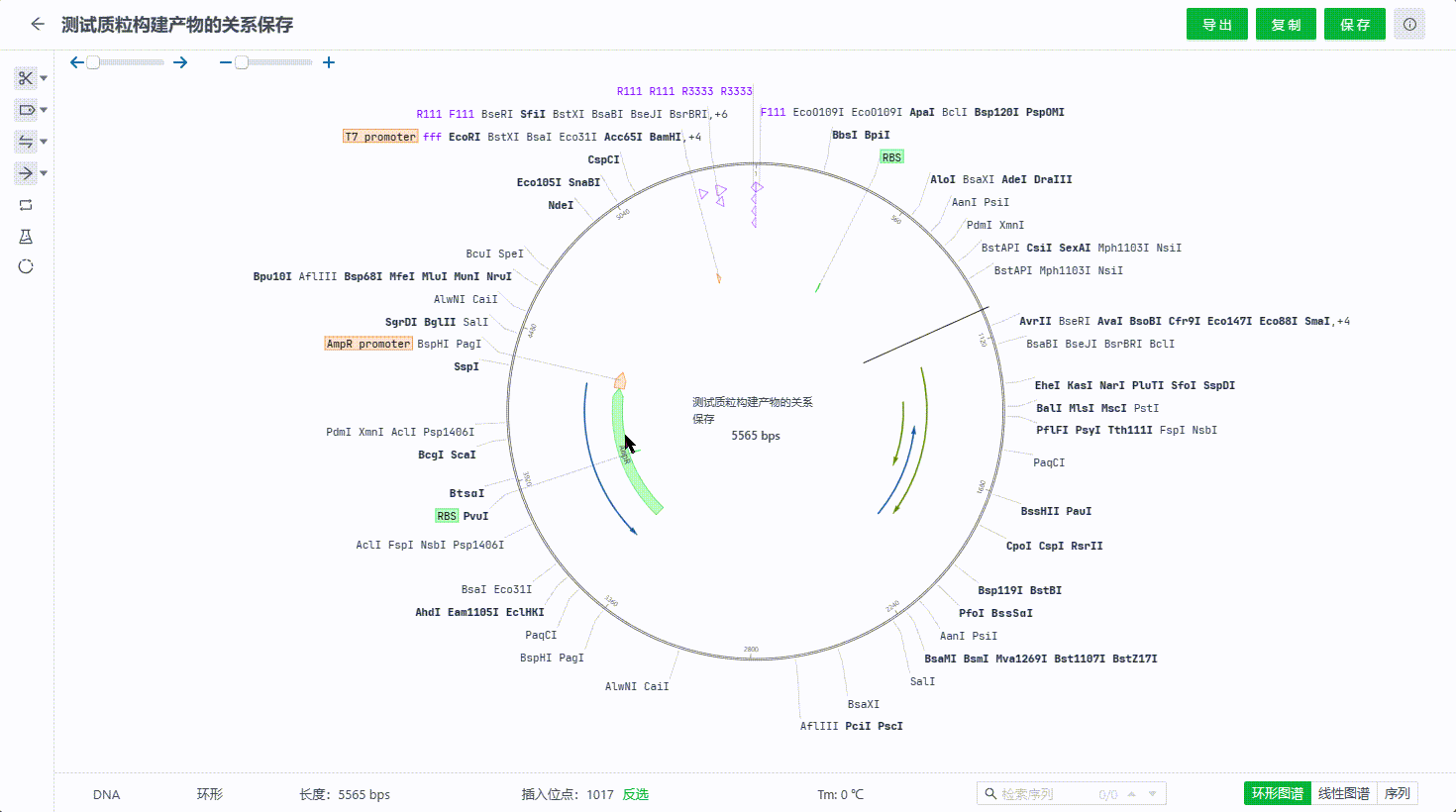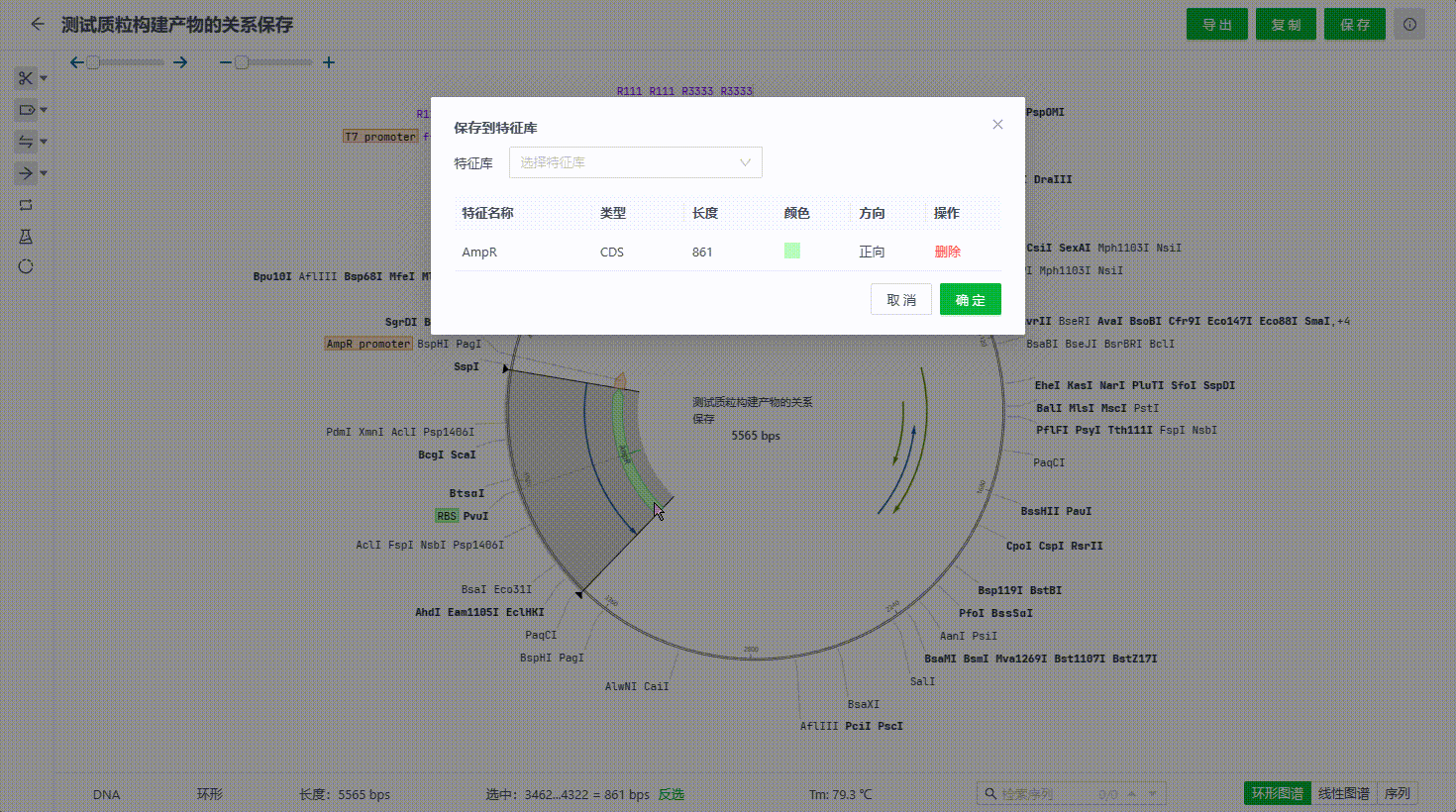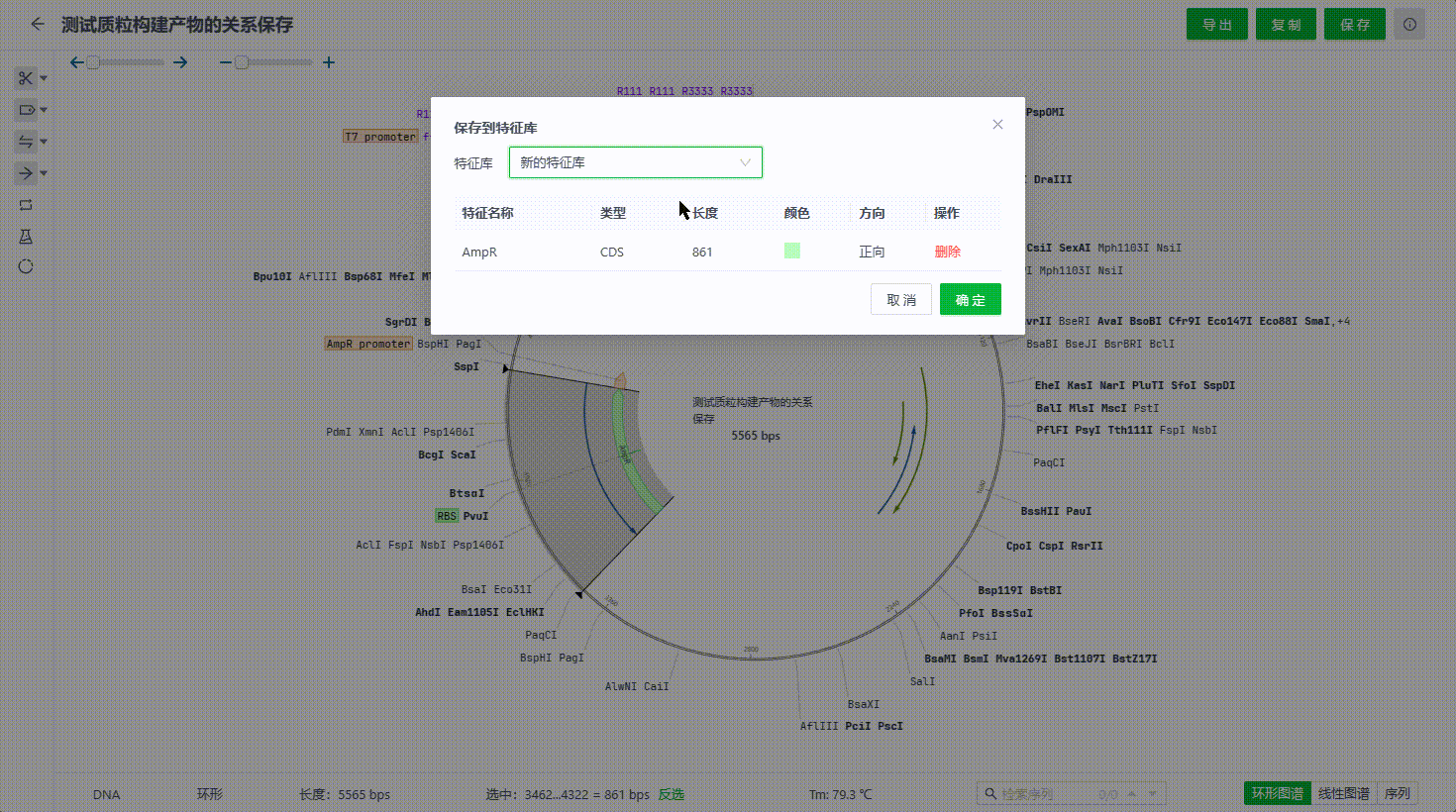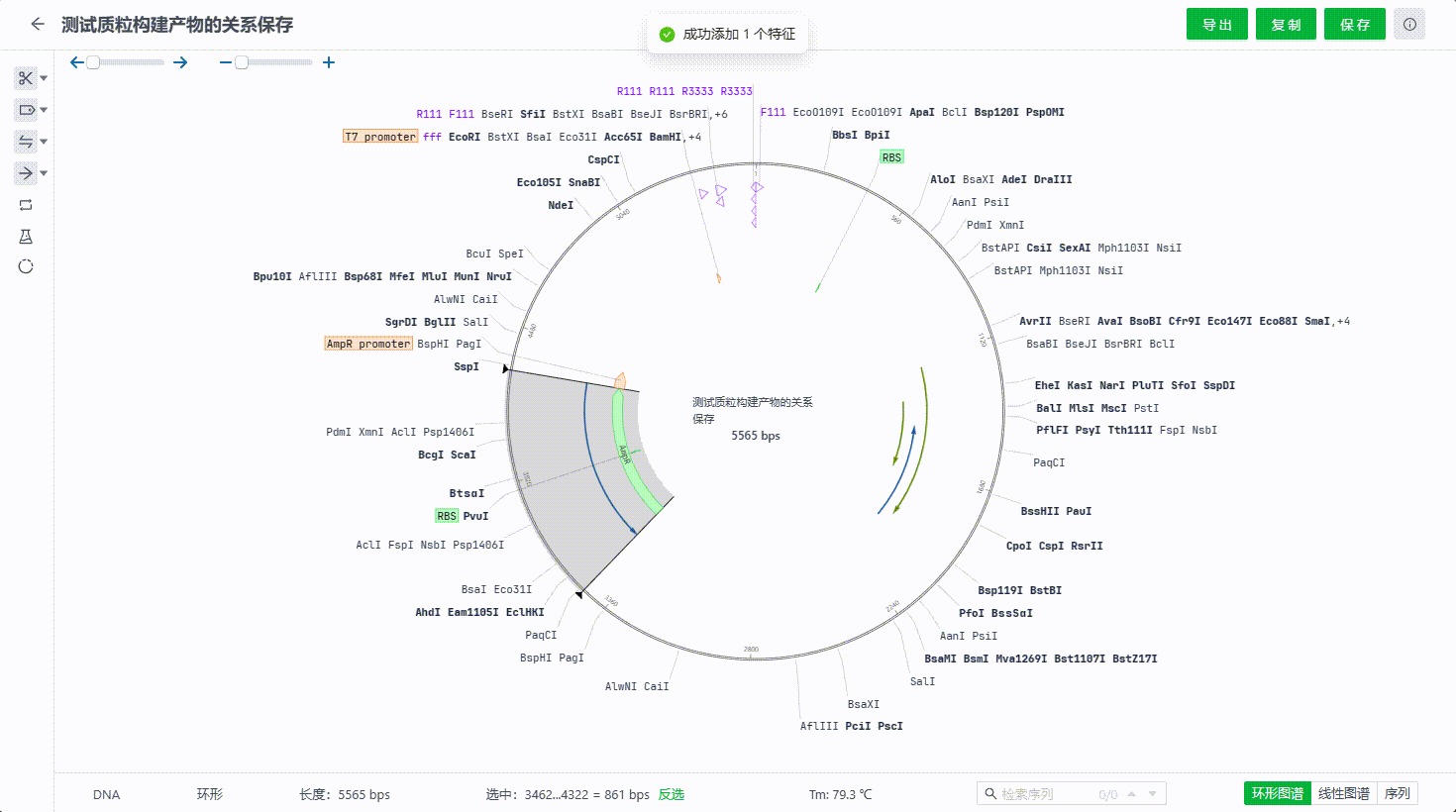
- 在特征列表中选中多个特征保存
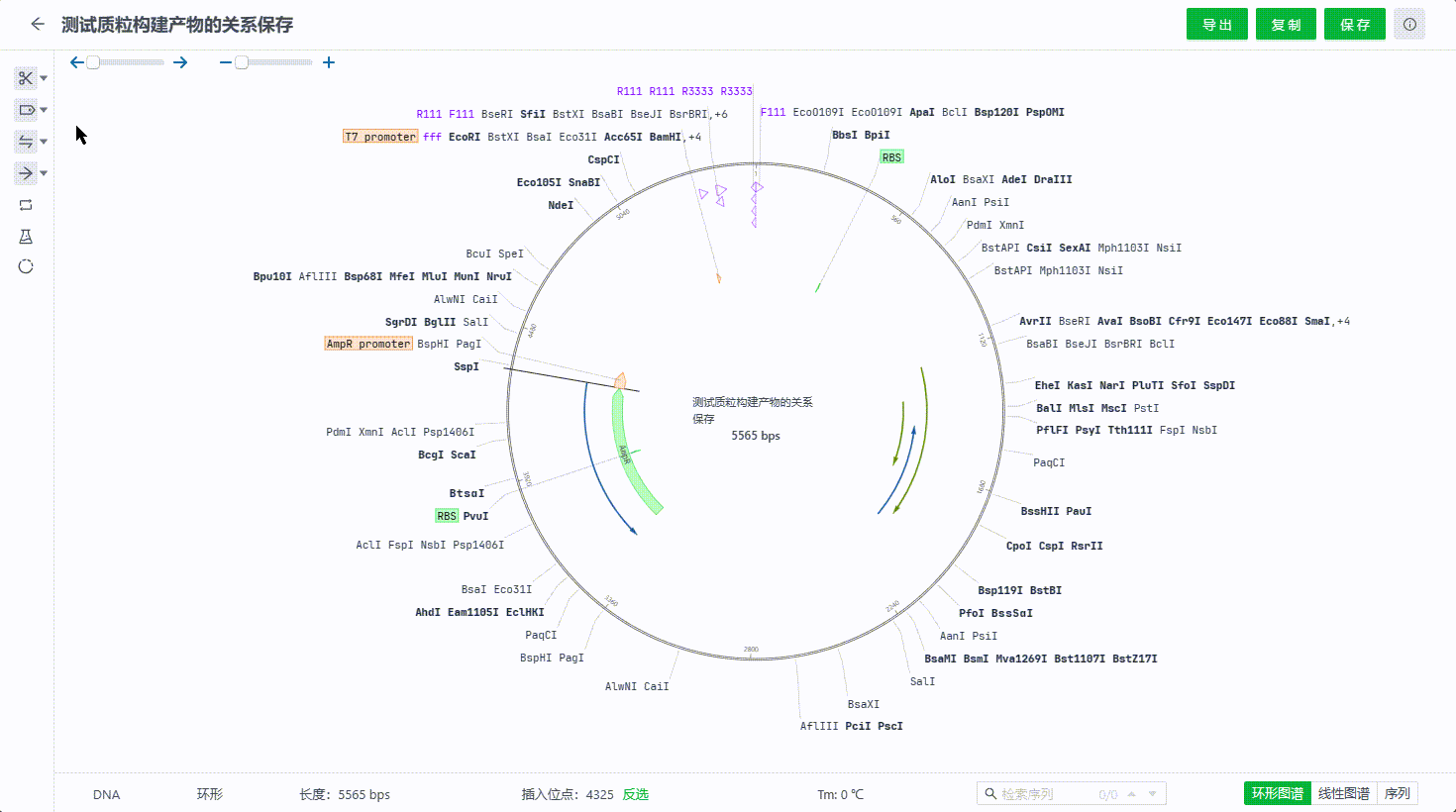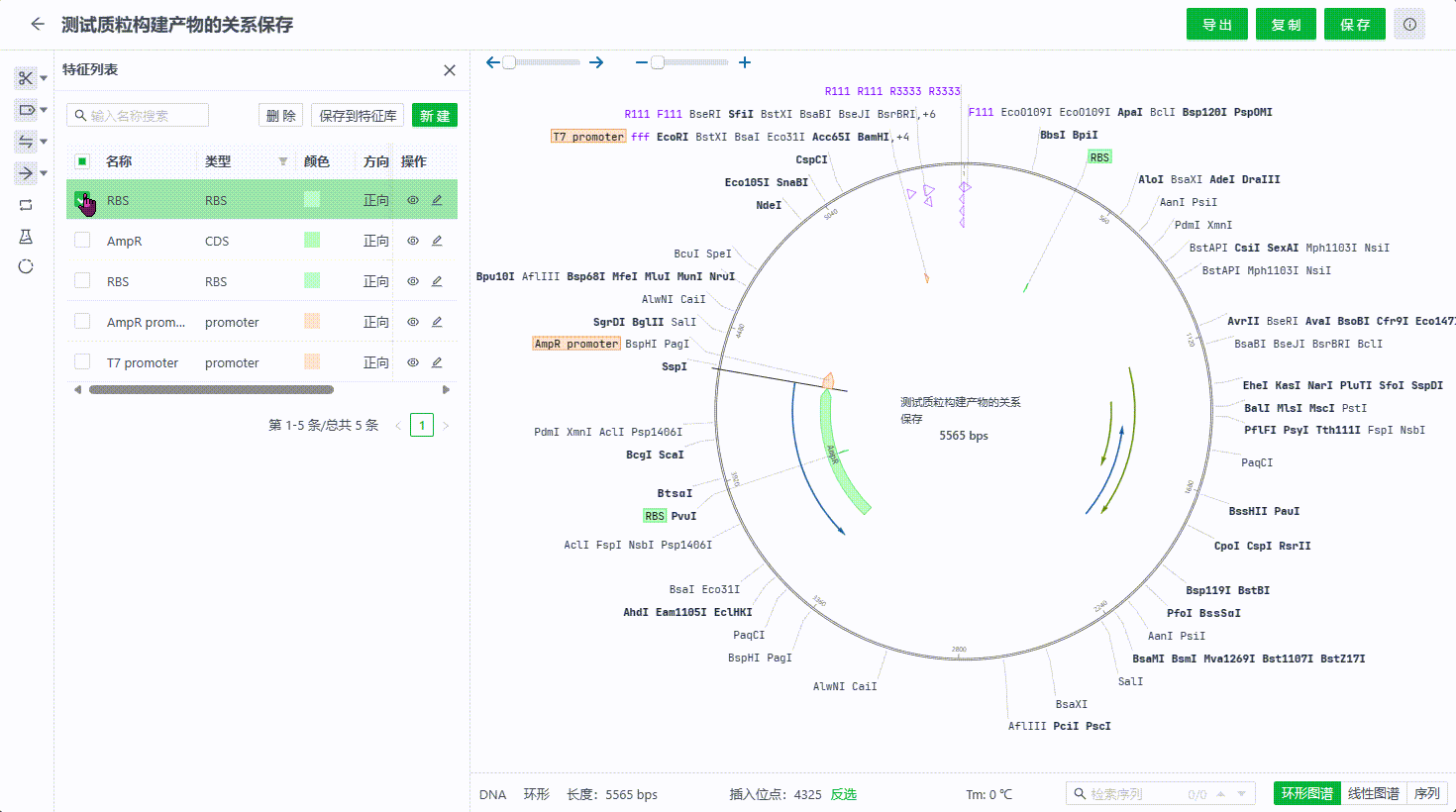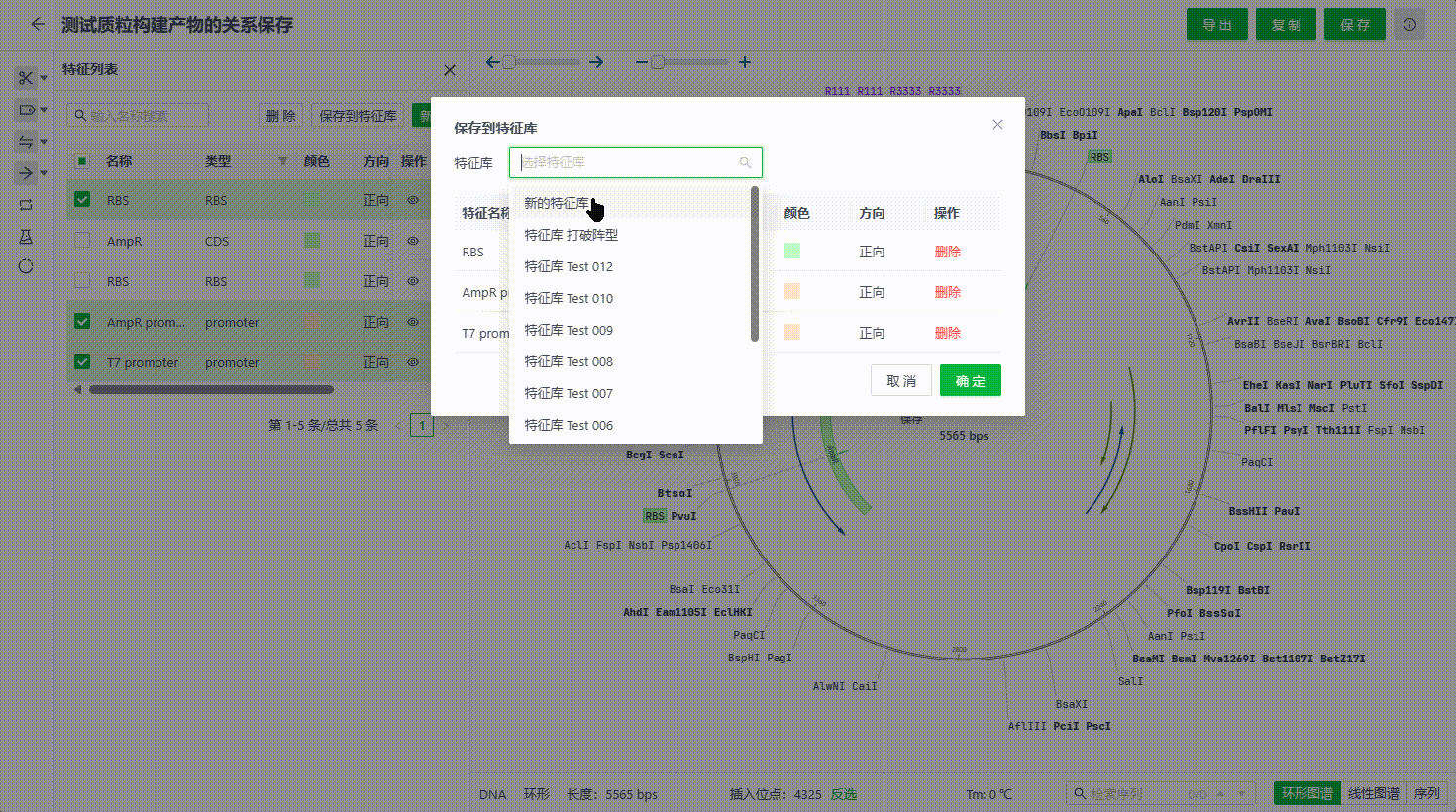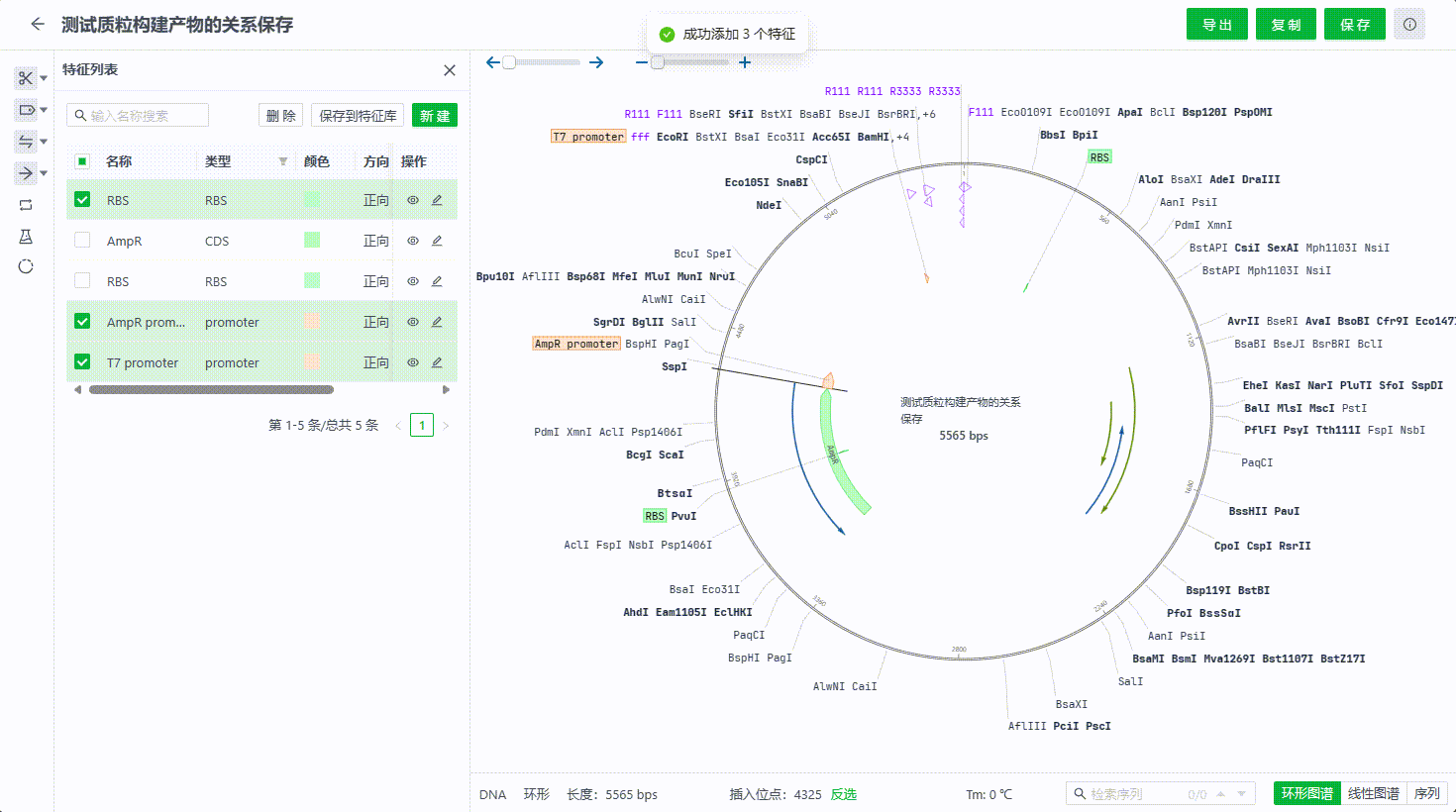
以下情况的特征将无法保存到特征库中:
- 特征名称已存在库中。
- 特征的序列、类型、方向等信息在特征库中已存在其他特征。
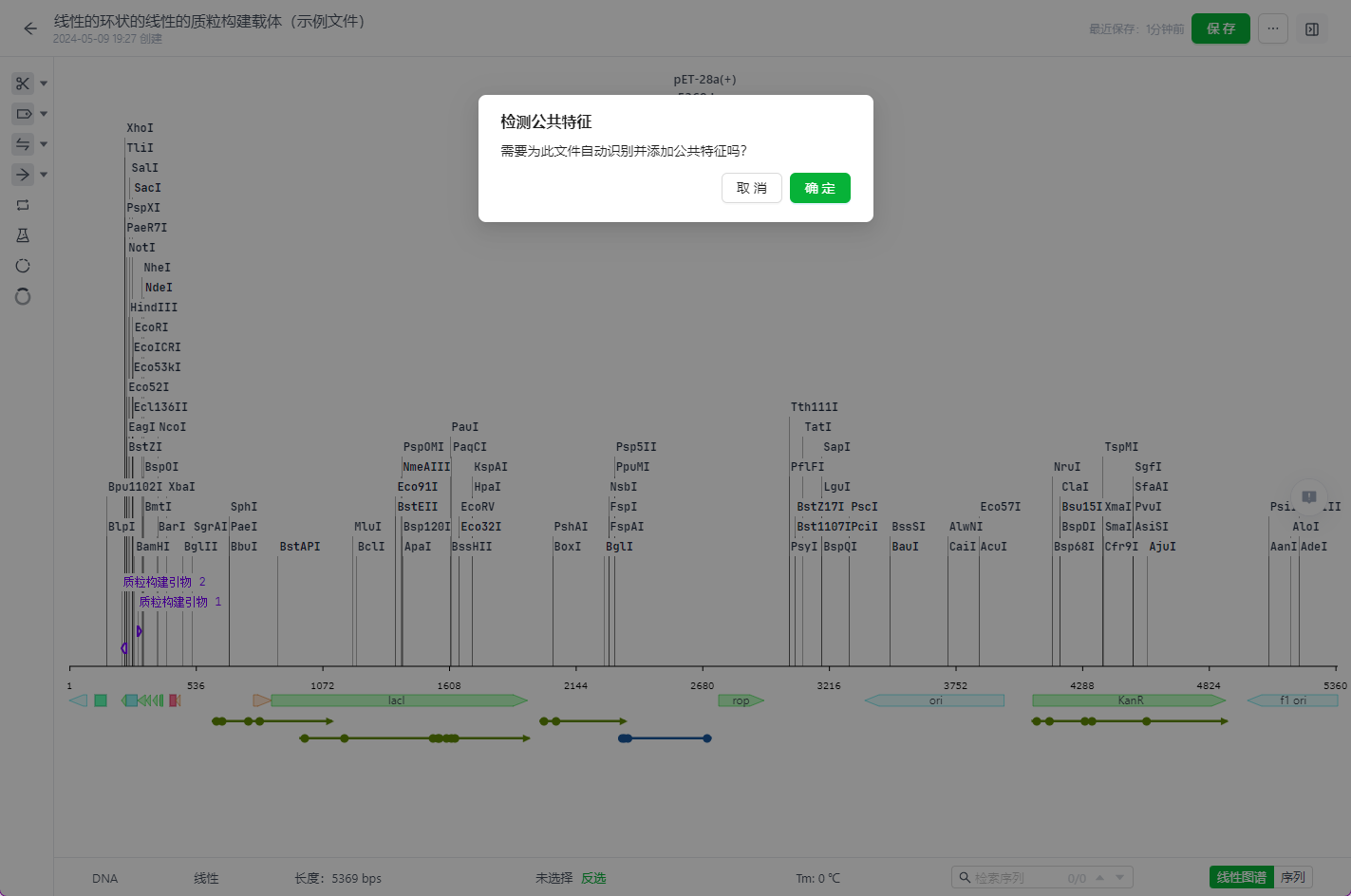
6.4 自动识别公共特征
用户在新建序列(包括复制、创建副本)或者导入序列后,在首次打开时,系统会提示用户是否需要自动识别公共特征。
- 自动识别特征弹窗,确定后系统会调用公共特征库对序列进行标注。
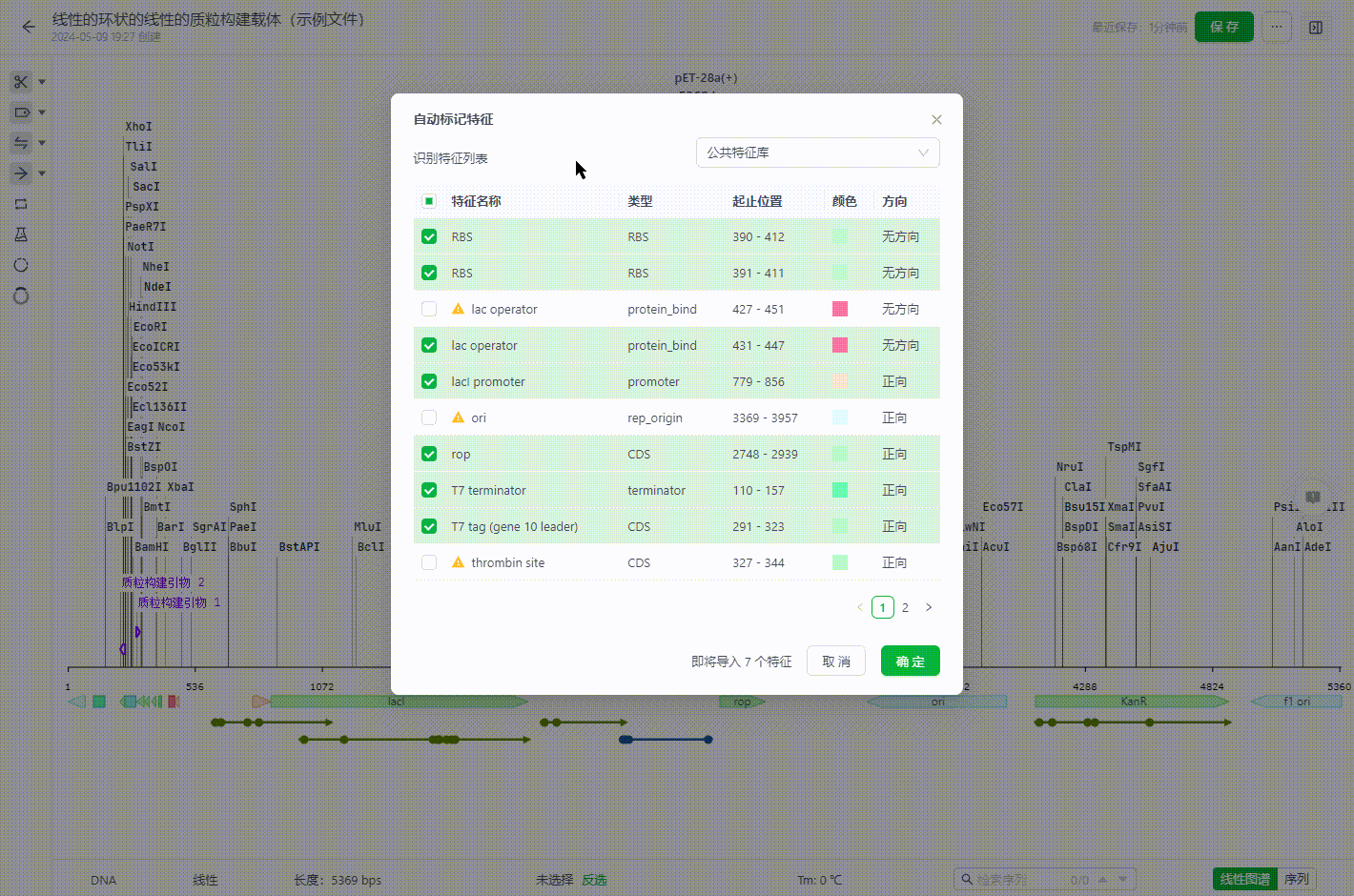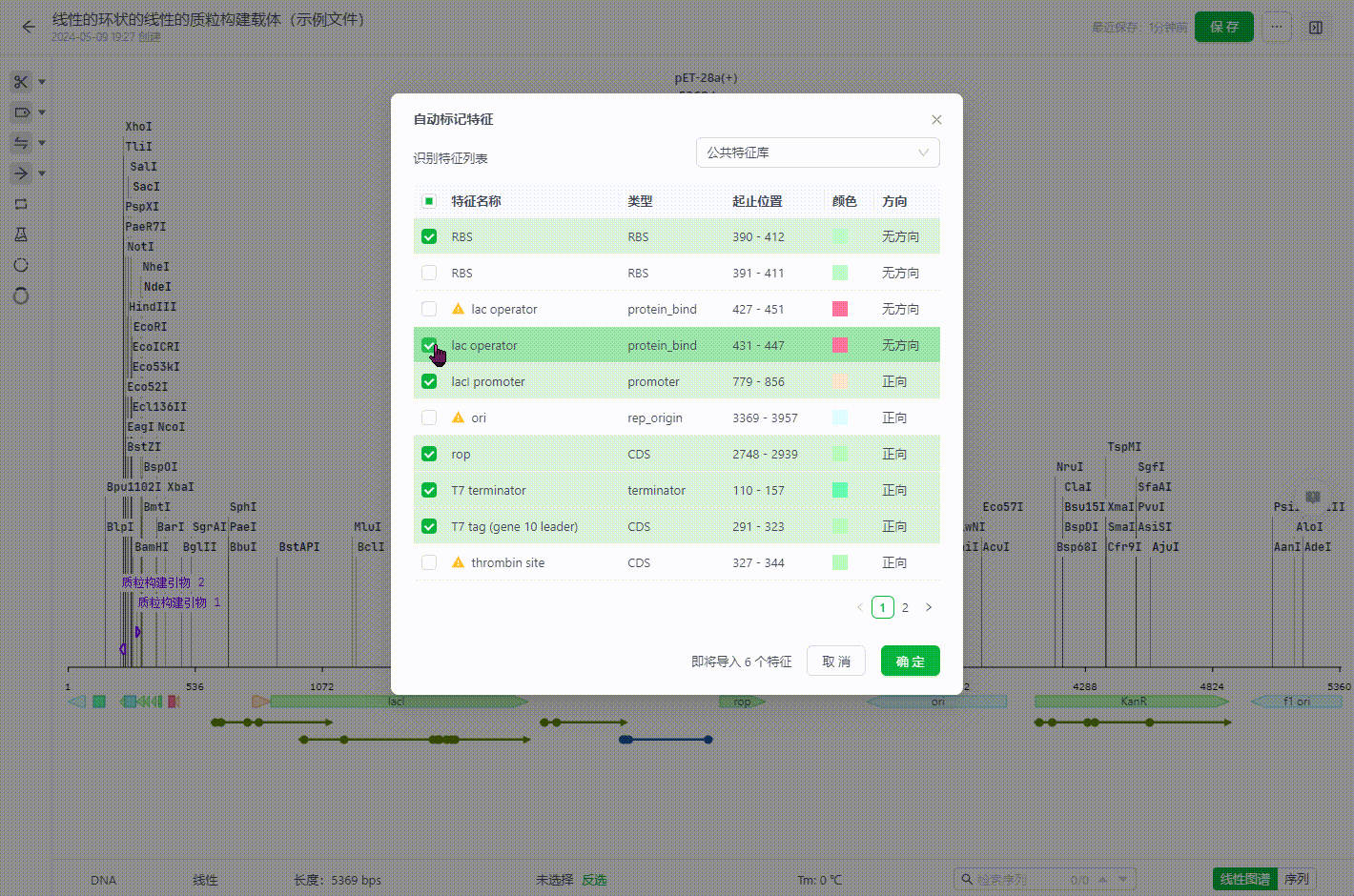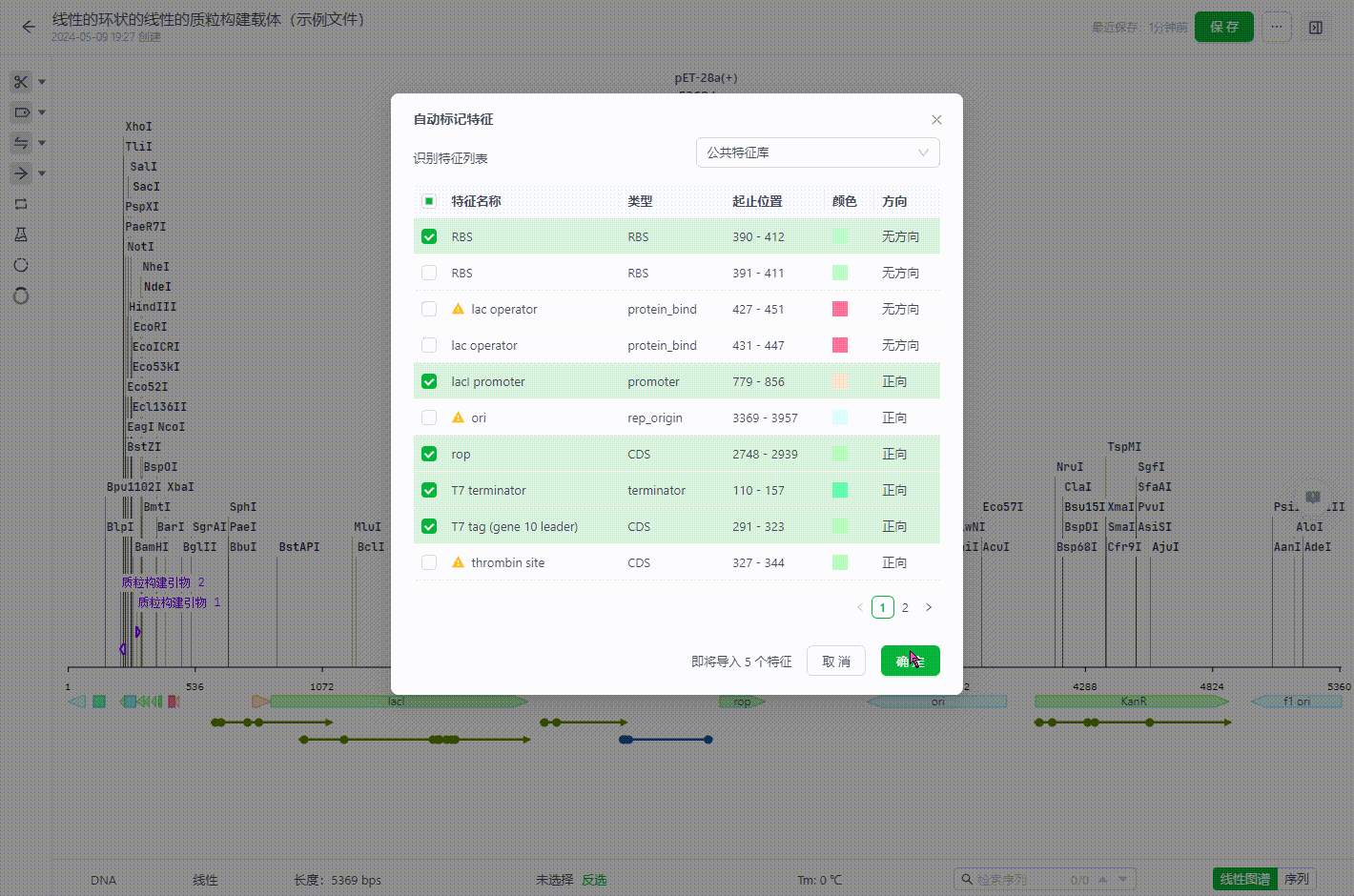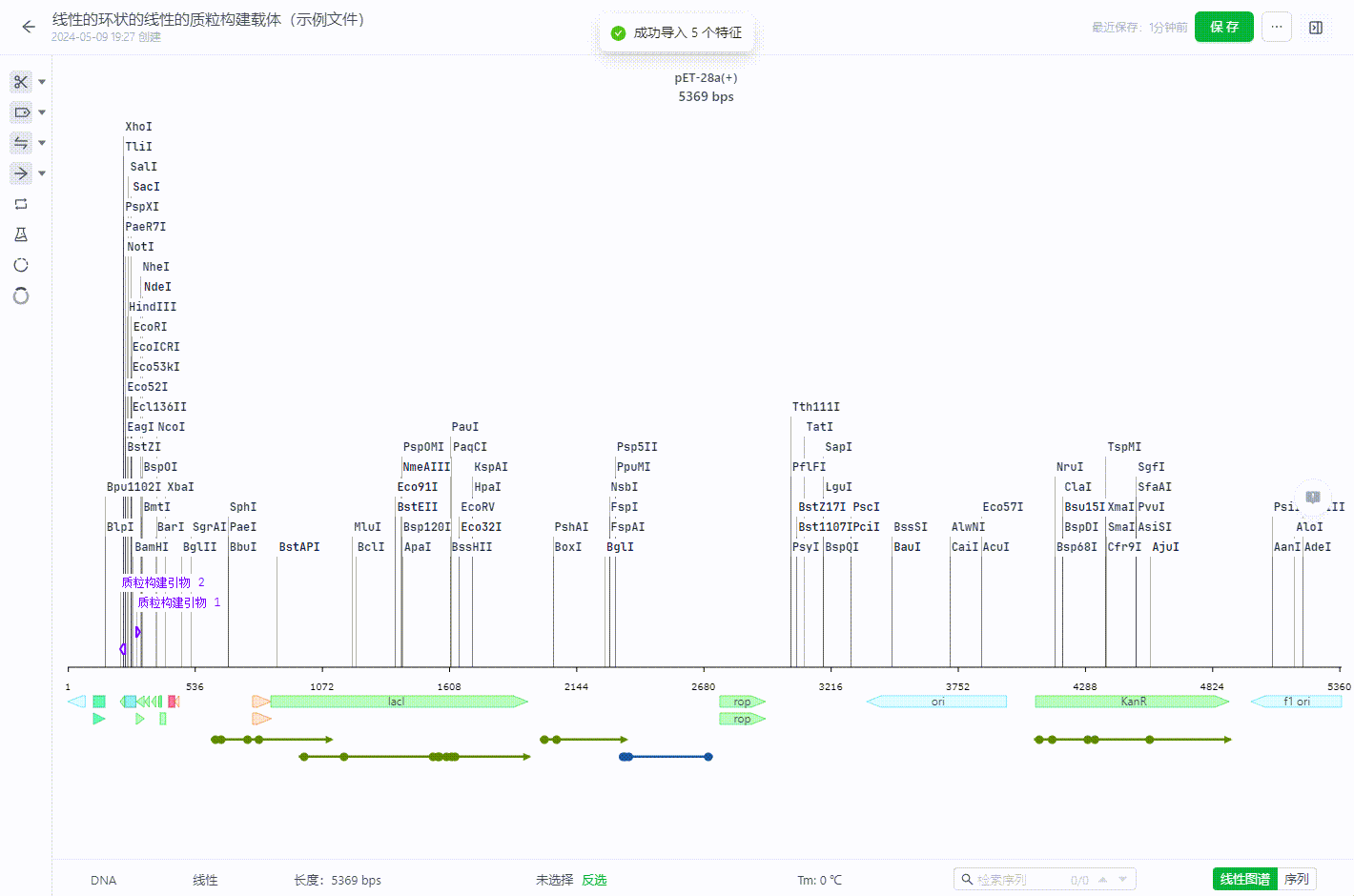
- 选择需要保留注释的特征信息
7. 引物相关操作
7.1 引物展示开关、添加编辑引物
左侧的引物开关可以打开或关闭整个文件的引物展示。
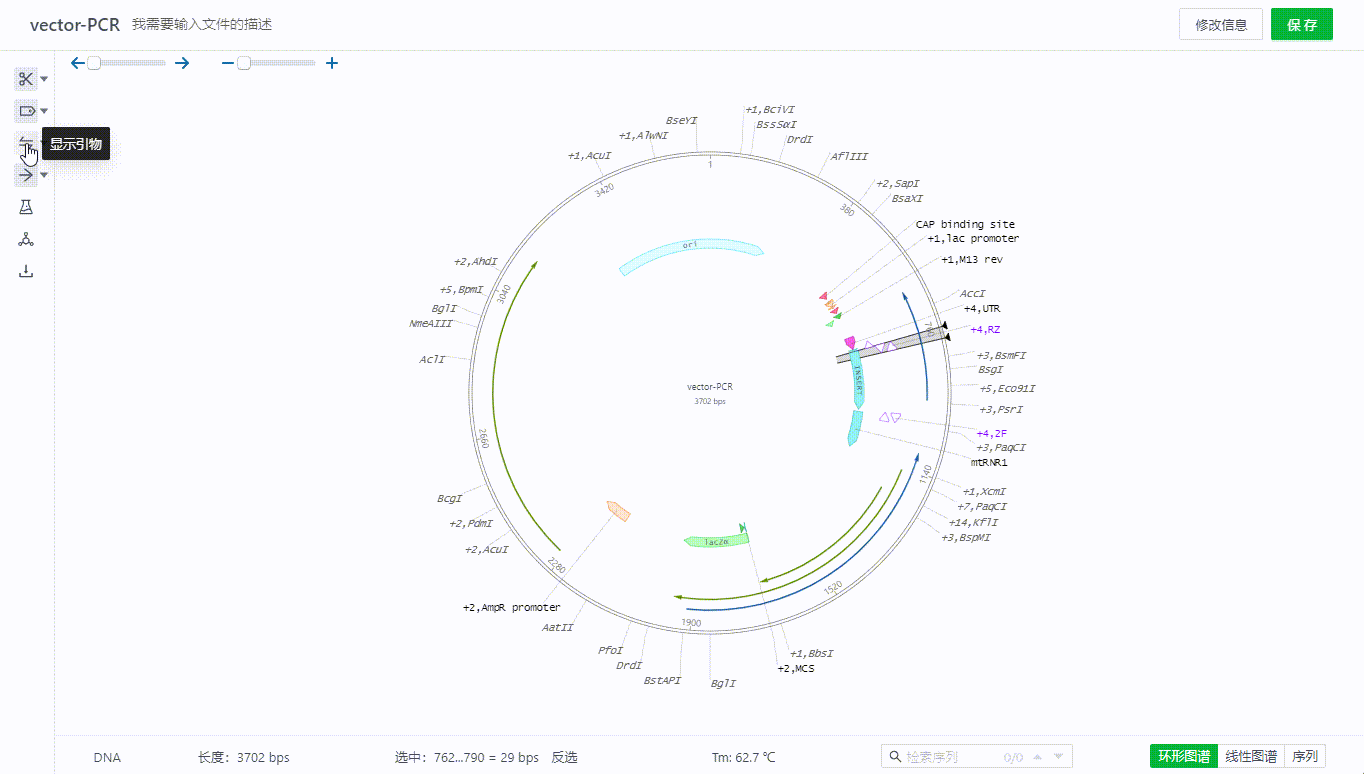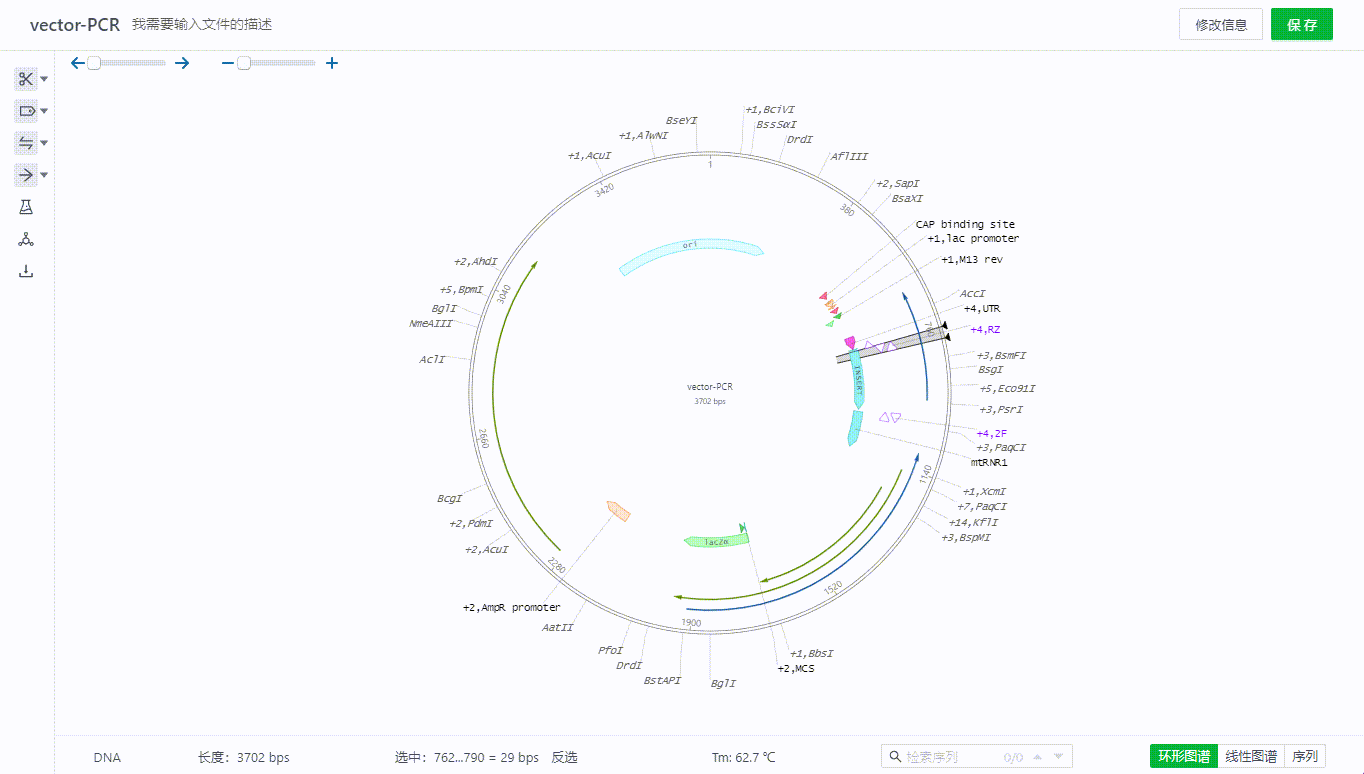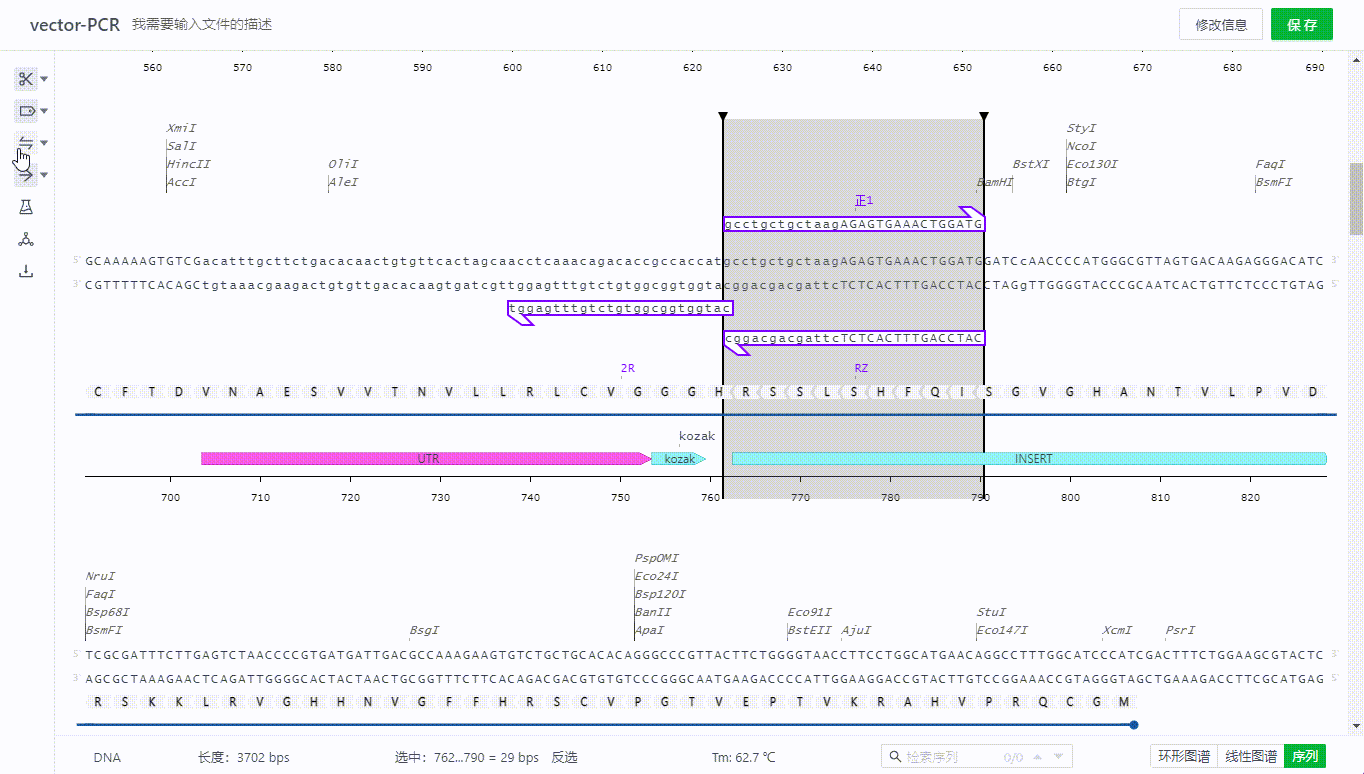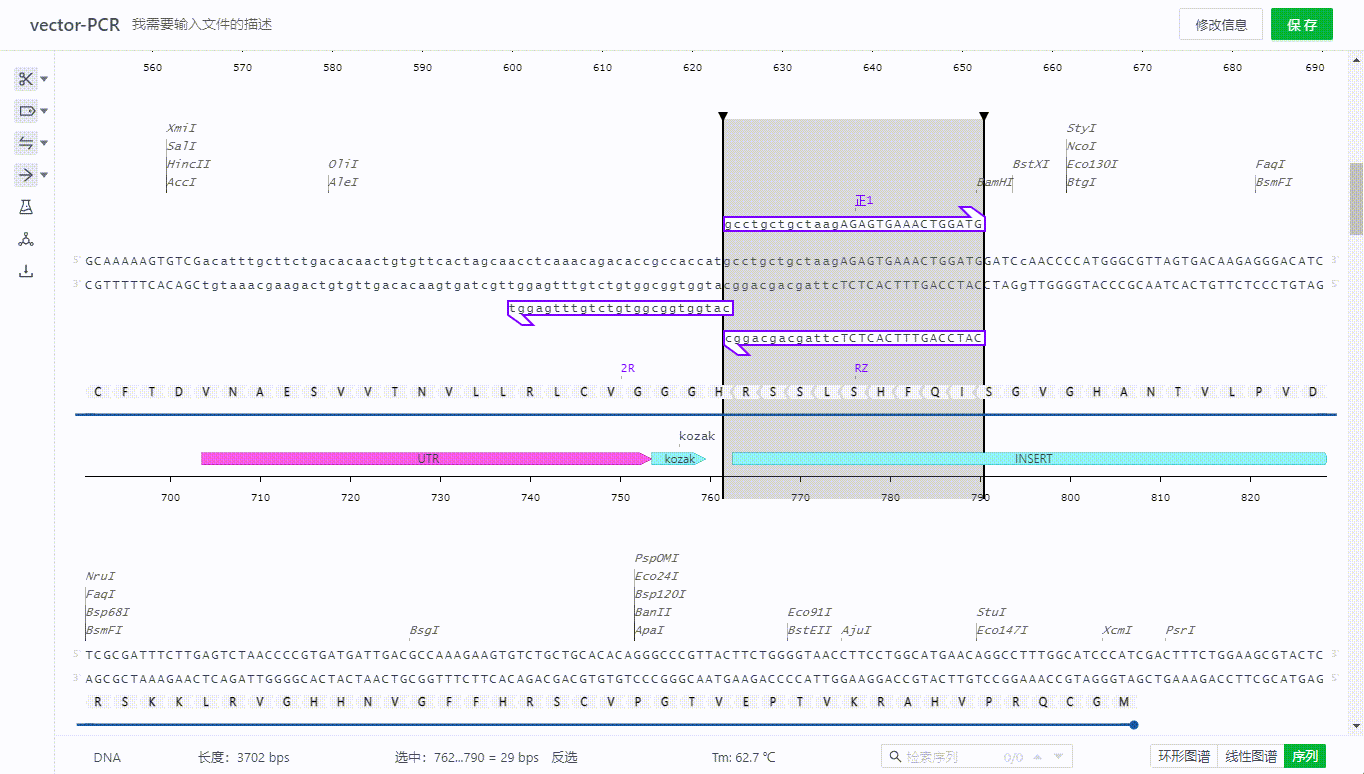
用户可以选取一段序列,然后右键创建引物,目前支持引物创建过程中正反向选择,描述引物,插入密码子,限制性内切酶等序列,同时会根据整个文件的杂交参数配置判断结合位点,如果有多个结合位点可以在画面中切换查看。
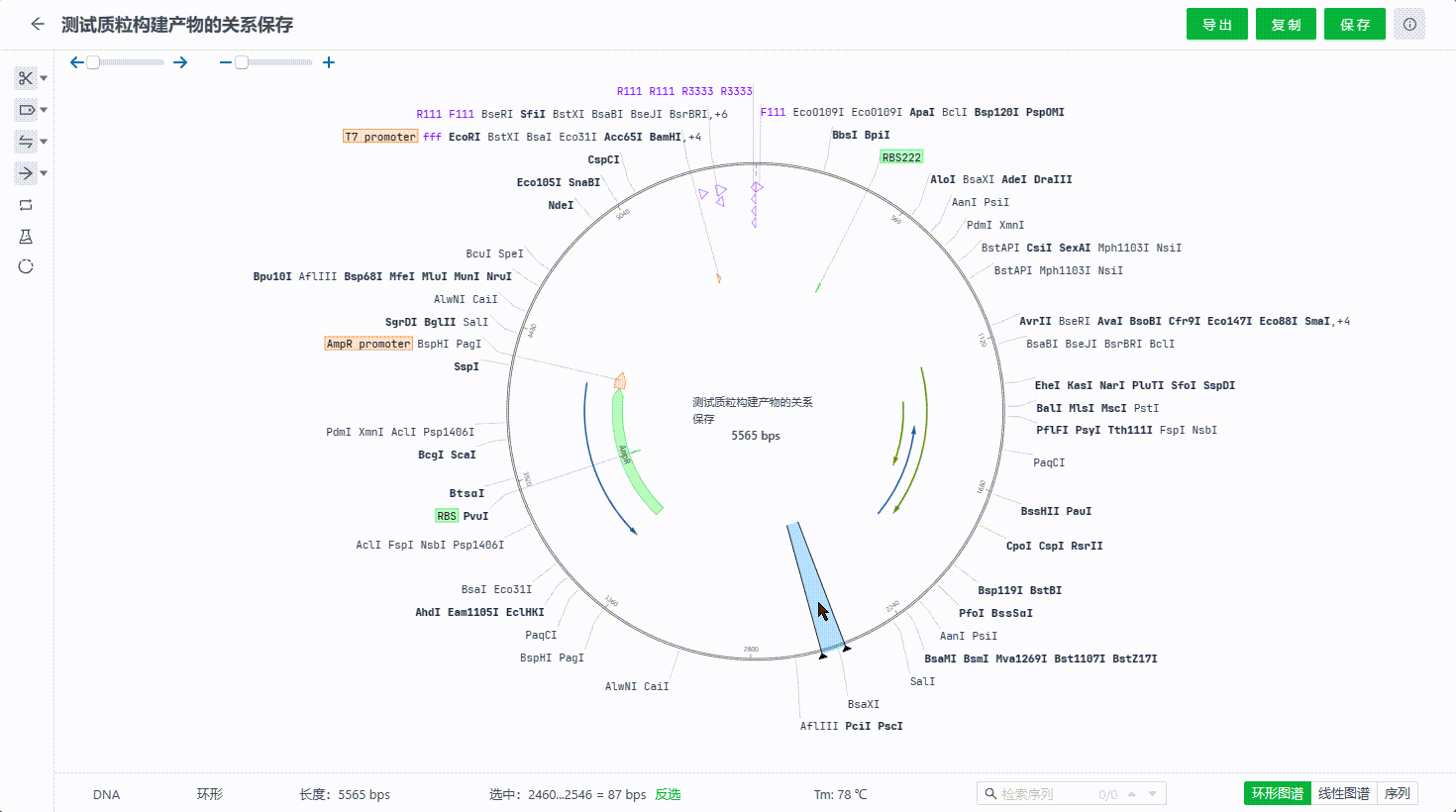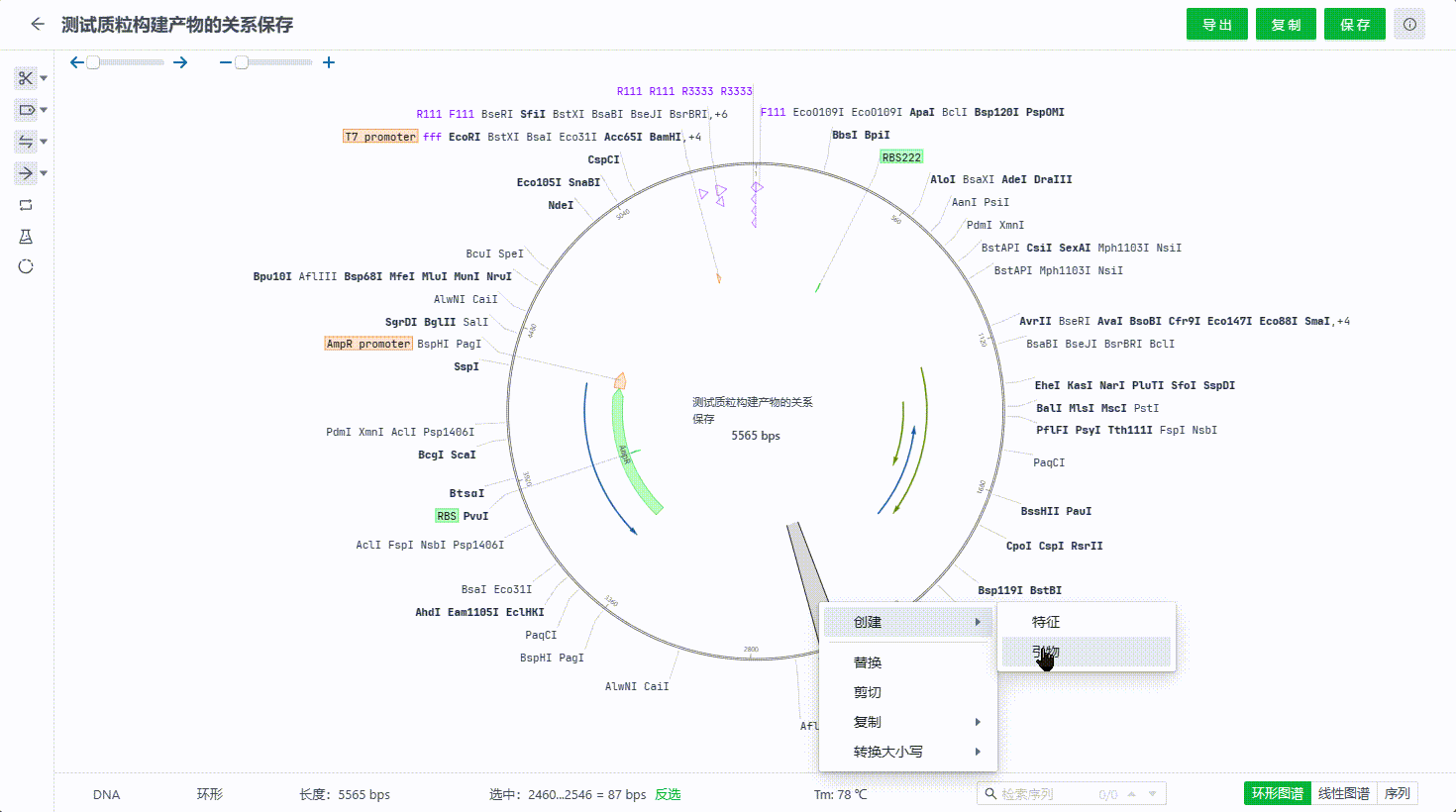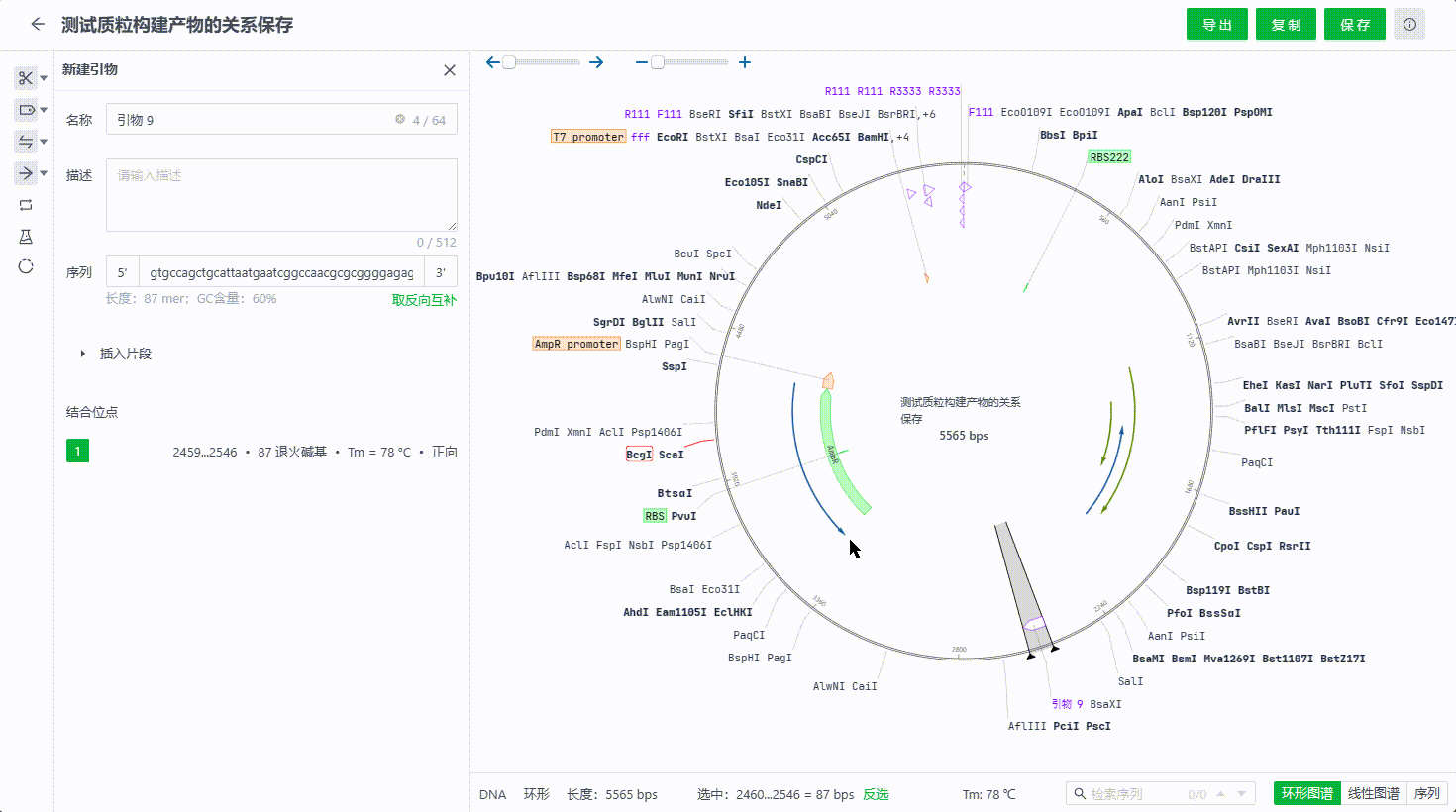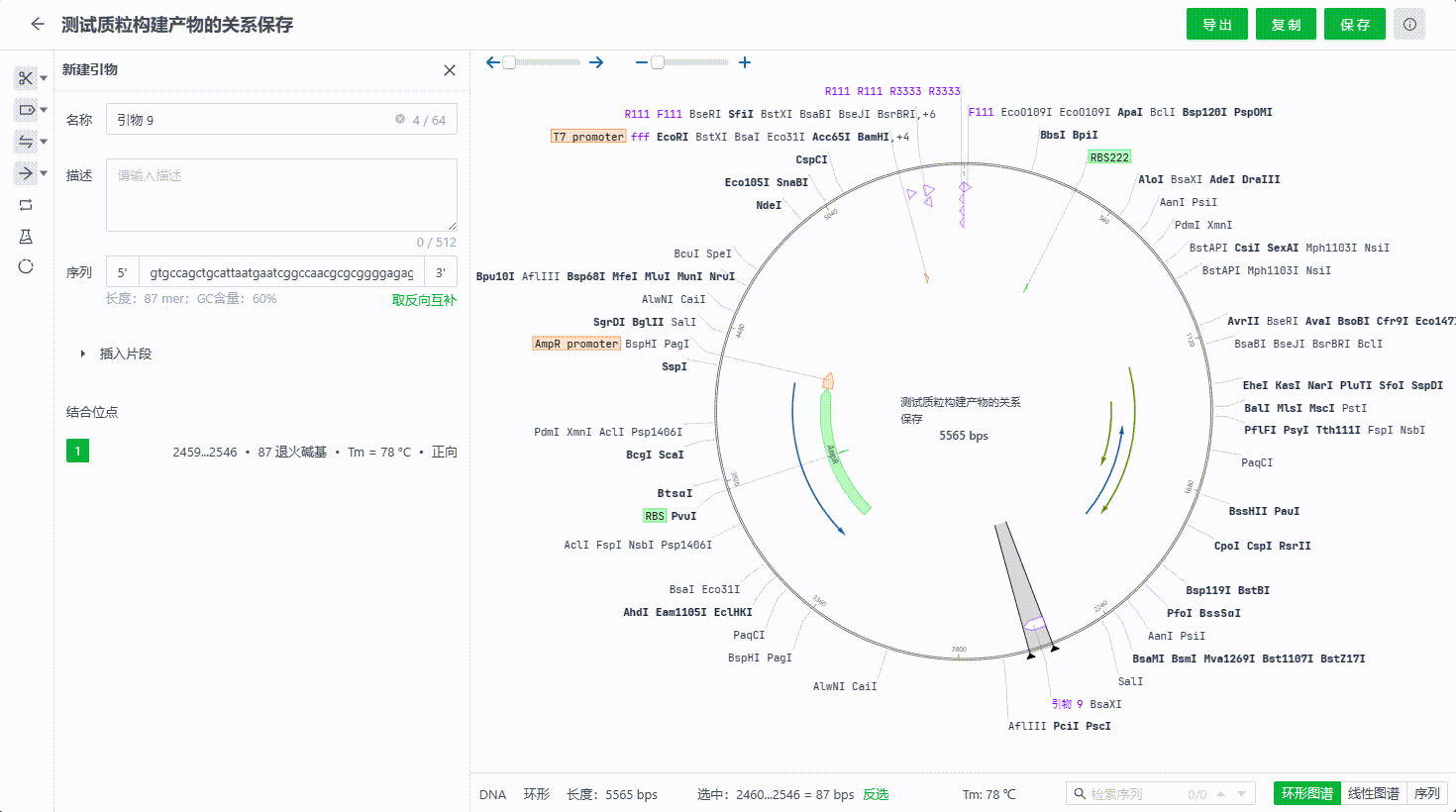
用户可以通过双击或右键引物编辑引物,删除引物,通过引物的列表隐藏单个引物搜索引物。
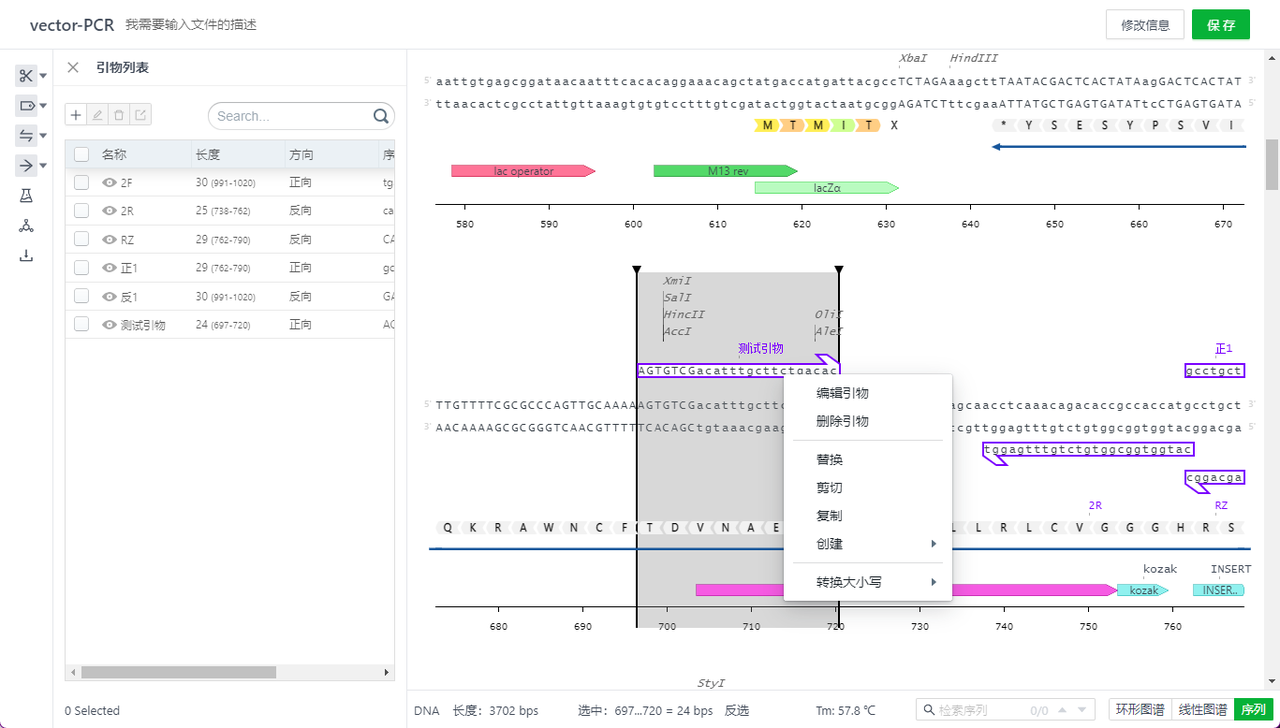
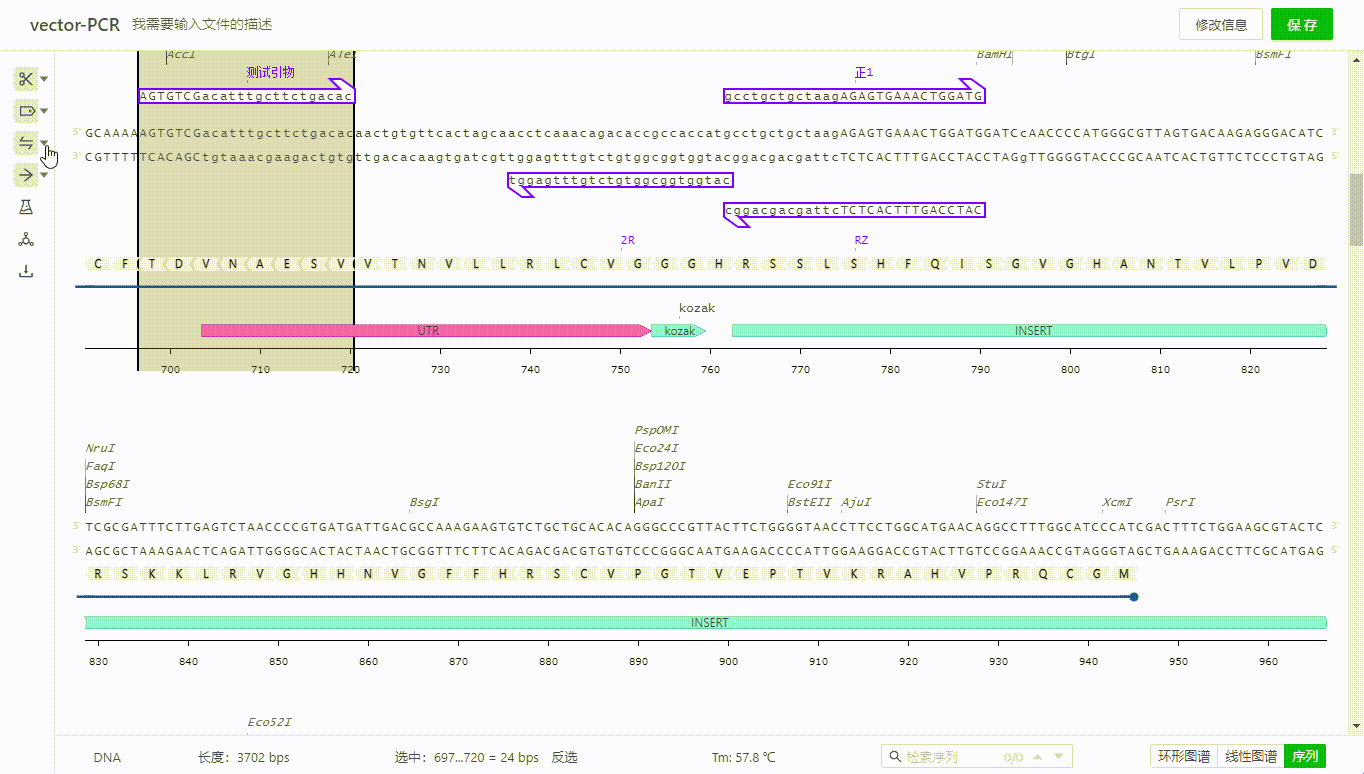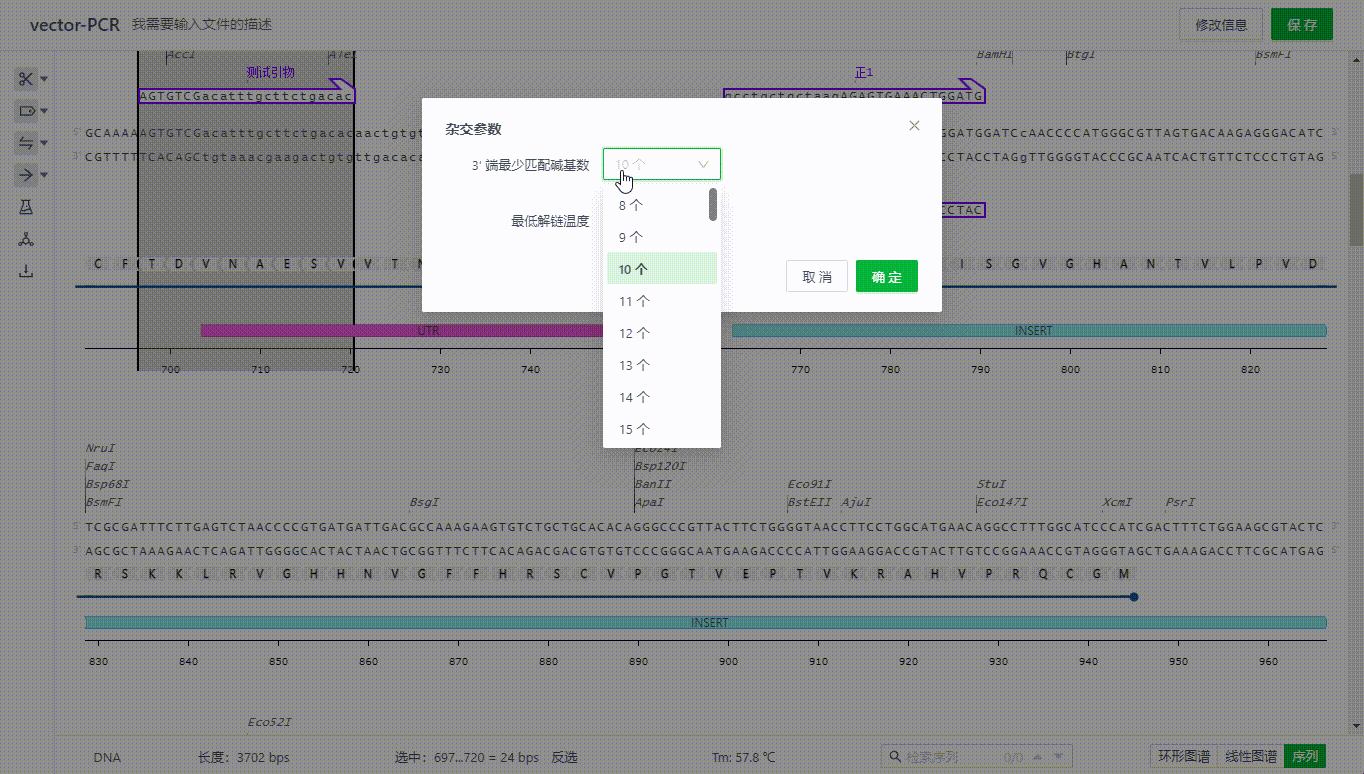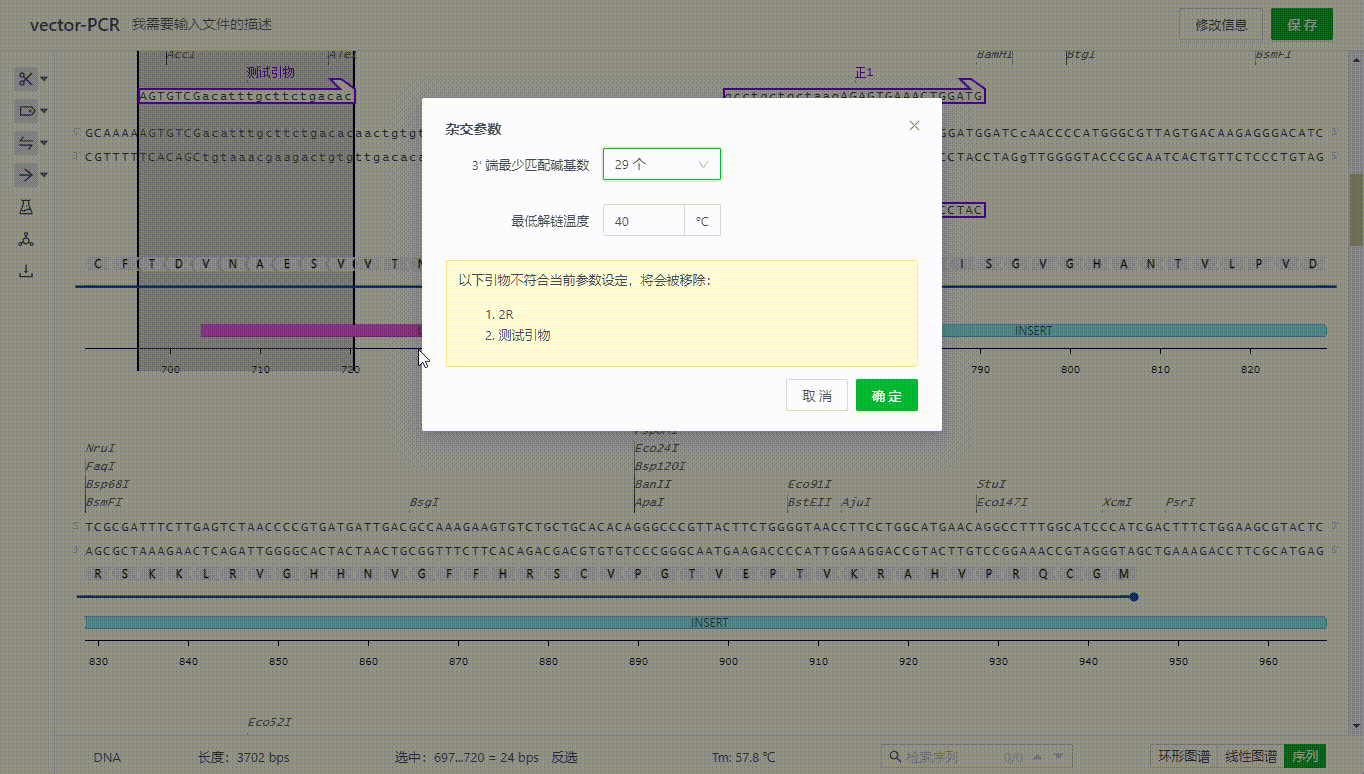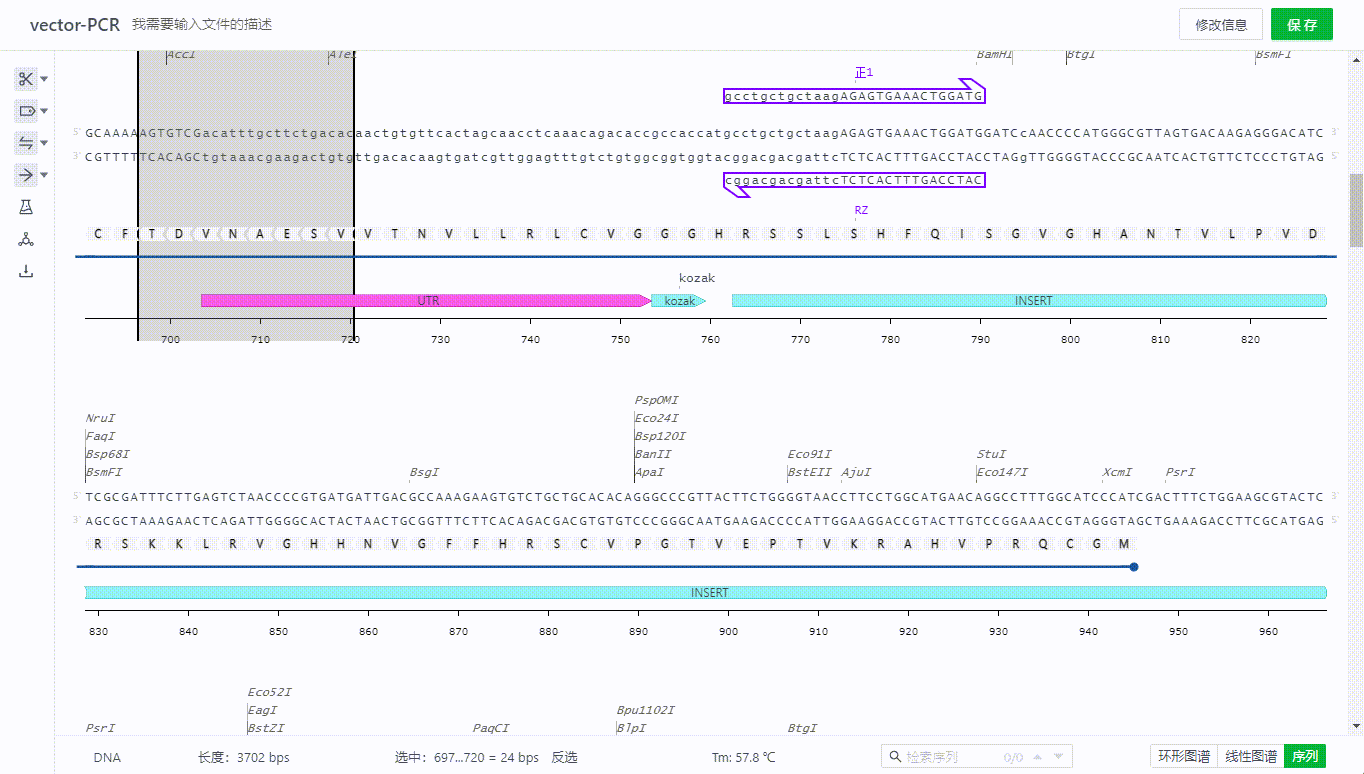
7.2 设置杂交参数
用户可以设置杂交参数,调整引物的结合位点判断逻辑,如果设置当前序列有不在满足的引物,将会自动隐藏,同时此改动将会影响到整个文件创建引物结合点位的算法。
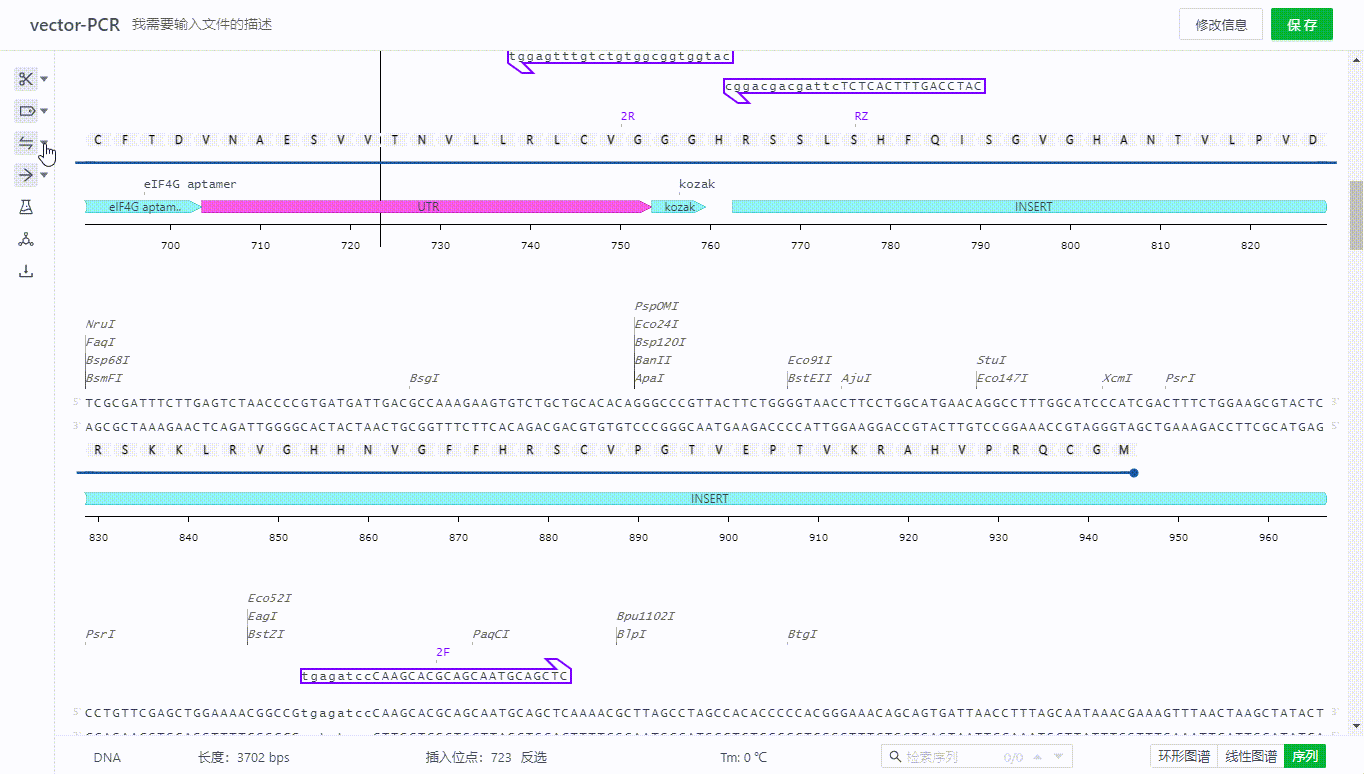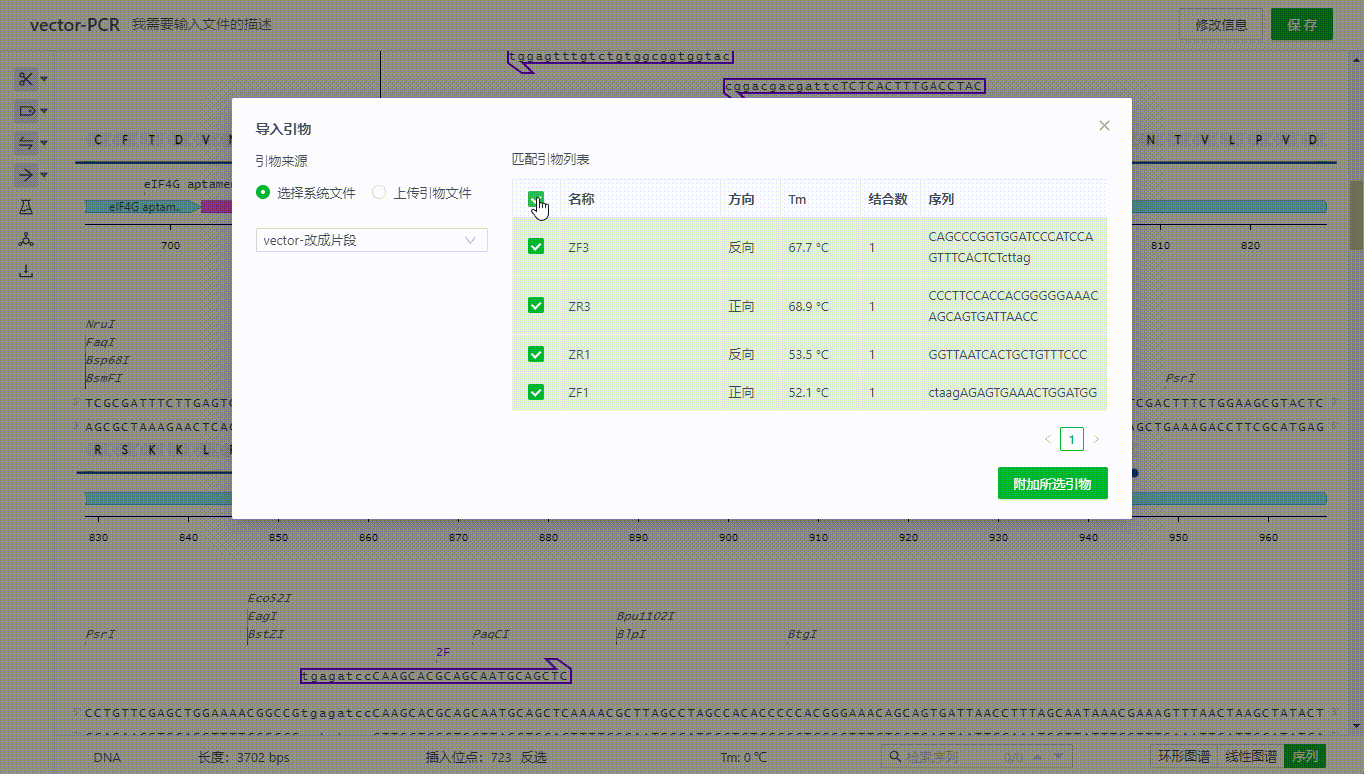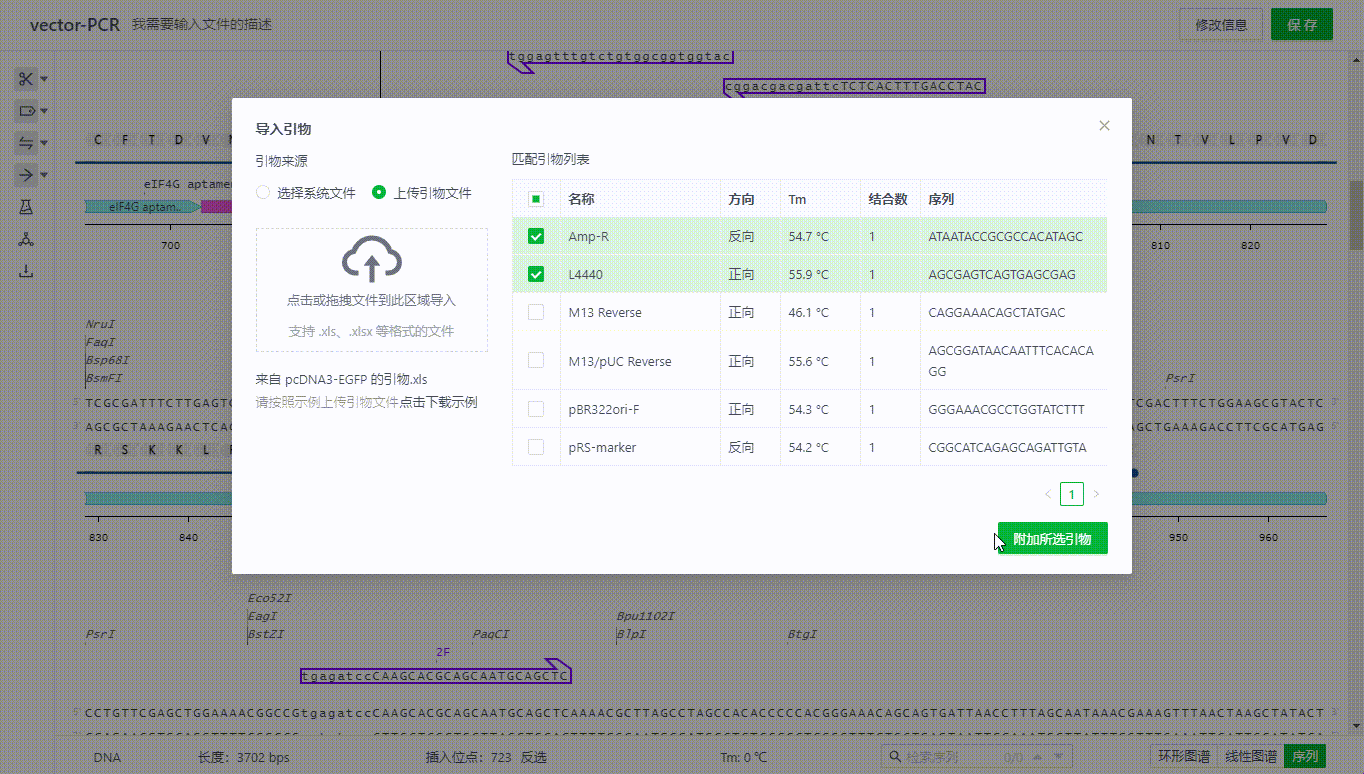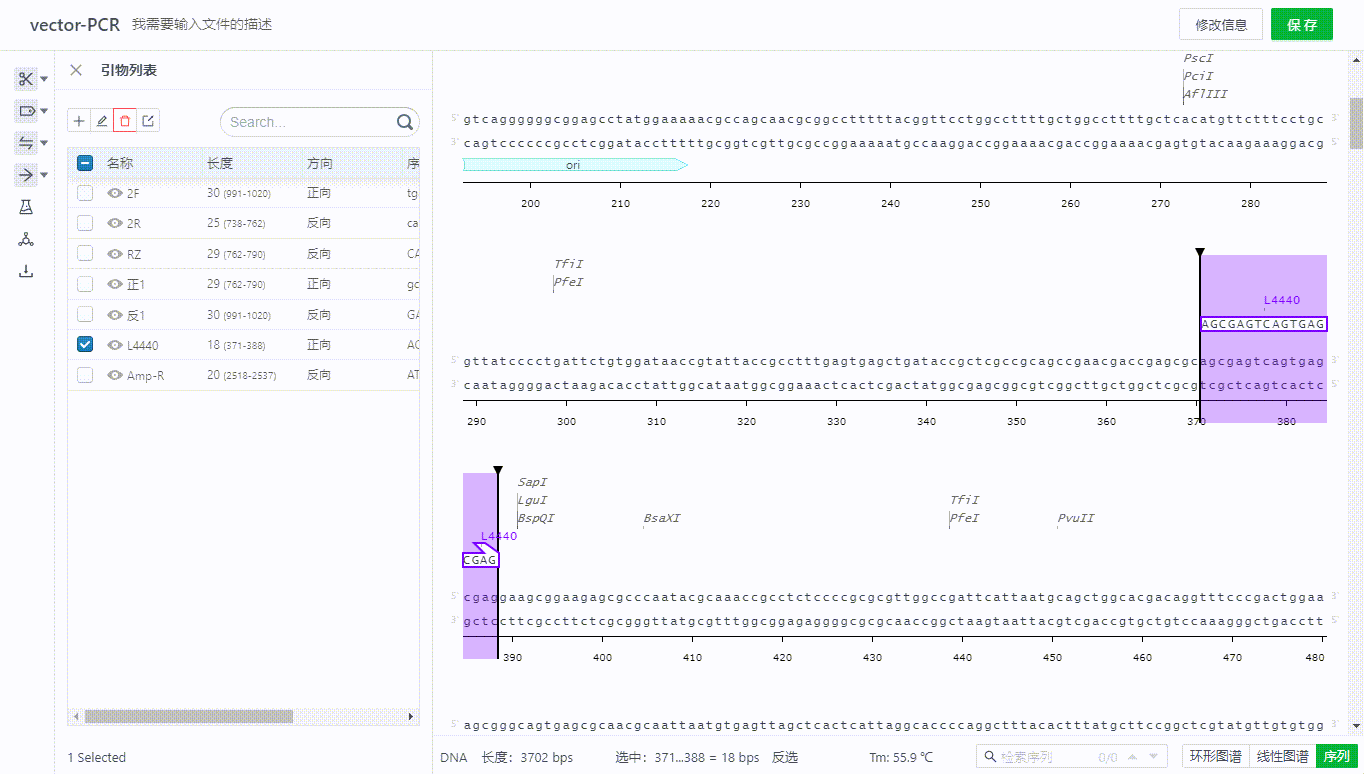
7.3 导入引物
用户可以选择项目中的文件,或者上传一个表单来实现导入引物,系统将会根据杂交参数的设置寻找系统中的结合位点,并展示可结合的引物,此时用户只需选择需要导入的引物即可导入引物。
8. 翻译及阅读框架显示方式(ORF)相关操作
8.1 添加需要翻译的区域
用户在添加特征的时候可以选择带有翻译属性的特征类型,该区域序列就会展示氨基酸。如果部分可翻译的特征不需要展示氨基酸,可以通过去除勾选项完成隐藏。
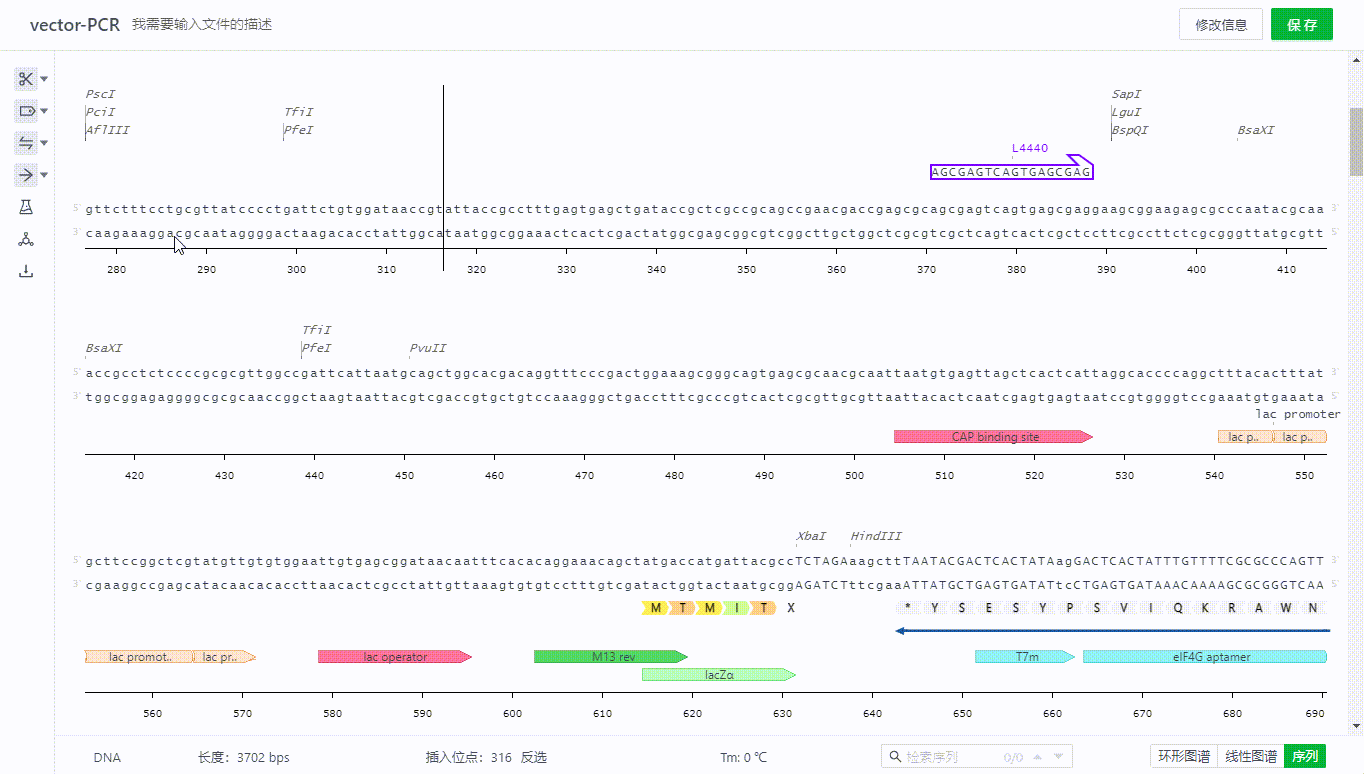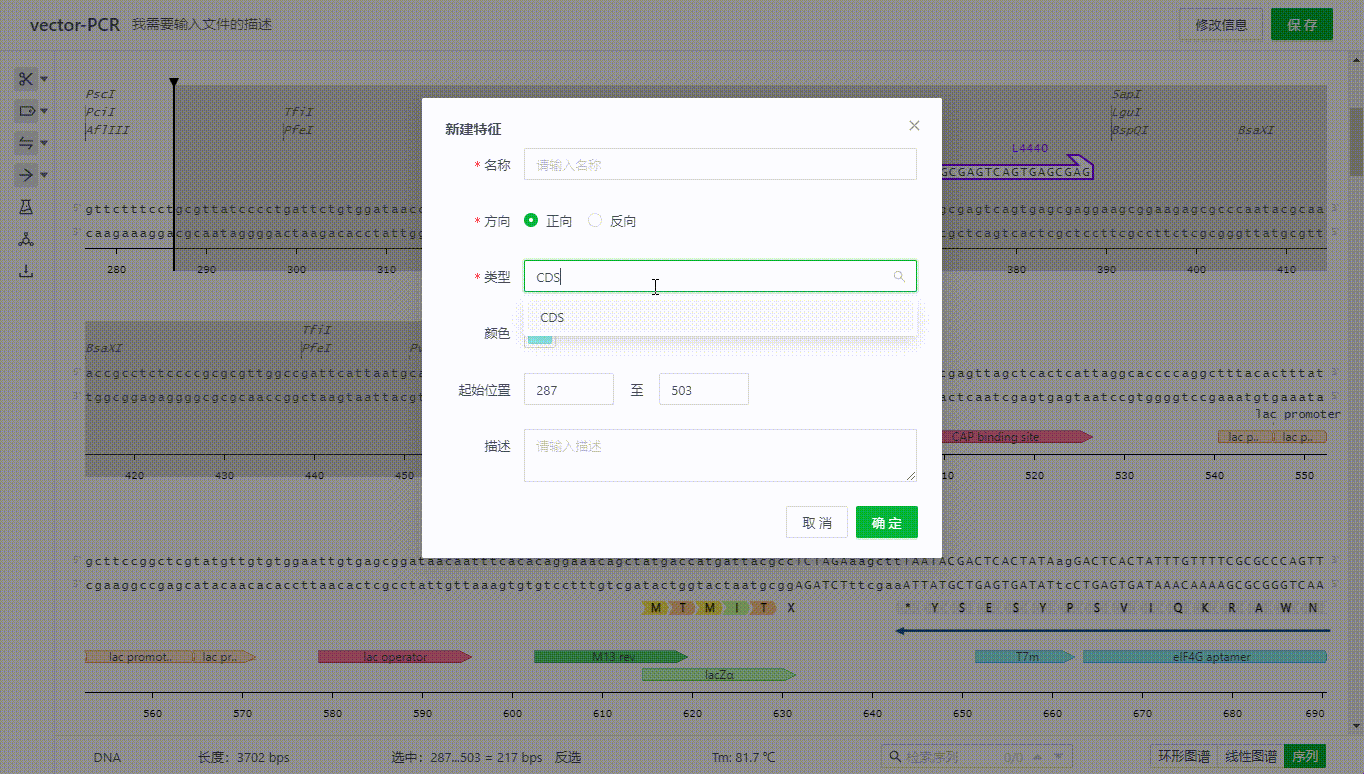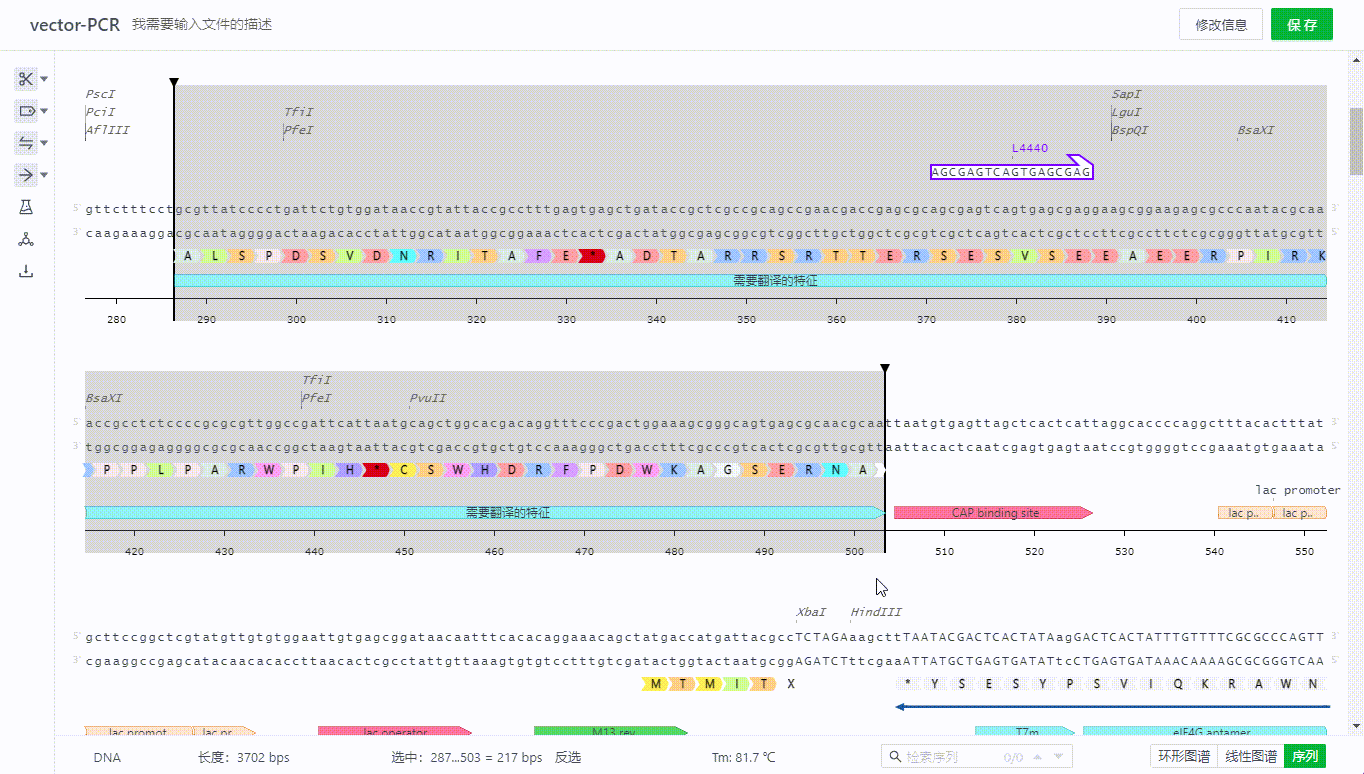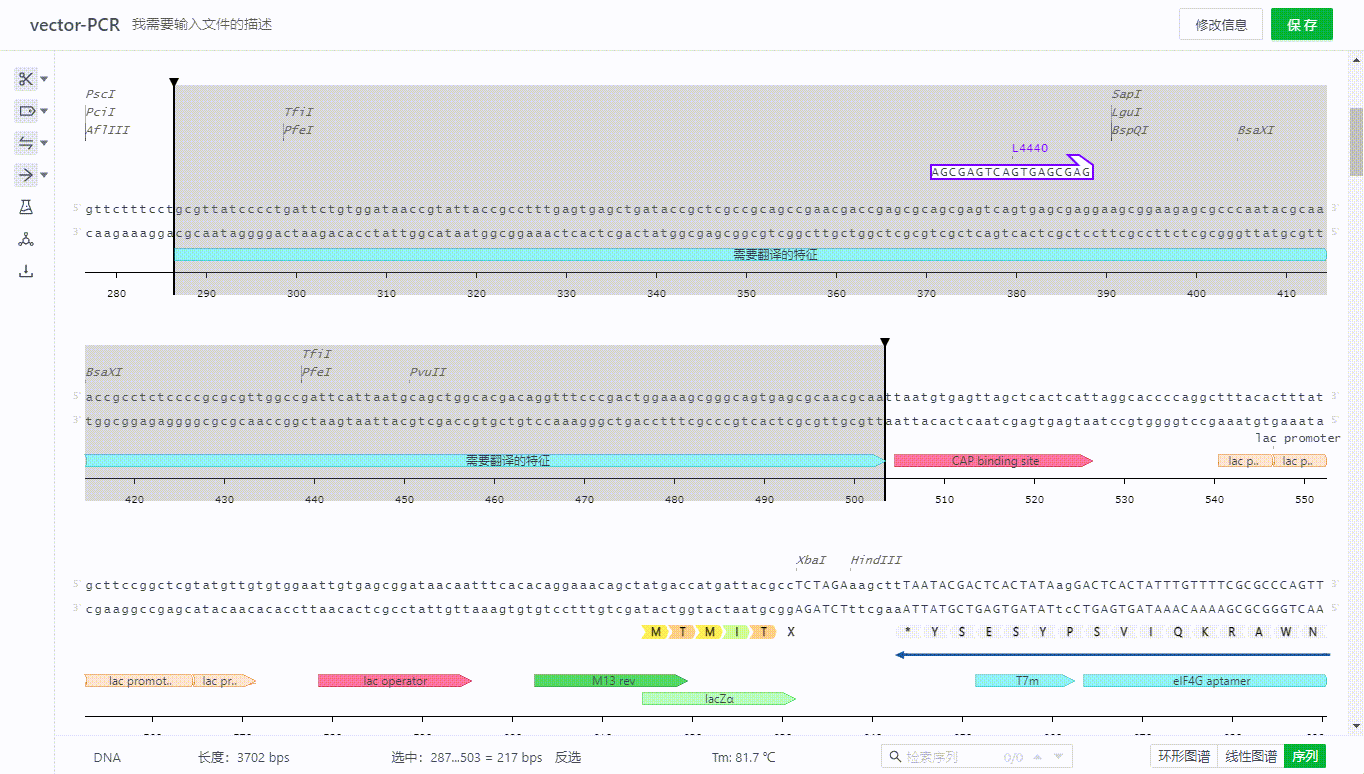
8.2 阅读框架显示方式(ORF)的展示开关
用户可以点击右侧展示开关打开阅读框架显示方式(ORF)可识别区,通过勾选不同方向的区域来隐藏无需观察的区域,可以选择以线条或字母的方式展示该区域。
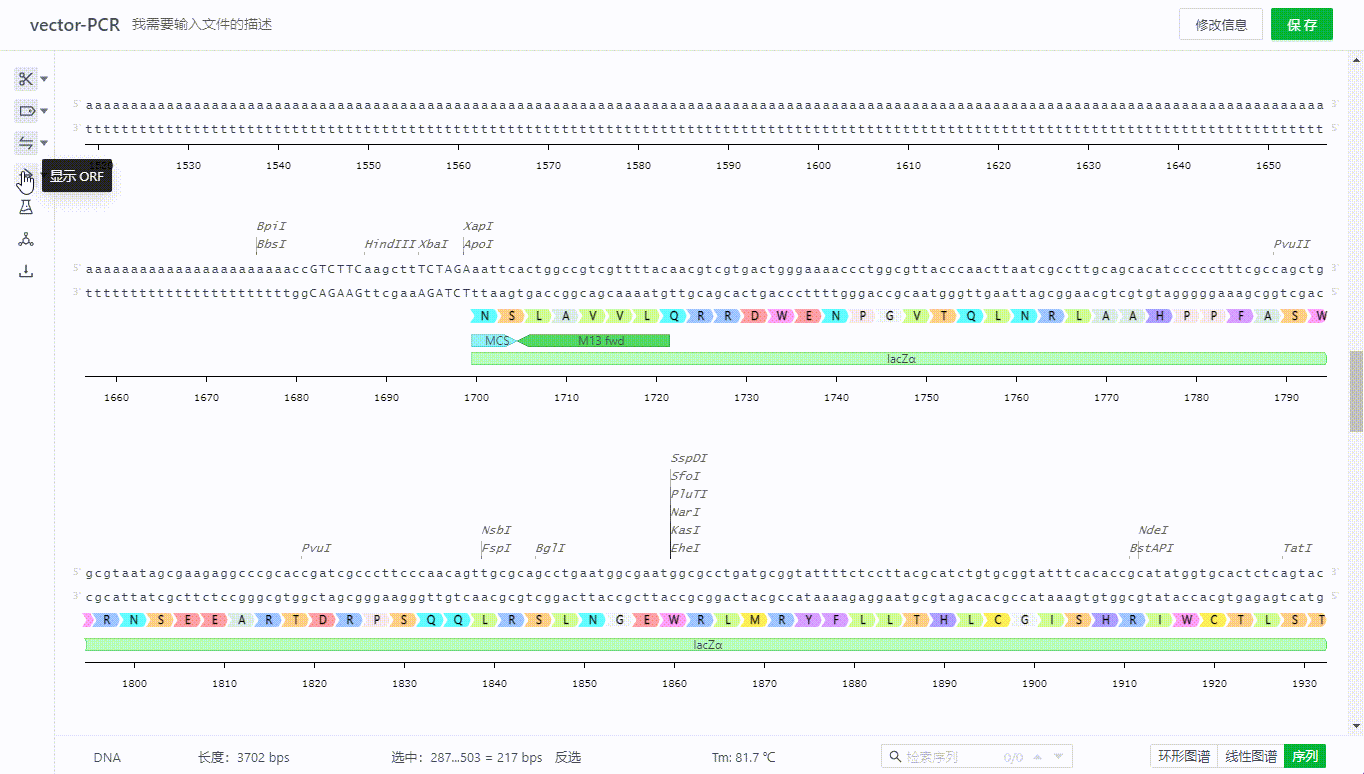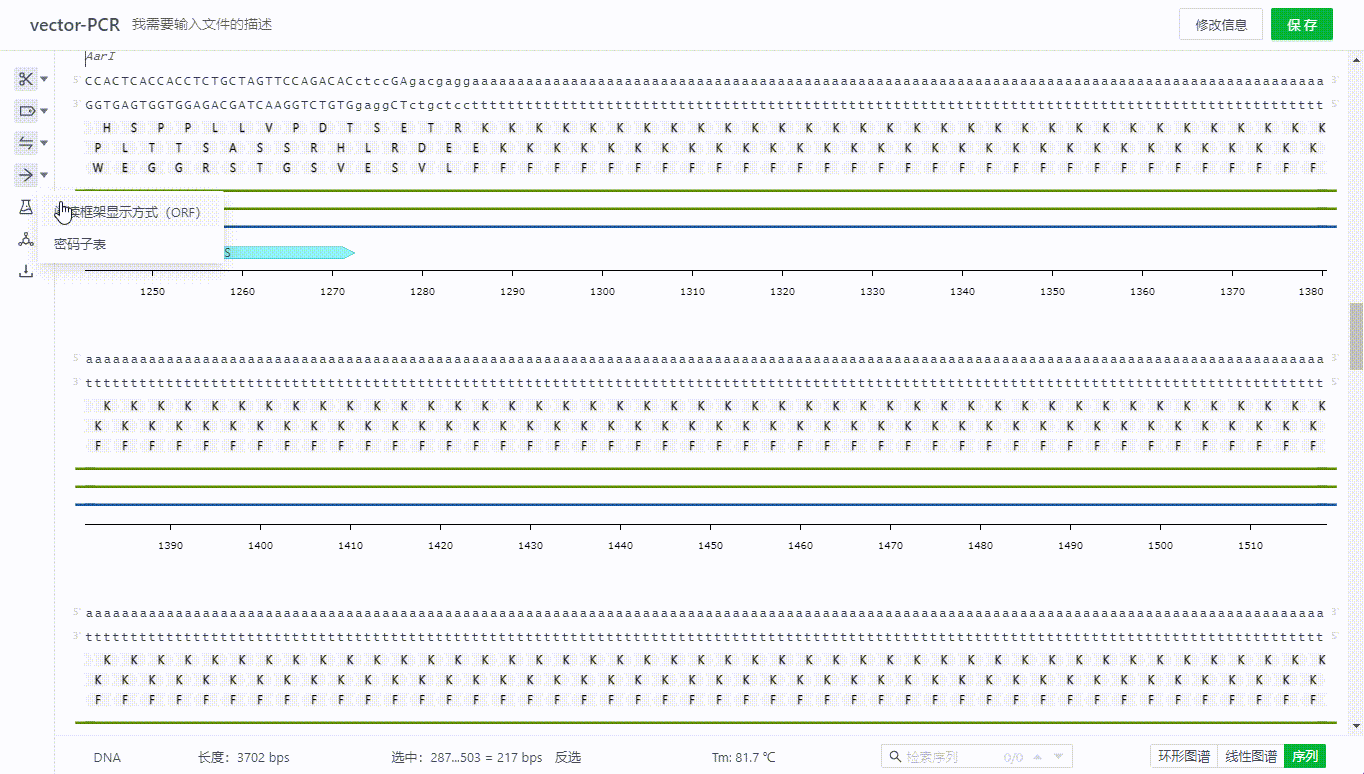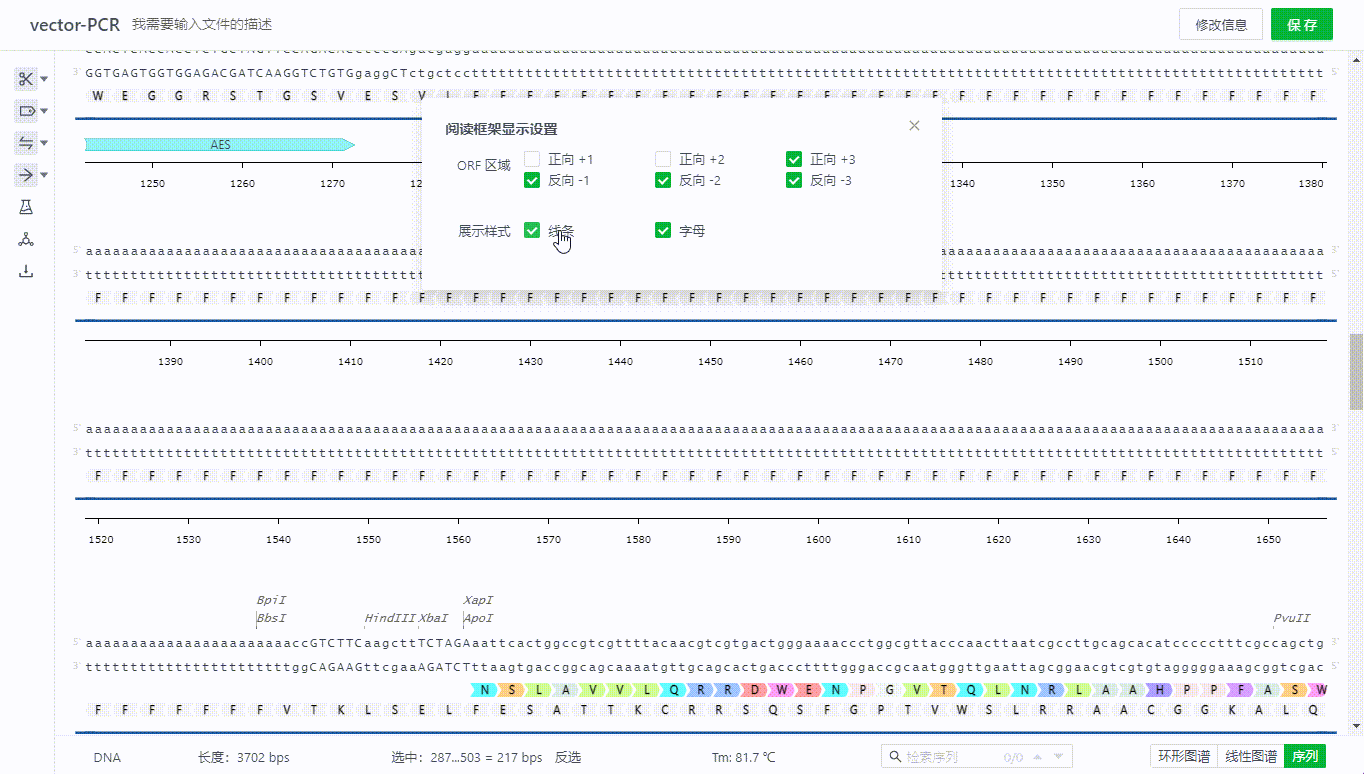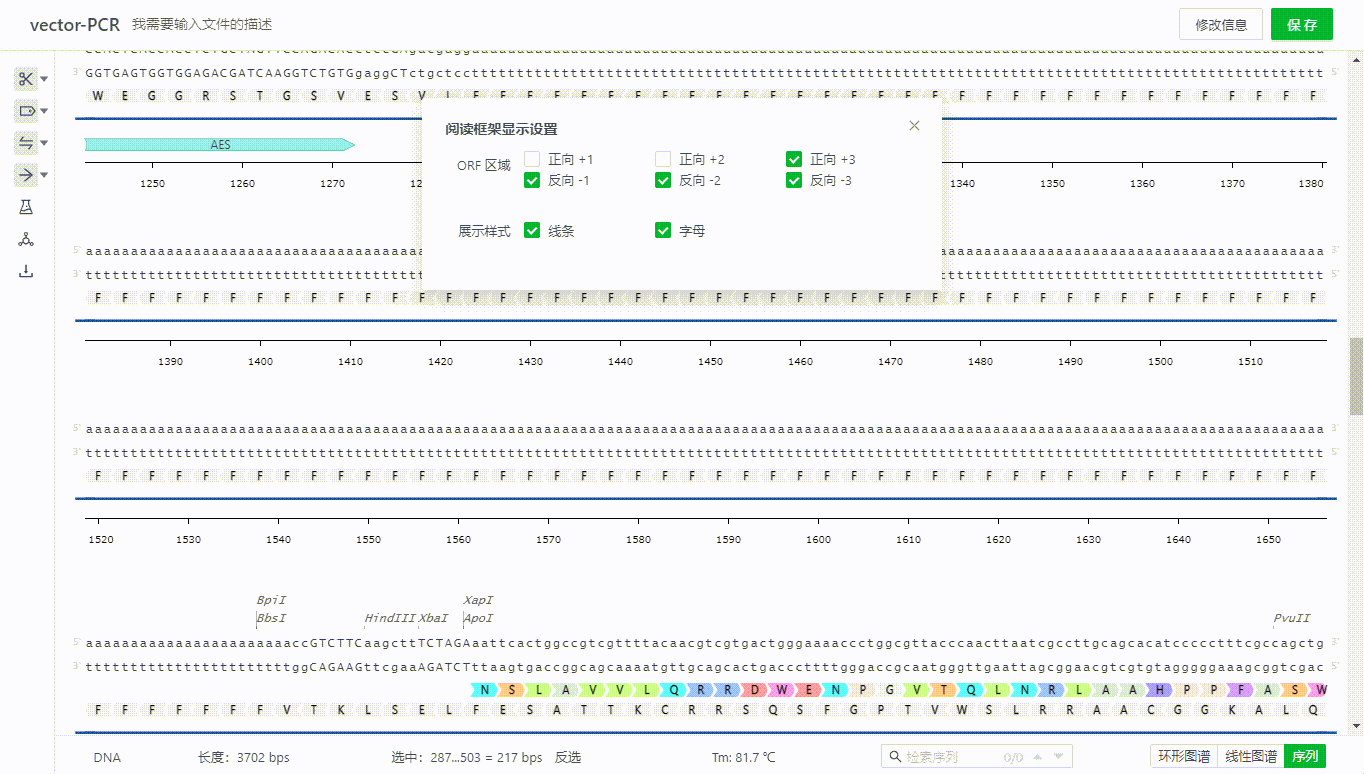
8.3 查看密码子表
系统会根据用户打开的文件类型自动展示对应的密码子表,用户可以拖拽表单,查看序列氨基酸信息。
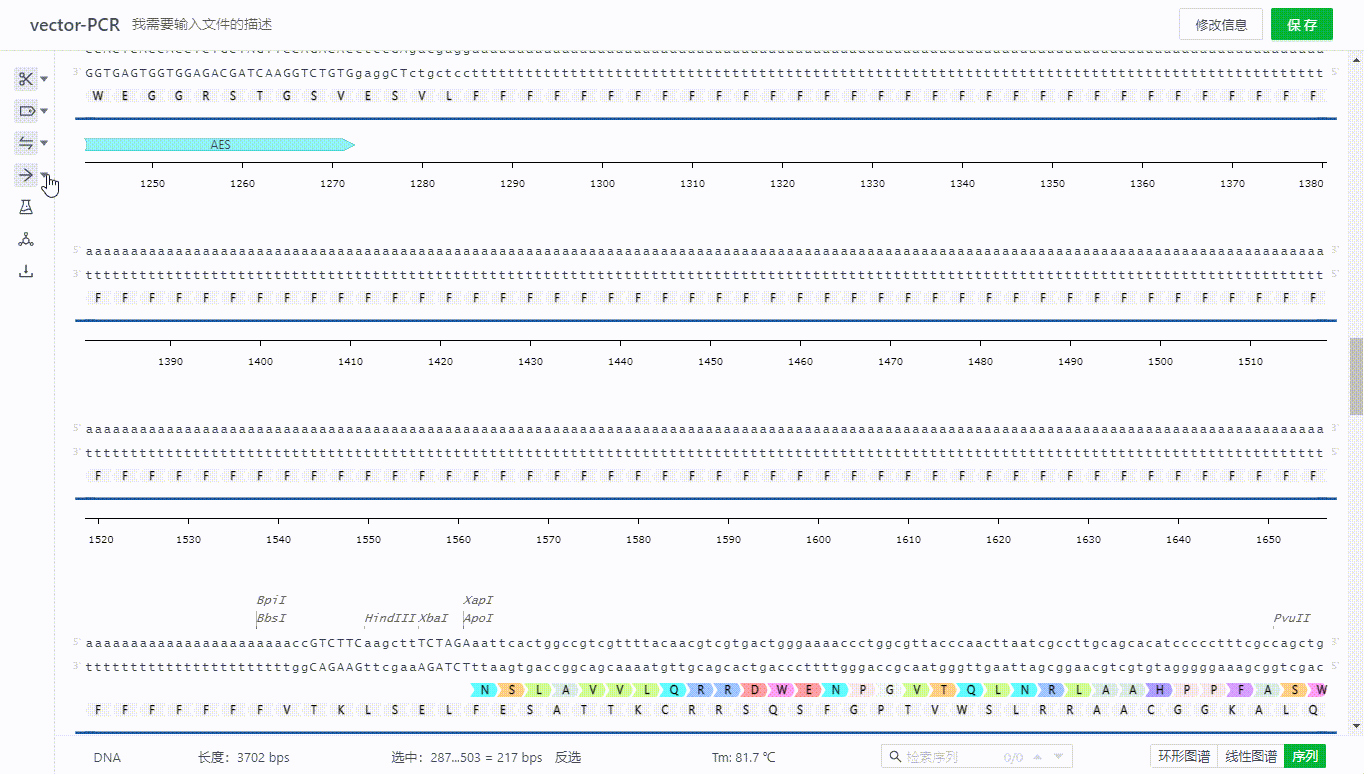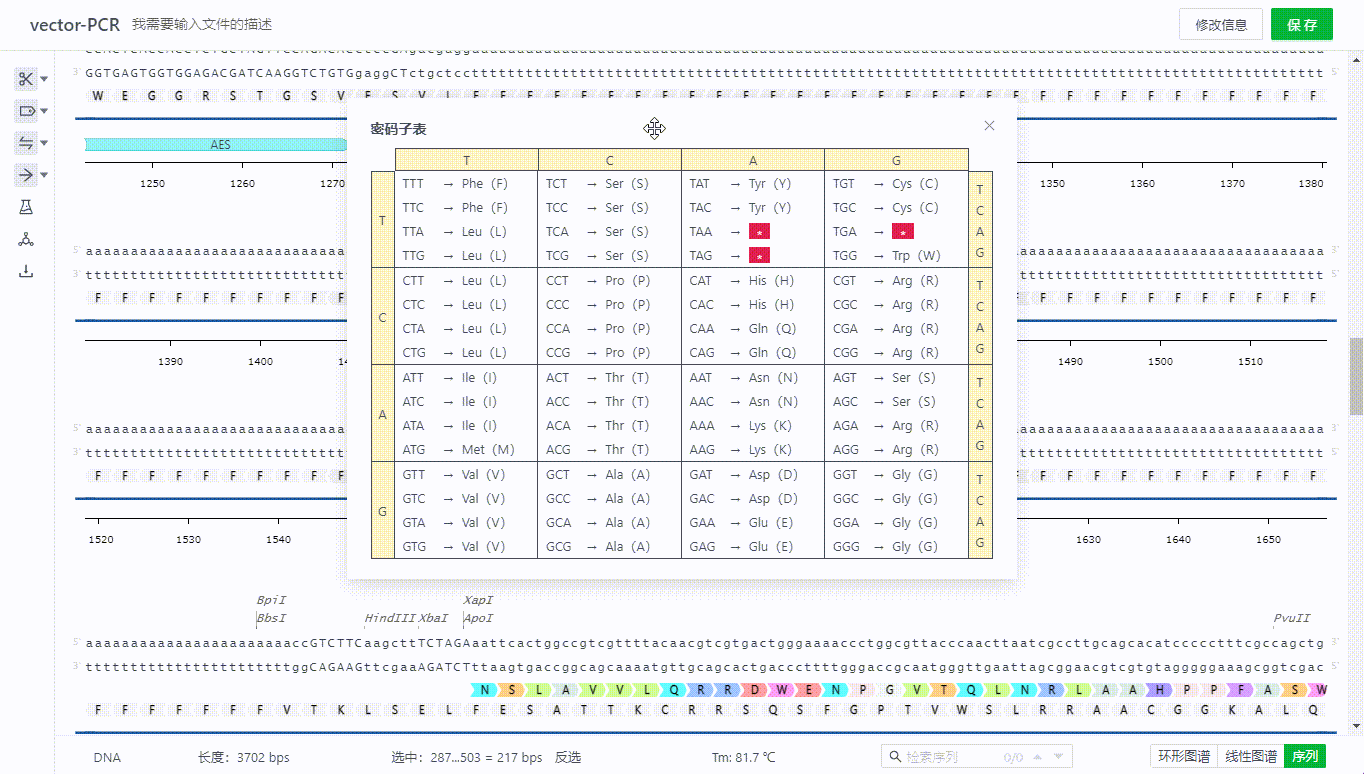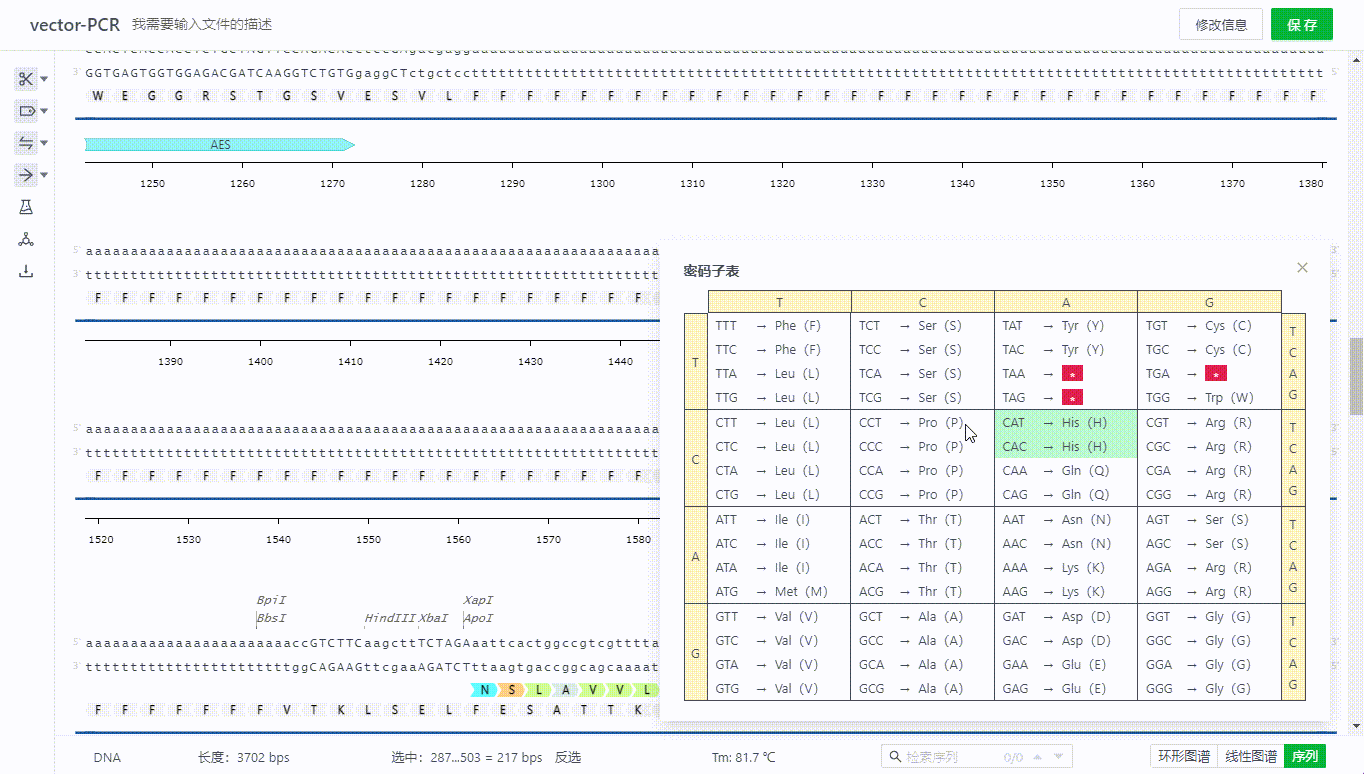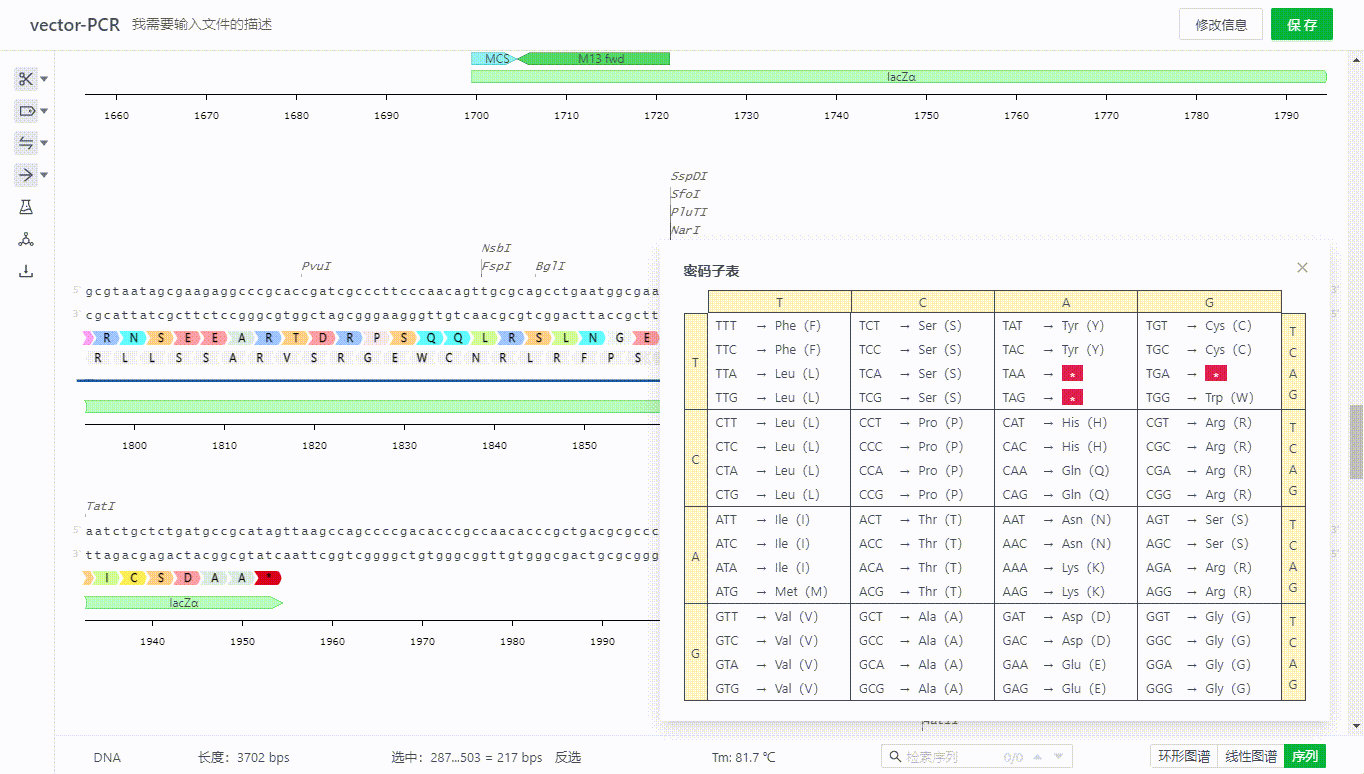
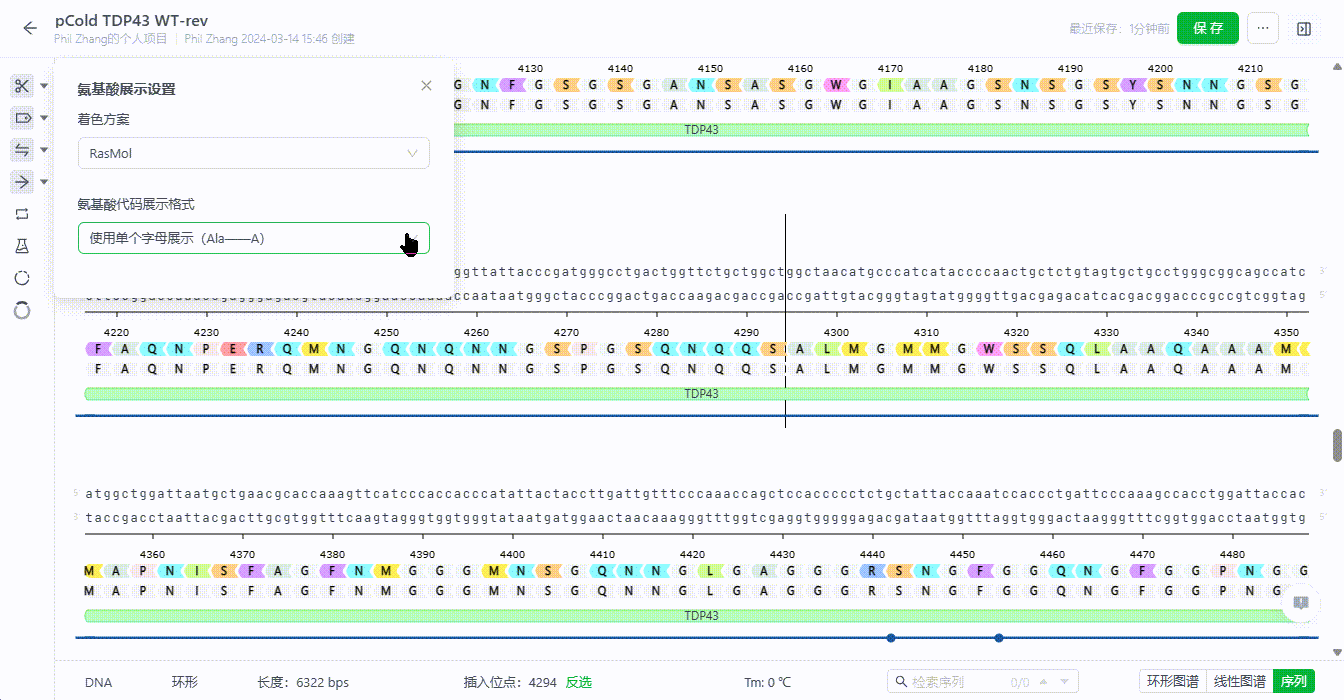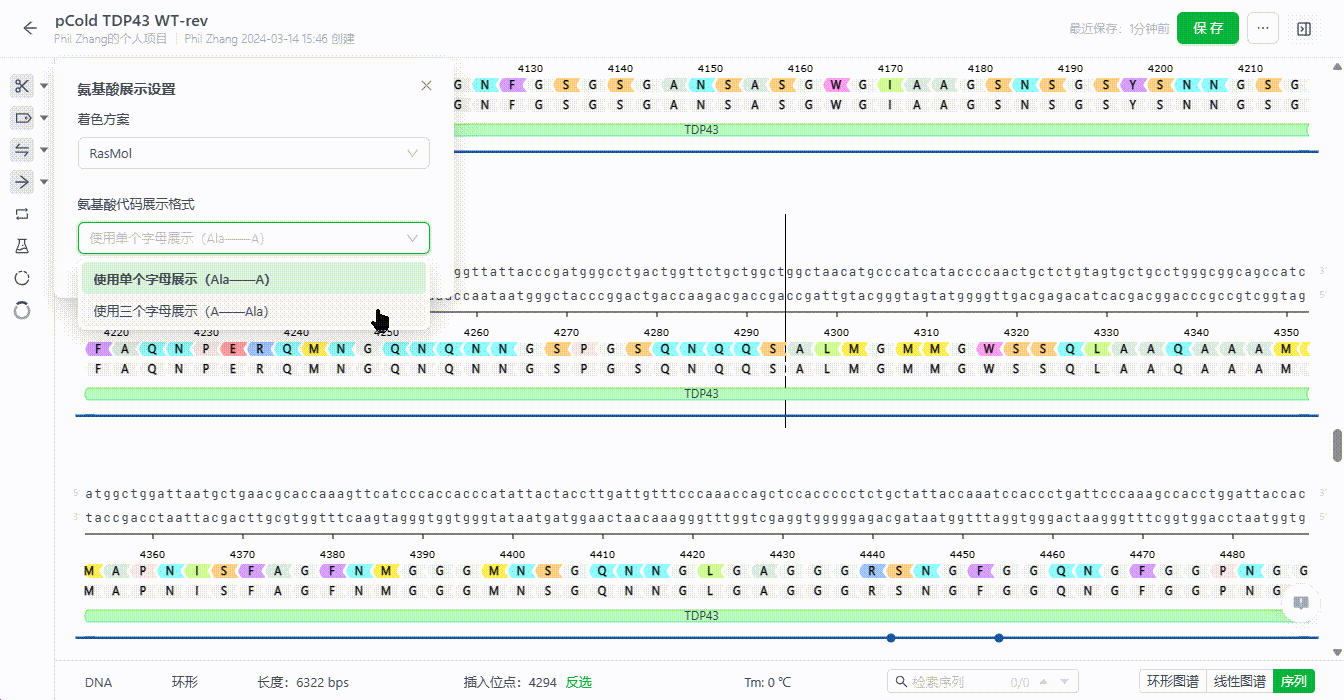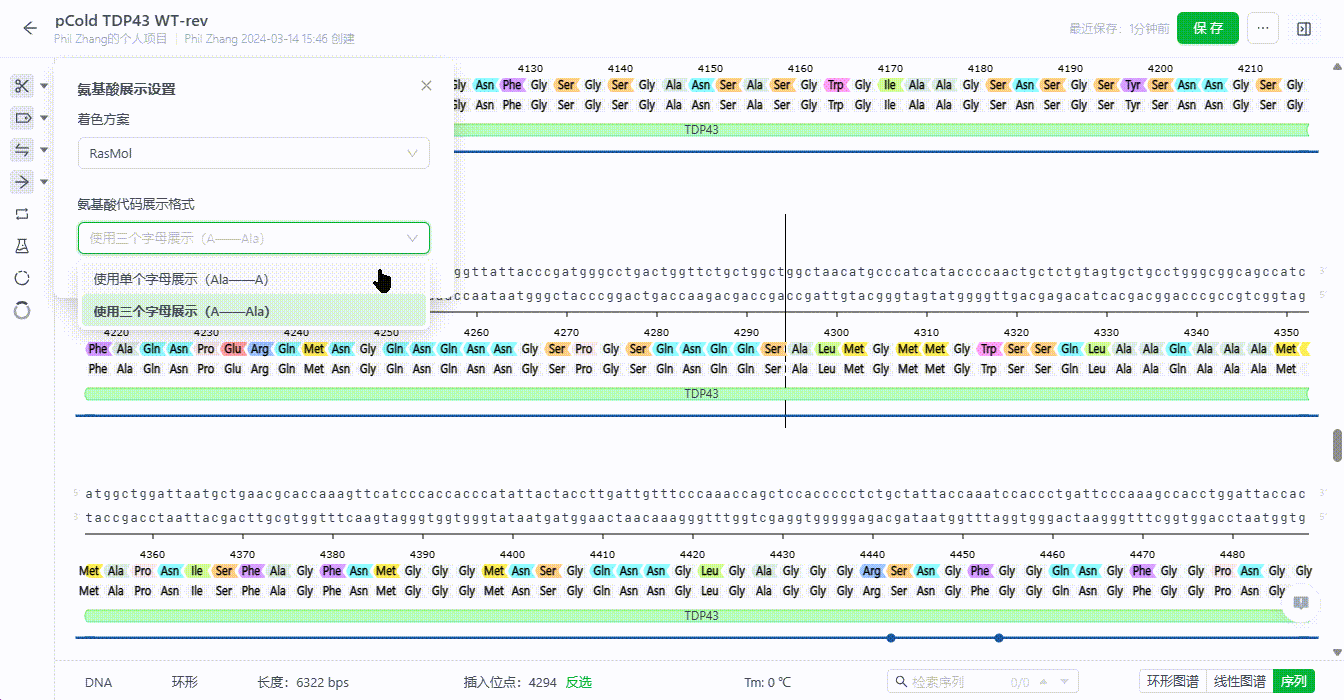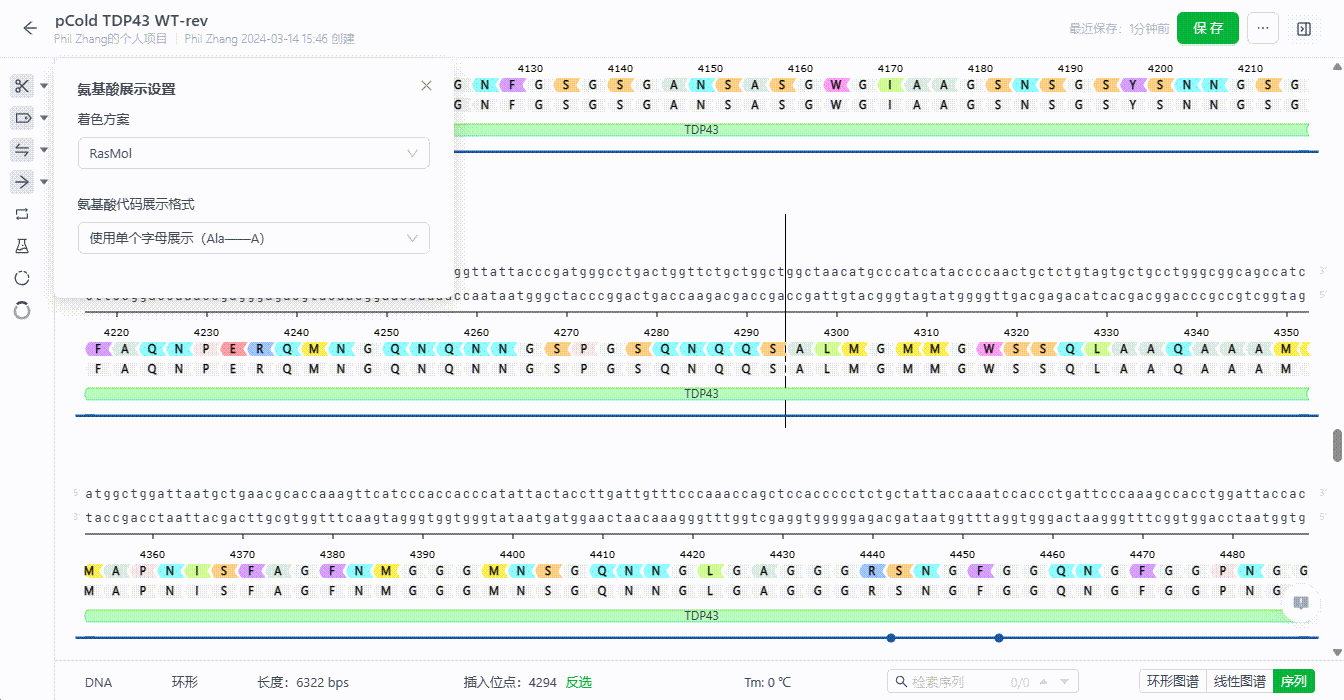
8.4 氨基酸展示设置
支持用户设置特征翻译的字母颜色,调整整个文件的氨基酸字母展示样式。

- 翻译字母改色
系统支持用户将氨基酸字母改为RasMol的着色方案,或者调为无着色。
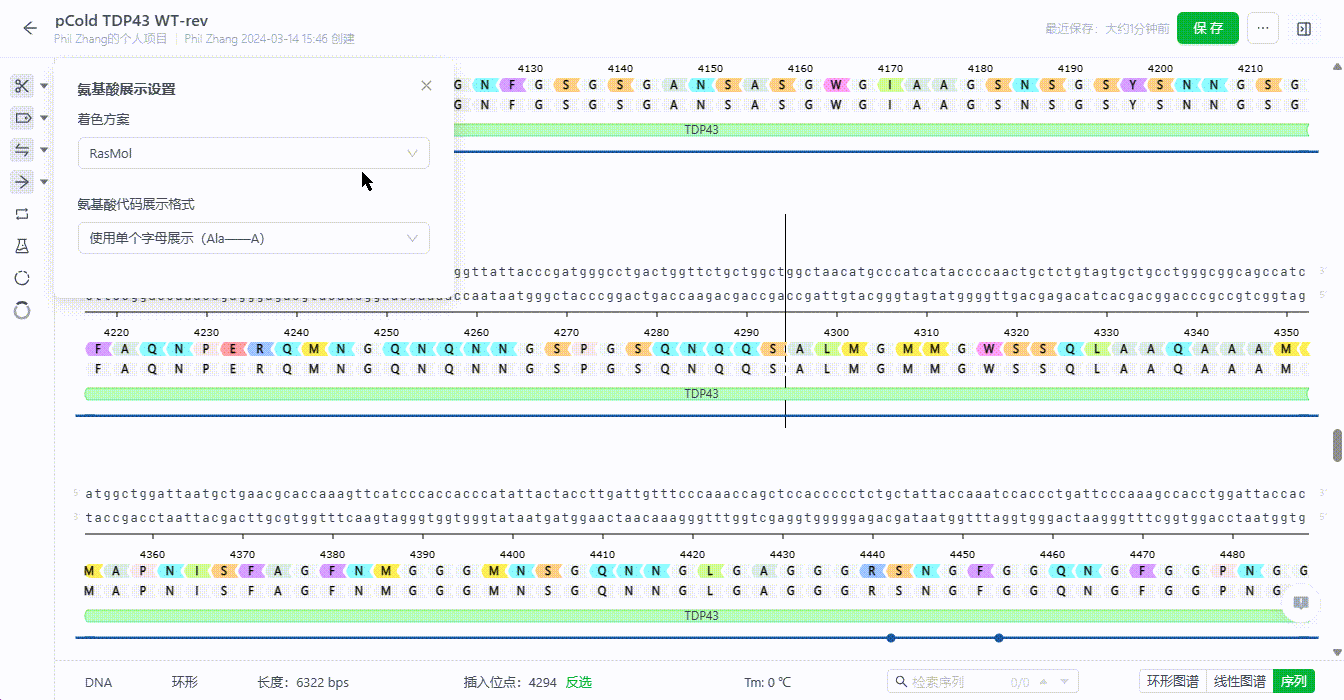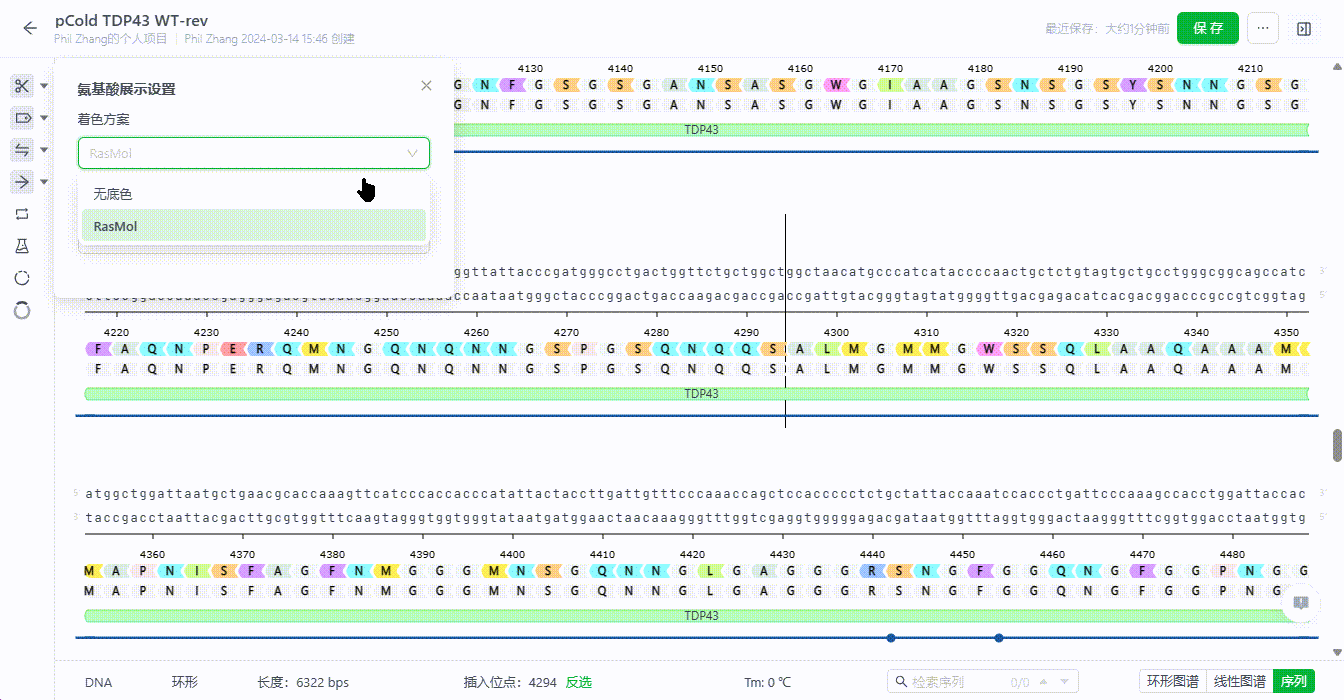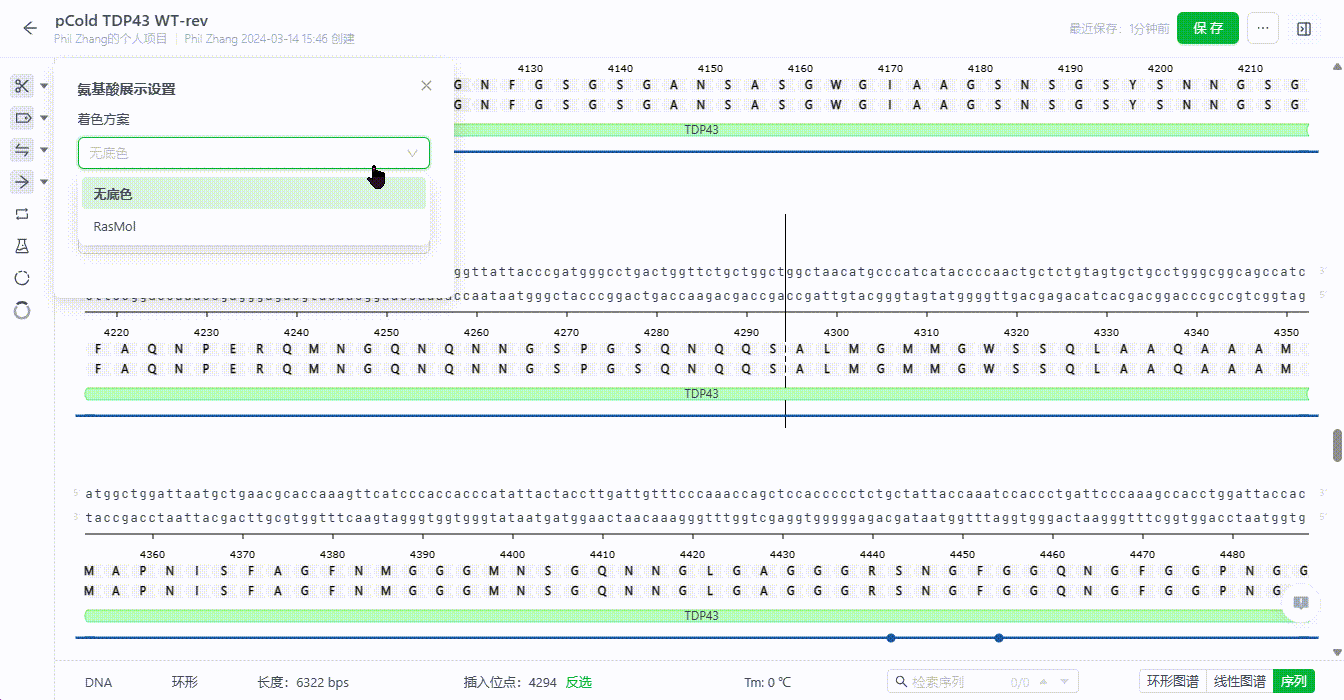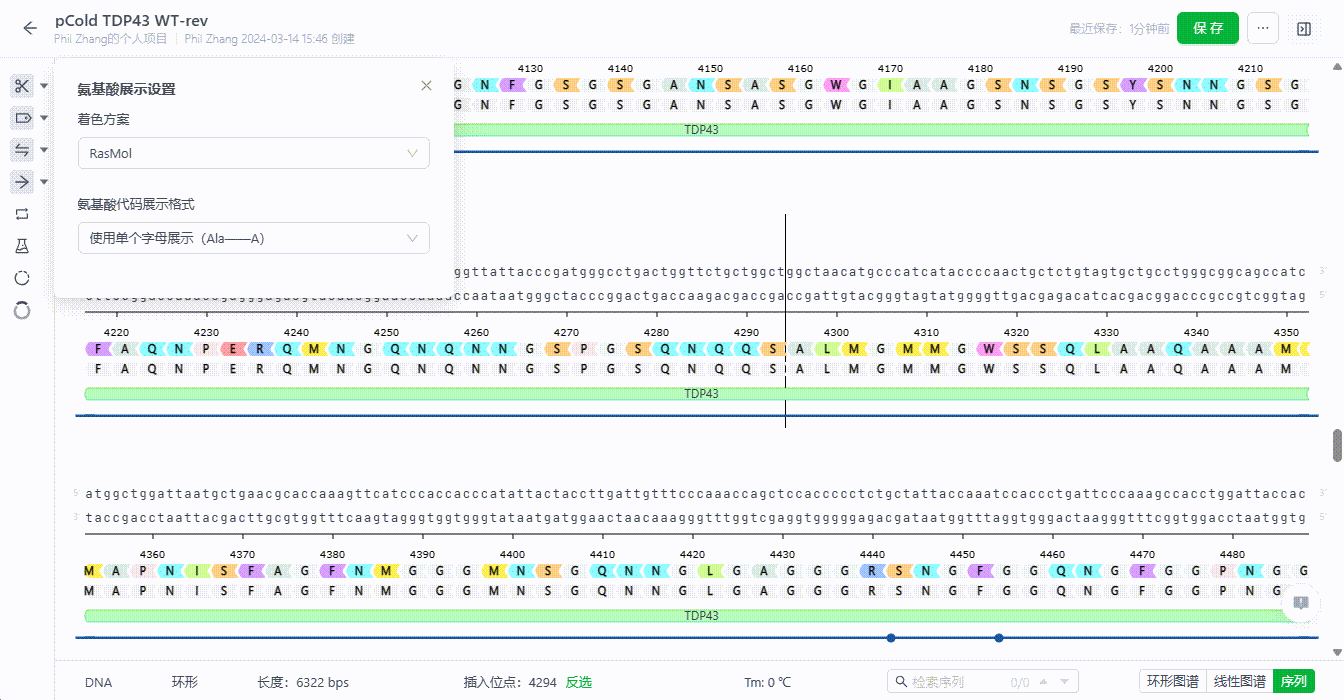
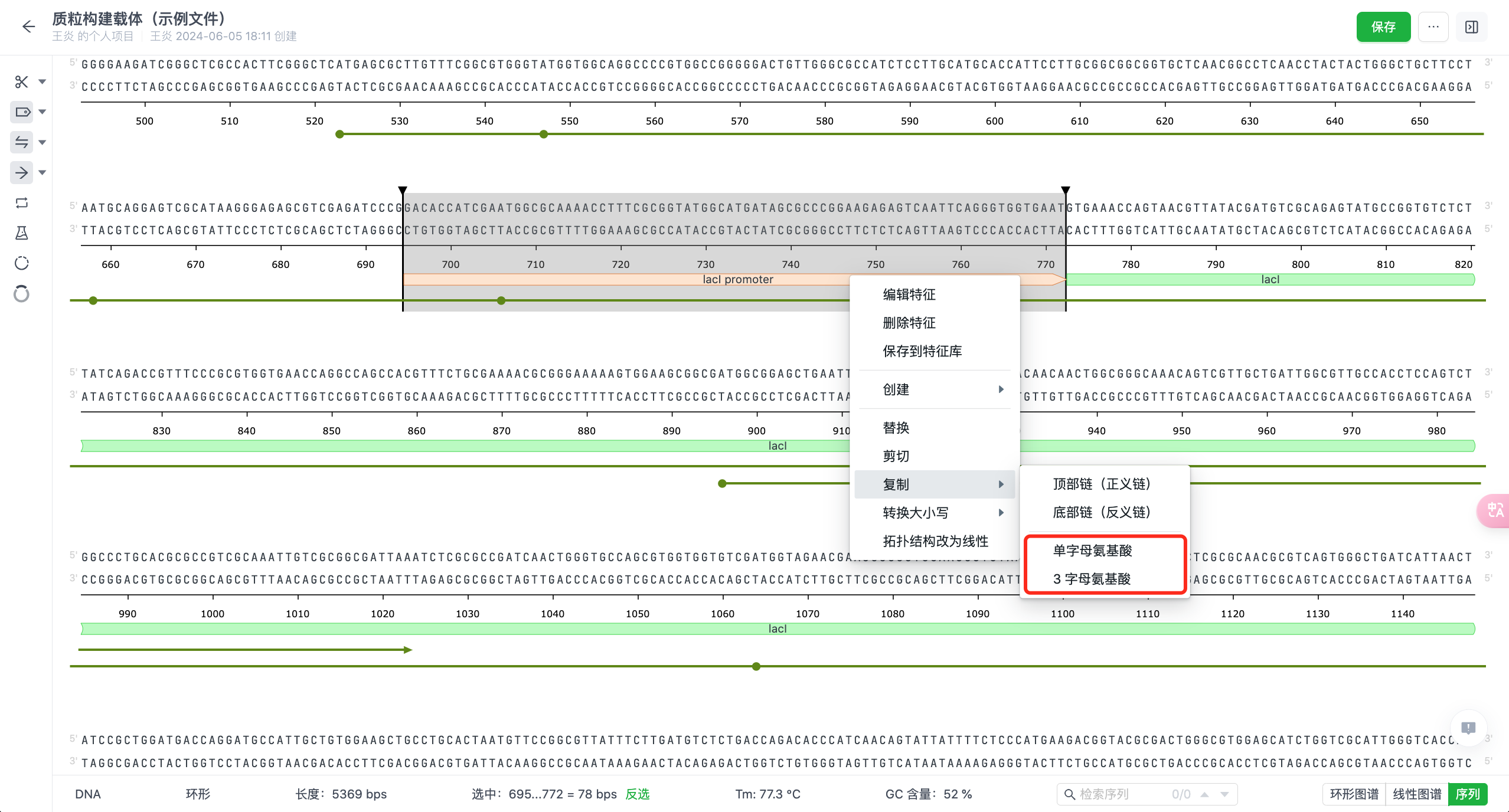
- 氨基酸字母样式调整
系统支持用户切换氨基酸字母的展示样式,可以设置为三个字母或单个字母。
9. 聚合酶链反应PCR操作
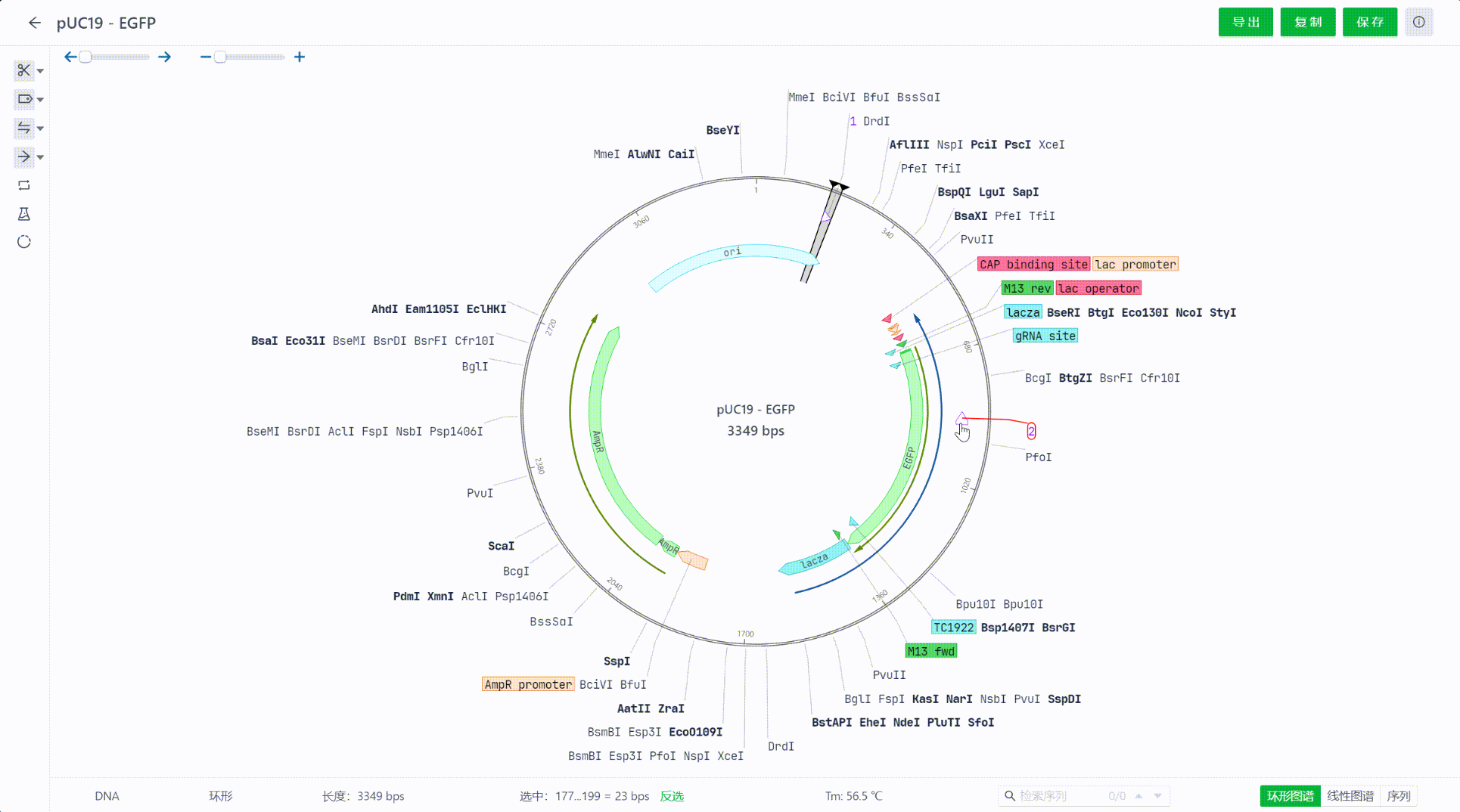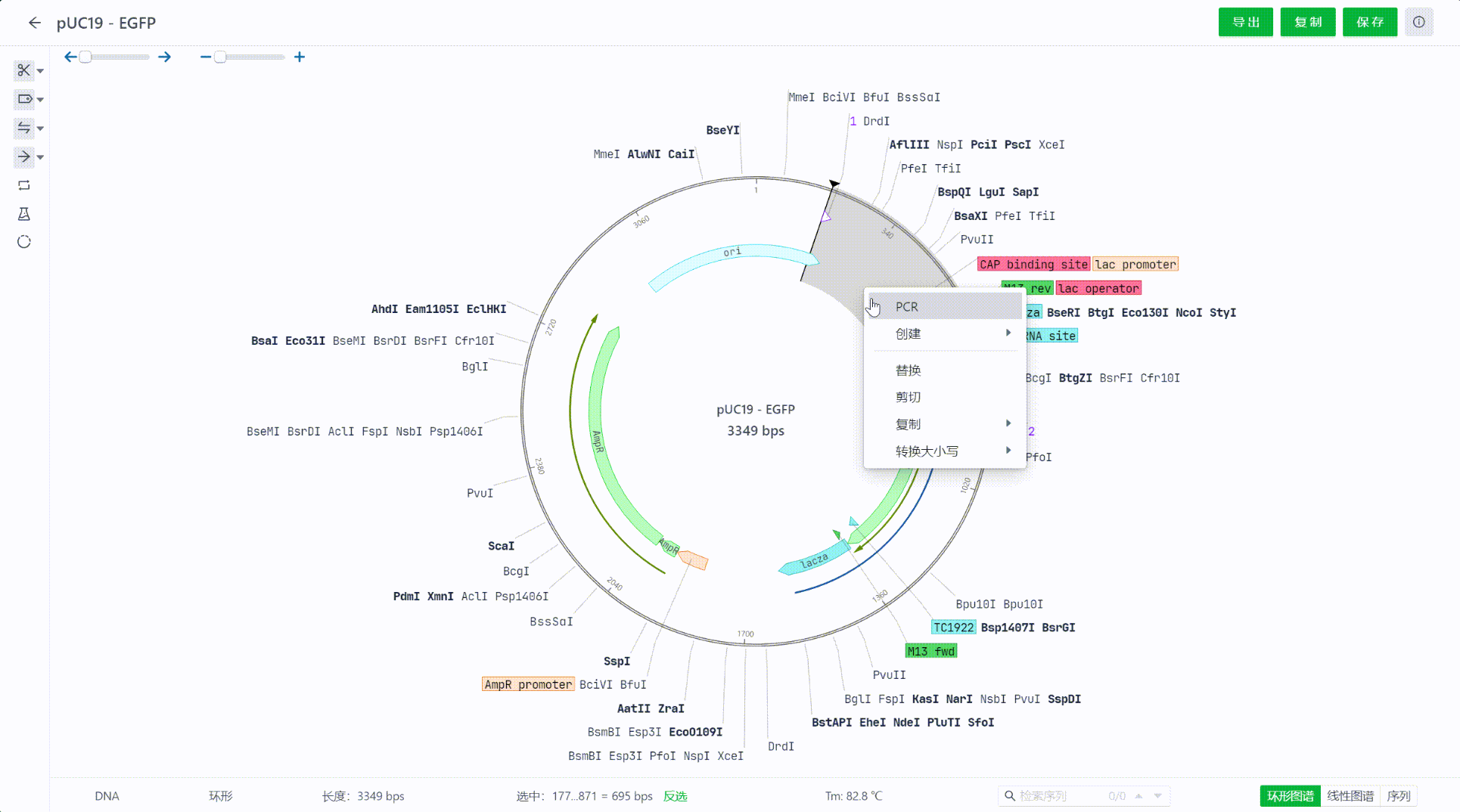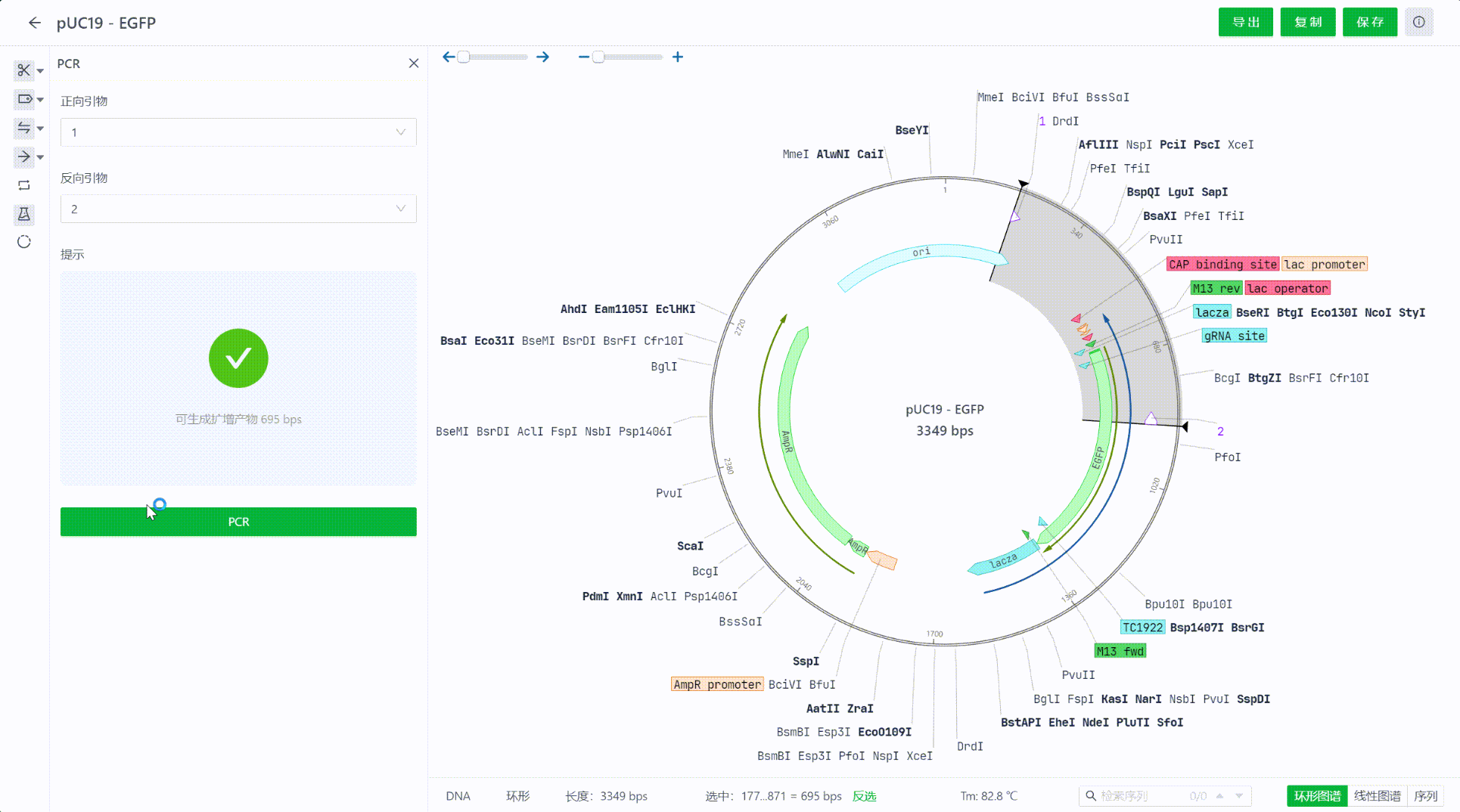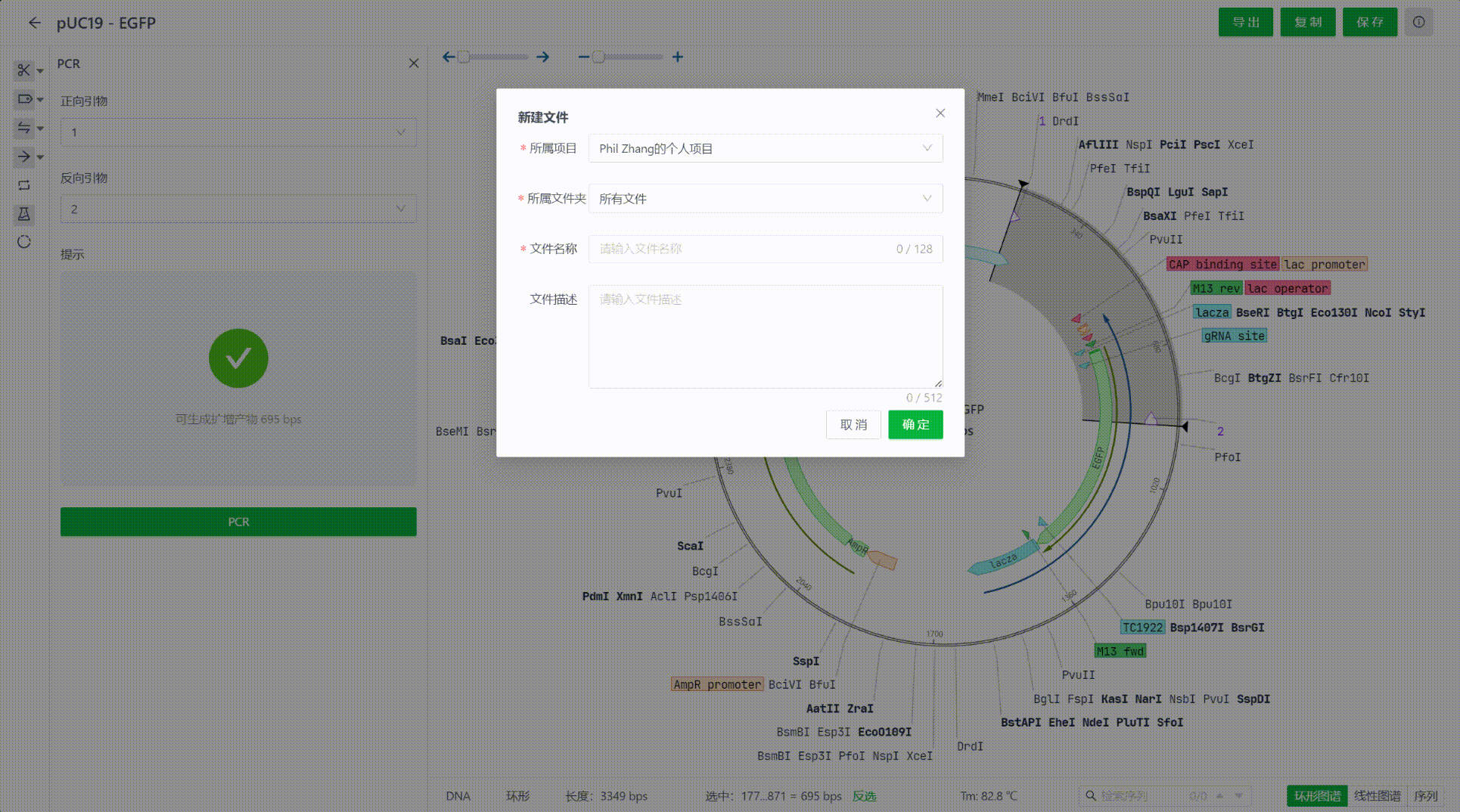
点击PCR,进入PCR扩增工作台,通过PCR引物选择,明确需要扩增的区域,命名扩增后产物的名称后,点击“PCR”即可生成新的PCR序列文件。
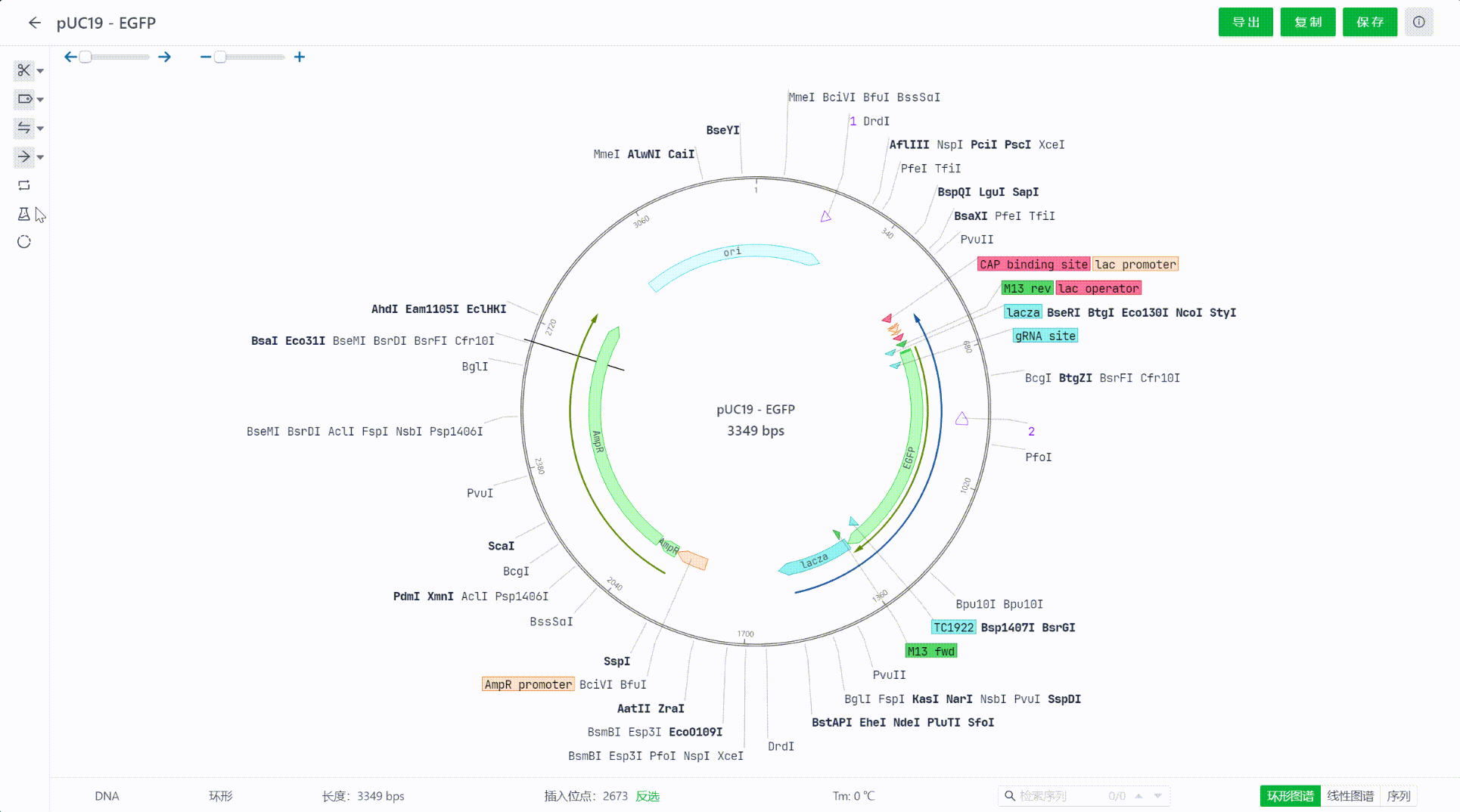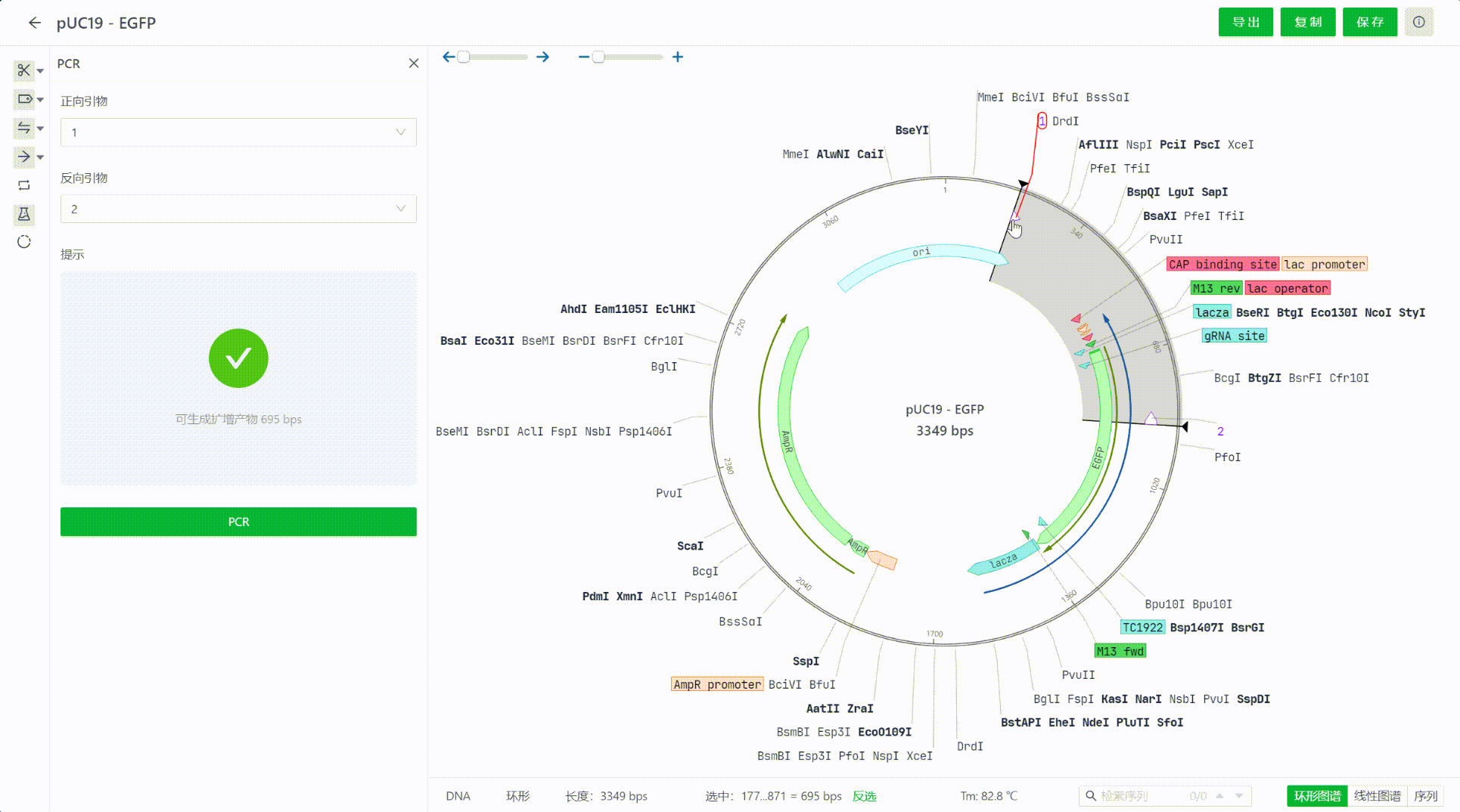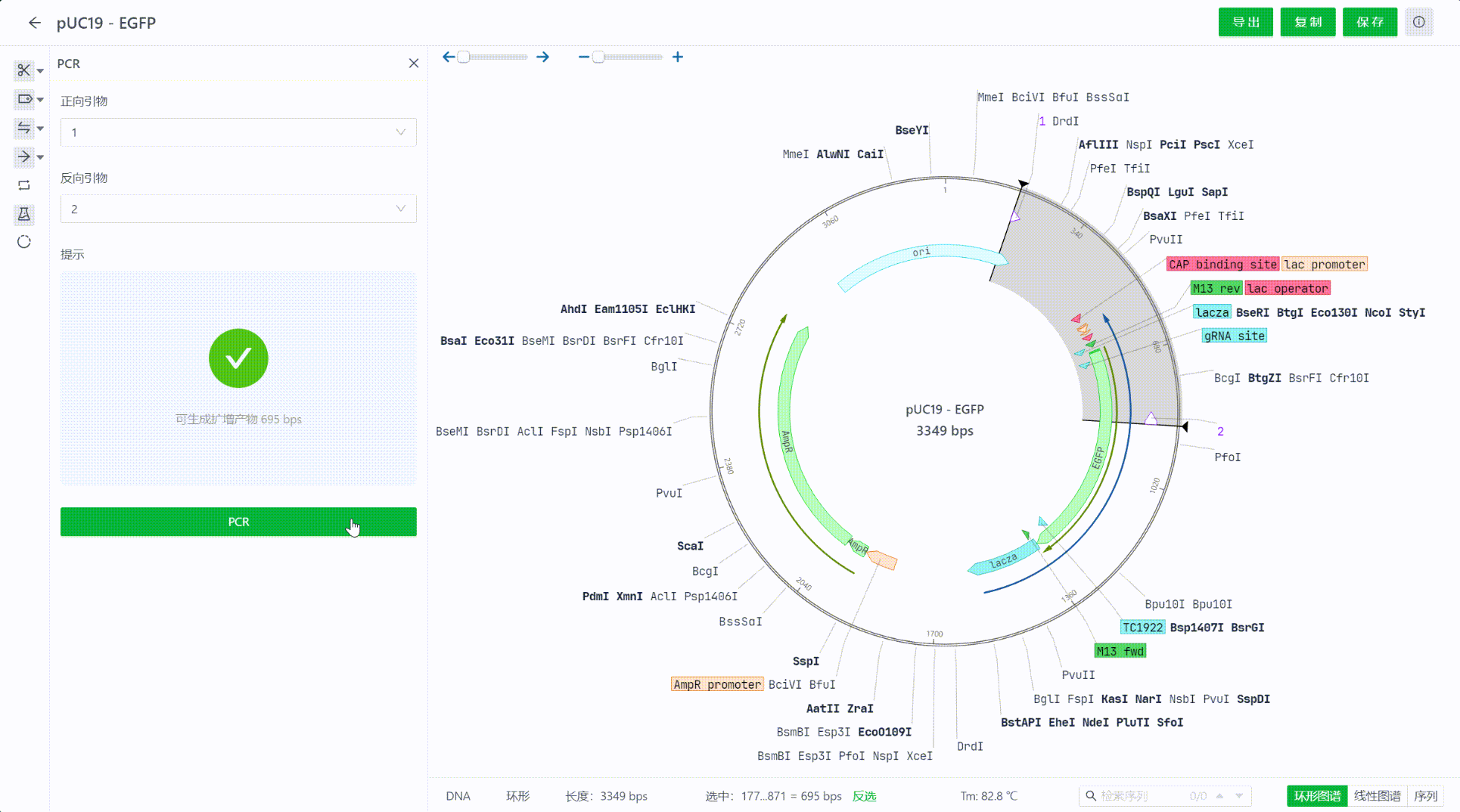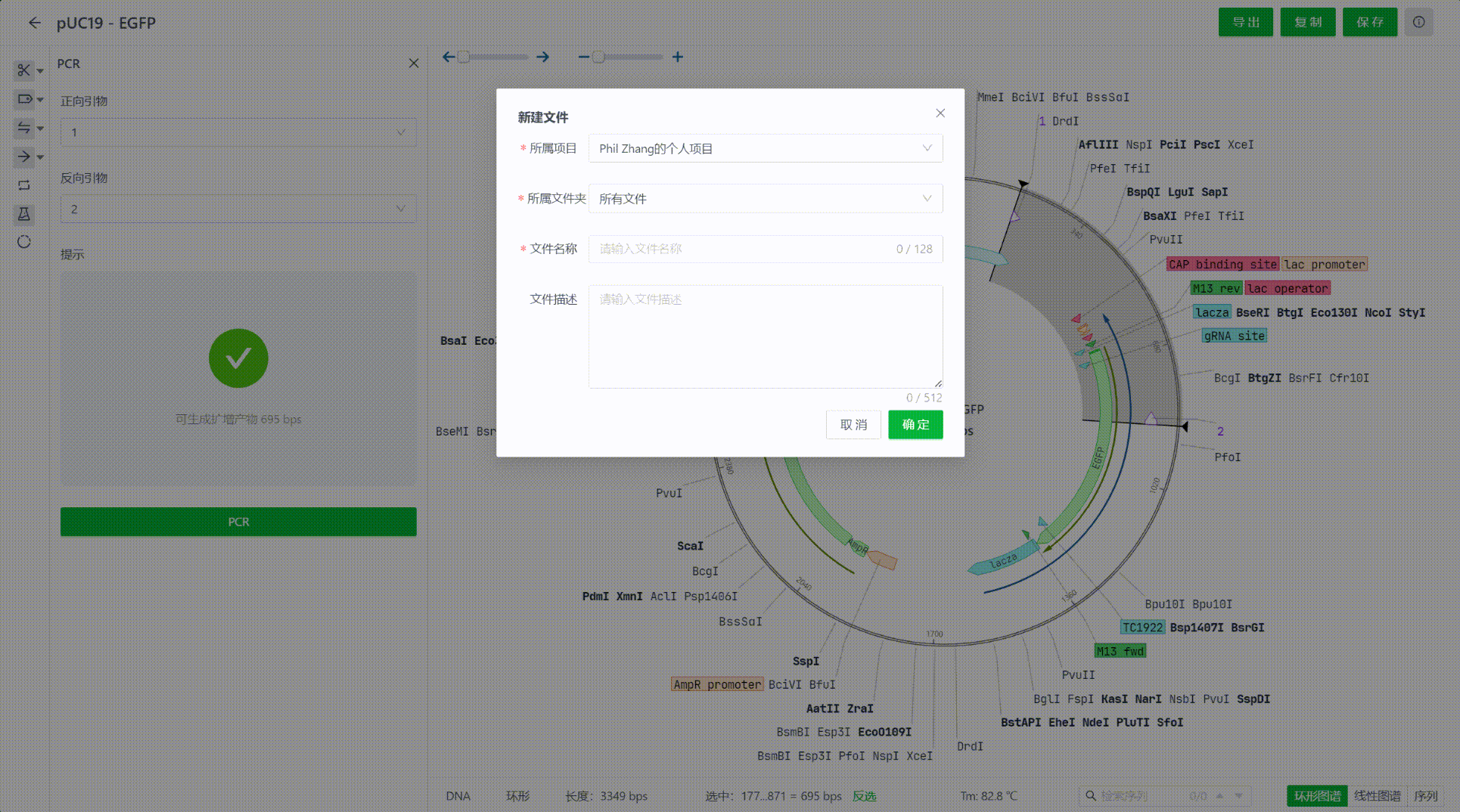
也可以直接选择两个引物,右键后直接进入PCR界面。
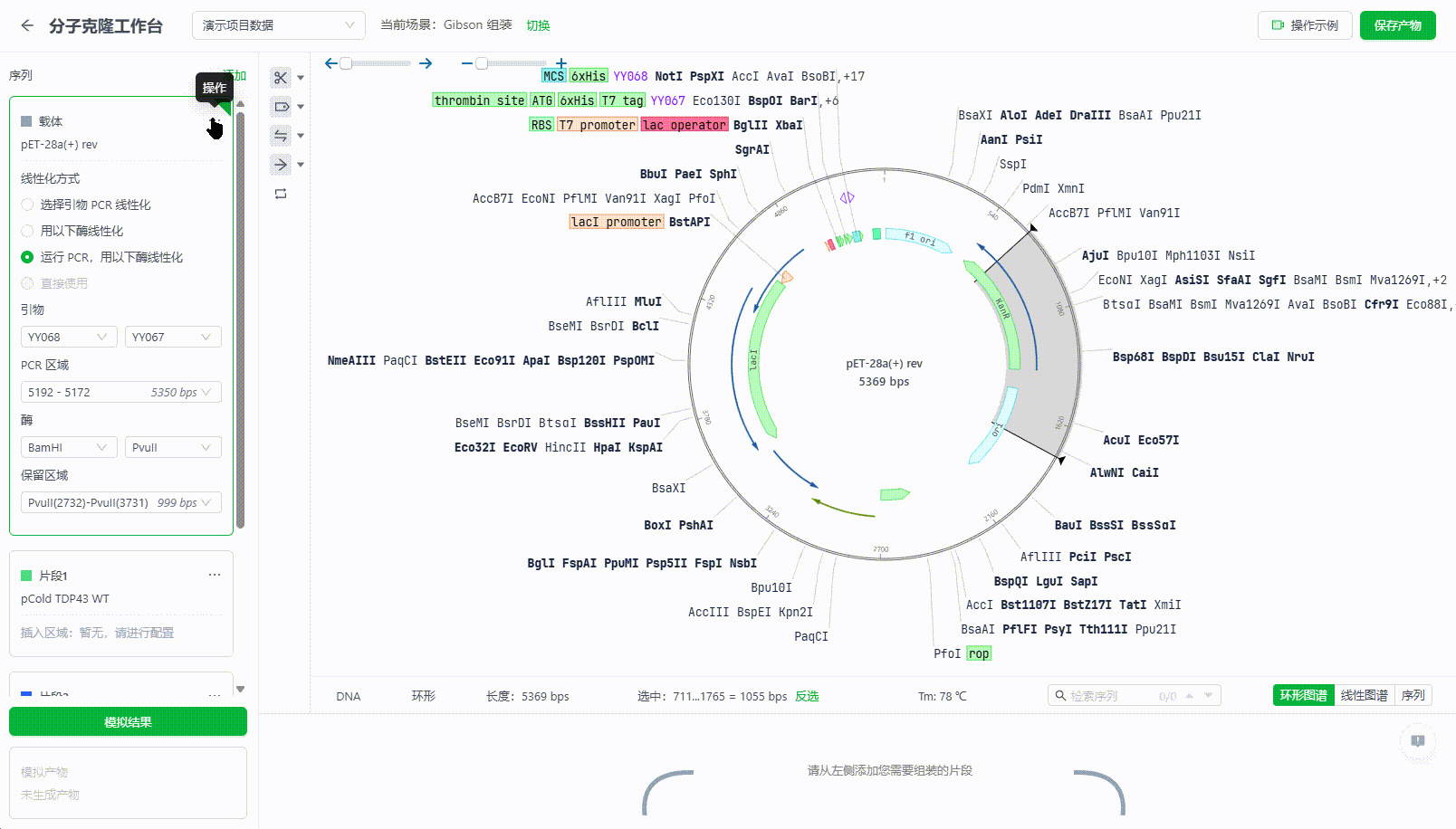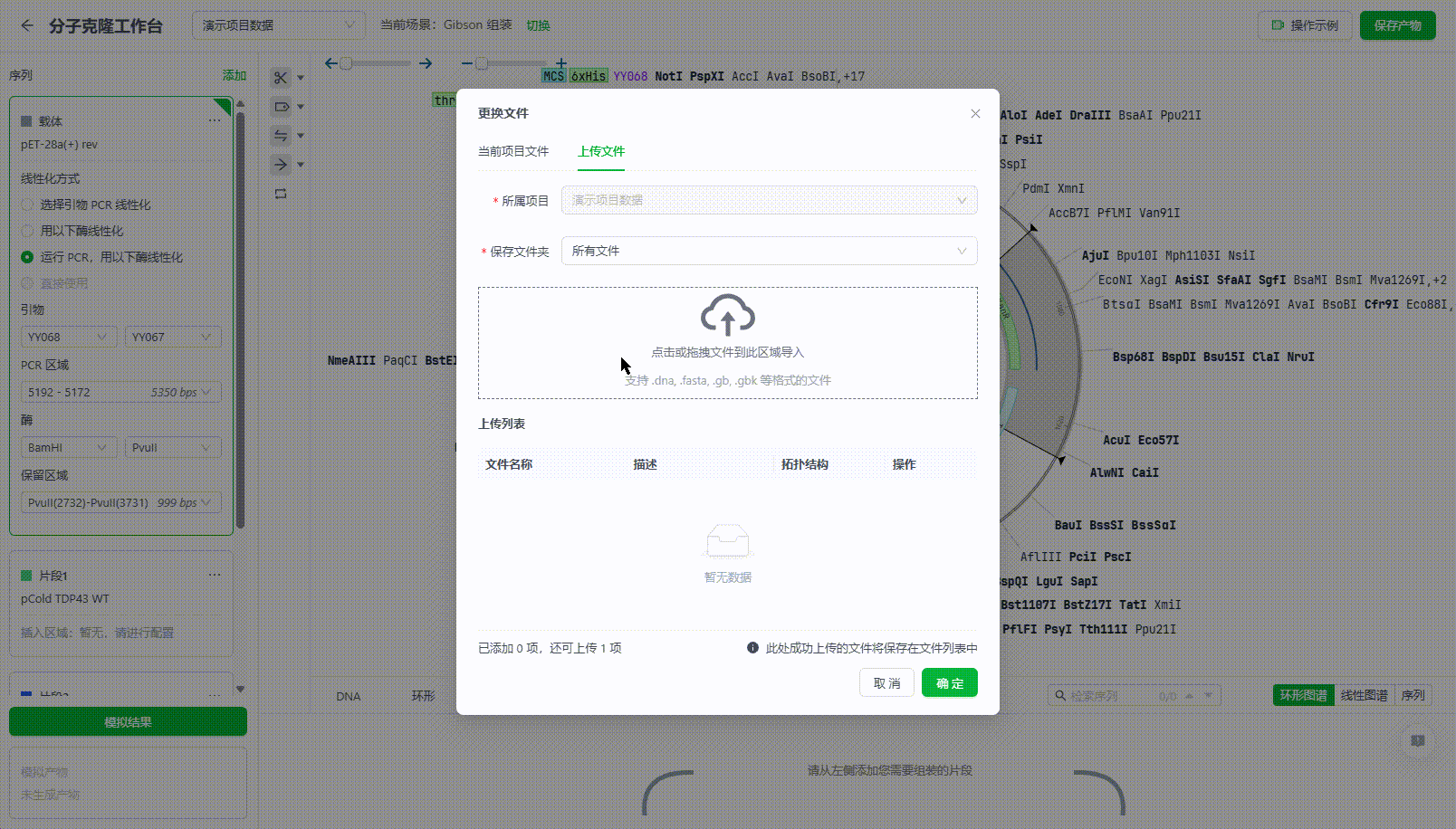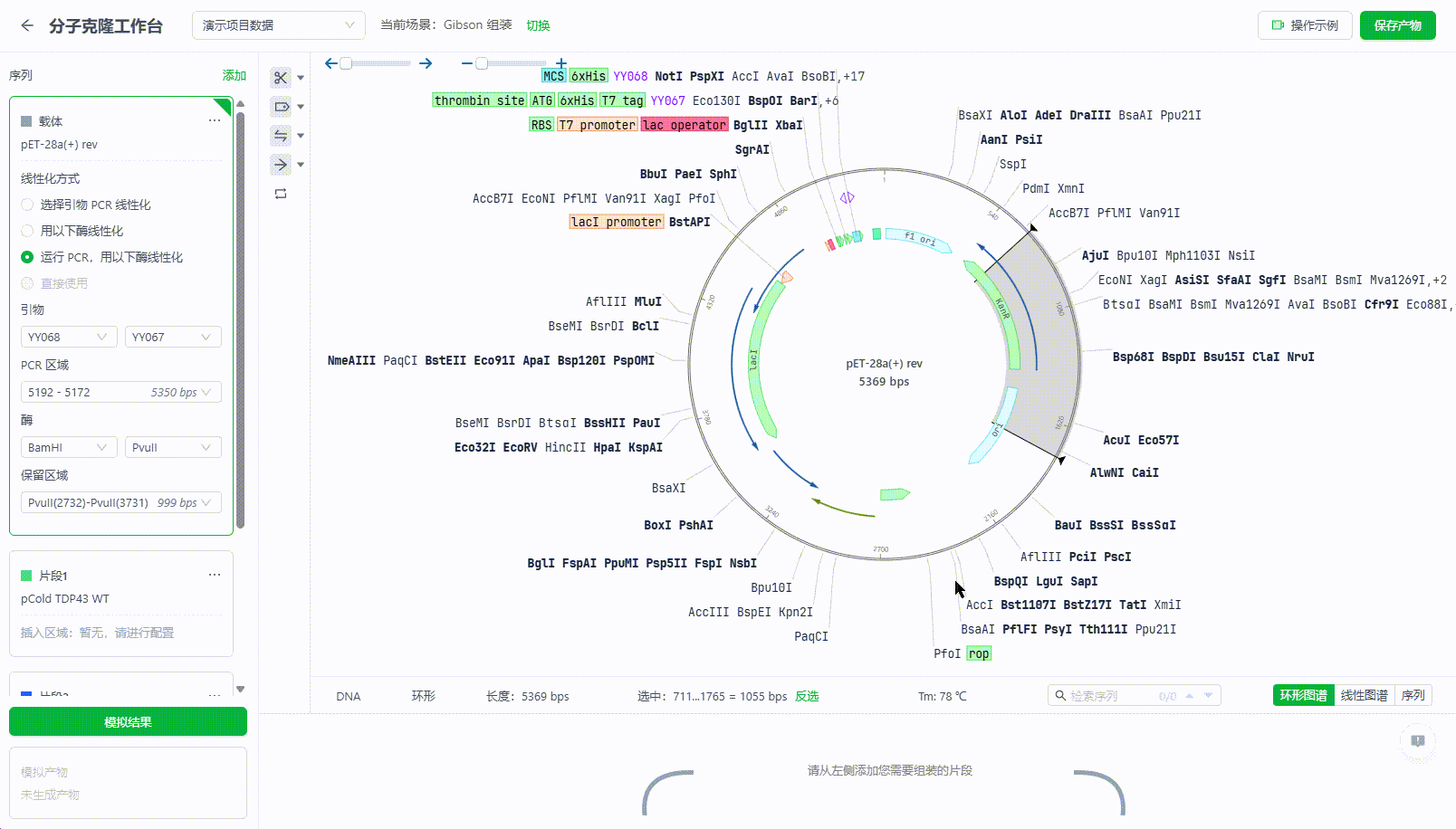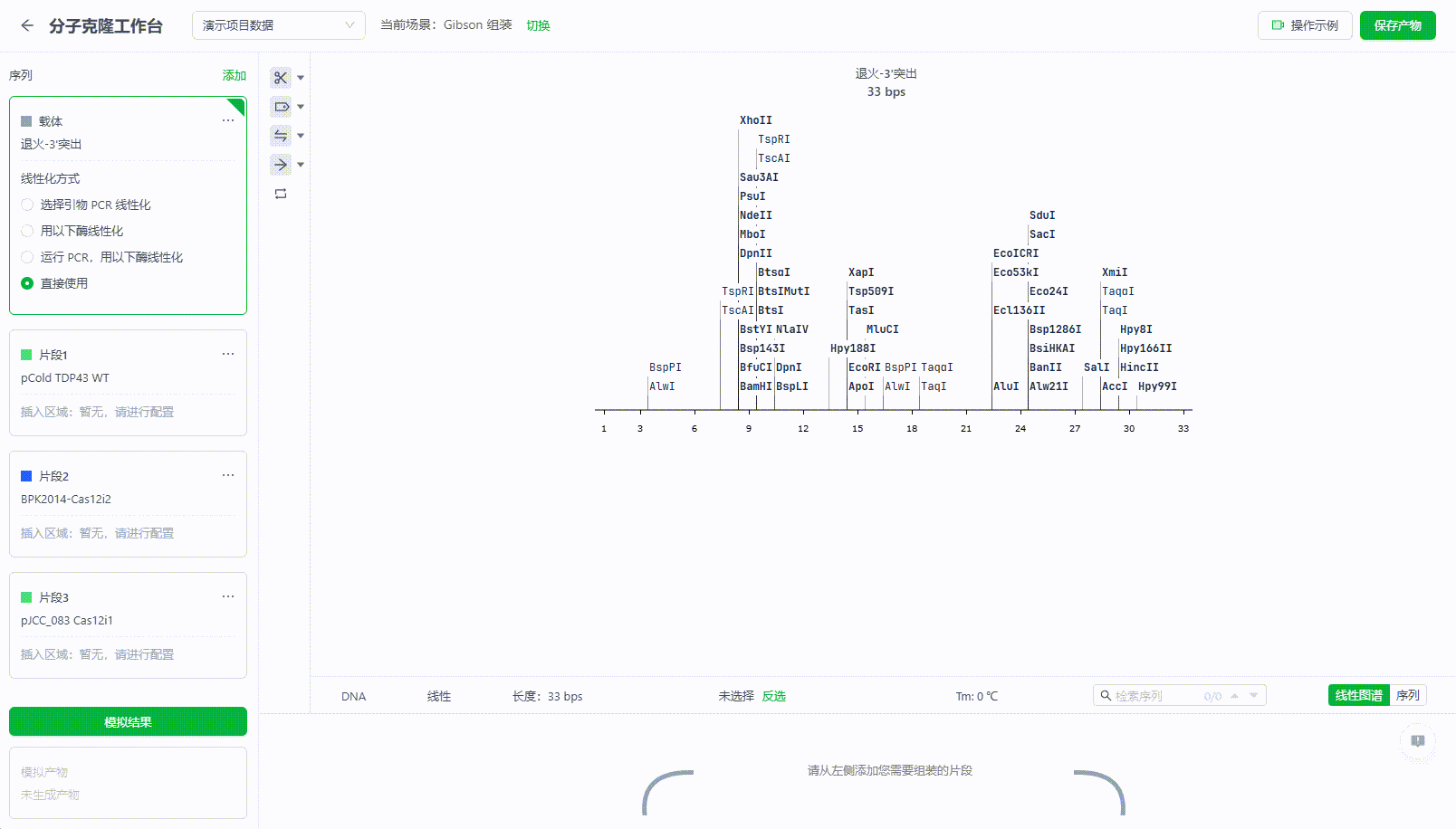
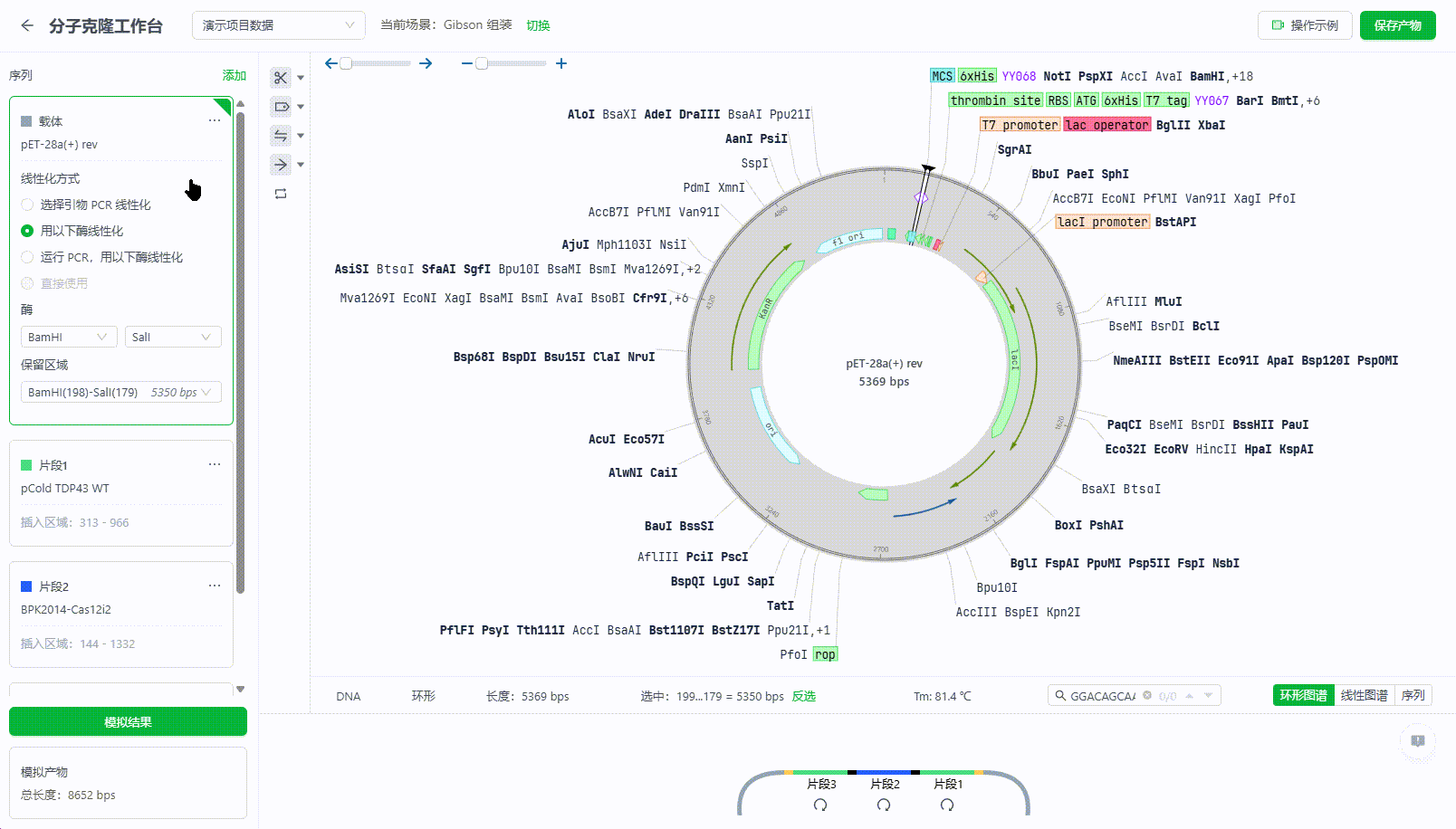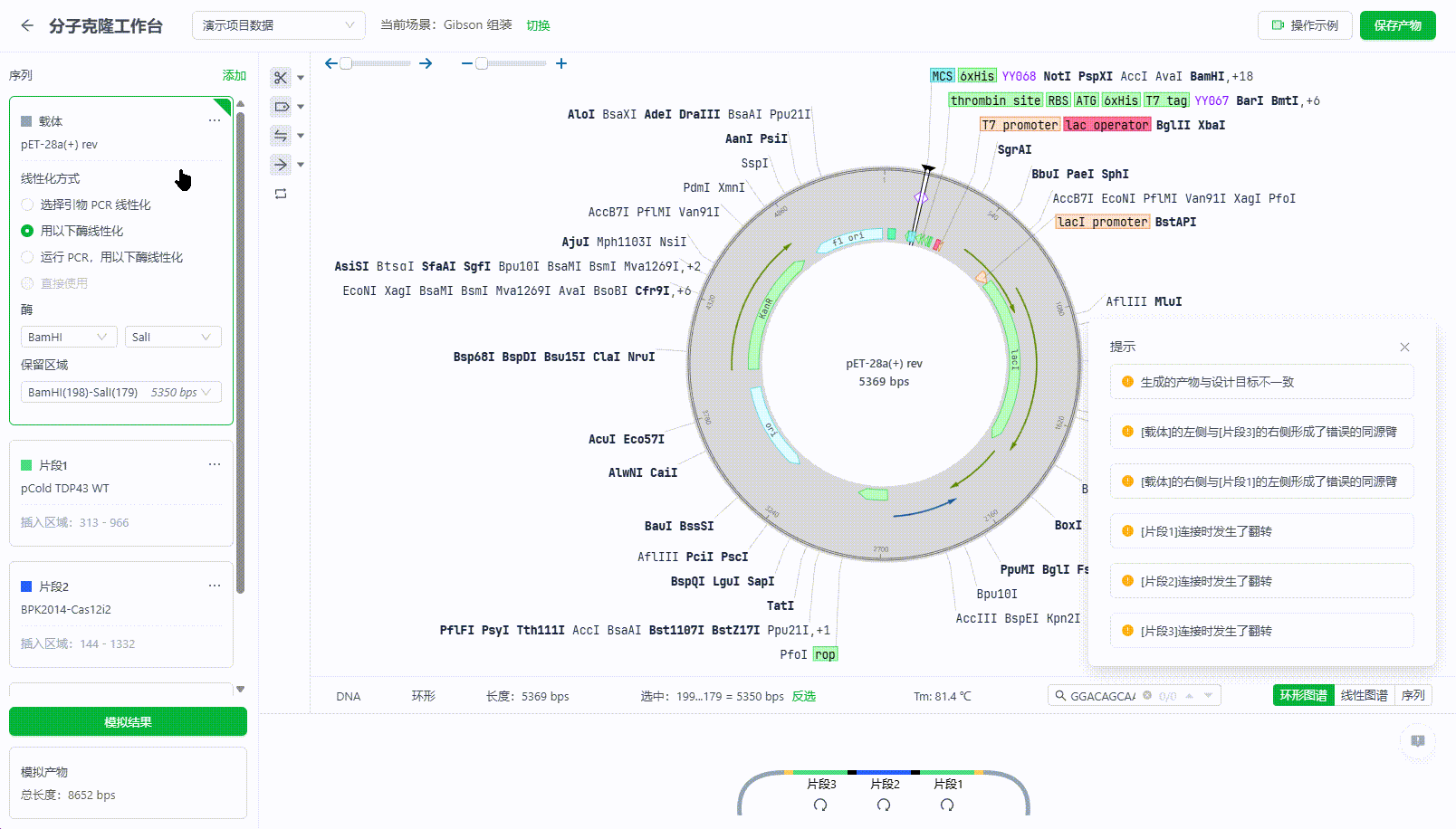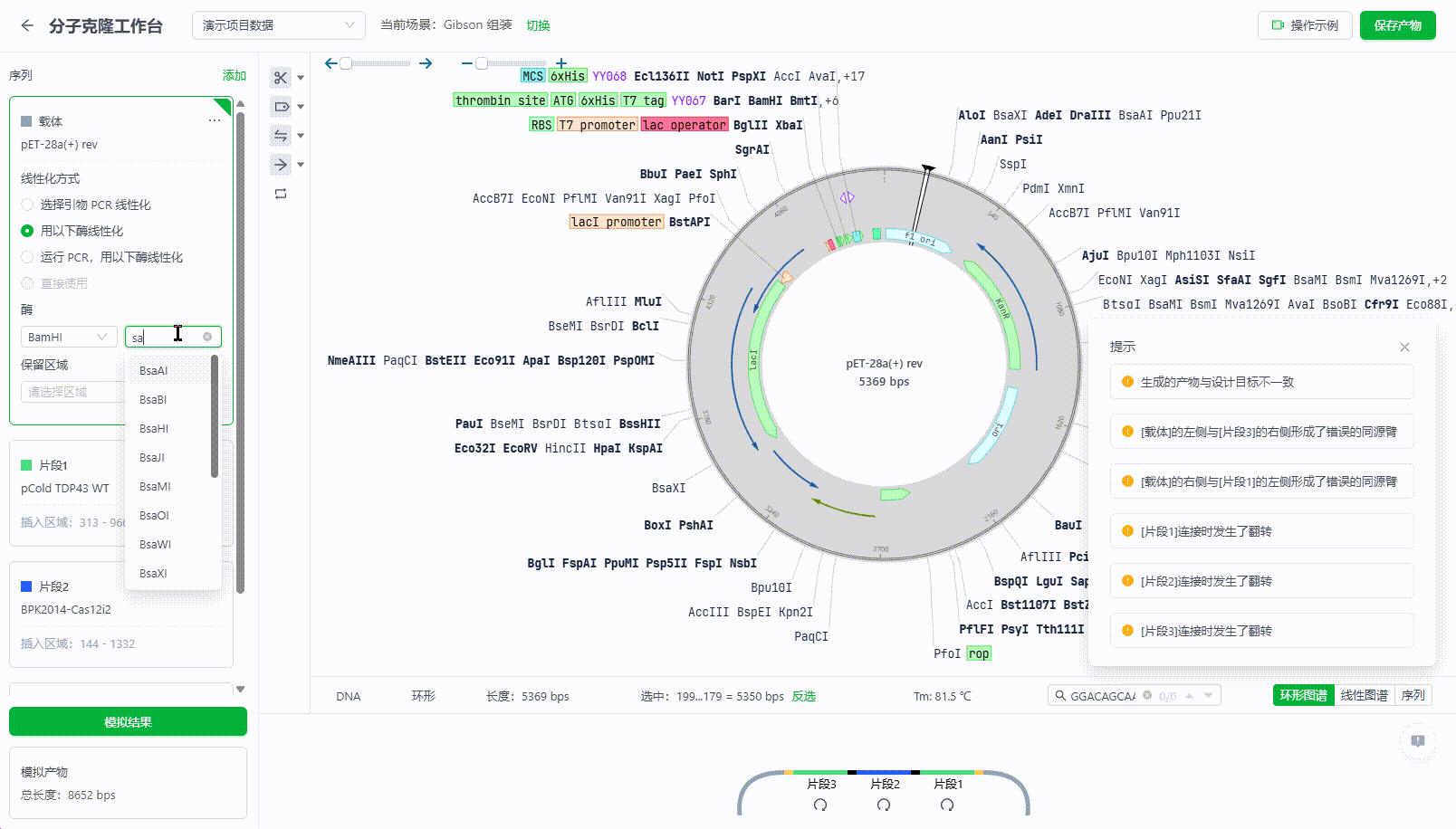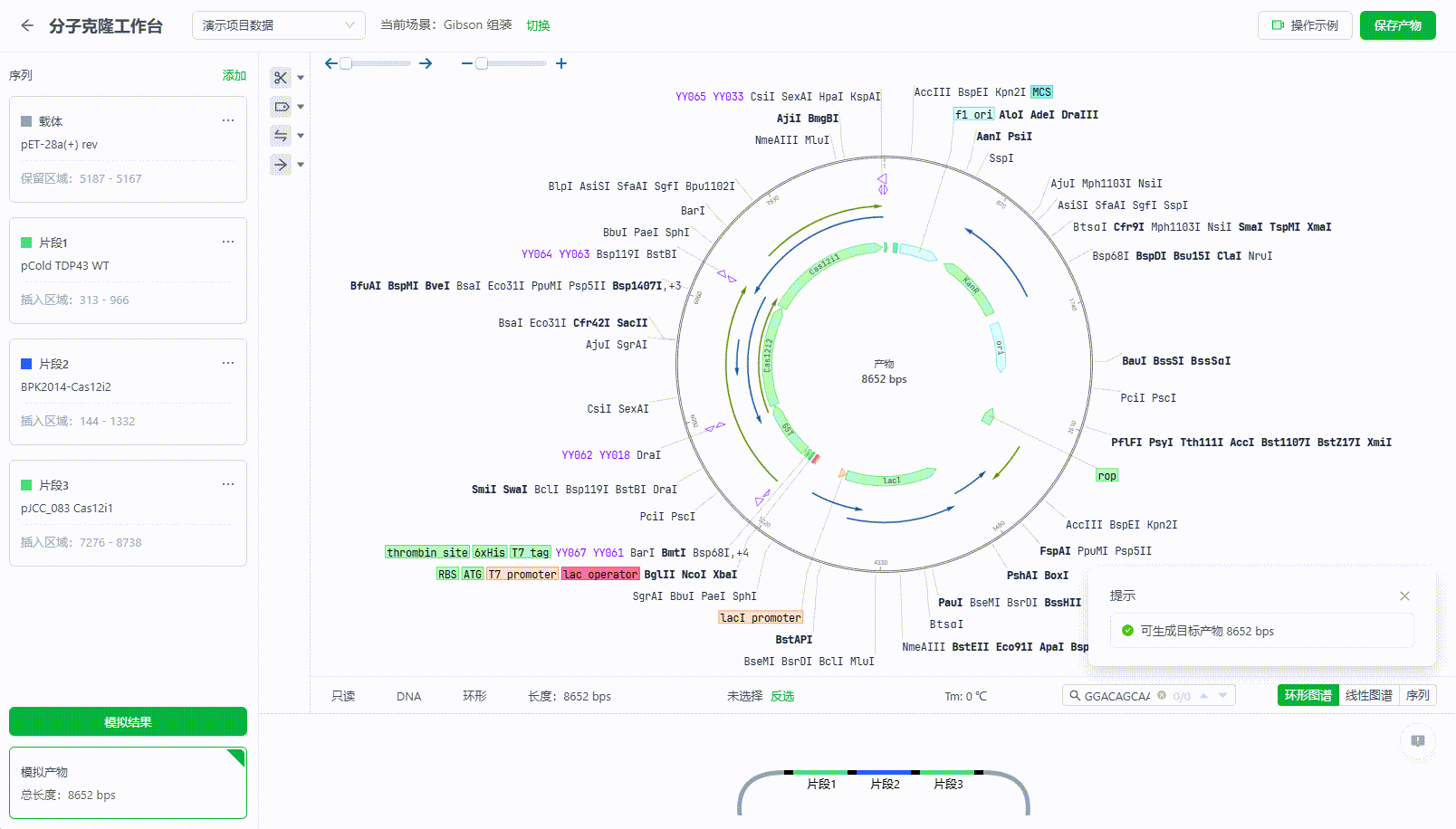
10. 分子克隆工作台
分子克隆工作台,旨在帮助研究员优化质粒设计的过程,提高设计效率,用户可以从工作台进入:
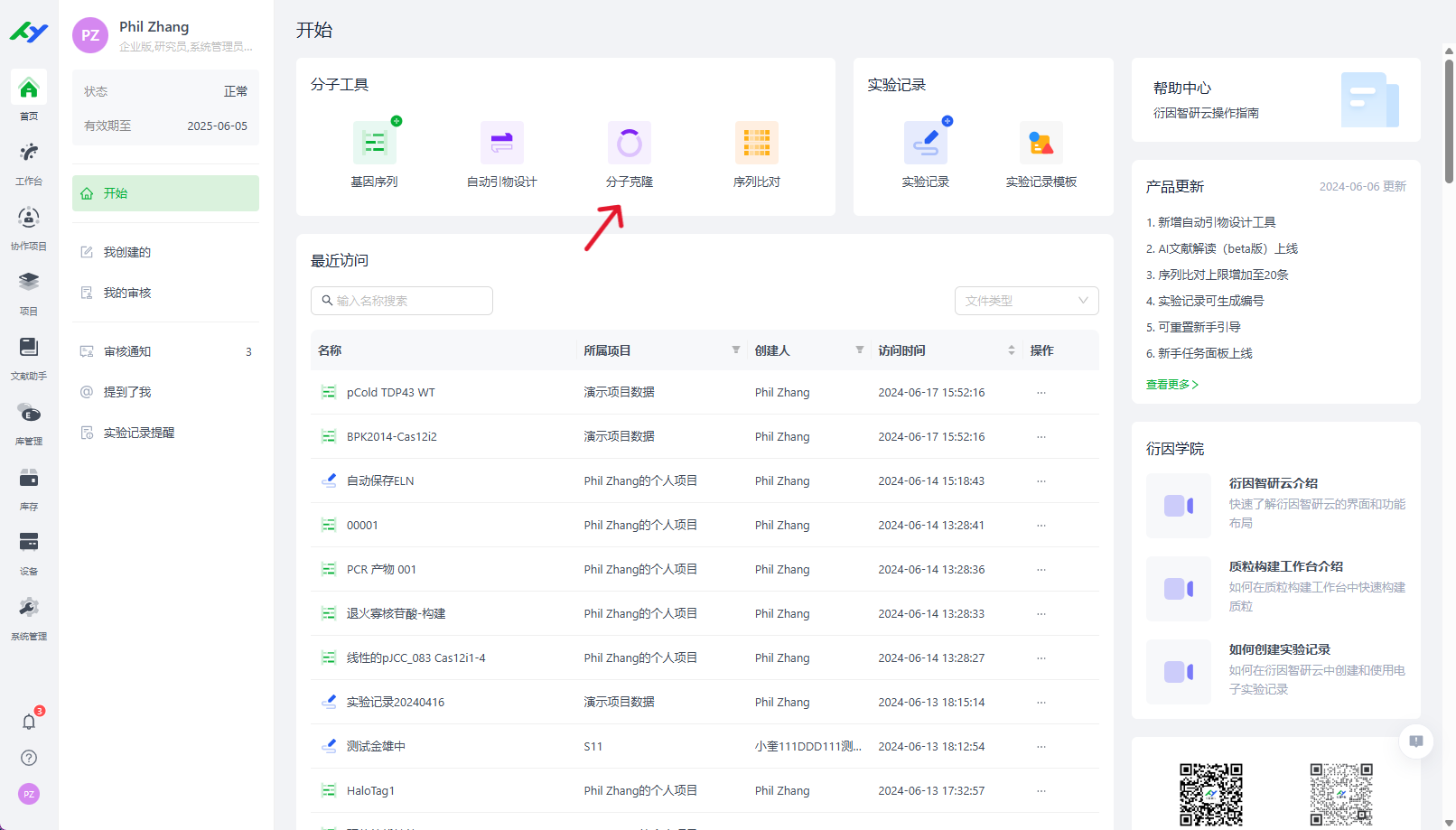
该工作台支持用户使用多种构建方法完成设计,目前包含:限制性酶切与连接、Golden Gate、Gibson 组装、In-Fusion四种方法。
用户需要通过加载载体,明确保留区域,然后再将需要组装的片段添加进工作台,并明确插入区域后即可模拟实验结果。系统会根据构建方法给与模拟结果的预览图及相关错误提示。
10.1. 选择载体、片段的序列文件
载体、片段提供的支持从系统中选择已有文件,也可将本地文件上传,上传的文件将会自动保存到文件列表中。
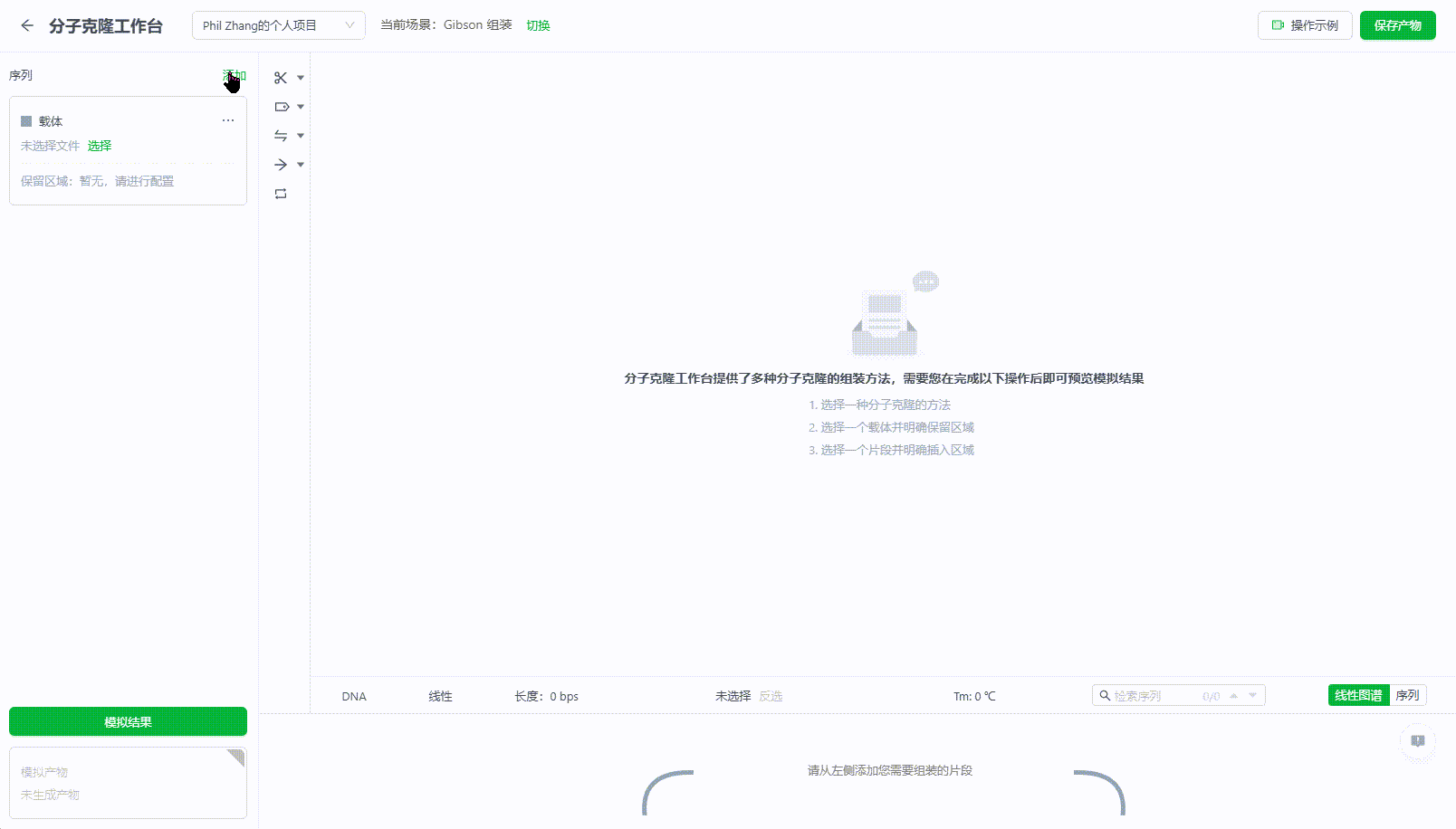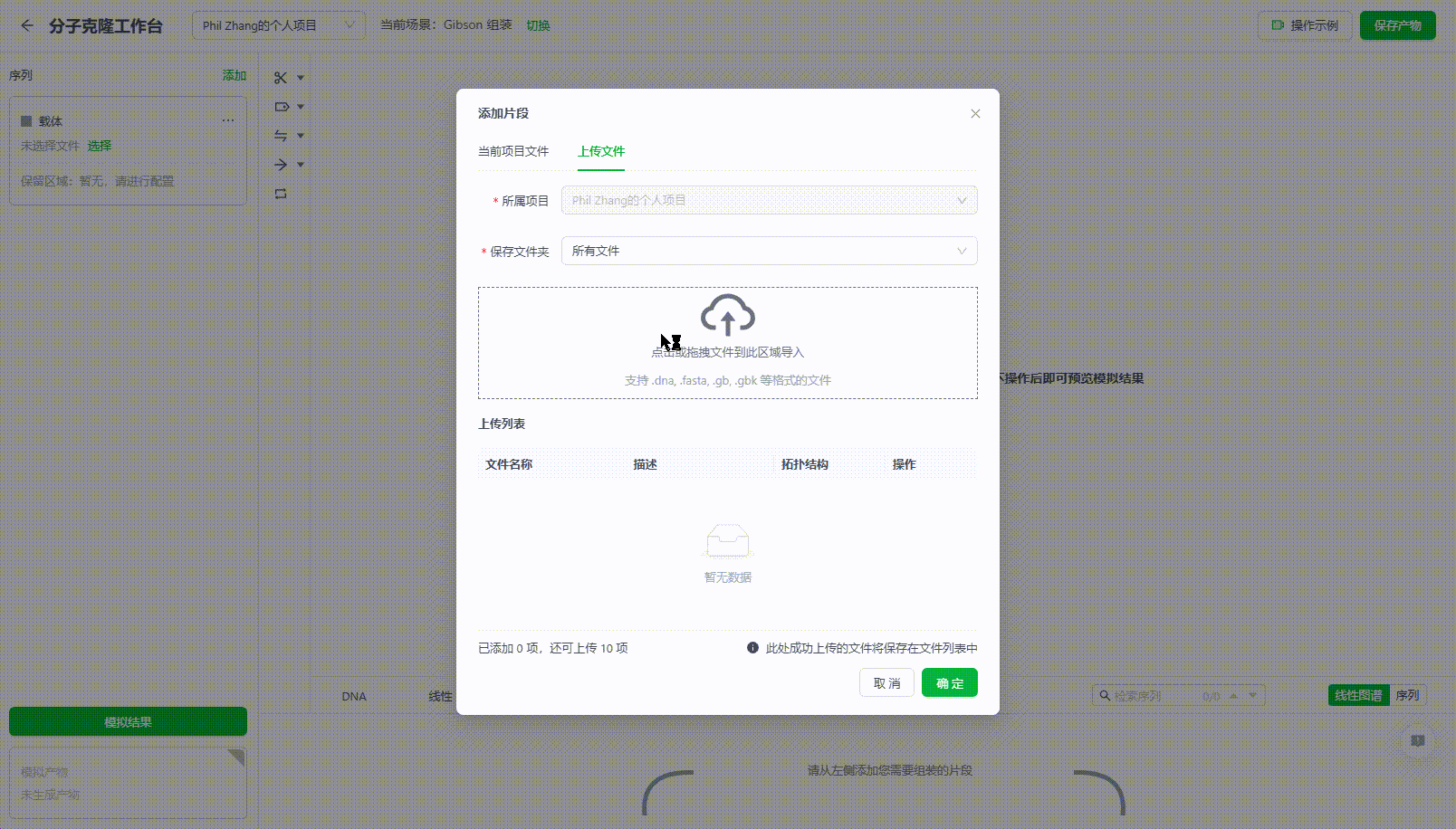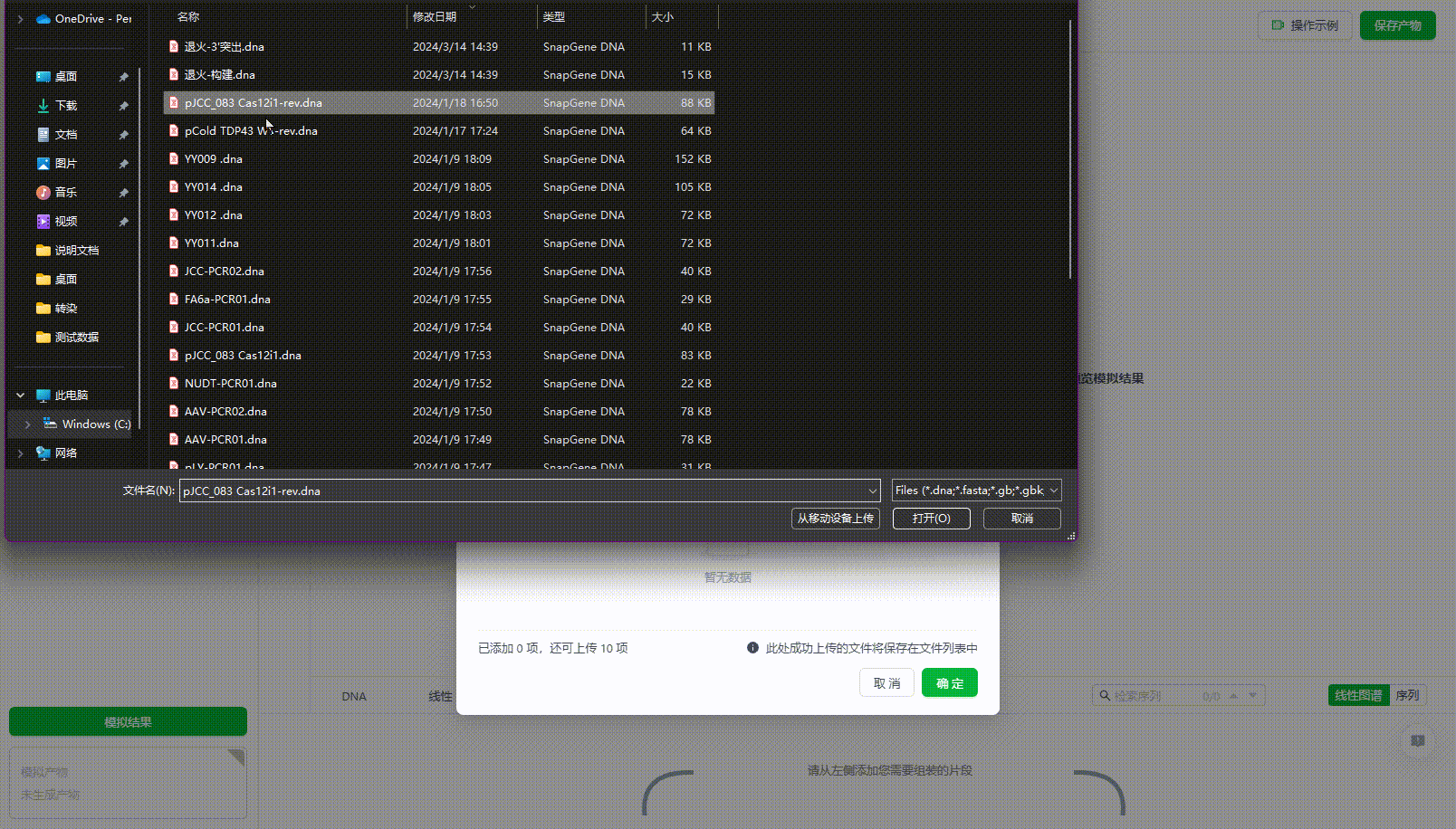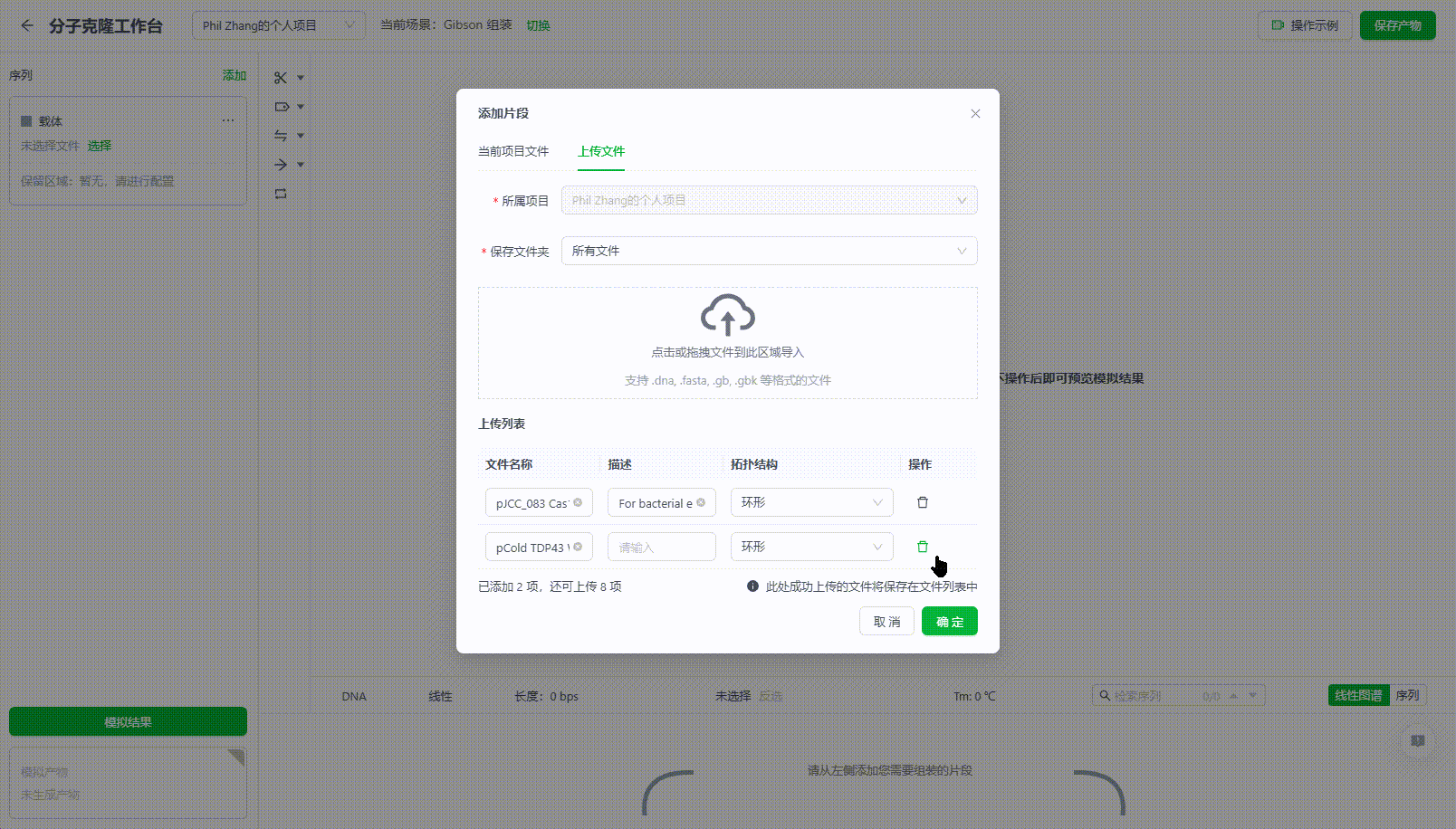
如果选择系统中的文件时,可以直接勾选以下选项创建副本,以防后续保存当前操作和产物时,意外覆盖当前不想修改的原文件。这些副本会自动保存到文件列表中。
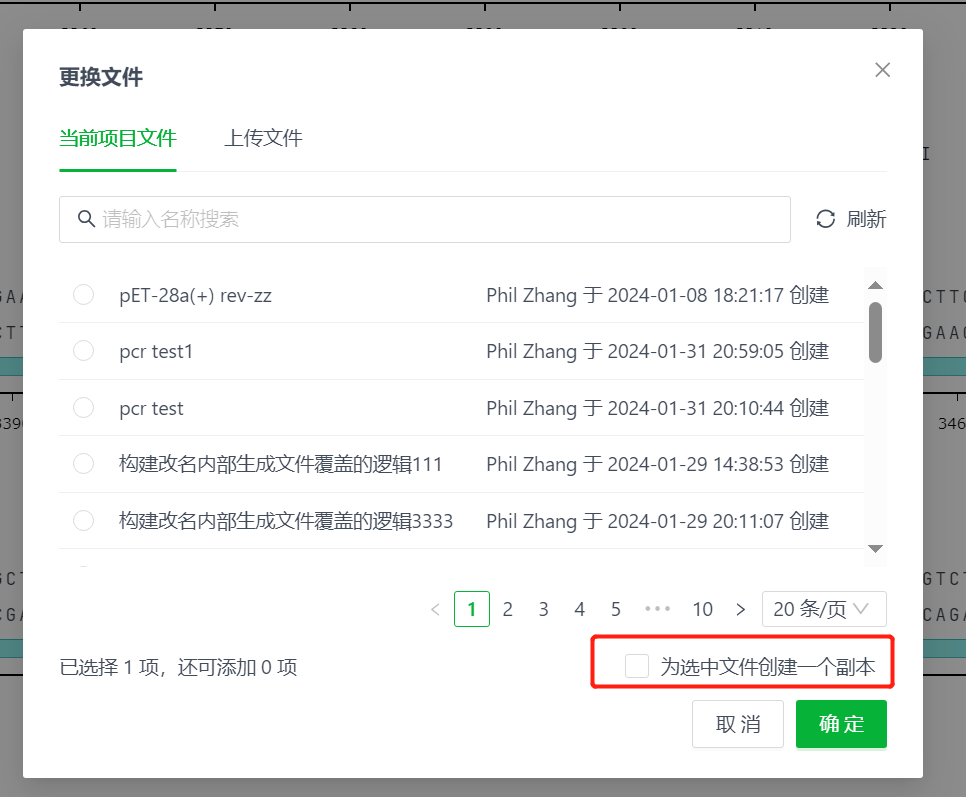
10.2. 选择文件的线性化方式,并明确载体的保留区域和片段文件的插入区域。
目前提供四项线性化方式:
选择引物PCR线性化:需要选中两个引物,并明确保留区域。

用以下酶线性化,需要选中两个酶来明确保留区域,支持使用单个酶消化。

运行PCR,然后用以下酶消化:需要选中两个引物,并从引物中定位两个酶来明确保留区域。

直接使用:使用整段序列线性化。仅线性文件可选。环形此选项禁用。
10.3. 预览模拟结果
系统将根据用户提供的载体和片段模拟实验结果,并给予调整建议。

10.3. 模拟结果预览图及提示说明
10.3.1. 预览图说明
若系统计算后当前提供的片段能够与载体形成产物时,将会形成产物的预览图大致如下:
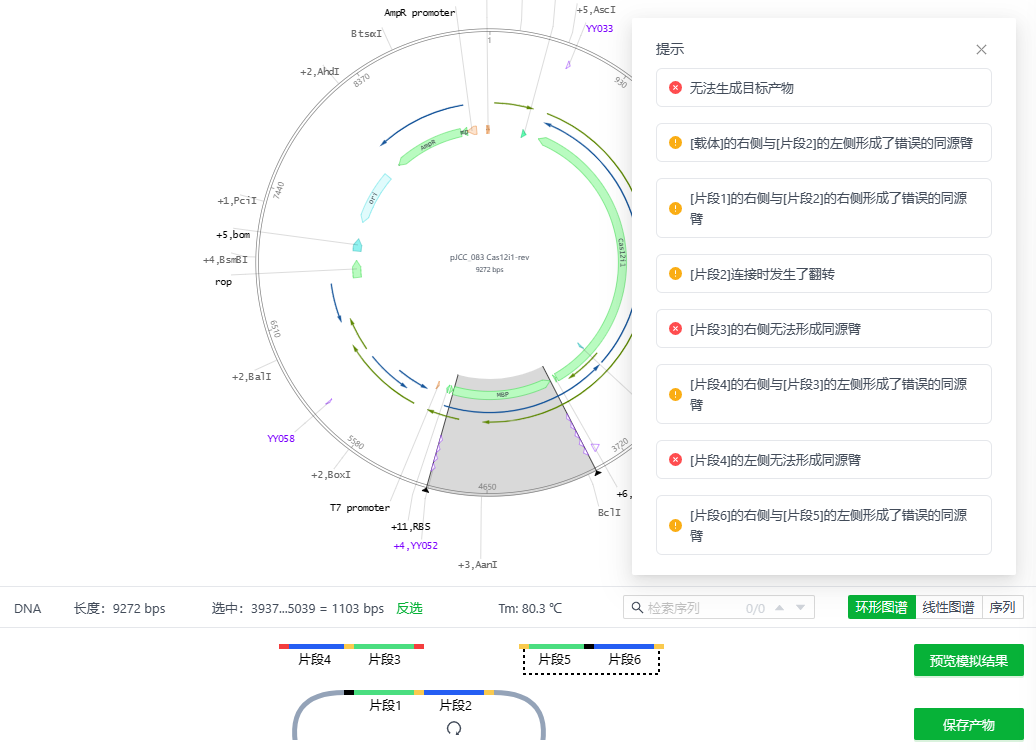
预览图将会根据端点的连接情况按颜色展示,上图中: 灰色:载体保留的区域 蓝色/绿色:片段插入的区域 黑色:正确连接的端点 红色:无法形成连接的端点。 黄色:该端点形成了连接,但未按照正常的顺序、方向连接,或者与其他端点形成了多个连接。
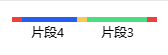
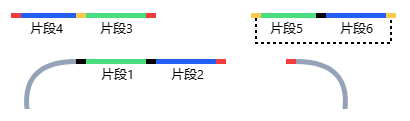
片段3与片段4能够连接,但他们的两端未连接到载体上,所以会显示在预览图的上方。
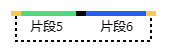
片段5与片段6能够连接,而且他们在未与载体连接的同时自己连接形成了额外的环状产物,所以会显示在预览图的上方。

片段2经过系统计算,需要翻转序列后与载体形成连接,此处会展示一个旋转的标识。
若系统计算后当前提供的片段无法与载体形成产物时,将会展示某个端点断开的预览图,下图中片段2的右端无法与载体的右端形成连接:
当一个端点有多个匹配时,系统会因为可能形成额外的产物而无法展示预览图;此时仅当能形成的产物中,有符合当前添加的片段顺序和方向的组合时,才会生成预览图。
10.3.2. 提示说明
系统提示分为两类:产物提示和片段提示。
【产物提示】
若系统计算后,片段能与载体两端形成连接,系统会提示“可生成目标产物及其长度”。
当片段的左右侧端点若会有多个额外的匹配值,会提示用户额外产物生成。
当生成的产物与添加的片段顺序或方向发生改变时,则会提示生成的产物与目标不一致。
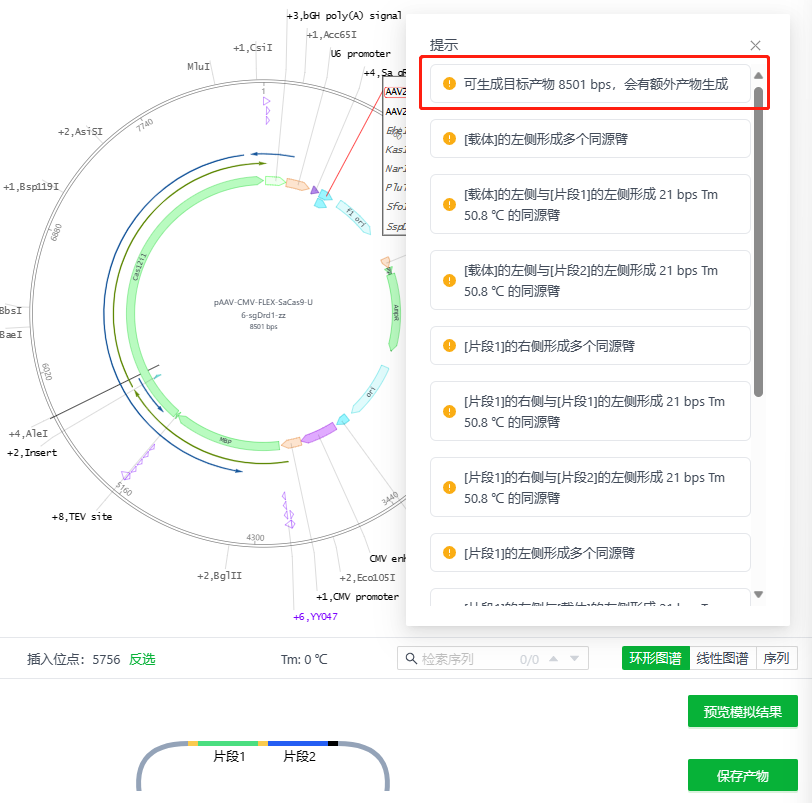
这些情况下,用户仍可以选择保存当前产物。
若系统计算后,片段与载体两端无法形成连接,系统会提示“无法生成目标产物”,此时只能通过修改设计方案�重新模拟。
【片段提示】
系统将根据端点连接的情况反馈提示:
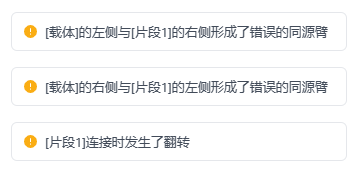
比如无法形成连接的端点。将提示该端点无法形成连接或形成同源臂。
如果该端点形成了多个连接,则会将其所连接的所有片段的端点都逐步罗列,如下:
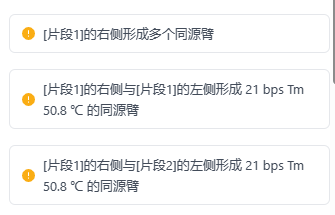
若系统计算后,片段在翻转后可与其他片段或载体形成链接,系统将会提示用户“片段n连接时发生了翻转”,同时提示该片段的两端所产生的错误链接提示。
10.4. 载体、片段文件修改及保存产物。
10.4.1. 载体、片段文件修改。
系统支持用户直接在当前操作界面中修改序列文件,添加引物,调整引物,创建删除特征,调整序列碱基。

10.4.2. 载体、片段文件顺序调整,翻转序列。
当模拟结果中,用户发现载体或者片段的顺序有问题时,可以直接拖拽片段来调整顺序,也可以点击上下箭头来切换顺序。
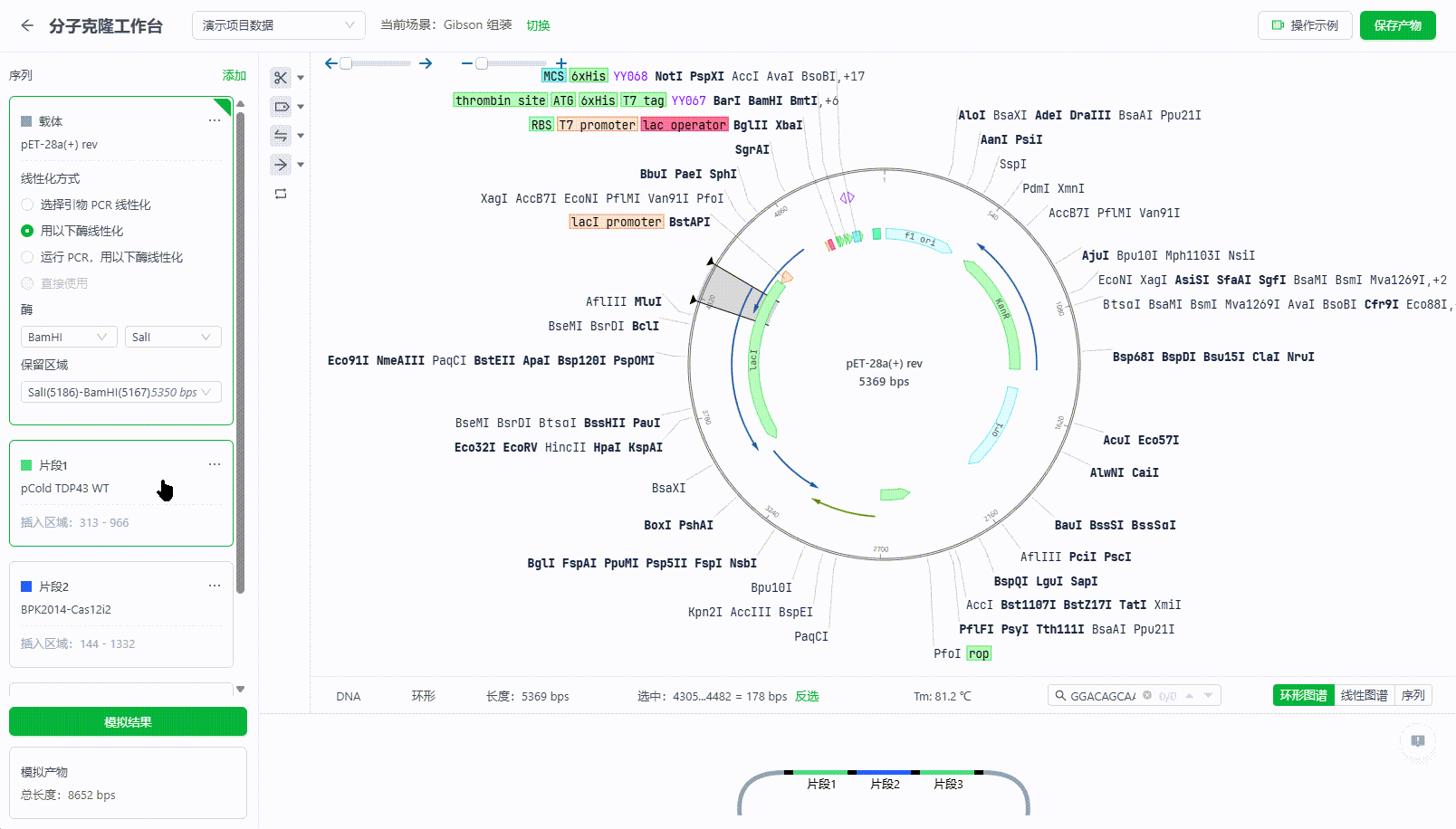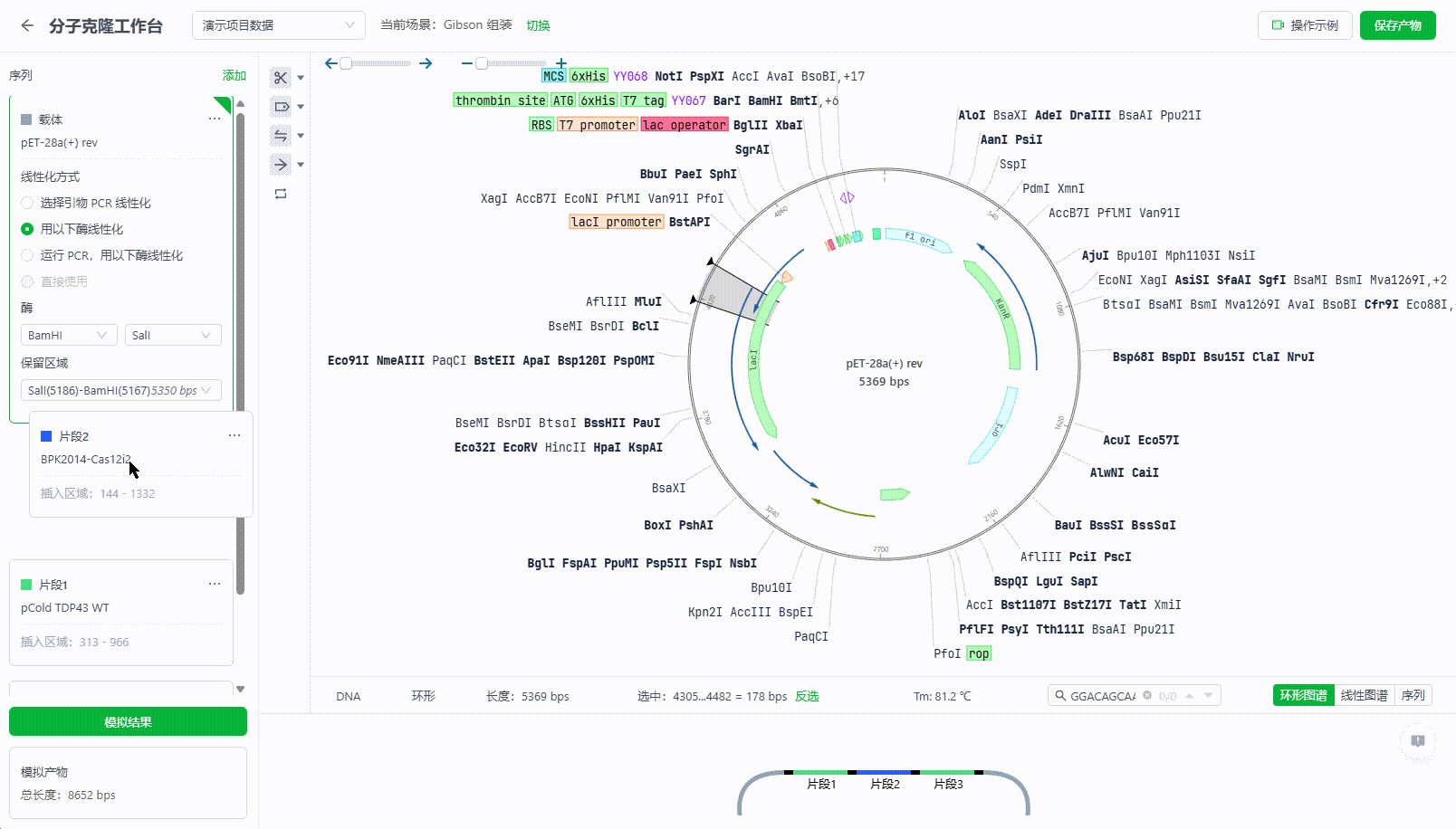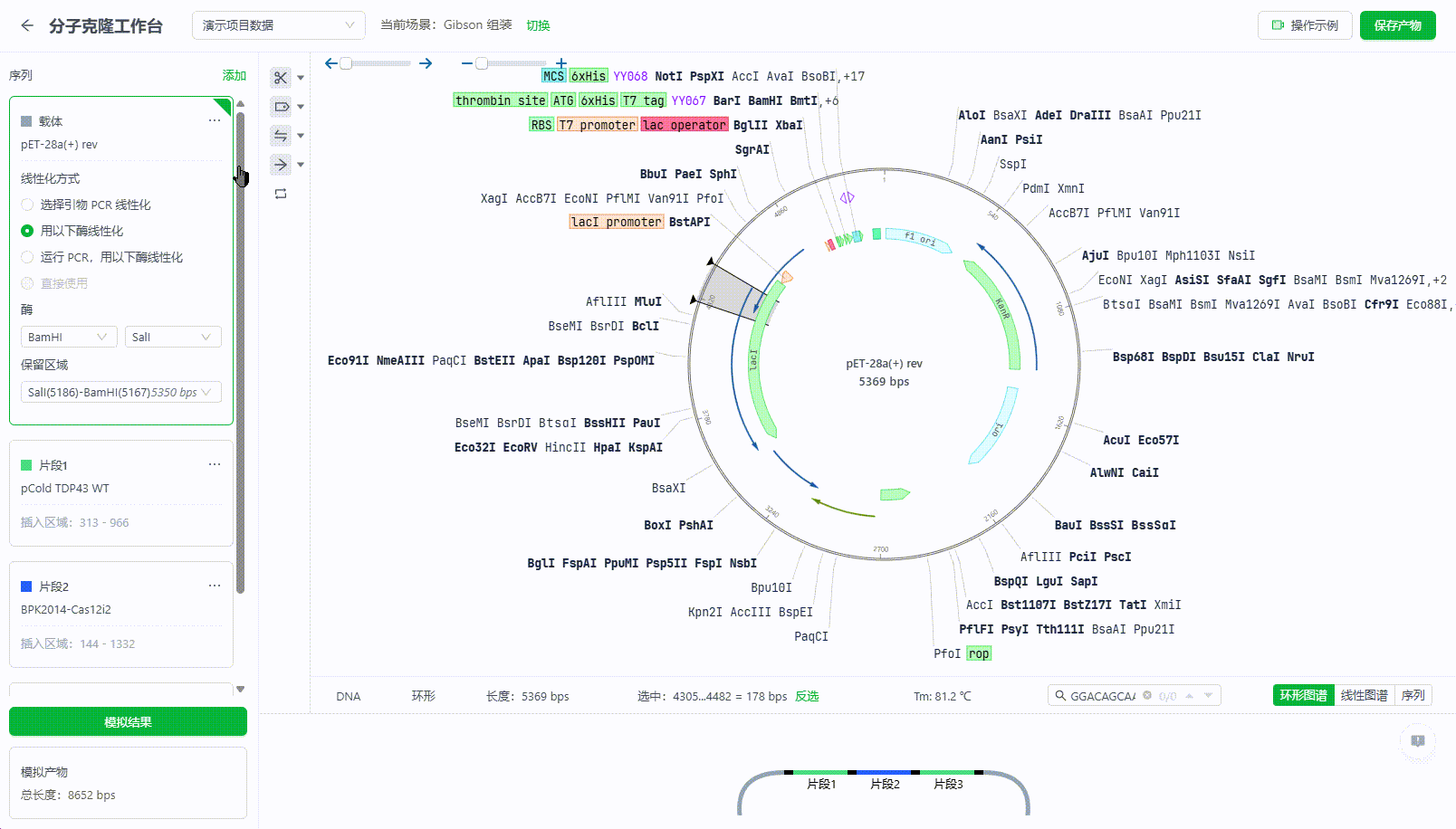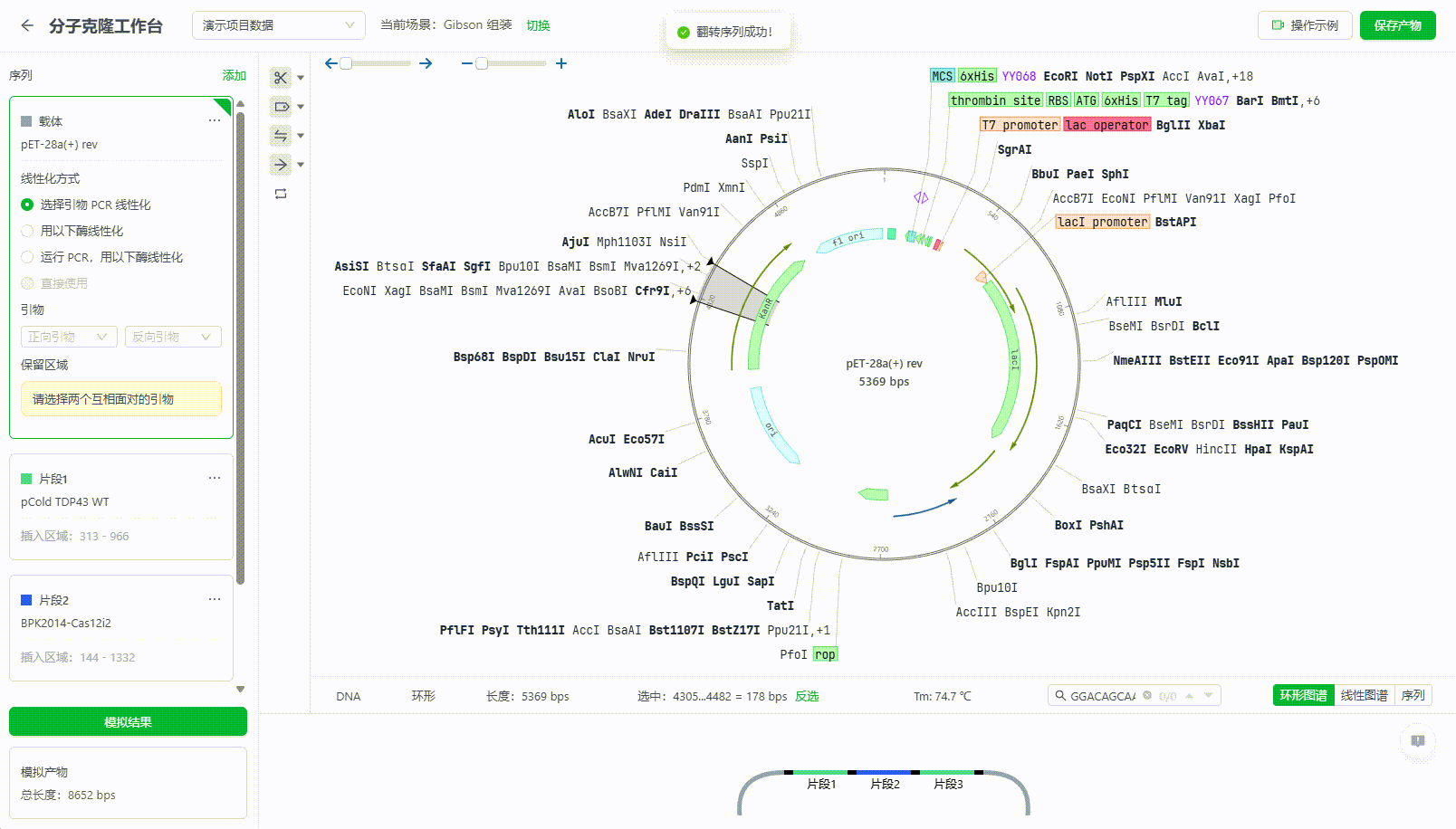
同样当发现需要翻转后才可正常连接时,用户可以直接翻转当前序列。
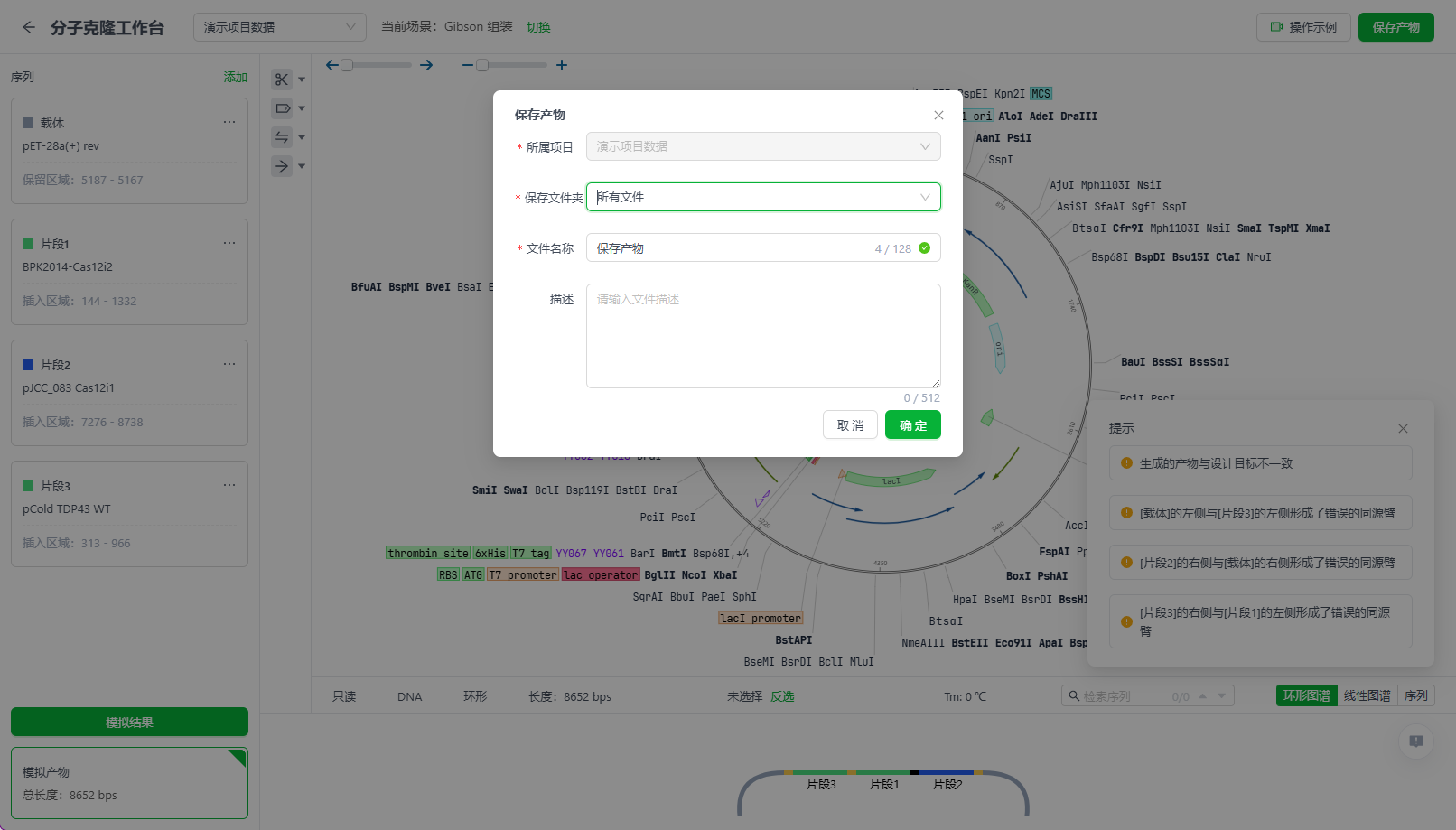
10.4.3. 保存产物。
模拟后的产物可以保存,点击保存产物后,需要对当前文件进行一次命名,然后该产物将以一个新的项目文件的形式存在系统中。此时如果需要将这个界面中的修改能够直接保存到引用的文件中,可以勾选下图中的选项,在保存产物时将直接存储到引用的文件中。
11. 序列比对
11.1 添加序列比对文件进行比对
用户可以工作台的序列比对按钮进入序列比对的工作台。
在此工作台中,用户可以添加10个文件用来比对测序的文件。
比对结果将会以文件的形式保存在系统中,所以点击开始比对后,需要填写生成的文件名称,提交后系统后台会进行比对计算,可以点击刷新查看比对结果。
完成比对的后的记录可以拖拽调整比对
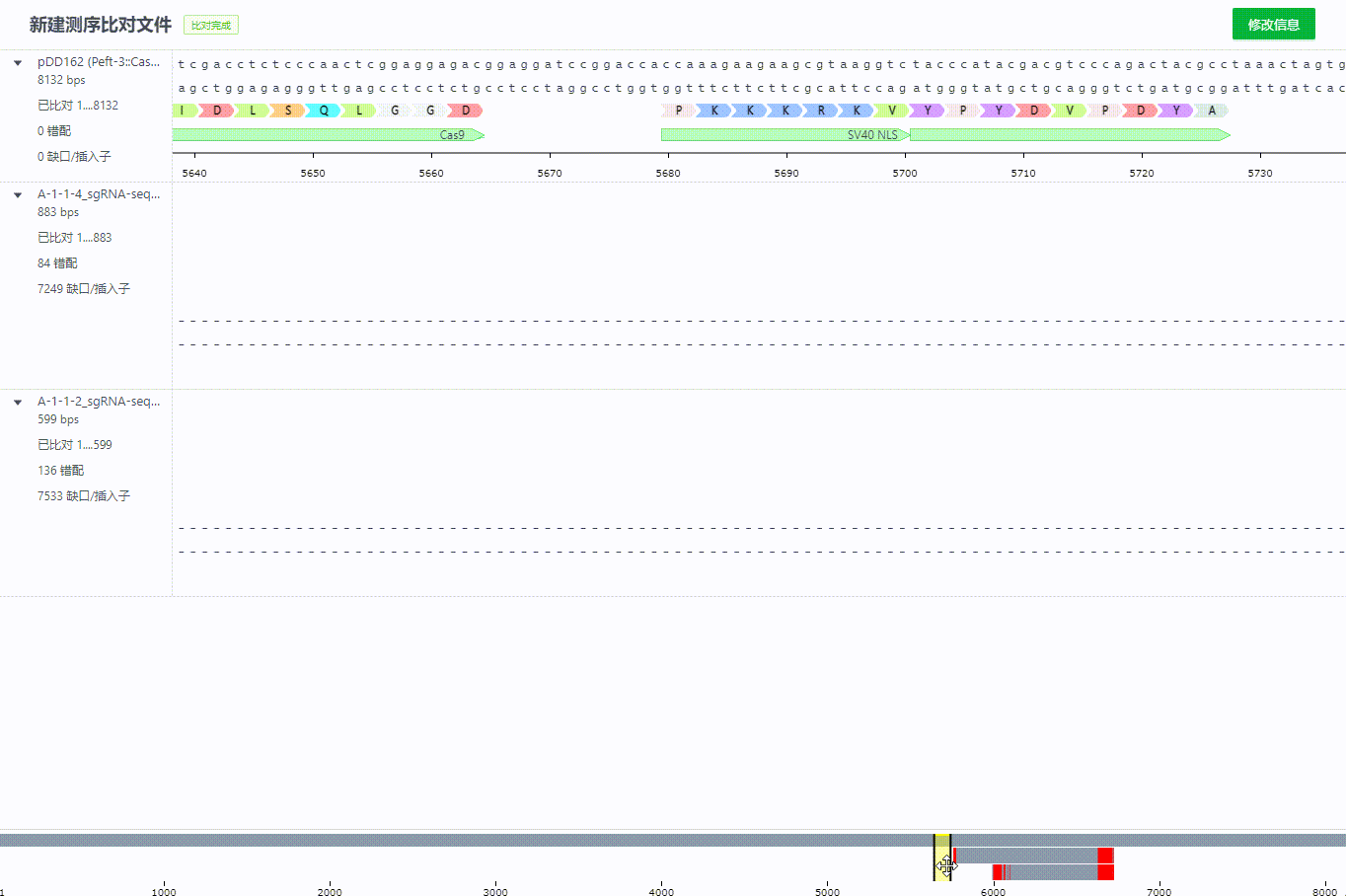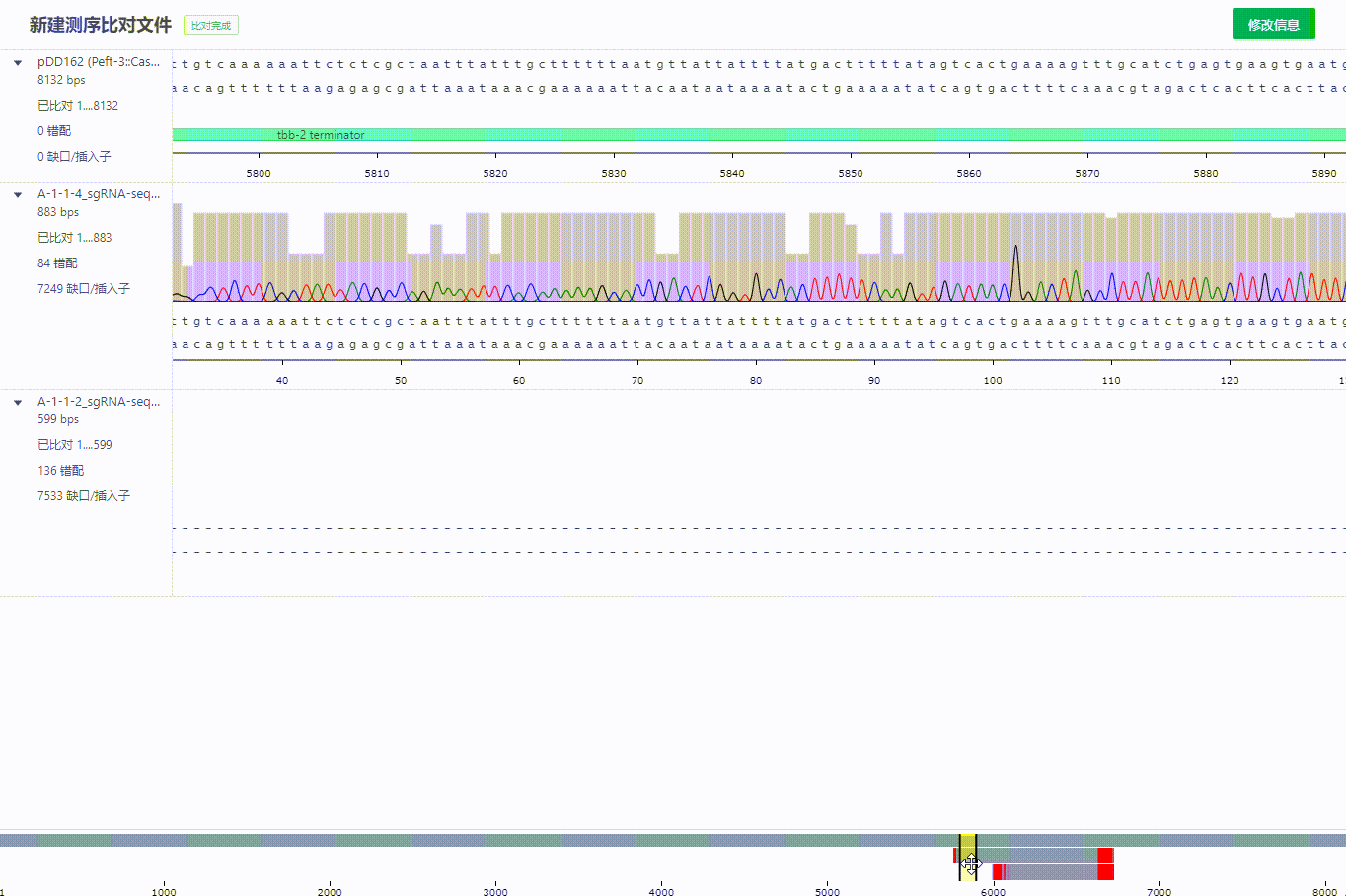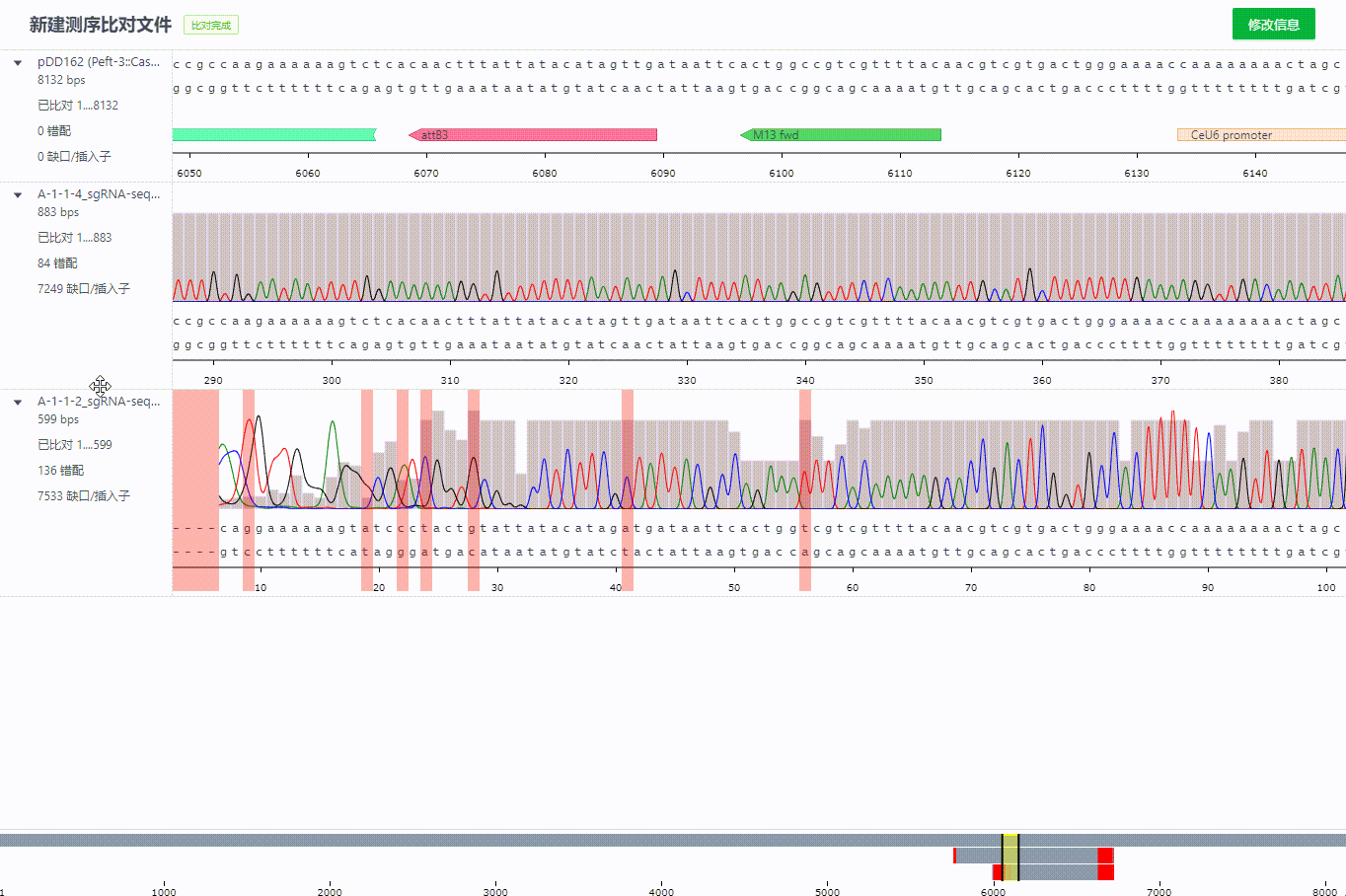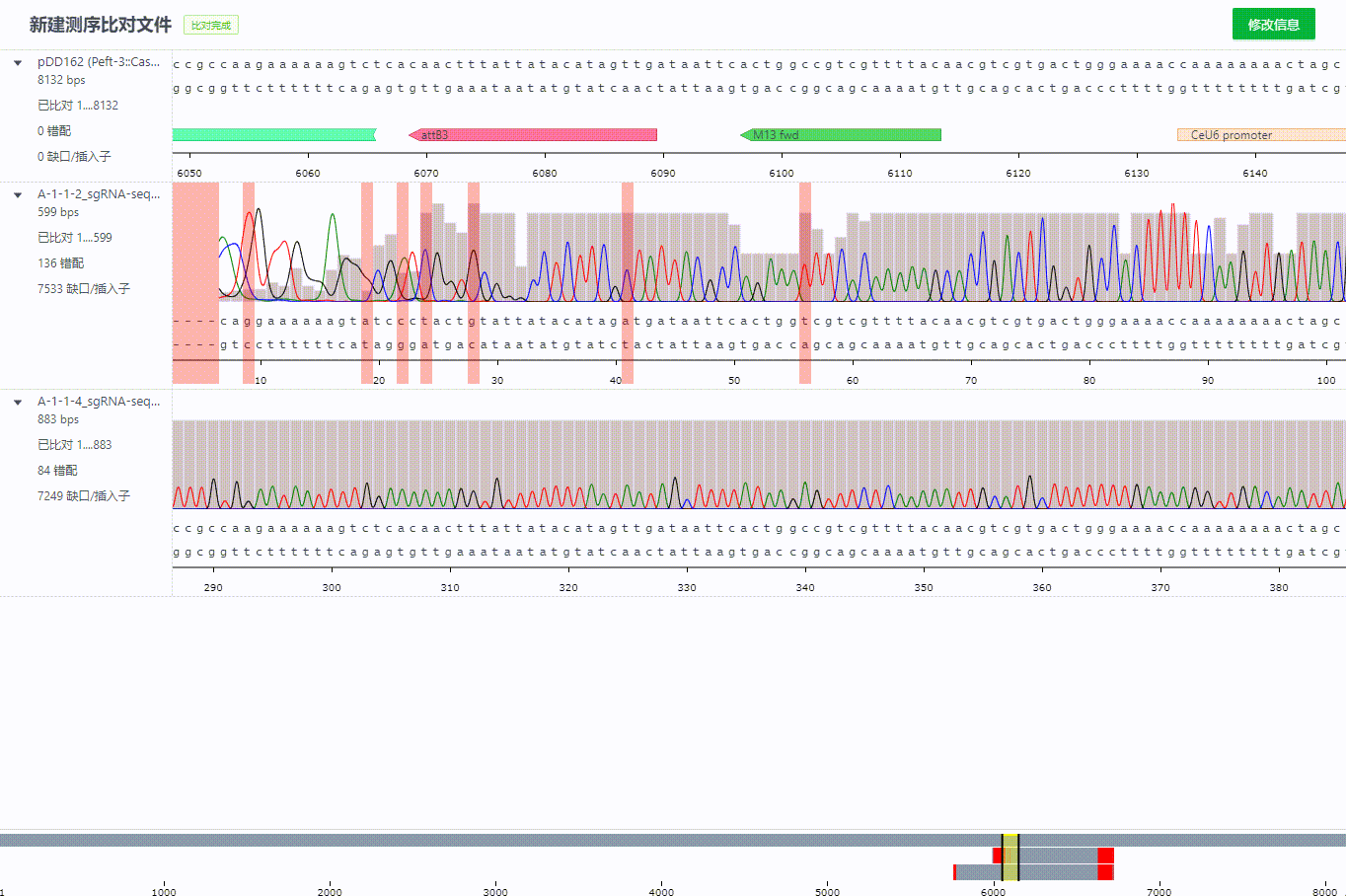
比对记录过程中序列会根据对齐算法自动识别方向不正确的文件,并直接旋转该文件。同时会在左侧标识哪些文件调整过方向。
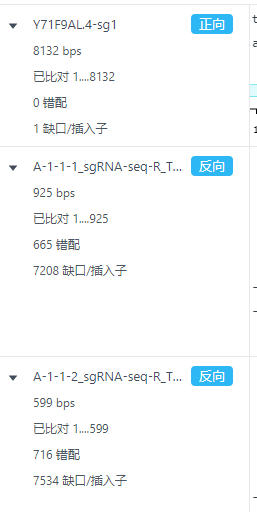
11.2 打开比对记录
比对记录将会保存在文件列表中,用户可以点击查看。
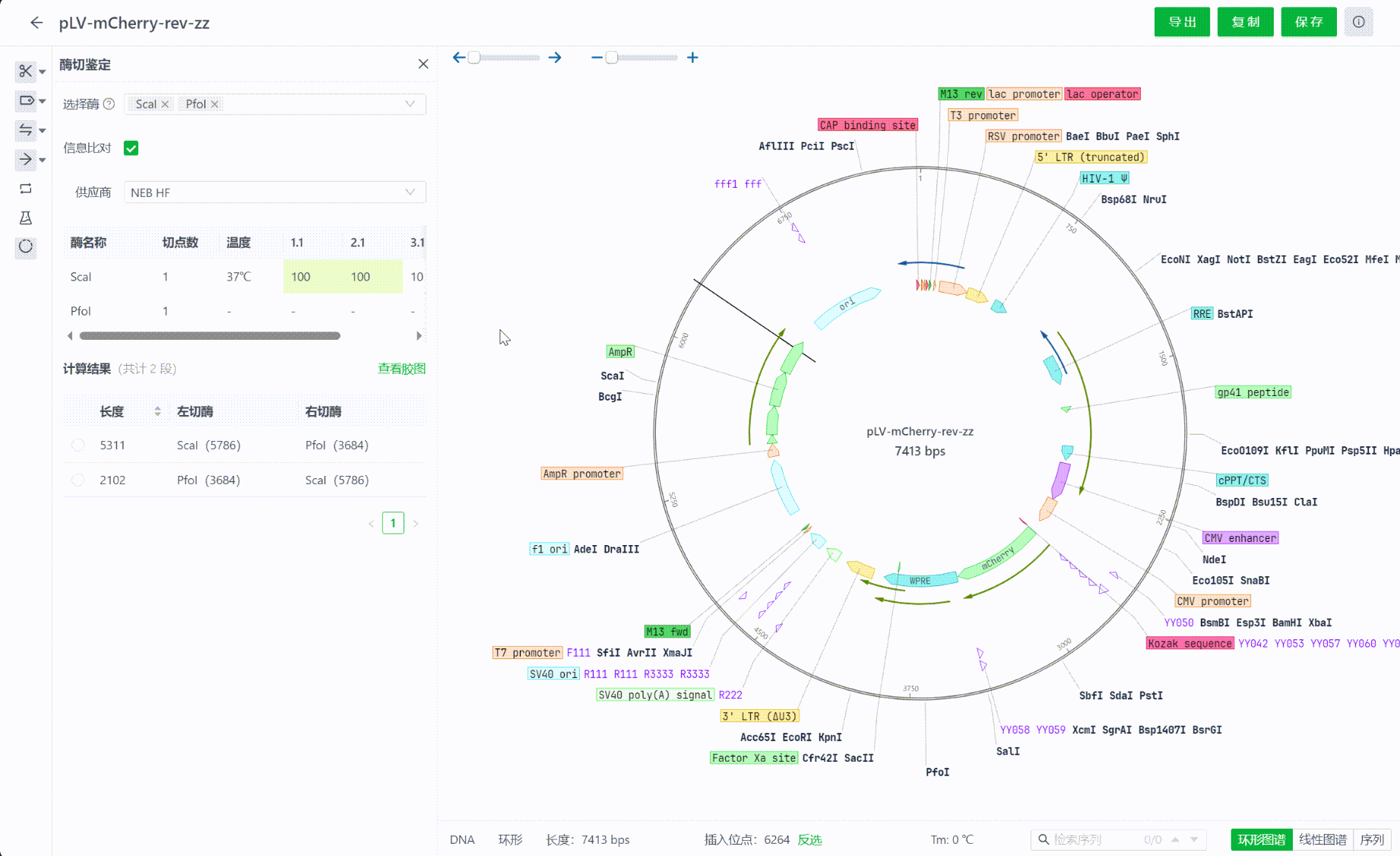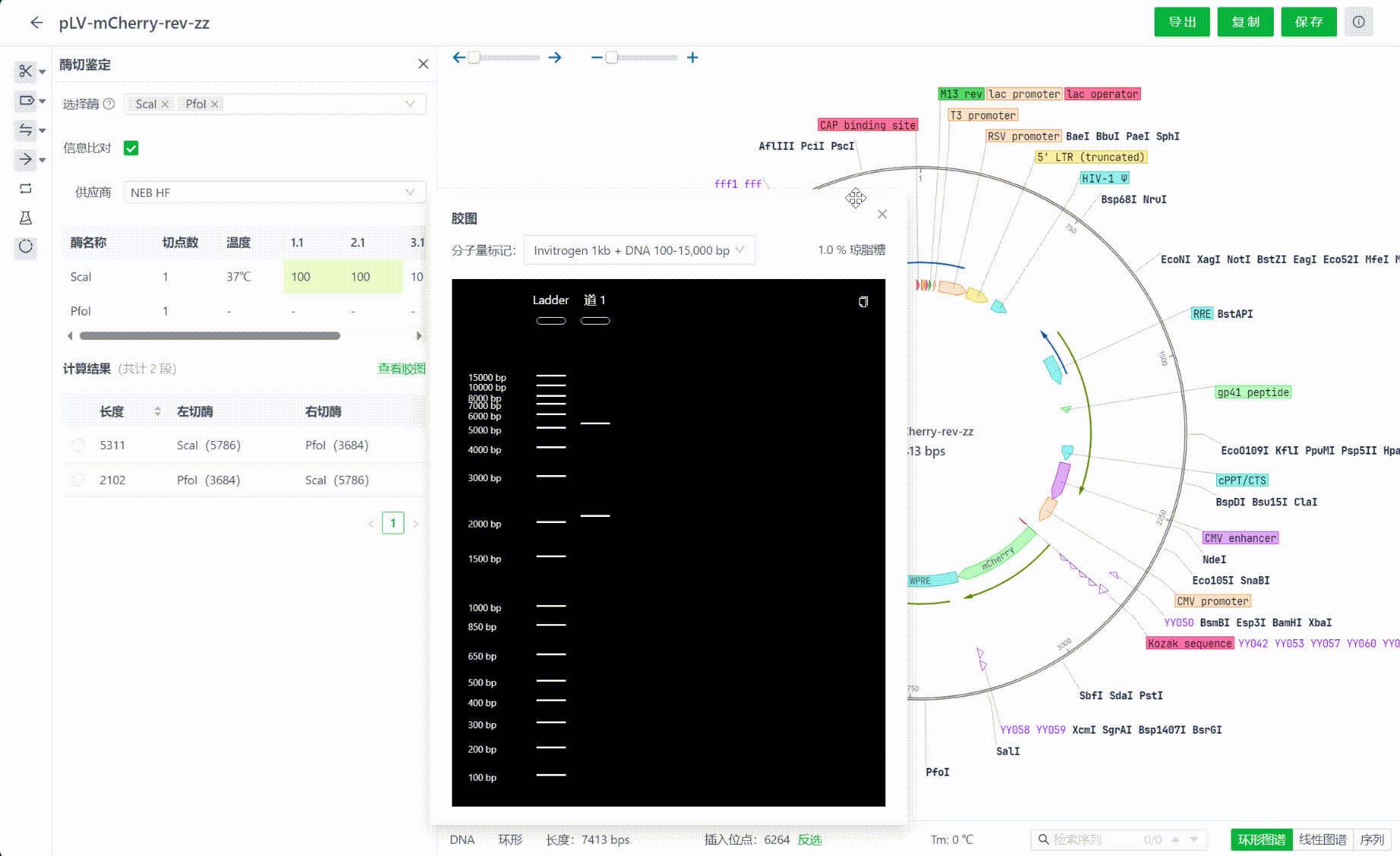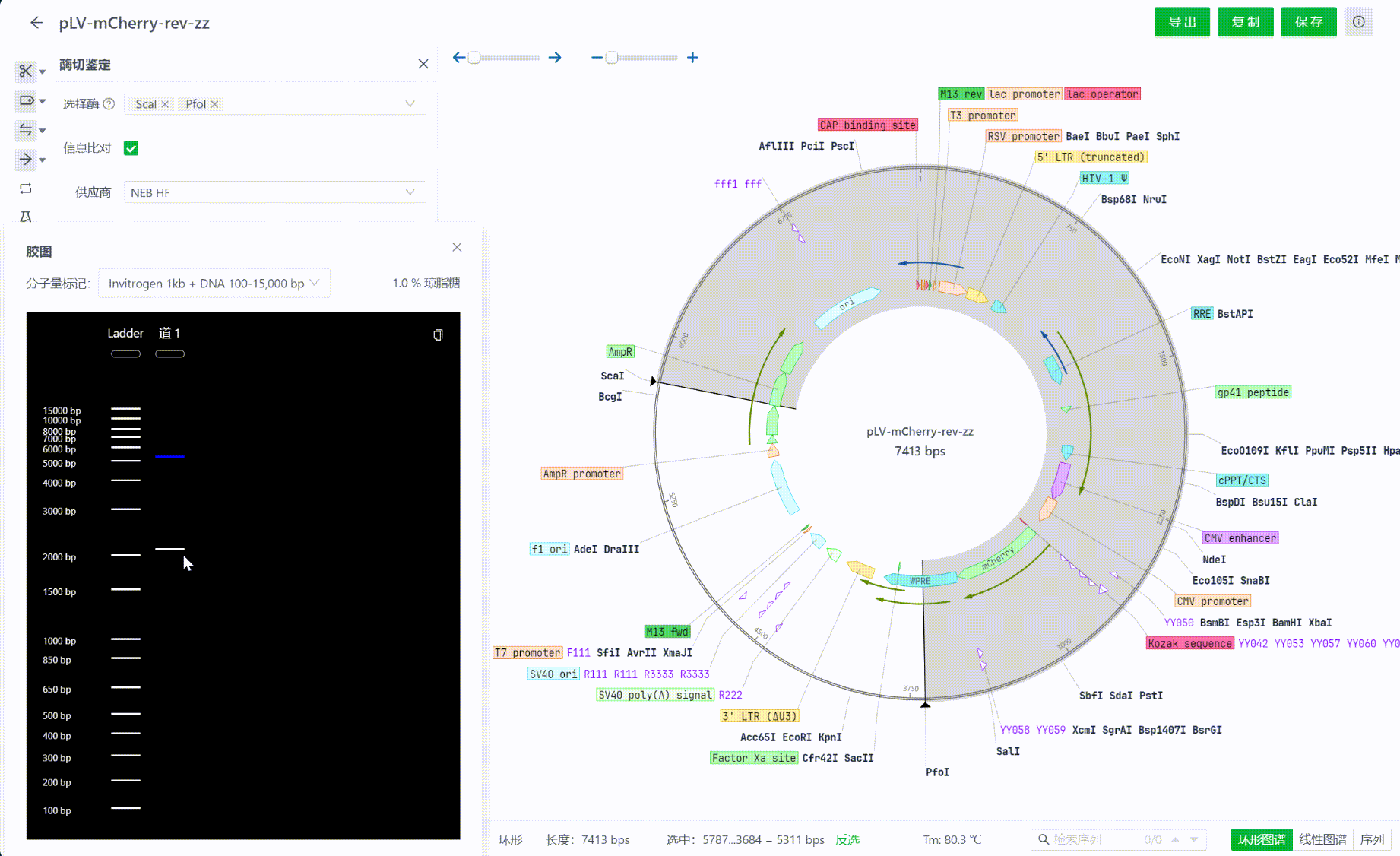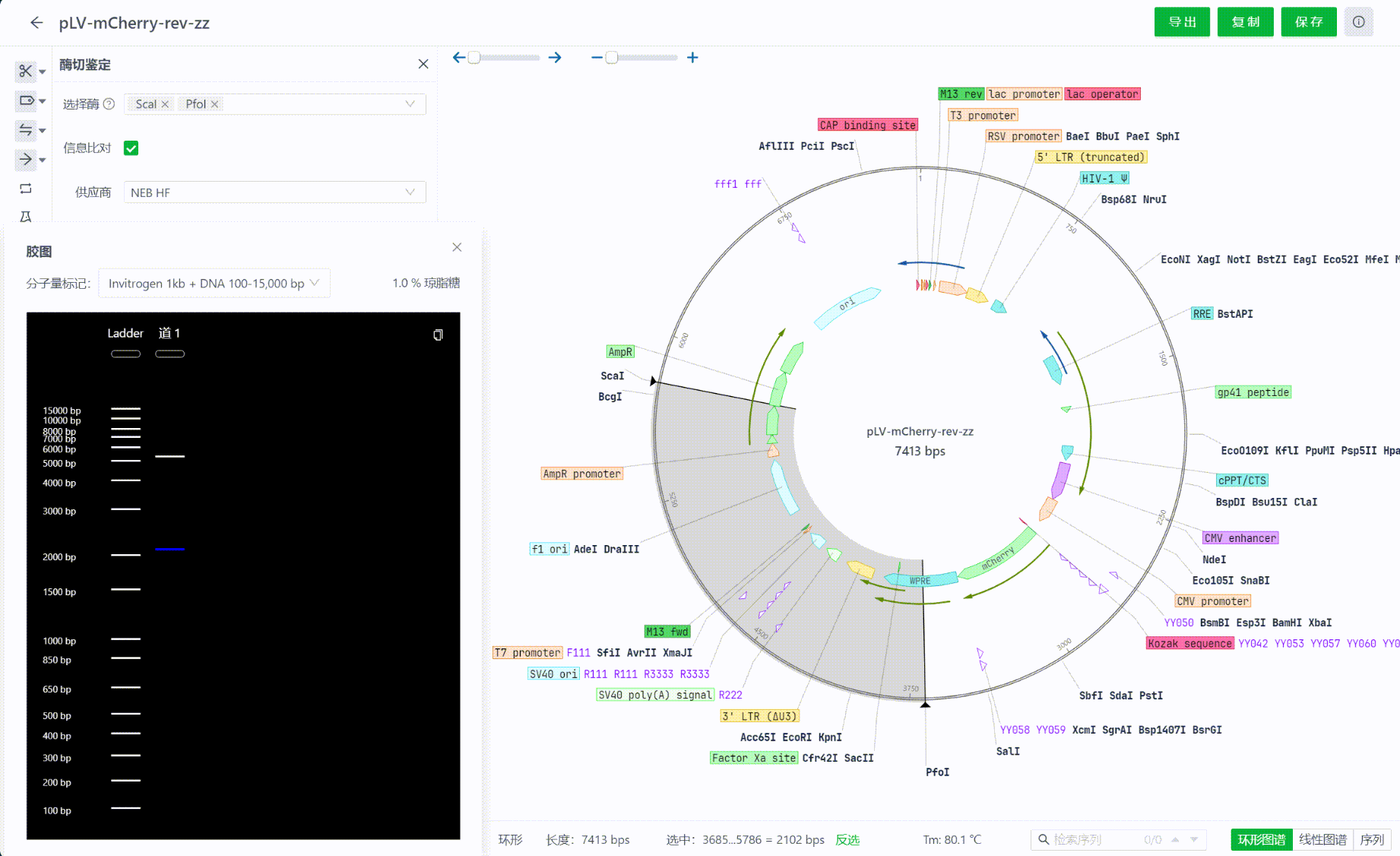
12. 酶切鉴定
12.1 选择需要鉴定的内切酶
用户可以在工具栏中找到酶切鉴定的工具入口,点击后可以在搜索框中输入最多4个内切酶。
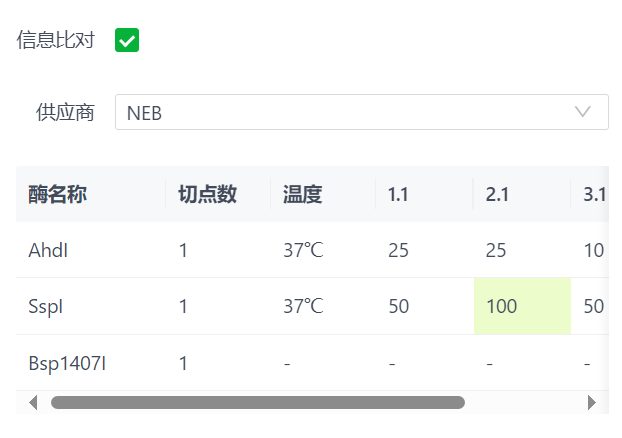
12.2 查看内切酶相关信息
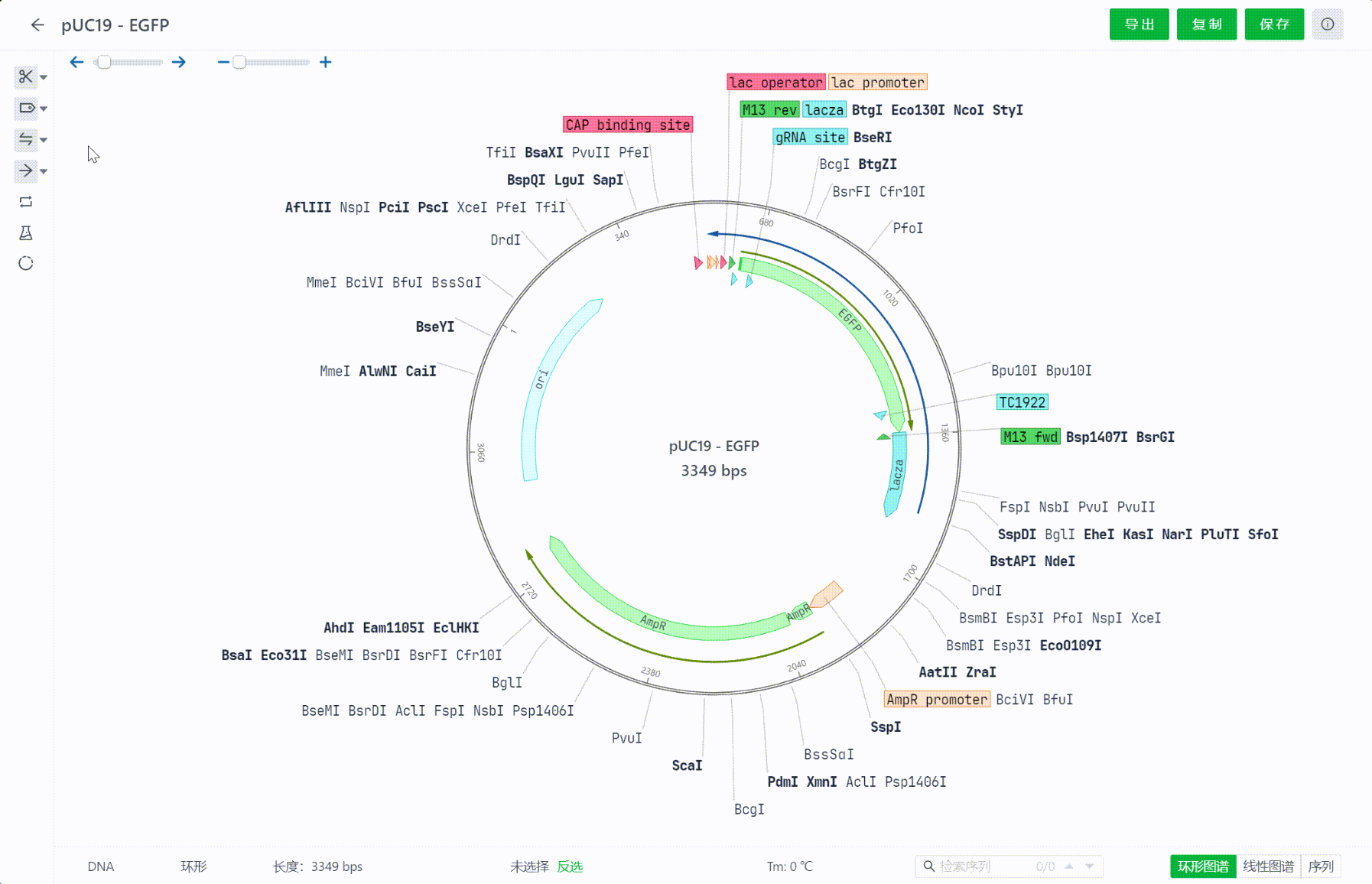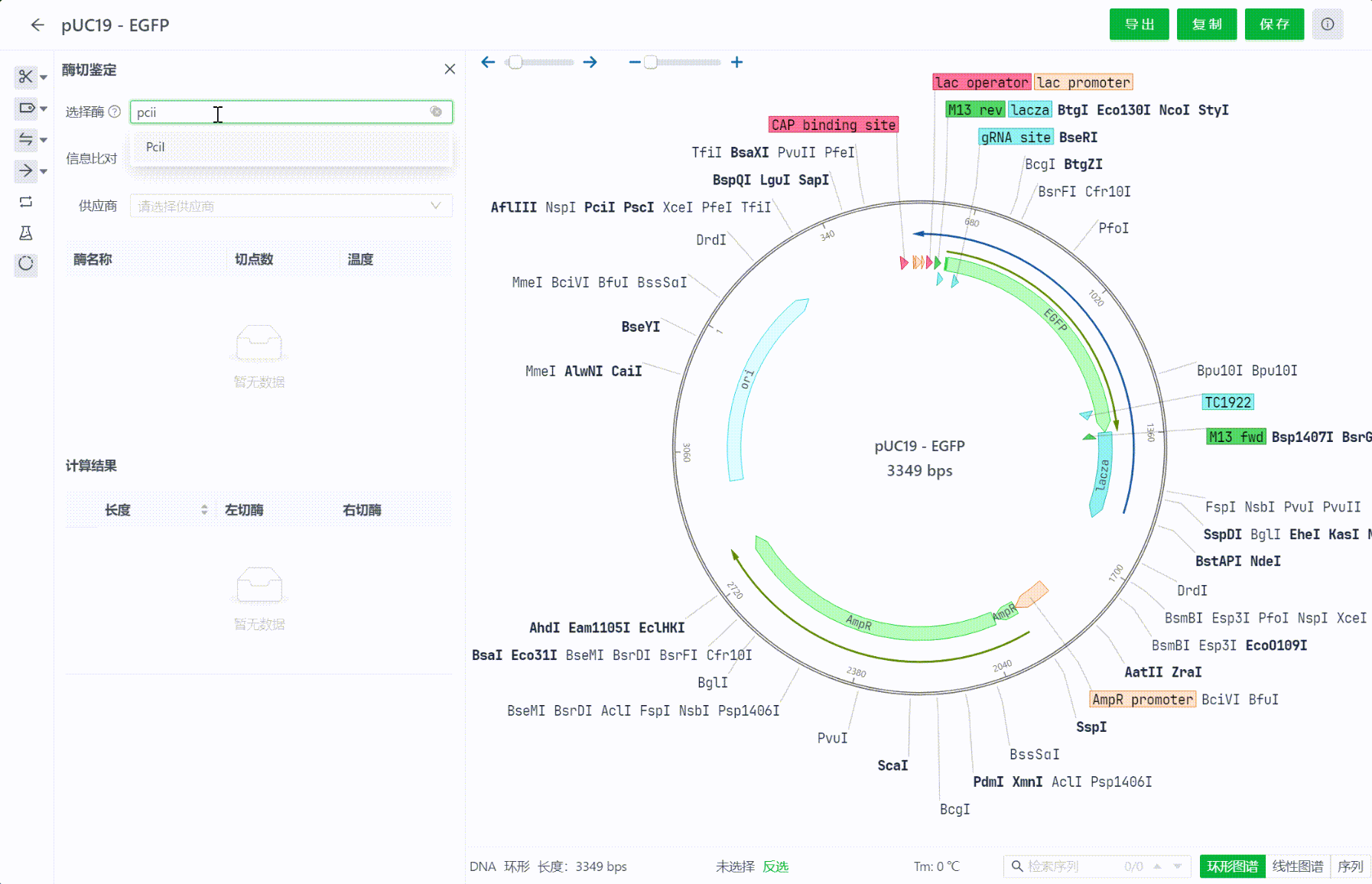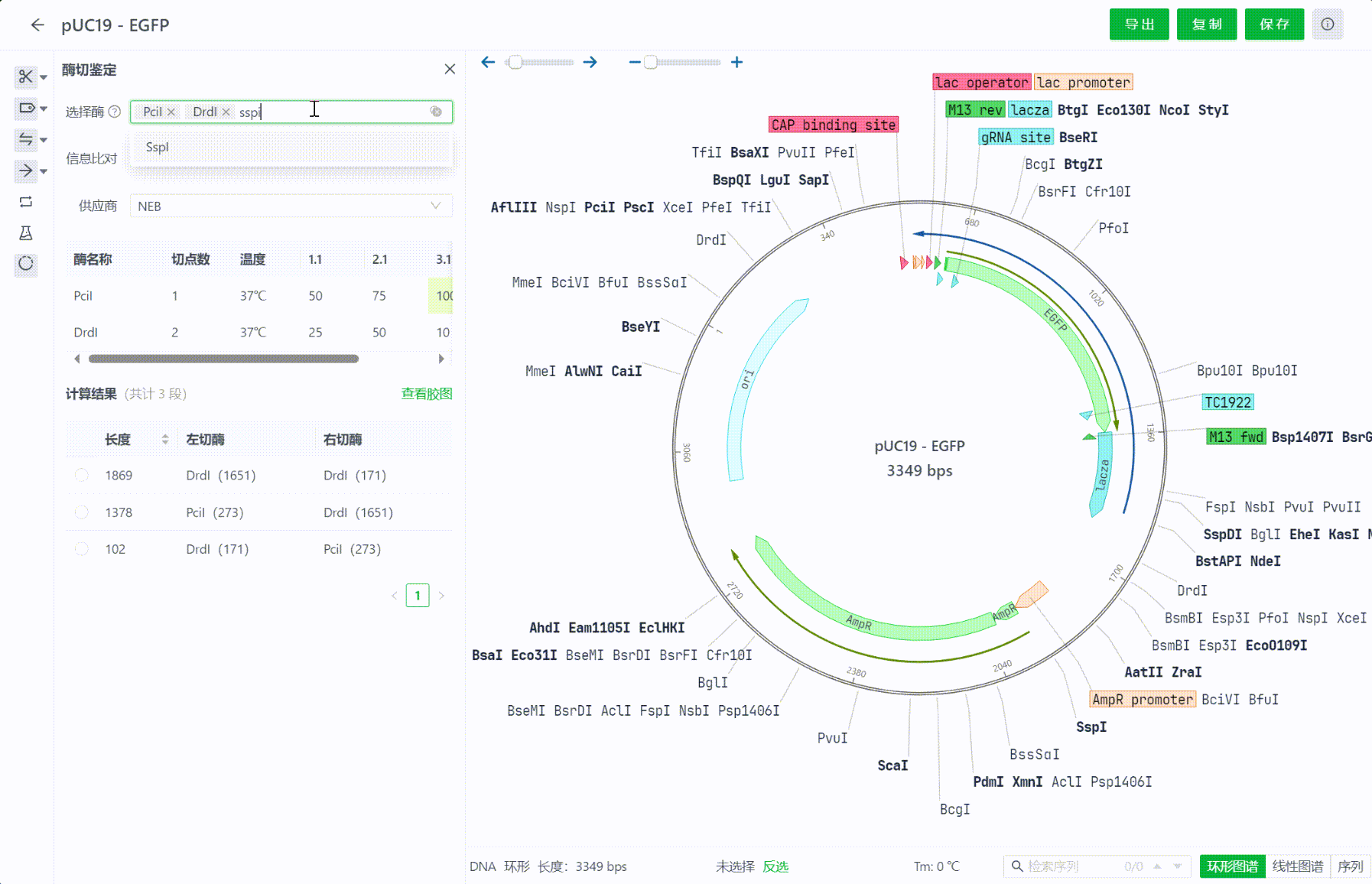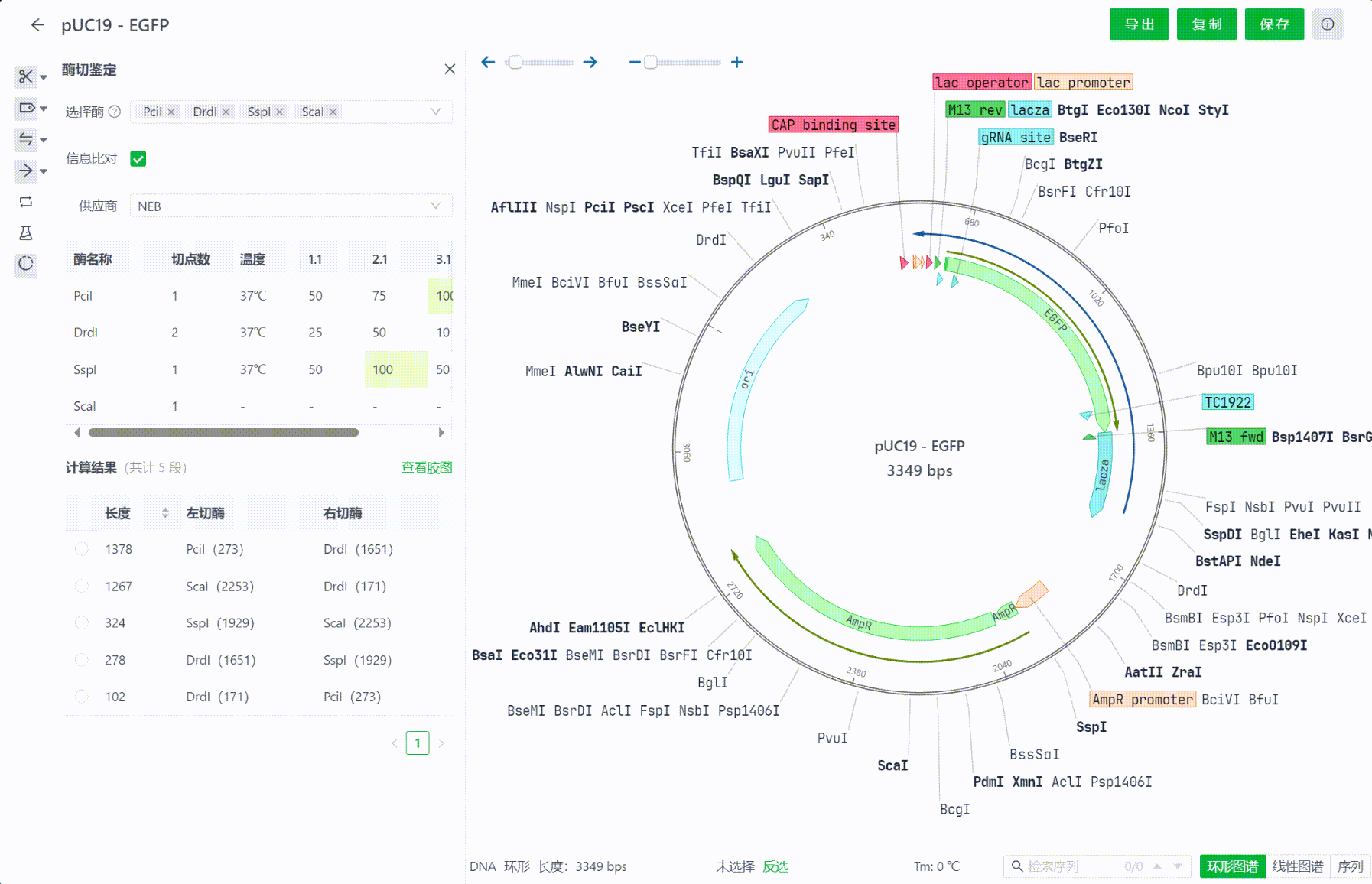
界面中将会展示这些内切酶在当前文件中的切点数,供应商相关信息,比如最适孵育温度,缓释液等等信息,可以切换查看不同供应商的这些信息。若想隐藏这些信息,可以点击信息比对的复选框来关闭该界面。
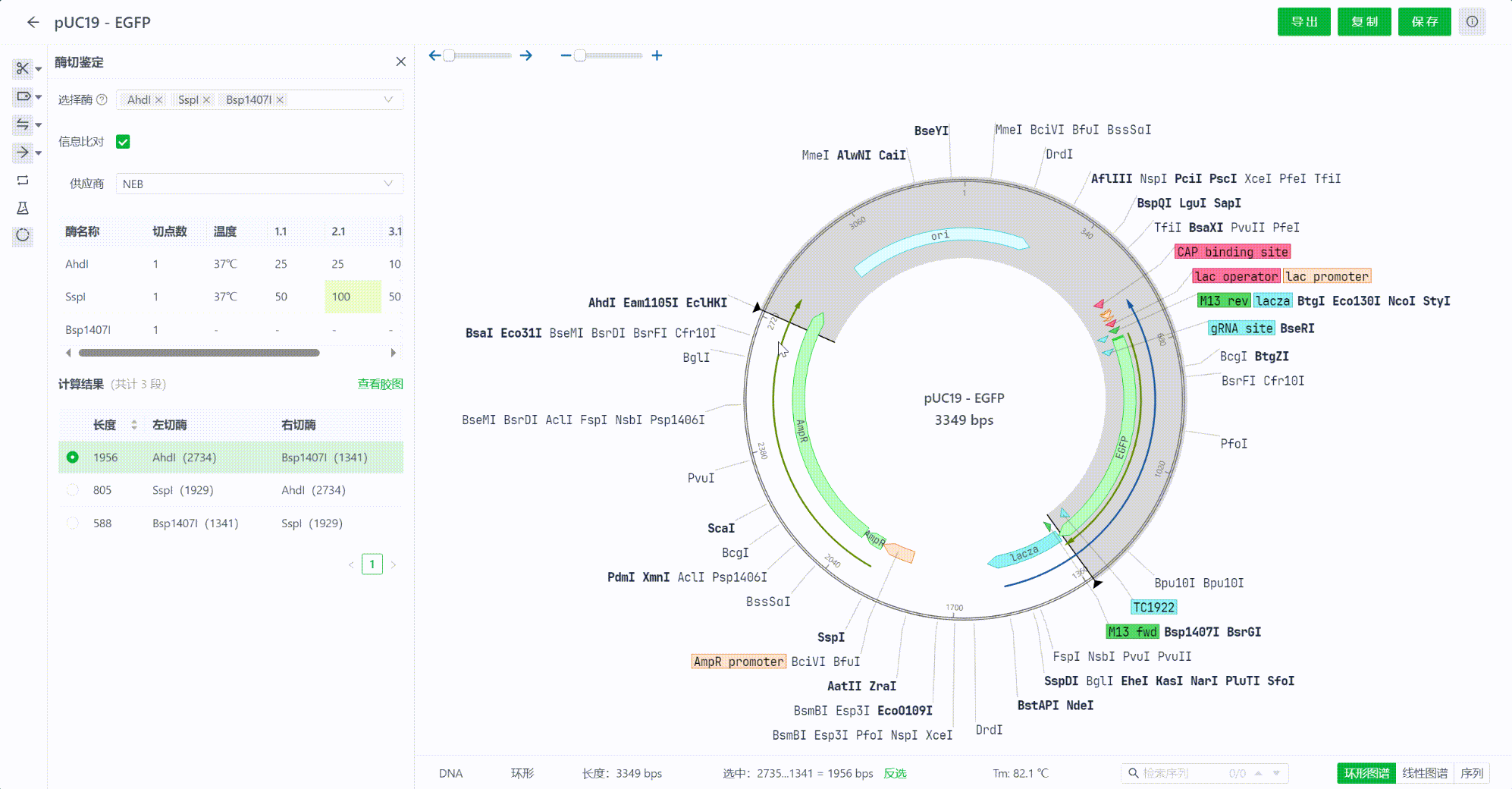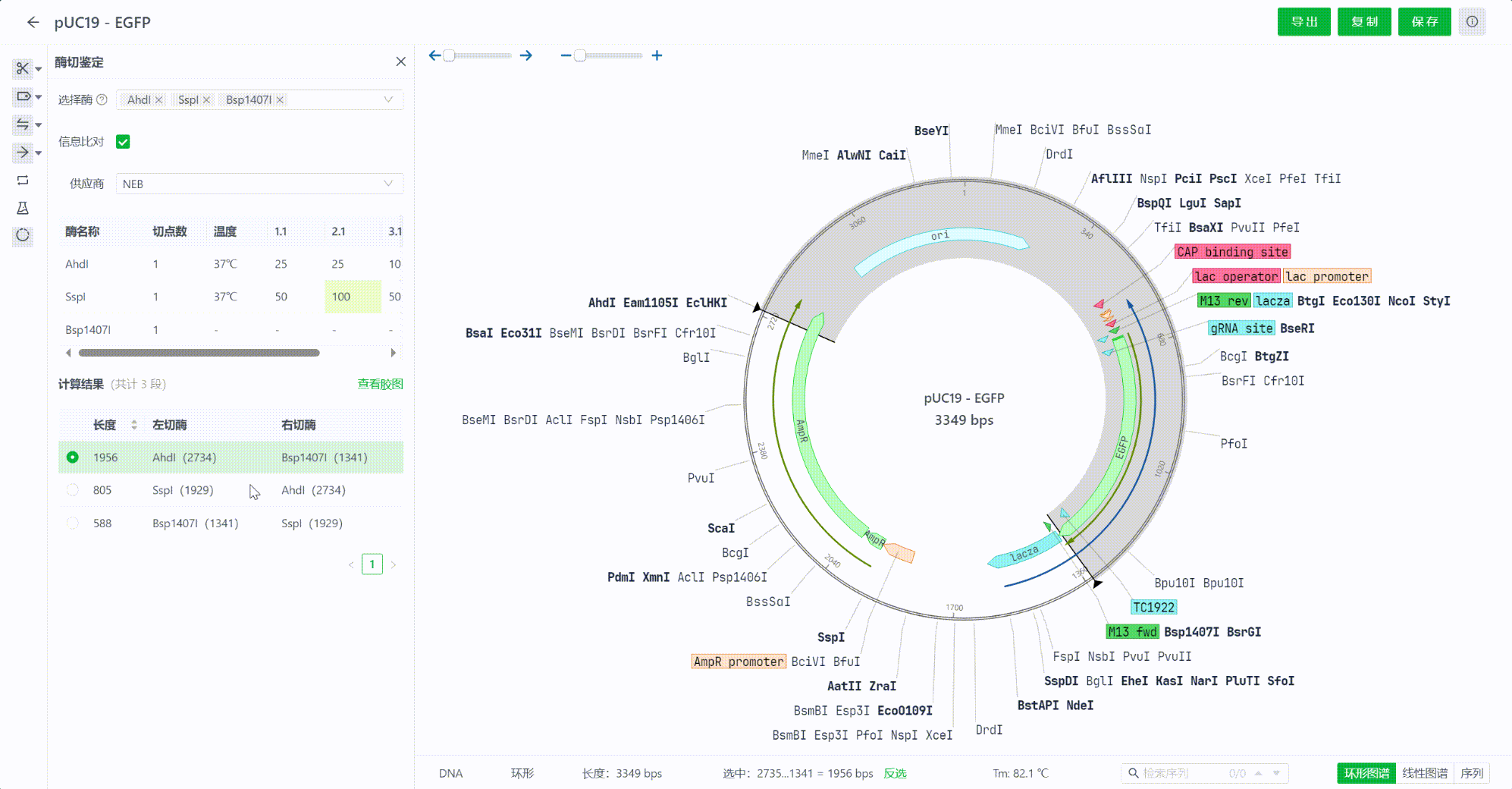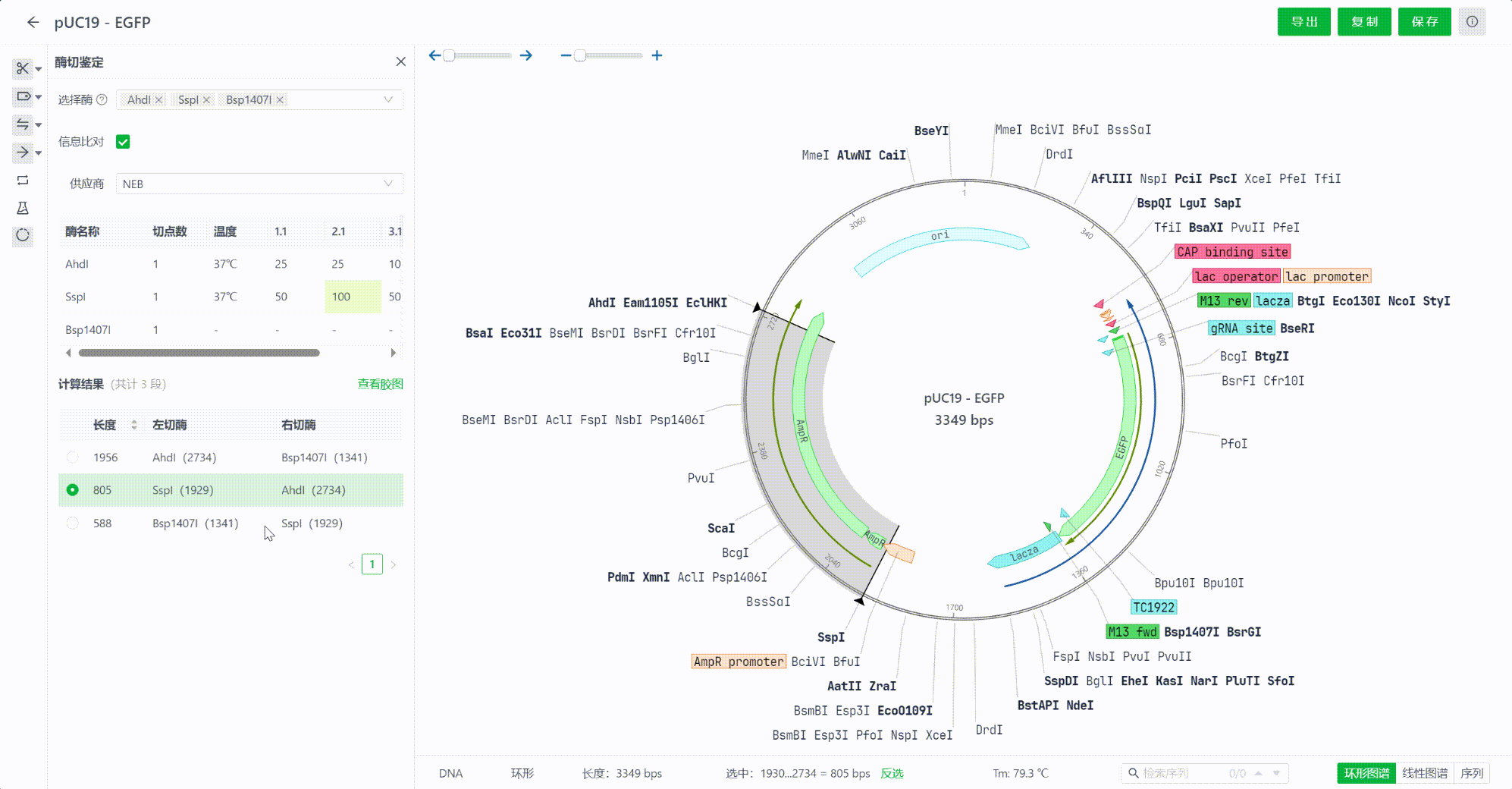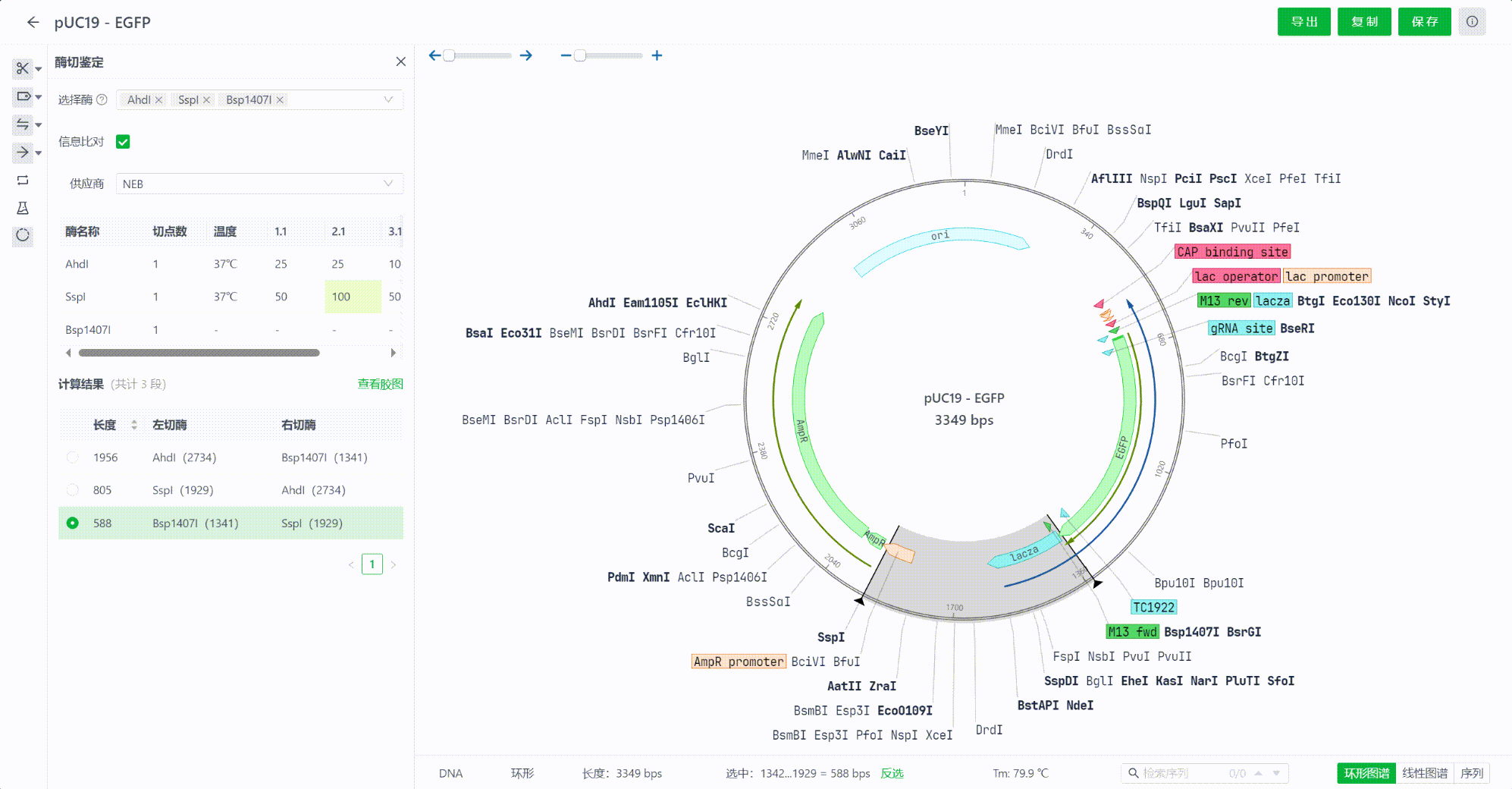
12.3 查看计算结果
选择内切酶的过程中,系统会实时计算酶切后的结果,系统将会把结果从长到短排序,用户可以点击每一个片段,在视图中查看切割的区域情况。
12.4 查看模拟胶图
在计算结果的同时,系统也会模拟渲染电泳实验过程中的胶图成像。胶图可以拖拽,可以点击其中泳道中的片段,每一次点击都会选中视图中的对应片段。
同时系统支持将当前胶图复制到剪切板,便于用户复制到实验记录中。
13. 退火寡核苷酸
13.1 手动创建退火寡核苷酸文件
用户可以系统中通过手动输入两个寡核苷酸的引物序列来实现退火寡核苷酸的文件生成。
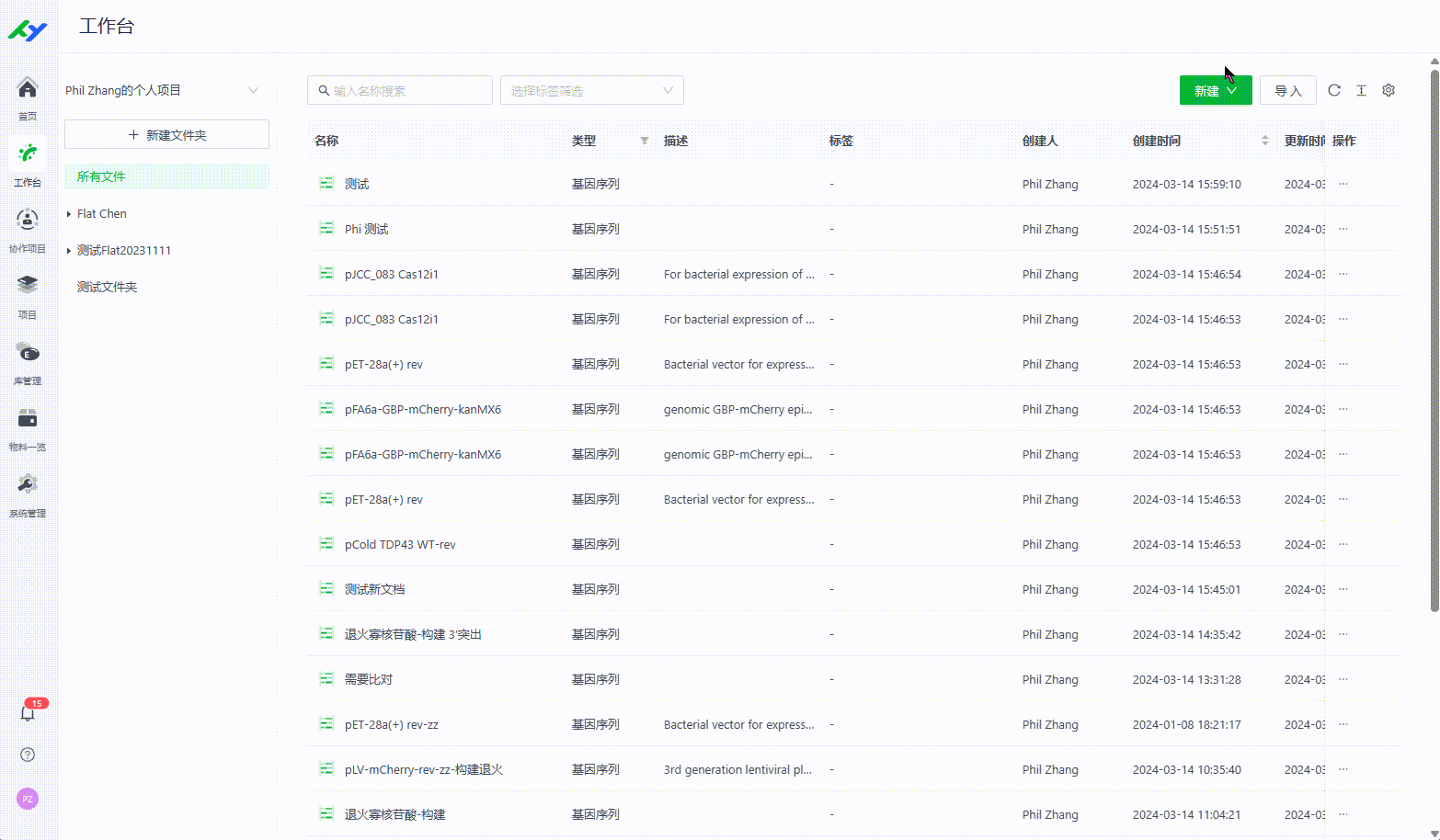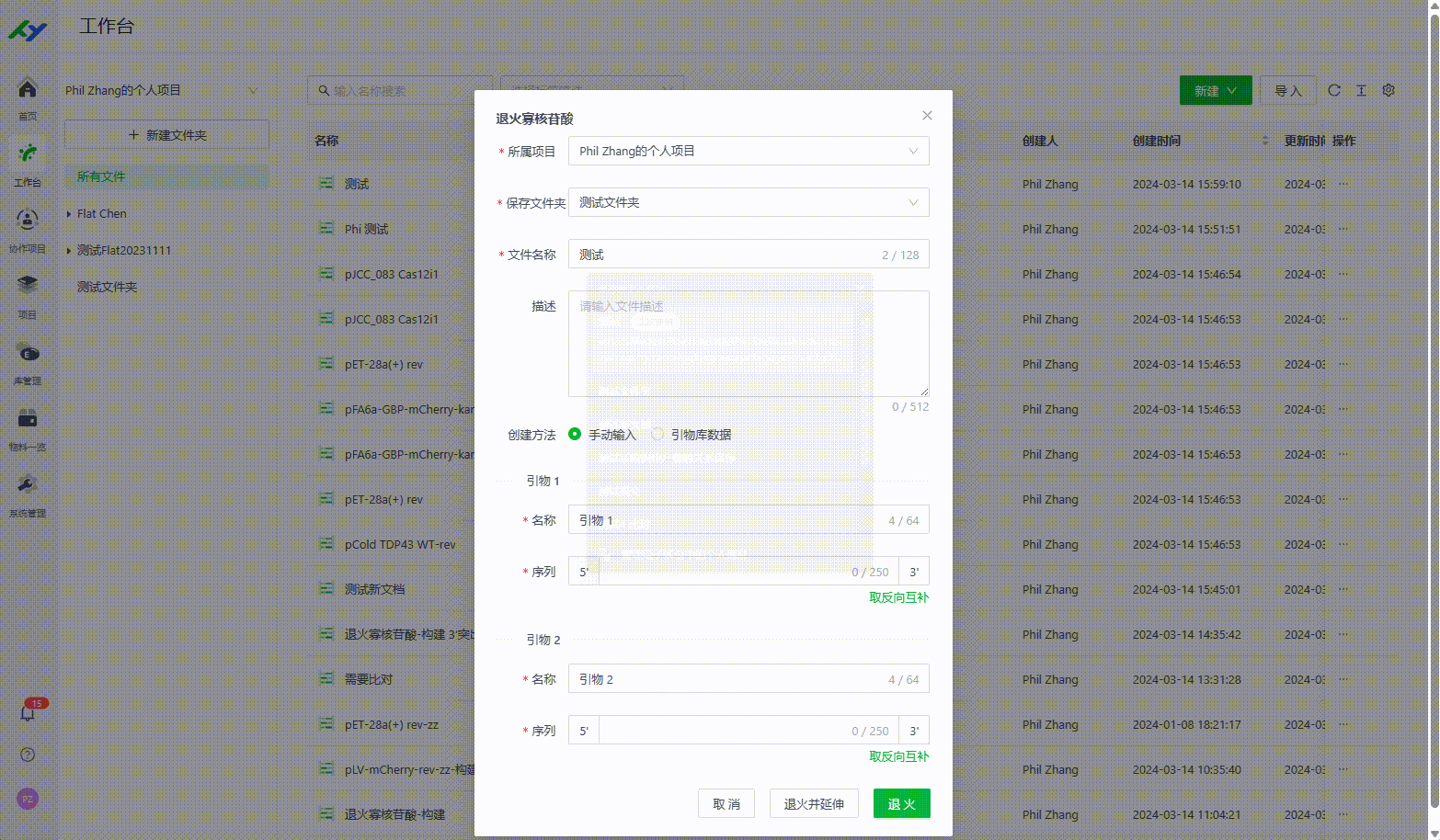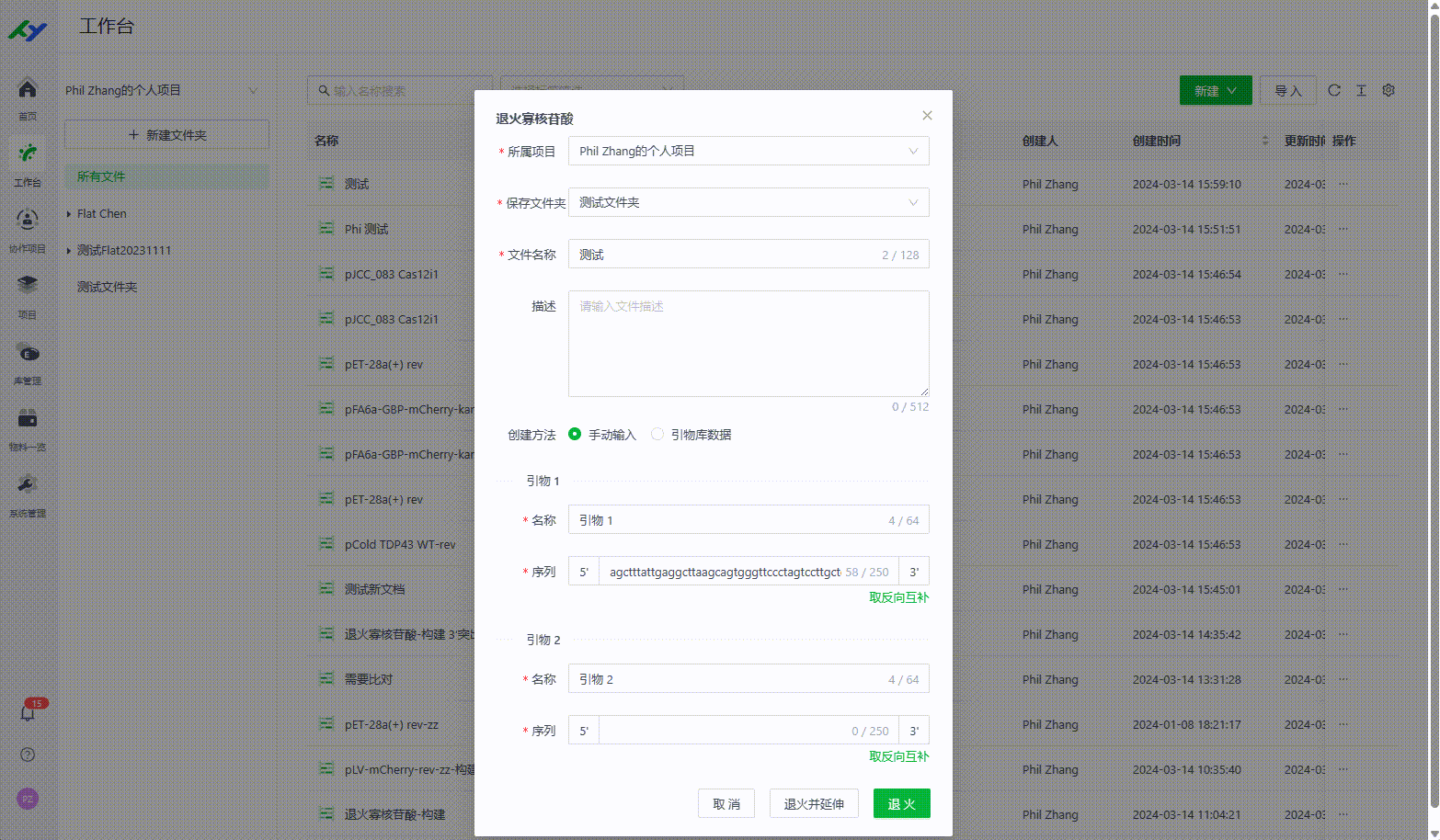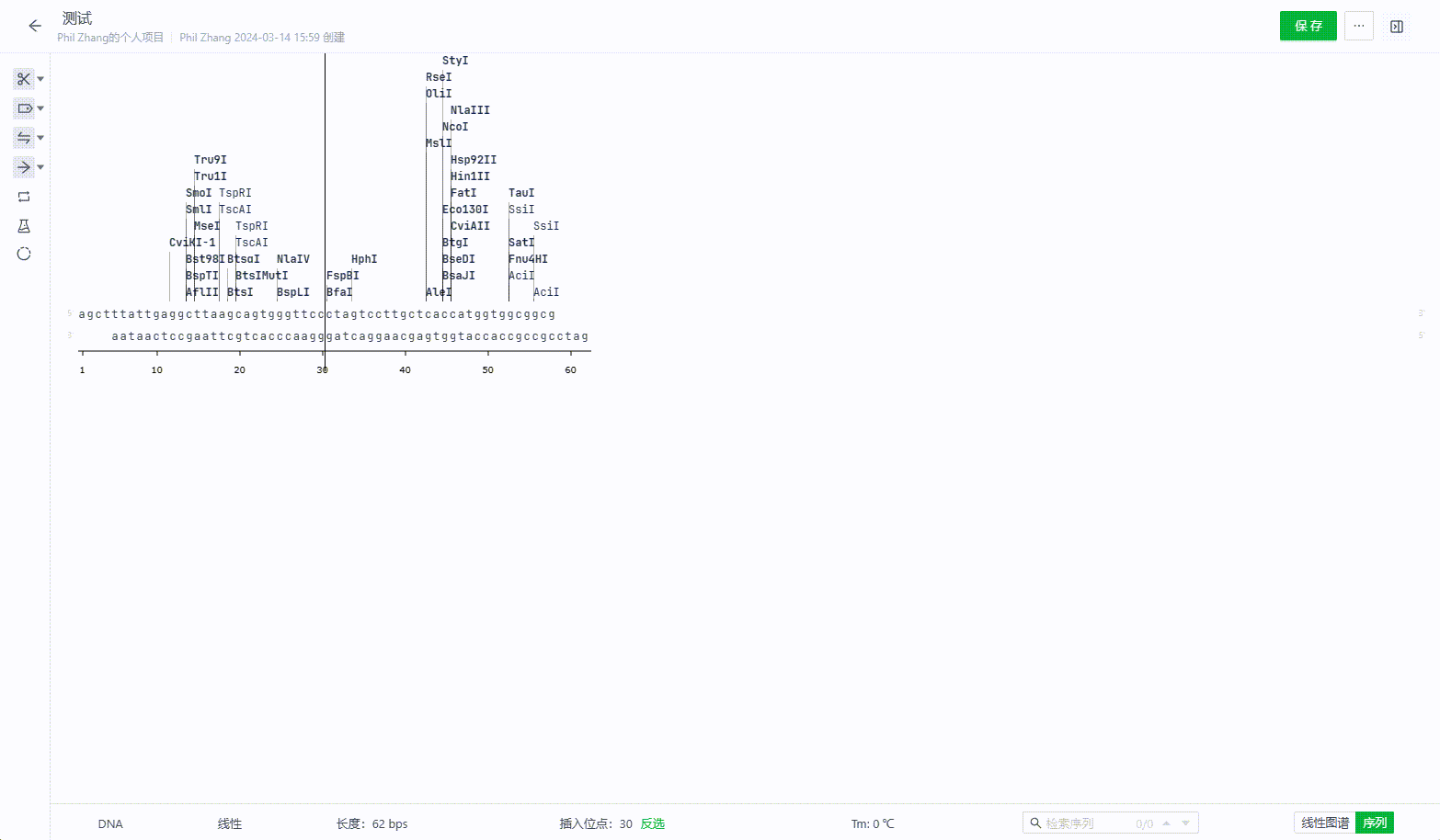
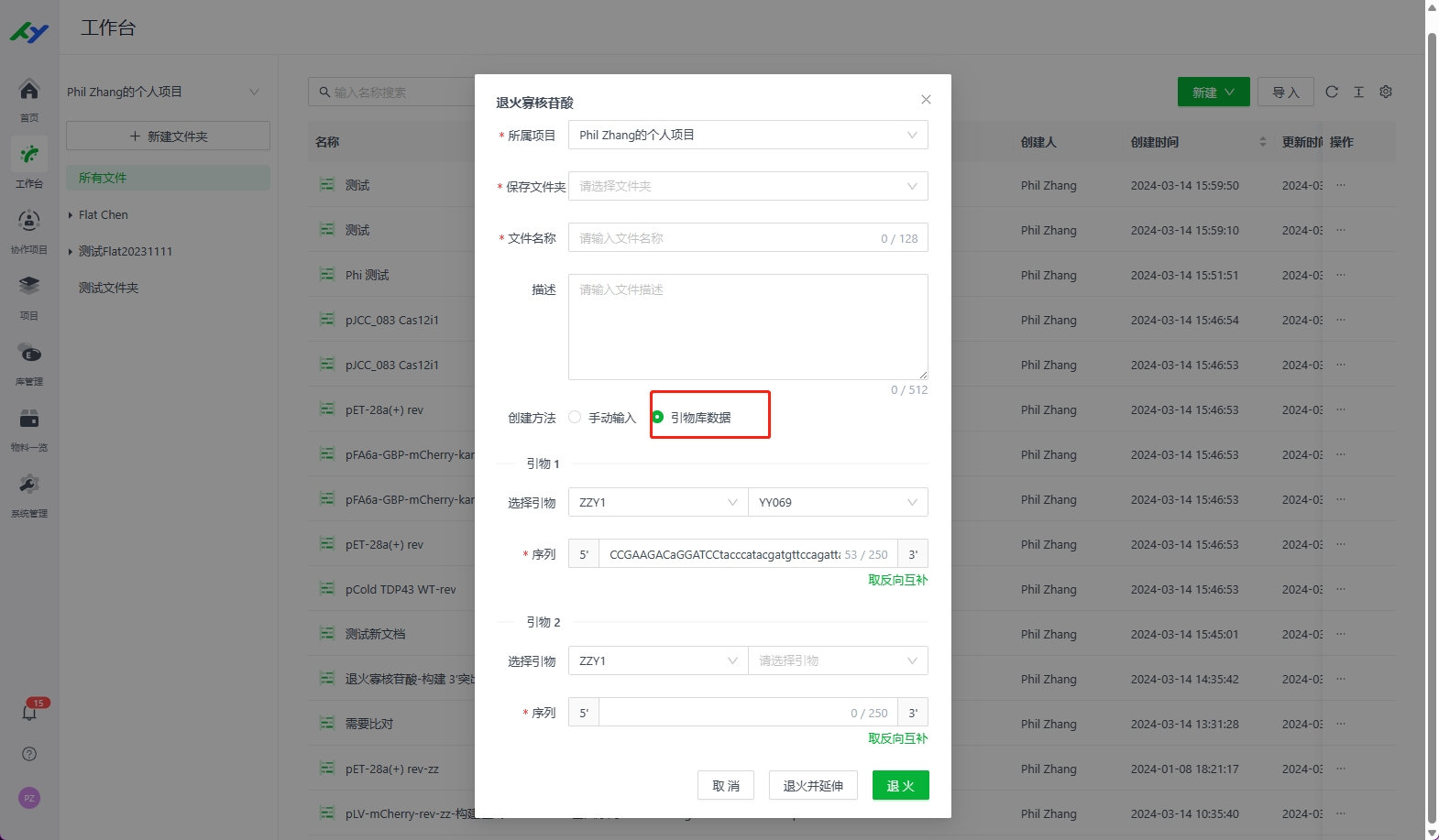
13.2 通过引物库创建
如果用户将序列文件中的引物提取保存至引物库,或者提前在引物库中已导入需要使用的引物,则可以直接在此选择引用。
14. 以当前文件作为载体构建��
用户可以在序列编辑的界面中,直接唤起分子克隆工作台,以此序列当作载体进行构建。